Clear Sky Science · tr
Derin öğrenme ve ara 2B haritalar kullanılarak RNA 3B yapı modellerinin kalite değerlendirmesi
RNA şekillerini değerlendirmek neden önemli
Her hücrenin içinde RNA molekülleri genlerin hangilerinin aktif olduğunu kontrol etmeye, kimyasal reaksiyonları yönlendirmeye ve hatta virüslerle mücadele etmeye yardımcı olan karmaşık üç boyutlu şekillere bükülür ve katlanır. Günümüzde güçlü bilgisayar programları bu şekillerin çoğunu tahmin edebiliyor, ancak bilim insanları hâlâ temel bir sorunla karşılaşıyor: bilgisayar aynı RNA için düzinelerce ya da yüzlerce aday şekil ürettiğinde, hangisi gerçeğe yakın? Bu makale, RNA 3B modellerini bir yapısal kalite denetçisi gibi değerlendirerek araştırıcıların en güvenilir tahminlere odaklanmasını sağlayan yapay zekâ aracı RNArank’i tanıtıyor.
RNA modelleri için yeni bir denetçi
RNArank, önerilen bir RNA şeklinin nasıl üretildiğini bilmeye gerek duymadan kalitesini yargılamak üzere geliştirildi. Model ister derin öğrenme sistemi, ister fizik tabanlı simülasyon, ister insan uzmanı tarafından oluşturulmuş olsun, RNArank yalnızca son 3B koordinatlara bakar. Ardından aslında şu soruyu sorar: “Bu yapı gerçekçi bir RNA’ya benziyor mu?” Bu tür bağımsız kalite değerlendirmesi önemlidir çünkü AlphaFold gibi araçların protein alanında sıklıkla kutudan çıktığı gibi güvenilir cevaplar verdiği durumların aksine, RNA tahmini hâlâ birden çok yöntemin ve insan bilgisinin karıştırılmasından ve ortaya çıkan modelleri akıllıca sıralamaya yarayacak yaklaşımlardan fayda sağlar.
Yapay zekâyı iyi RNA’yı nasıl gördüğünü öğretmek
RNArank’i eğitmek için yazarlar yaklaşık 200.000 RNA yapısını bir araya getirdiler; bu yapılar açıkça yanlış olandan neredeyse mükemmele kadar geniş bir yelpazeyi kapsıyordu. Bunlar, modern derin öğrenme belirleyicileri, atomik hareketleri taklit eden moleküler dinamik simülasyonları ve doğru yapılara kasıtlı bozulmalarla oluşturulmuş “kandırmacalar” da dahil olmak üzere çeşitli yaklaşımlardan türetilmiş deneysel olarak bilinen yapılardan oluşturuldu. Her model için ekip, RNA’ya özgü rafine bir doğruluk puanı olan lDDT_RNA kullanarak modelin gerçek, deneysel olarak belirlenmiş RNA’ya ne kadar yaklaştığını hesapladı. Bu puan, nükleotidler arasındaki mesafelerin ne kadar iyi yeniden üretildiğine odaklanır; hem genel kıvrımı hem de yerel ayrıntıları yakalar ve molekül uzunluğuna aşırı duyarlı değildir.
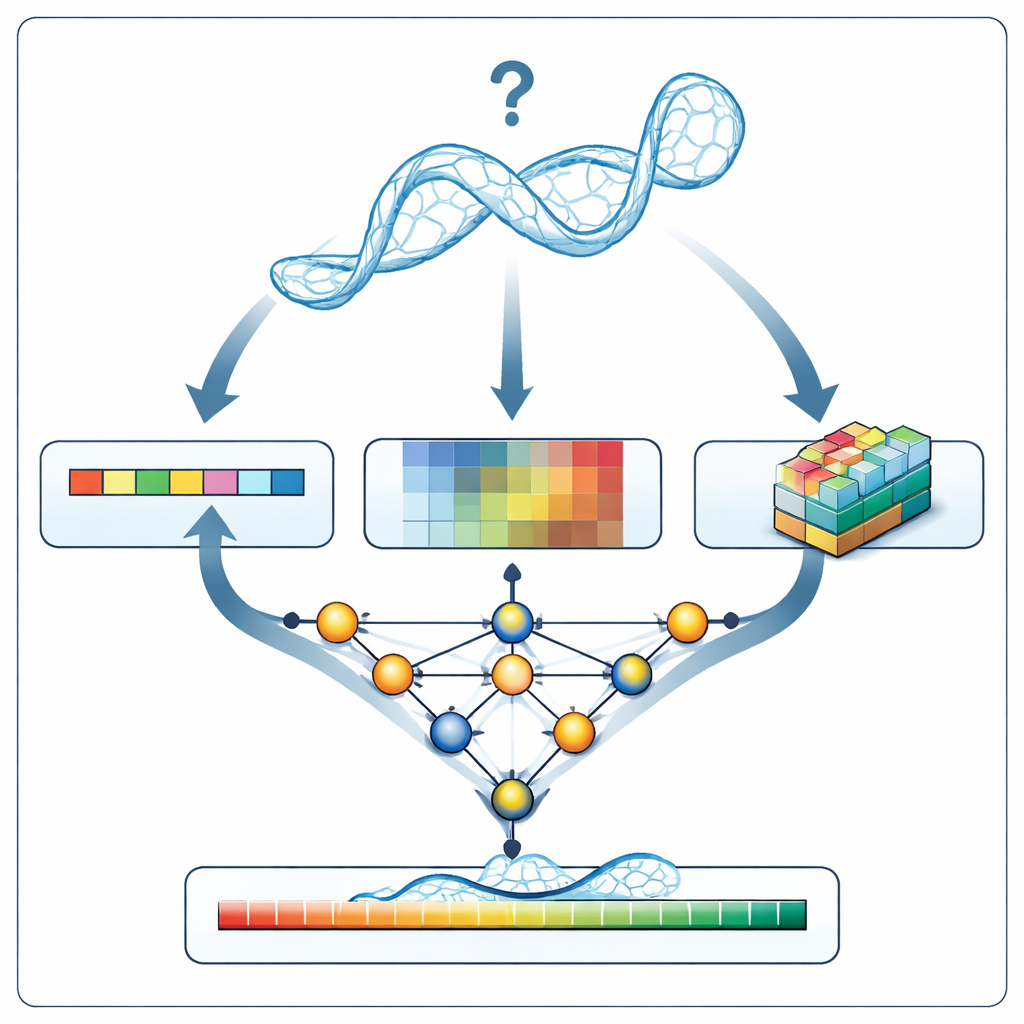
RNArank bir RNA’yı nasıl okur ve puanlar
RNArank yeni bir RNA modelini incelediğinde, önce yapıyı üç tür bilgiye çevirir: zincir boyunca dizinin ve omurga geometrisinin 1B tanımı, her nükleotid çifti arasındaki ilişkileri (mesafeleri, tahmini etkileşim enerjileri ve olası atom çakışmaları) gösteren 2B tanımlar ve her nükleotidin çevresindeki atom bulutunu yakalayan küçük 3B “voxel” görüntüleri. Çok parçalı bir sinir ağı bu ipuçlarını birleşik bir resimde örer ve ardından iki ara 2B harita tahmin eder: hangi nükleotidlerin temasta olması muhtemel olduğu ve modellenen her mesafenin bilinmeyen gerçek yapıdan ne kadar sapma göstereceği. Bu haritalardan RNArank, hem nükleotid başına güven skorunu hem de tüm RNA modeli için genel bir puanı yeniden inşa eder.
Yöntemi teste sokmak
Ekip RNArank’i üç zorlu veri kümesi üzerinde değerlendirdi: Protein Veri Bankası’ndan 24 yeni çözülmüş RNA seti ve birçok grubun önceden cevapları bilmeden modeller sunduğu iki uluslararası kör tahmin yarışması olan CASP15 ve CASP16’nın RNA hedefleri. Binlerce aday yapı üzerinden RNArank’in puanları, birkaç yerleşik enerji-tabanlı puanlama yöntemi ve diğer derin öğrenme yaklaşımlarından daha yakından gerçek model kalitesi ile örtüştü. Havuzdan en iyi veya neredeyse en iyi modelleri seçmede ve bir yapının hangi kısımlarının güvenilir olmayabileceğini belirlemede özellikle güçlüydü. Yazarlar ayrıca RNArank’in eğitim sırasında gördüklerinden dizilim açısından açıkça farklı RNA’larda bile performansını koruduğunu gösterdiler; bu da ezberden ziyade gerçek bir genellemenin işaretiydi.
Bugünün sınırlamaları ve yarının olasılıkları
RNArank kusursuz değil: birçok şekil benimseyebilen özellikle esnek RNA’larla ve büyük moleküler makineler içinde proteinler tarafından sıkıştırıldığında biçim değiştiren RNA’larla hâlâ zorlanıyor. Ancak birkaç yüz nükleotit uzunluğundaki RNA’lar için çok sayıda modeli saniyeler içinde işleyebilecek kadar hızlıdır ve topluluk çapında yapılan testlerde otomatik sunucuların daha yüksek kaliteli tahminler seçmesine şimdiden yardımcı oluyor. Yöntem-agnostik, yalnızca yapıya dayanan bir RNA model hakemi sağlayarak RNArank, ham bilgisayar çıktısını güvenilir yapısal hipotezlere dönüştürmek için biyologlara daha keskin bir filtre sunuyor; bu da alanı RNA şekillerinin rutin ve güvenilir tahmini yönünde bir adım daha ileri taşıyor ve bu çok yönlü moleküllerin nasıl çalıştığına dair daha derin içgörüler sağlıyor.
Atıf: Liu, X., Wang, W., Du, Z. et al. Quality assessment of RNA 3D structure models using deep learning and intermediate 2D maps. Commun Biol 9, 293 (2026). https://doi.org/10.1038/s42003-026-09582-2
Anahtar kelimeler: RNA 3B yapısı, derin öğrenme, model kalite değerlendirmesi, yapısal biyoinformatik, RNArank