Clear Sky Science · tr
CiCLoDS: Tek hücre mekânsal transkriptomik için ortak hücre kümeleme ve gen seçimi
Hücre Şehrinde Mahalleleri Bulmak
Modern mikroskoplar artık dokudaki her hücreyi yerinde tutarken yüz binlerce hücrede hangi genlerin aktif olduğunu okuyabiliyor. Bu “mekânsal transkriptomik” devrimi, bulanık bir şehir haritasını her evin sokak düzeyi görünümüne çevirmek gibi. Ancak bir sorun var: bu haritalar hücre başına binlerce gen için ölçüm içeriyor; bu, bilim insanlarının kolayca yorumlayabileceğinden veya takip deneylerinde ölçmeyi göze alabileceğinden çok daha fazla. Bu çalışma, anlamlı hücresel mahalleleri bulurken aynı zamanda bu mahalleleri tanımlayan küçük ve yorumlanabilir bir gen listesi seçen yeni bir yöntem olan CiCLoDS’u tanıtıyor.
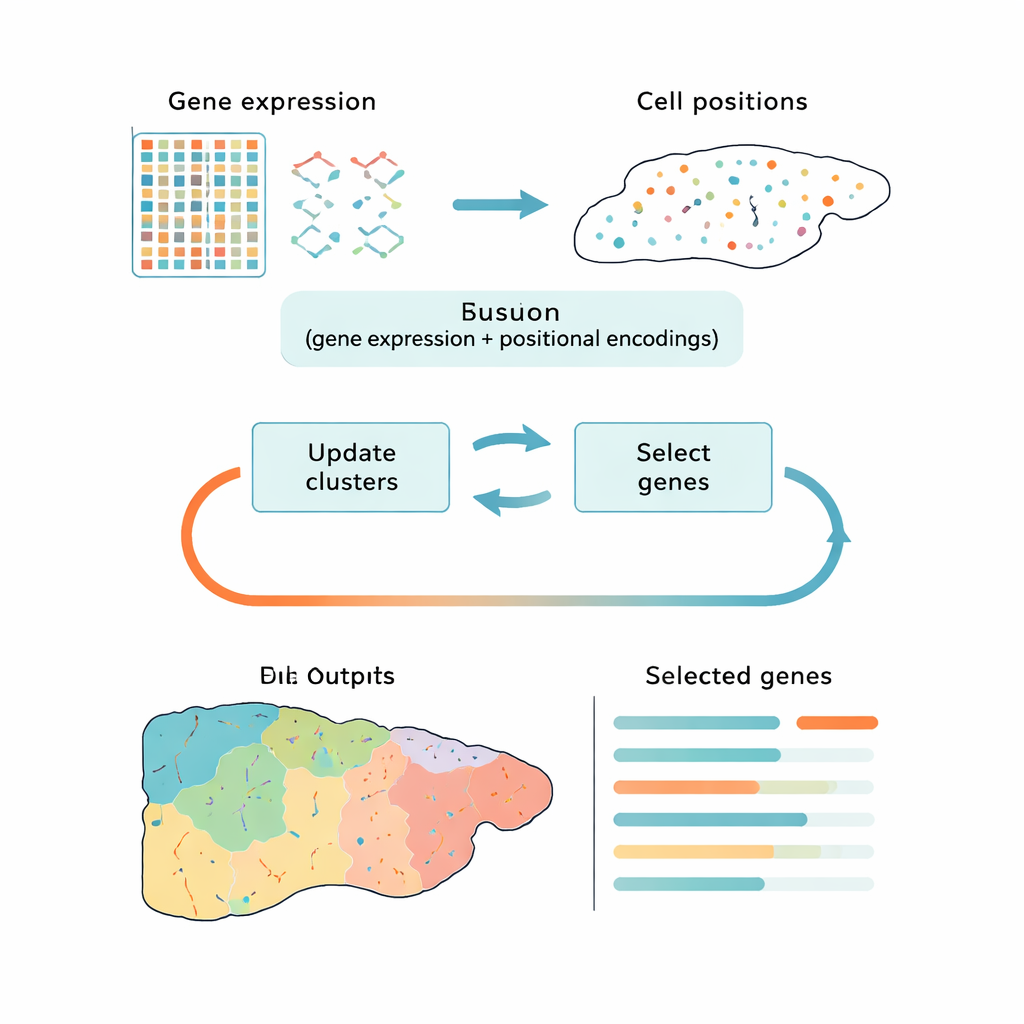
Büyük Veriyi Küçültmenin Daha Akıllı Yolu
Çoğu güncel araç bu zorluğun üstesinden iki ayrı adımda geliyor: önce veriyi basitleştiriyorlar, sonra hücreleri kümelere ayırıyorlar. Ana bileşen analizi (PCA) gibi popüler yaklaşımlar genel varyasyonu korur fakat teknik gürültüye veya hücre döngüsü gibi genel sinyallere odaklanabilir; bunlar önemli biyolojik farklardan ziyade alakasız değişkenlikleri vurgulayabilir. Diğer yöntemler desenleri bulmak için derin öğrenme kullanır, ancak bunlar kara kutu gibi davranır ve hangi genlerin en önemli olduğunu net şekilde söylemez. CiCLoDS farklı bir yol izliyor. Gen seçimini ve kümelenmeyi, tutulabilecek gen sayısı için kullanıcı tarafından belirlenen bir “bütçe” altında ortak bir problem olarak ele alıyor. Özetle, hem gen aktivitesi bilgisine hem de mevcutsa dokudaki fiziksel konumlara bakarak hücrelerin belirgin gruplara nasıl ayrıldığını en iyi açıklayan sınırlı gen seti hangisidir diye soruyor.
Mattan Gerçek Dokuların Haritalarına
Yazarlar, altuzay kümeleme adı verilen matematiksel olarak şeffaf bir teknik ailesini, veri setlerinin milyonlarca hücre içerebildiği mekânsal transkriptomik gerçeklerine uyarlıyor. CiCLoDS, hücre başına gen tablosu üzerinde çalışır; hücreleri kümelere atarken her genin bu kümeleri ayırmaya ne kadar yardımcı olduğunu puanlar. Ayrıca konumel “kodlamalar” ekleyerek her hücrenin dokuda nerede yer aldığını tanımlayan mekânsal bilgiyi çekirdek optimizasyonu değiştirmeden birleştirebilir. Yüksek çözünürlüklü görüntüleme platformlarıyla elde edilen büyük fare karaciğeri ve insan kolon veri setlerinde CiCLoDS, standart bilgisayarlarda dakikalar içinde çalışır ve orijinal verinin zengin yapısını hâlâ yakalayan birkaç düzine ile birkaç yüz gen arasında kompakt gen panelleri üretir.
Gizli Bölgeleri ve Kan Damarlarını Açığa Çıkarmak
CiCLoDS’u fare karaciğerine uygulayan ekip, yöntemin bilinen “zonasyon” desenlerini — lobülün bir tarafından diğerine hepatosit fonksiyonundaki kademeli değişimleri — yeniden elde edip edemeyeceğini sordu. PCA ve geneBasis adlı önde gelen bir gen seçim aracına kıyasla CiCLoDS, referans harita ile uyumu ölçen nicel metriklerde görüldüğü üzere daha keskin sınırlarla ve çok daha az yanlış atanmış bölgeyle daha temiz mekânsal zonlar üretti. Dikkat çekici şekilde, daha fazla gen kullanmasına izin verildiğinde CiCLoDS, anahtar belirteç gen AXIN2 hakkında bilgi verilmemesine veya açık mekânsal koordinatlar sunulmamasına rağmen uzmanların tanımladığı referans kümelere yakın peri‑portal‑benzeri ve peri‑santral‑benzeri hepatosit gruplarını yeniden keşfetti. Mekânsal kodlamalar eklendiğinde CiCLoDS ayrıca hücre yüzeyi ve damar ilişkili işlevler açısından zenginleşmiş gen panelleri öğrendi ve gerçek kan damarlarını görüntüleme artefaktlarından doğru şekilde ayırt edebildi—basit yöntemlerin ya başaramadığı ya da ancak daha ad‑hoc düzeltmelerle başarabildiği bir şey.
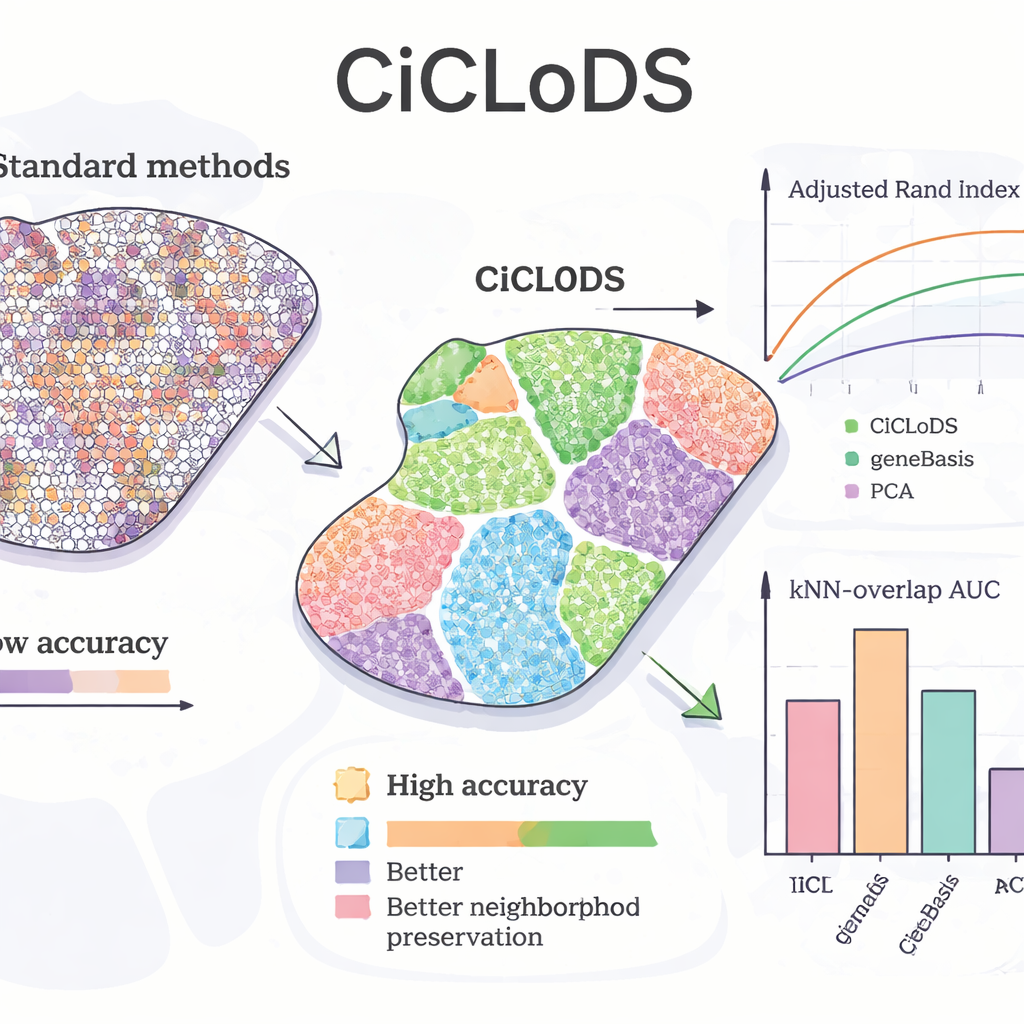
Beyinler Arası Genelleme ve Diğer Yöntemleri Güçlendirme
CiCLoDS’un çok farklı dokular ve bireyler arasında dayanıp dayanmadığını test etmek için yazarlar üç bağışçıdan alınan insan dorsolateral prefrontal korteks örneklerini analiz etti. Burada CiCLoDS, BayesCafe ve BayesSpace gibi uzmanlaşmış mekânsal yöntemlerle karşılaştırıldığında eşdeğer veya daha iyi performans gösterdi; özellikle diğer araçların zorlandığı bir örnekte. Çalışma ayrıca bir “hibrit” kullanım biçimini vurguluyor: önce stabil kümeler elde etmek için CiCLoDS’u çalıştırmak, sonra bunları BayesSpace’e beslemek. Bu sıcak başlangıç stratejisi genel doğruluğu artırdı ve uzman anotasyonlarla en iyi eşleşen beyin katman desenlerini üretti; bu da CiCLoDS’un hem tek başına kullanılabileceğini hem de sonraki olasılıksal modelleri daha güvenilir hale getirebileceğini gösteriyor.
Biyoloji ve Tıp İçin Neden Önemli
Uzman olmayanlar için çıkarılacak ana nokta şudur: CiCLoDS, bunaltıcı hücresel haritaları özlü, biyolojik açıdan anlamlı özetlere dönüştürüyor. Binlerce gürültülü ölçümle uğraşmak yerine araştırmacılar, gerçek doku organizasyonunu yansıtan yönetilebilir bir gen listesi ve net mekânsal kümeler elde ediyor—karaciğerde metabolik zonlar, kan damarları ve bunların nişleri, beyinde katmanlı yapılar gibi. Gen bütçesi kullanıcı tarafından kontrol edildiği ve hesaplamalar hafif olduğu için CiCLoDS, gelecekteki deneyler için hedefli gen panelleri tasarlamaya, karmaşık mekânsal veri setlerinin yorumlanmasına rehberlik etmeye ve daha kapsamlı modelleme için sağlam başlangıç noktaları sağlamaya yardımcı olabilir. Veri toplamanın artık darboğaz olmadığı, anlayışın öncelik olduğu bir dönemde CiCLoDS gibi araçlar yüksek boyutlu doku haritalarını hem pratik hem de içgörülü hale getirme sözü veriyor.
Atıf: Wang, N., He, Y., Ray, E. et al. CiCLoDS: Joint cell clustering and gene selection for single-cell spatial transcriptomics. Sci Rep 16, 5356 (2026). https://doi.org/10.1038/s41598-026-39168-1
Anahtar kelimeler: mekânsal transkriptomik, hücre kümeleme, gen paneli seçimi, doku mimarisi, tek hücre analizi