Clear Sky Science · tr
Hi-C temas matrisi ve sinir ağları kullanılarak yapısal varyant tespiti için bir yöntem
DNA’nın 3B şeklinde kıvrılması neden önemli
DNA’mız genellikle basit bir harf dizisi olarak çizilir, fakat her hücrenin içinde karmaşık üç boyutlu bir biçimde katlanır. Bu dizinin büyük parçaları silindiğinde, ters çevrildiğinde veya yer değiştirildiğinde—yapısal varyasyonlar olarak adlandırılan değişiklikler—genleri bozabilir ve kanseri tetikleyebilir. Bu çalışma, 3B DNA katlanma haritalarını okuyup bu riskli büyük ölçekli değişiklikleri mevcut araçlardan daha doğru tespit eden yeni bir yapay zeka sistemi olan VarHiCNet’i tanıtıyor; bu, kanser genomlarını ve diğer hastalıkları incelemenin yeni bir yolunu sunuyor.
3B temas haritalarıyla genom değişikliklerini görmek
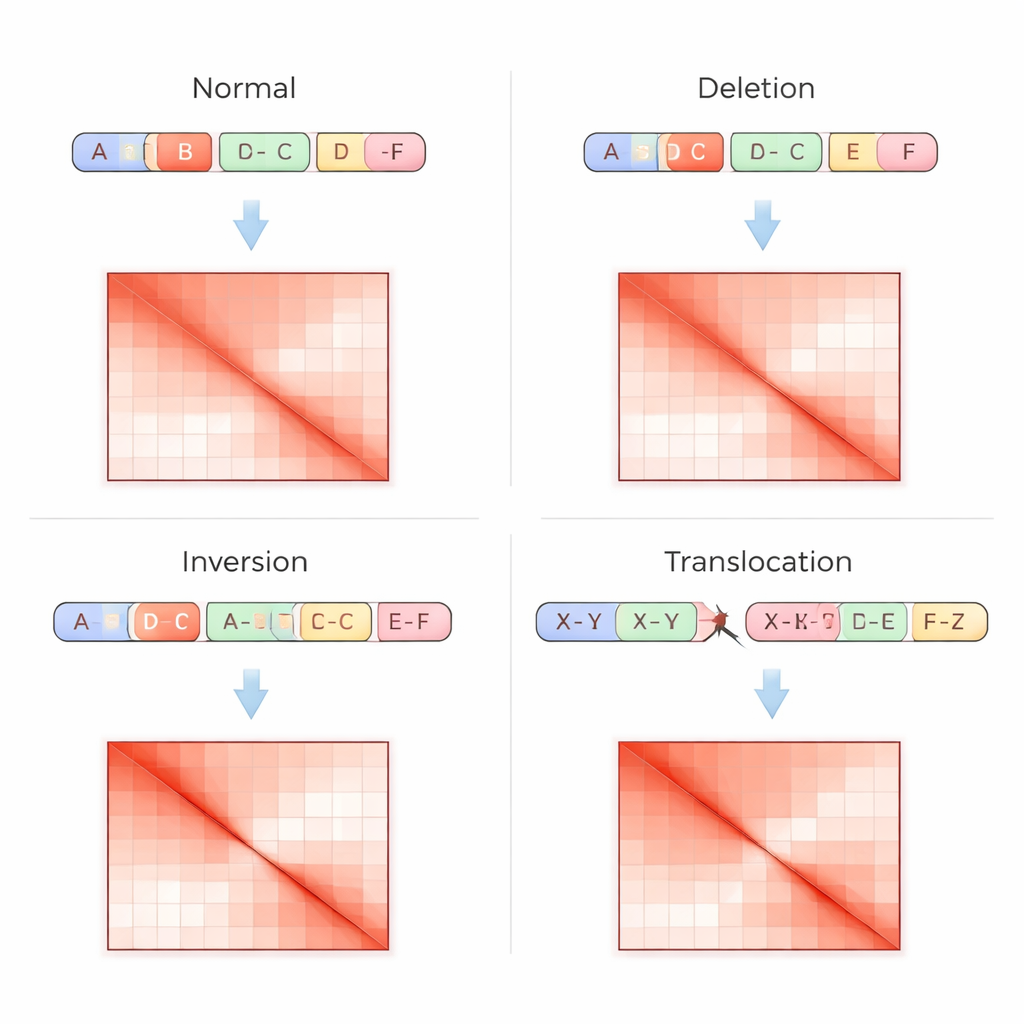
Geleneksel genom testleri DNA’yı düz bir dizi olarak okur; bu da özellikle tekrarlayan bölgelerde veya kopya sayısını değiştirmeden parçalar taşındığında karmaşık yeniden düzenlemeleri tespit etmeyi zorlaştırır. Hi-C tekniği soruna farklı bir açıdan yaklaşır: çekirdeğin içinde uzak DNA parçalarının fiziksel olarak ne sıklıkta temas ettiğini ölçer ve bu temasları, daha parlak noktaların daha güçlü etkileşimi gösterdiği bir ızgara ya da temas matrisi olarak kaydeder. Yapısal varyasyonlar bu matrislerde belirgin parmak izleri bırakır—örneğin bir bölge silindiğinde kaybolan şeritler, bir segment ters çevrildiğinde aynalanmış desenler veya iki kromozom kaynaştığında köşegen dışı sıcak noktalar gibi. VarHiCNet bu görsel desenleri otomatik olarak tanımak üzere tasarlandı.
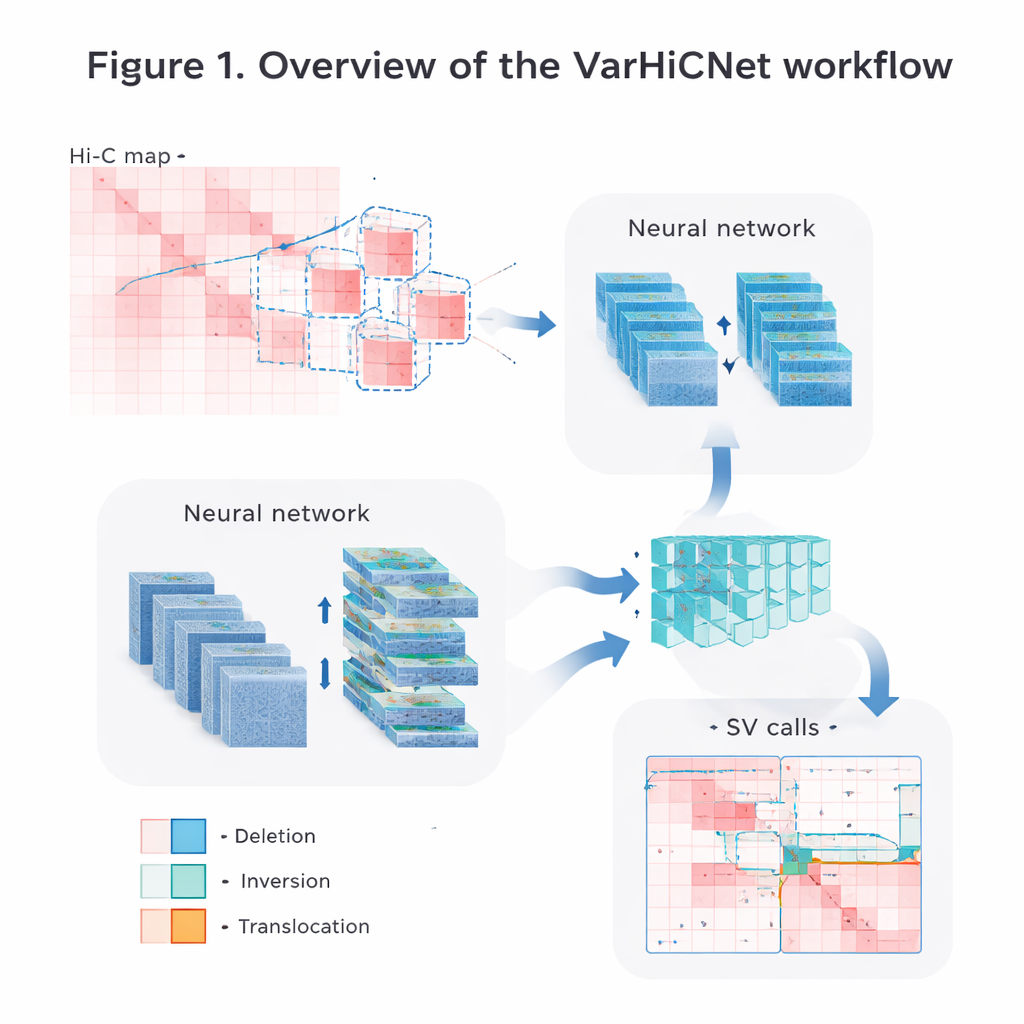
Genom haritalarını yapay zeka için resimlere dönüştürmek
Yazarlar ham Hi-C temas verilerini, bilgisayarlı görü sistemlerinin kolayca işleyebileceği resimlere dönüştürüyor. Önce, DNA segmentleri uzaklaştıkça temas sıklığının doğal olarak azalmasını düzeltmek için matrisleri dikkatle normalize ediyorlar; bu sırada hem yakın hem de uzun menzilli etkileşim sinyallerini koruyorlar. Ardından her kromozomu örtüşen kare pencerelerle tarayıp birçok küçük alt matris kesiti alıyorlar. Her alt matris standartlaştırılmış 800’e 800 piksellik renkli bir resme yeniden boyutlandırılıyor; farklı temas güçleri üç renk kanalında kırmızı tonlu yoğunluklara dönüştürülüyor. Bu görüntü benzeri temsil, modelin fotoğraflardaki nesneleri tanımak için geliştirilen güçlü teknikleri yeniden kullanmasına olanak tanıyor.
Nesne tespitinden alınan yöntemler
VarHiCNet her potansiyel yapısal varyantı görüntüde bir “nesne” gibi ele alıyor. Konvolüsyonel sinir ağları ve Transformer’ların kombinasyonunu kullanan modern bir nesne tespit çerçevesi olan RT-DETR üzerine inşa ediliyor; bu çerçeve önemli bölgeleri vurguluyor. Bir ResNet omurga önce çok ölçekli özellikler çıkarıyor: sığ katmanlar tam kopma noktalarını belirlemek için gereken ince ayrıntıları korurken, daha derin katmanlar büyük olayları haber veren daha geniş desenleri yakalıyor. Bir özellik harmanlama modülü daha sonra birkaç katmandan gelen bilgileri birleştirerek hem yerel hem de küresel ipuçlarının korunmasını sağlıyor. Uzamsal piramit havuzlamadan esinlenen başka bir özel blok, modelin aynı anda “gördüğü” çevre boyutunu ayarlayarak nispeten küçükten çok büyük DNA aralıklarını kapsayan varyantlara duyarlı olmasını sağlıyor.
Aday bölgelerden kesin varyant türlerine
VarHiCNet Hi-C görüntüsünde aday bölgeler önerdikten sonra, bunları kesin kopma noktalarına ve delesyon, inversiyon, duplikasyon veya translokasyon gibi belirli varyant türlerine dönüştürmesi gerekir. Bunu yapmak için sistem her tahmin edilen kopma noktasının çevresine yakınlaştırır ve temas deseninin en keskin değiştiği yerleri vurgulayan temel bileşen analizi adı verilen matematiksel bir teknik kullanarak karmaşıklığı azaltır. Bu kompakt temsiller daha sonra yerel desenlerdeki ince farkları öğrenen Transformer tabanlı bir sınıflandırıcıya beslenir. Sonuç, her olay için ayrıntılı bir çağrıdır: genomda nerede olduğu ve hangi tür yapısal değişikliği temsil ettiği.
Çeşitli kanser hücre hatlarında performans
Araştırmacılar VarHiCNet’i kan, meme, beyin, böbrek, akciğer ve prostat tümörlerini kapsayan altı farklı insan kanser hücre hattından elde edilmiş Hi-C verileri üzerinde test ettiler. Güvenilir bir bilinen yapısal varyant katalogunu altın standart olarak kullanarak, Hi-C verilerini analiz eden önde gelen birkaç araçla yöntemlerini karşılaştırdılar. Hem kromozom içi hem de kromozomlar arası olaylarda VarHiCNet genel olarak daha yüksek veya karşılaştırılabilir F1 puanları elde etti; bu da duyarlılık ve doğruluğu diğer yaklaşımlara göre daha iyi dengelediği anlamına geliyor. Özellikle dengeli translokasyonlar ve inversiyonları—standart DNA dizilemede genellikle az iz bırakan ama 3B katlanma imzalarında belirgin olan yeniden düzenlemeleri—tespit etmede güçlüydü. Yazarlar ayrıca görüntü çözünürlüğü ve özellik harmanlama modülleri gibi tasarım seçimlerinin kontrollü testlerde performansı tutarlı biçimde iyileştirdiğini gösterdiler.
Hastalığı anlamanın önemi
Günlük ifadeyle, VarHiCNet bilim insanlarına genomun 3B’de nasıl katlandığını “görmek” ve geleneksel dizileme ile kaçabilecek büyük, hastalıkla ilişkili yeniden düzenlemeleri tespit etmek için daha akıllı bir yol sunuyor. Karmaşık temas haritalarını görüntülere dönüştürüp modern görsel stil sinir ağlarını uygulayarak yöntem, farklı kanser hücre tiplerinde birçok yapısal varyasyon türünü yüksek güvenilirlikle tespit edip kategorize edebiliyor. Hâlâ çok küçük veya aşırı karmaşık bazı değişikliklerle başa çıkmakta zorlanması ve zengin eğitim verilerine bağlı olması gibi sınırlamaları olsa da VarHiCNet, 3B genom mimarisinin kanser ve diğer hastalıkların altında yatan genetik değişiklikleri okumada, yorumlamada ve nihayetinde hedeflemede rutin bir parça haline geleceği bir geleceğe işaret ediyor.
Atıf: Shen, J., Wang, H., Zhai, H. et al. A method for structural variant detection using Hi-C contact matrix and neural networks. Sci Rep 16, 7324 (2026). https://doi.org/10.1038/s41598-026-37678-6
Anahtar kelimeler: yapısal varyasyon, Hi-C, derin öğrenme, kanser genomikleri, 3B genom