Clear Sky Science · tr
Çin'den on bir Lilium türünün rDNA oligo-probları ile FISH kullanılarak karşılaştırmalı kariotip analizi
Arka plandaki önemi: zambak kromozomları neden laboratuvarın ötesinde önem taşır
Bahçe zambakları yalnızca güzel çiçekler ve geleneksel ilaçlar değildir: aynı zamanda yeni bitki türlerinin nasıl ortaya çıktığını ve bunların doğru şekilde nasıl sınıflandırılacağını anlamaya yardımcı olan genetik modellerdir. Bu çalışma, gıda veya ilaç olarak kullanılan birçok türü de içeren on bir Çin zambak türünün hücrelerinin içini inceleyerek kromozomlarının nasıl düzenlendiğini ve işaretlendiğini araştırır. Bu gizli yapıların karşılaştırılmasıyla yazarlar hangi zambakların gerçekten yakın akraba olduğunu netleştirir ve uzun süredir devam eden zambak soy ağacı tartışmalarına çözüm getirecek kanıt sağlar.
Karmaşık zambak soy ağacını çözmek
Lilium cinsi, Çin’i ana çeşitlilik merkezlerinden biri olarak alarak, Kuzey Yarımküreye yayılmış yaklaşık 125 tür içerir. Bir asırdan uzun süredir botanikçiler bu türleri büyük ölçüde çiçek biçimi gibi görünür özelliklere dayanarak doğal bölümlere ayırmaya çalıştı. Ancak benzer görünen çiçekler her zaman yakın akrabalık anlamına gelmez ve kloroplast ile çekirdek DNA’sı çalışmalarından elde edilen genetik veriler zambakların nasıl ilişkilendiği konusunda bazen çelişkili cevaplar verdi. Özellikle Leucolirion olarak adlandırılan grup ve onun iki alt bölümü (6a ve 6b) ile güneybatı ve orta Çin’den bazı türlerin güvenle yerleştirilmesi zor oldu.
Kromozomlarda barkod okuma
Bu sorunu ele almak için yazarlar kromozomların çalışıldığı sitogenetiğe yöneldi. İncelenen on bir türün hepsi aynı temel on iki kromozom setini paylaşıyordu; diploidlerde genellikle 24 kromozom olarak bulunuyordu; Lilium lancifolium’un iki popülasyonu üçlü (triploid) olup 36 kromozoma sahipti. Mikroskop altında her tür iki büyük ve on küçük kromozom gösteriyordu, ancak şekil ve uzunluktaki ince farklılıklar gözle görmekte zor olabiliyordu. Bu nedenle ekip kromozom boyutlarını hassas şekilde ölçtü ve her kromozom boyunca parlak barkodlar gibi davranan belirli ribozomal DNA (rDNA) bölgelerine parlayan DNA etiketleri bağlamak için floresans in situ hibridizasyon (FISH) adı verilen tekniği kullandı.
Zambak genomlarında desenleri bulmak
Araştırmacılar her türün kromozomlarında iki tip rDNA—5S ve 35S—haritaladı. Çoğu zambakta bir 5S bölgesi ve genellikle karakteristik konumlarda iki ila altı arasında değişen 35S bölgesi vardı. Örneğin geleneksel olarak Leucolirion altbölümü 6a'ya yerleştirilen dört tür (L. leucanthum, L. sargentiae, L. sulphureum ve L. regale) aynı kromozom çiftlerinde çok benzer rDNA işaret desenlerini paylaşıyordu; bu durum L. regale bazı ek değişiklikler gösterse bile yakın bir ilişkiyi işaret ediyor. Buna karşılık, kardeş altbölüm 6b türleri ve bazı Sinomartagon zambakları belirgin şekilde farklı rDNA düzenlemeleri göstererek bu iki grup arasında gerçek bir ayrımı vurguladı. Leucolirion dışındaki türlerde ise güçlü paylaşılan desenler genişçe kültürü yapılan L. lancifolium’u L. pumilum ve L. davidii ile ilişkilendiriyordu; bu, daha önceki DNA dizileme çalışmalarının onları bir araya koymasıyla uyumlu bulunuyor.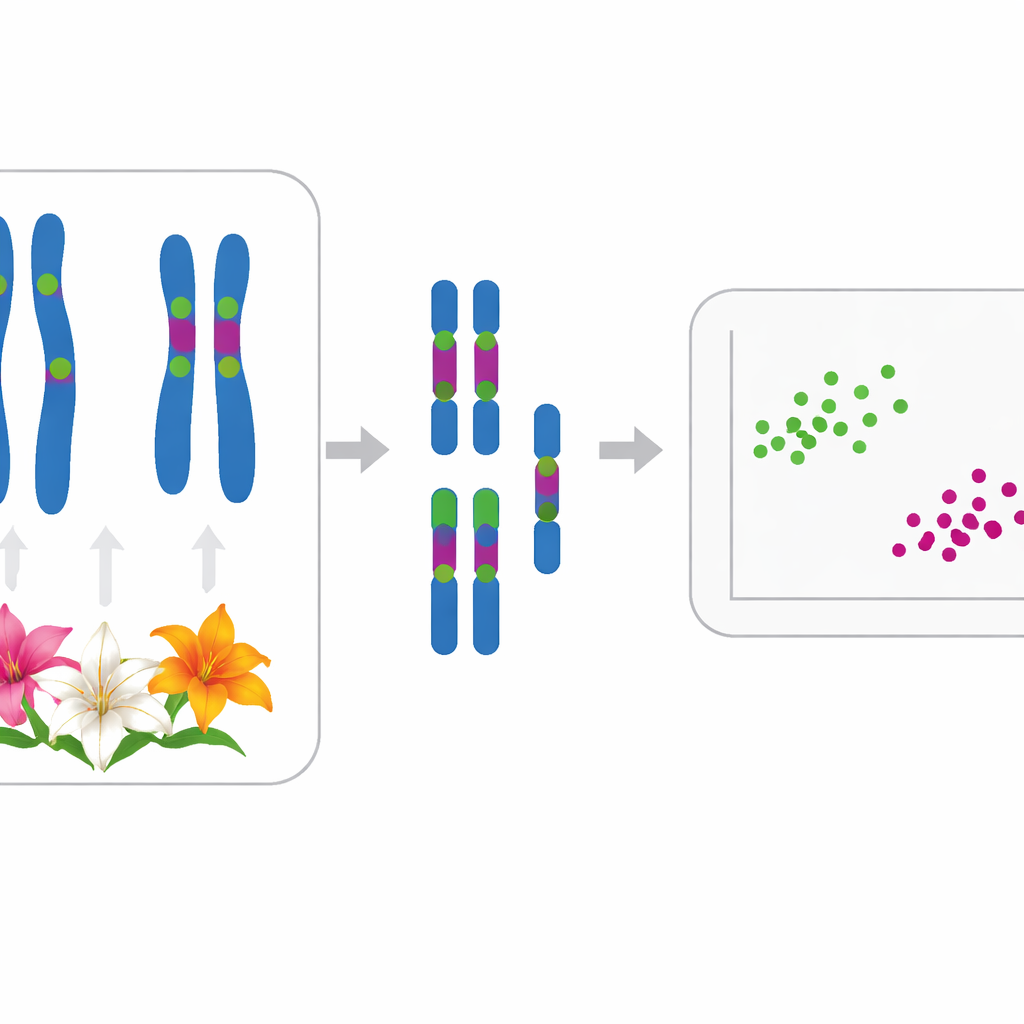
Ölçümleri ilişki haritasına dönüştürmek
Barkod konumlarının ötesinde ekip, her kariotipin ne kadar dengesiz olduğunu—hem sentromer konumları (kromozomun "bel") hem de kromozom uzunlukları açısından—nicelendirildi. Bu özellikleri yakalamak için MCA ve CVCL adlı iki istatistiksel indeksi kullandılar ve on bir türü iki boyutlu bir grafikte çizdiler. Her tür kendi belirgin noktasını işgal etti; bu da dikkatle ölçüldüğünde görünüşte benzer kariotiplerin bile ayırt edilebileceğini gösterdi. Daha geniş bir istatistiksel analiz (ana koordinat analizi) zambakları evrimsel tarihinde çıkarılanlara iyi karşılık gelen iki ana kümeye ayırdı. Bir küme L. pumilum, L. jinfushanense, L. brownii var. viridulum, L. regale ile L. lancifolium ve L. davidii formlarını; diğer küme ise L. leucanthum, L. sargentiae, L. sulphureum, L. henryi ve L. rosthornii’yi içeriyordu.
İsimlendirme ve kullanım açısından ne anlama geliyor
Detaylı kromozom ölçümlerini rDNA barkod haritalarıyla birleştirerek bu çalışma, zambak türlerinin kariotiplerinde daha önce düşünüldüğünden daha fazla farklılık olduğunu ve bu farklılıkların açık bir evrimsel sinyal taşıdığını gösteriyor. Pratik açıdan, çalışma Leucolirion 6a altbölümünü Lilium cinsi içinde doğal, iyi tanımlanmış bir grup olarak ele almayı destekliyor; bu, son sınıflandırma önerileriyle uyumlu. Yetiştiriciler, bitkisel uygulayıcılar ve koruma planlayıcıları için zambaklar arasındaki akrabalık ilişkilerinin daha doğru bir resmine sahip olmak melezlemeyi yönlendirebilir, genetik çeşitliliği koruyabilir ve tıbbi ile yenilebilir çeşitlerin doğru tanımlanıp kullanılmasını sağlayabilir.
Atıf: Yang, YD., Jiang, XH., Zhang, BY. et al. Comparative karyotype analysis of eleven species of Lilium from China using FISH with rDNA oligo-probes. Sci Rep 16, 9446 (2026). https://doi.org/10.1038/s41598-026-37297-1
Anahtar kelimeler: Lilium, kromozomlar, hücre içinde floresans hibridizasyon, bitki evrimi, sitotaksonomi