Clear Sky Science · tr
Doğrudan ve pleiotropik SNP etkilerini ayırmak: yonca (Medicago sativa L.) üzerinde nedensel grafik öğrenimi kullanımı
Çiftlikler ve gıda için neden önemli
Yonca, modern tarımın temel taşlarından biridir; süt ineklerini besler ve sağlıklı toprakların oluşmasına katkıda bulunur. Buna karşın daha iyi yonca geliştirmek—kışa dayanıklı, hasara dirençli ve yüksek kaliteli yem sağlayan bitkiler elde etmek—genetik kompleksitenin büyüklüğü nedeniyle yavaş ilerlemektedir. Bu çalışma, uzun ve kafa karıştırıcı DNA işaretçisi listelerinden, hangi genom parçalarının gerçekten önemli gövde özelliklerini etkilediğini ve hangilerinin sadece birlikte hareket ettiğini gösteren açık nedensel haritalara geçiş için yeni bir yöntem sunuyor.
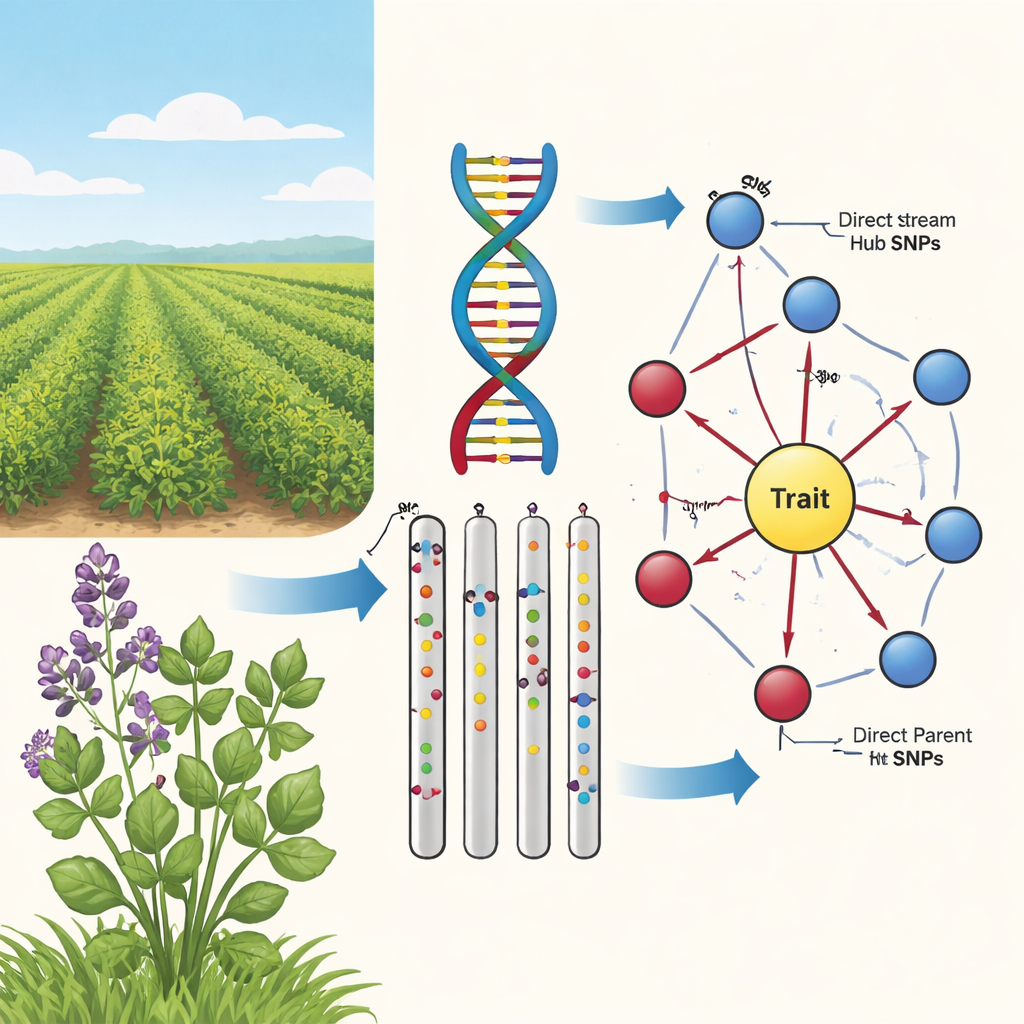
Gevşek bağlantılardan nedene dayalı ilişkilere
Geleneksel genom çapında ilişkilendirme çalışmaları, SNP adı verilen DNA varyasyonlarını tarayarak bir özellik (örneğin gövde rengi veya kışa dayanım) ile birlikte görülen işaretçileri tespit eder. Ancak yoncada durum özellikle karışıktır: her kromozomun dört kopyası vardır, büyük DNA parçaları birlikte hareket eder ve bitkiler genetik olarak yüksek düzeyde karışıktır. Bu, birçok işaretçinin önemli görünmesine rağmen yalnızca birkaçının gerçekten özelliği etkilediği bir "korelasyon sisi" oluşturur. Yazarlar, ıslahçıların basit istatistiksel bağlantılardan daha fazlasına ihtiyaç duyduğunu; hangi işaretçilerin genotipten gözlemlenen bitki özelliklerine giden gerçek nedensel yollarda yer aldığını bilmeleri gerektiğini savunuyor.
Yeni çerçeve nasıl çalışıyor
Araştırmacılar modern makine öğrenimi ile nedensel grafik kuramından fikirleri birleştiren iki aşamalı bir çerçeve kurdular. Önce, 500 yonca genotipinde yaklaşık 2.400 SNP'yi taramak için Double Machine Learning adı verilen bir teknik kullandılar. Bu adım, aile geçmişi ve coğrafya gibi gizli faktörlerin etkisini, genomun temel bileşenlerini vekil olarak kullanarak ortadan kaldırır. Sonuç, bu çakışan etkiler hesaba katıldıktan sonra hangi işaretçilerin hâlâ özelliğe doğrudan etkisi olduğunu daha temiz gösteren bir görünümdür. Bu filtrelenmiş görünümde, güçlü ve kararlı sinyal zirveleri ağırlıklı olarak kromozom 2 ve 4'te belirdi ve anahtar işaretçiler güven aralıkları sıfırı açıkça dışlayan etki büyüklükleri göstererek gerçek nedensel etkiye işaret etti.
İşaretçileri genetik yol haritalarına dönüştürmek
İkinci aşamada ekip, en umut verici işaretçileri yönlü bir ağda birbirine bağlamak için PC algoritması olarak bilinen bir nedensel grafik öğrenme algoritması kullandı. Bu diyagramlarda düğümler SNP'leri ve özelliği temsil eder; oklar ise muhtemel etki yönünü gösterir. Temel biyolojiyle çelişen kenarları (örneğin özelliklerin alttaki DNA'yı değiştiremeyeceği) budayarak ve yalnızca özelliğe giden SNP'leri tutarak, yazarlar kompakt ve biyolojik açıdan mantıklı haritalar elde ettiler. Bu "ayçiçeği" ağları katmanlı bir yapı ortaya koyuyor: doğrudan özelliğe bağlanan Doğrudan Ebeveyn SNP'lerin iç halkası ve birden fazla ebeveyne etki eden fakat doğrudan özelliğe dokunmayan Yukarı Akış Hub SNP'lerin dış halkası.
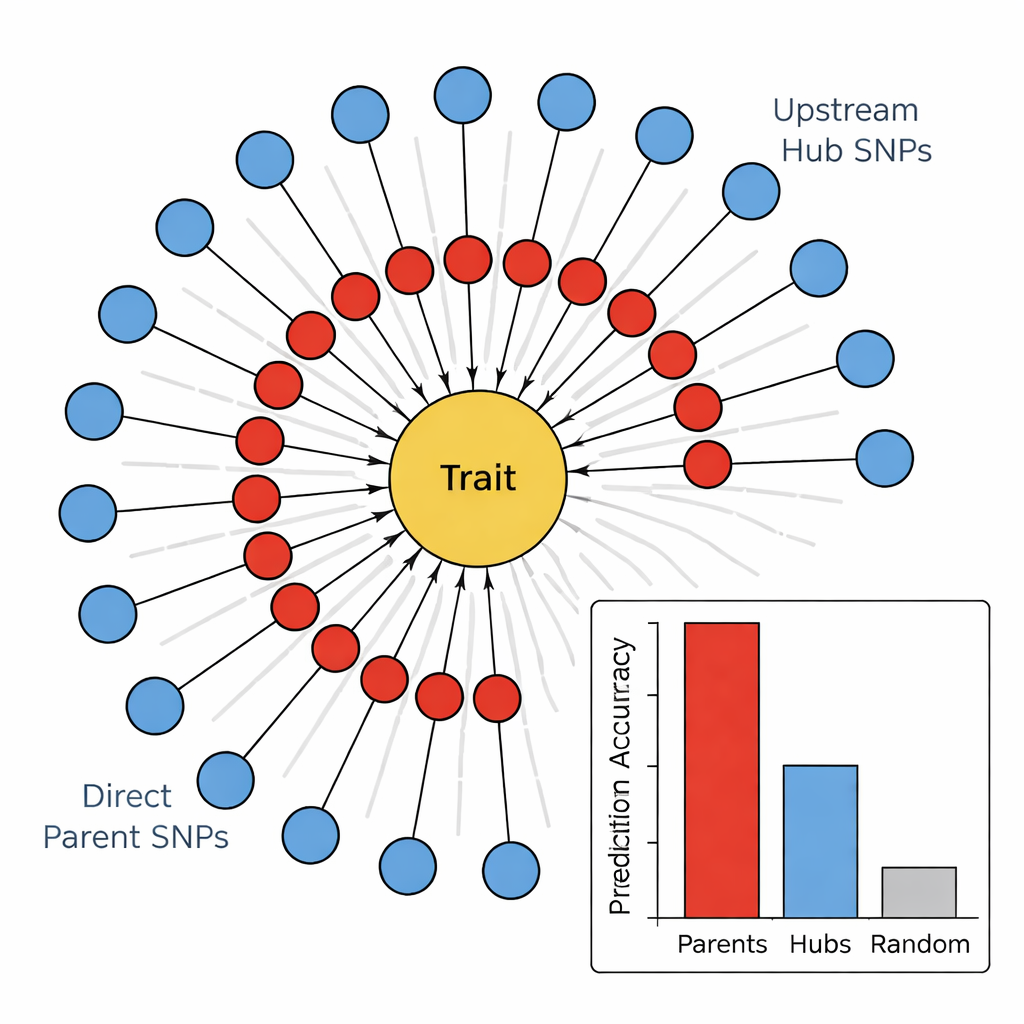
Genomda uygulayıcılar ve yöneticiler
Bu hiyararşinin anlamlı olup olmadığını test etmek için yazarlar, farklı işaretçi gruplarının gövde ile ilgili dört özelliği — gövde rengi, gövde doluluğu, gövde dayanımı ve kış zedelenmesi — ne kadar iyi tahmin edebildiğini karşılaştırdılar. Tüm özellikler genelinde, Doğrudan Ebeveyn SNP'ler tutarlı şekilde en iyi tahmin edicilerdi ve genellikle rastgele seçilmiş işaretçilerden veya Yukarı Akış Hub'lardan birkaç kat daha fazla varyasyonu açıkladılar. Buna karşılık, hub'lar ağda yüksek bağlılığa rağmen zayıf veya hatta negatif tahmin gücü gösterdiler. Ekip bu SNP'leri bilinen genlerle ilişkilendirdiğinde bir desen ortaya çıktı: Doğrudan Ebeveynler sıklıkla hücre duvarları, pigmentler veya stres hasarına doğrudan etki eden enzimler veya yapısal proteinlerle eşleşirken, Hub'lar genellikle birçok yolu geniş ölçüde ayarlayan transkripsiyon faktörleri ve düzenleyici proteinlerle ilişkilendi.
Geleceğin yonca ıslahı için taşıdığı anlam
Islahçılar ve genetikçiler için bu çalışma, gürültülü ilişkilendirme sonuçlarını kesip atmanın ve belirli özellikleri gerçekten etkileyen DNA değişikliklerine odaklanmanın bir yolunu sunuyor. Yazarlar, karıştırılmadan arındırılmış tarama ile nedensel grafiklerin birleştirilmesinin ezberlemeyi (overfitting) engellemeye yönelik yerleşik bir güvenlik sağlayabileceğini, uzun aday listelerini bilinen biyolojiyle uyumlu küçük, yorumlanabilir ağlara dönüştürebileceğini gösteriyor. Pratik açıdan, Doğrudan Ebeveyn SNP'ler daha iyi gövdeli veya kışa dayanıklı bitkilerin seçilmesinde yüksek doğruluklu markörler haline gelirken, Yukarı Akış Hub'lar daha geniş stres tepkilerini yeniden şekillendirebilecek anahtar anahtarlar olarak öne çıkıyor; ancak bunların olası takasları olabilir. Genomun bu yapısal görünümü, karmaşık ekinlerde daha güvenilir genomik seçilim için ve gelecek veri katmanlarını—örneğin gen ekspresyonu ve metabolizma—nedensel ve etki-odaklı bitki performans modellerine entegre etmek için bir temel oluşturur.
Atıf: Lee, Y., Medina, C.A. & Xu, Z. Disentangling direct and pleiotropic SNP effects in alfalfa (Medicago sativa L.) using causal graph learning. Sci Rep 16, 5216 (2026). https://doi.org/10.1038/s41598-026-35876-w
Anahtar kelimeler: yonca genetiği, nedensel grafik öğrenimi, genomik seçilim, bitki ıslahı, poliploid ekinler