Clear Sky Science · tr
Kök ilişkili protein tahmini: bir protein büyük dil modeli ve hipergraph konvolüsyonel ağları kullanarak
Neden kökler ve görünmez yardımcıları önemli
Bitkileri sağlıklı tutmayı düşündüğümüzde genellikle yaprakları ve meyveleri hayal ederiz. Oysa bir bitkinin başarısının büyük kısmı gözden uzakta, toprakta gerçekleşir. Orada, köğe bağlı özel proteinler bitkilerin su ve besin alımına yardımcı olur ve kuraklık ya da kötü toprak gibi streslerle başa çıkmasını sağlar. Bu hayati proteinleri yalnızca laboratuvar deneyleriyle bulmak yavaş ve pahalıdır. Bu çalışma, Hypergraph-Root adını taşıyan güçlü bir bilgisayar modeli sunuyor; bu model protein dizilerini hızla tarayarak hangilerinin kökle ilişkili olma olasılığının yüksek olduğunu tahmin edebiliyor — daha dayanıklı bitkilere ve daha iyi ürünlere daha hızlı bir yol sunuyor.
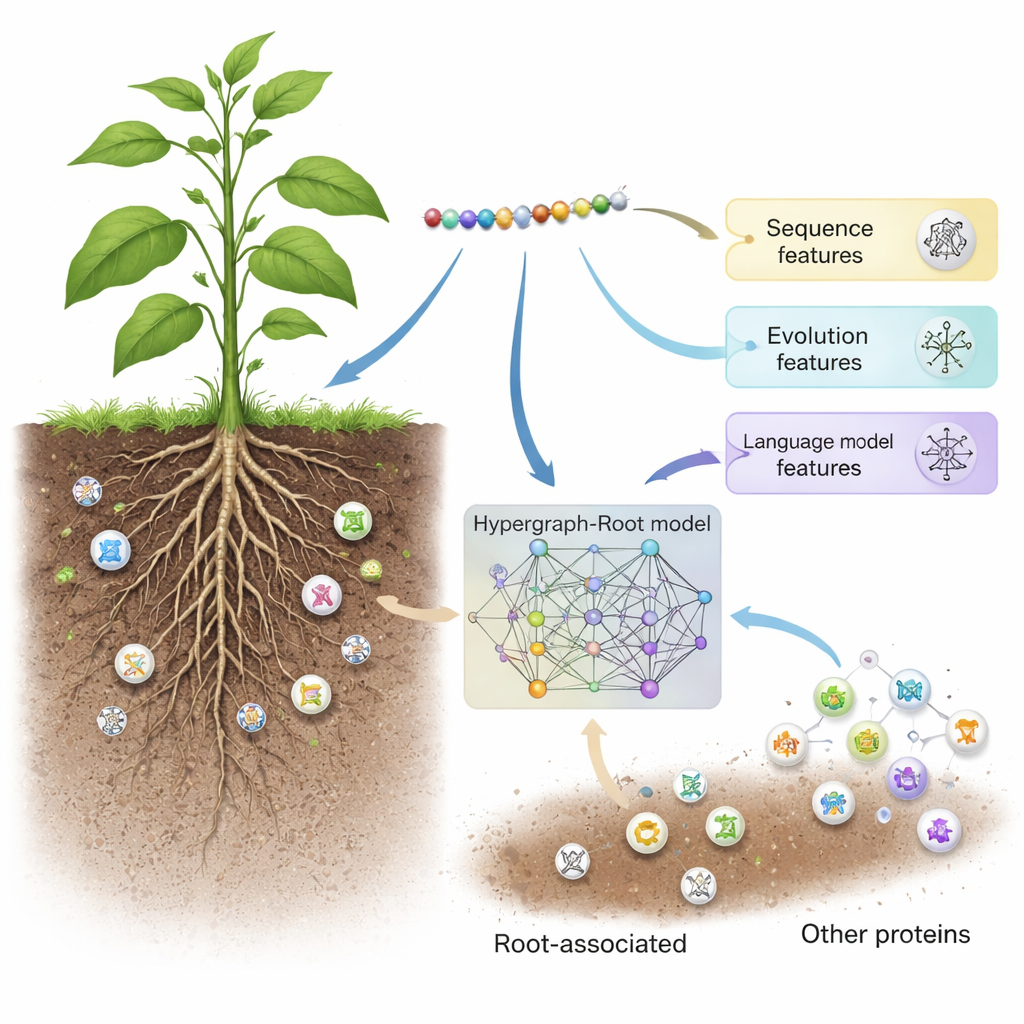
Topraktaki görünmez işçiler
Bitki kökleri yalnızca bitkiyi yerinde tutmaz. Sürekli çevrelerini algılar, mineral çeker ve toprak mikroplarıyla iletişim kurar. Kök ilişkili proteinler bunların tümünde merkezi bir rol oynar; köklerin nasıl büyüdüğünü, sıcaklık, kuraklık veya besin eksikliğine nasıl yanıt verdiğini ve faydalı mikroplarla nasıl etkileşime girdiğini şekillendirir. Bu proteinler verim ve dayanıklılığı güçlü biçimde etkilediği için çiftçiler ve ıslahçılar doğrudan görmeseler bile onları önemser. Yine de birçok protein keşfedilmemiş durumda; bunun başlıca nedeni geleneksel yöntemlerin—proteomik ve gen ekspresyonu çalışmaları gibi—maliyetli araçlar, karmaşık analizler ve titiz deneyler gerektirmesidir.
Protein dizilerinden ipuçları çıkarmak
Proteinler amino asit dizilerinden oluşur ve bu dizilerdeki desenler sıklıkla bir proteinin bitkide nerede çalıştığını ve ne yaptığını ortaya koyar. Önceki bilgisayar modelleri bu desenleri kullanmaya çalıştı ancak doğrulukları genellikle yüzde 80’in altındaydı. Bunun bir nedeni, amino asitler arasındaki ilişkileri çoğunlukla çiftler halinde basitçe ele almalarıydı. Diğeri ise dizilerden çıkarılan özellik türlerinin sınırlı olmasıydı. Yazarlar, her proteinin daha zengin betimlemelerinin ve amino asit ilişkilerini modellemenin daha akıllı yollarının kökle ilişkili işlevlere bağlı daha incelikli desenleri ortaya çıkarabileceği sonucuna vardı.
Dilden ve ağlardan ödünç alınan yöntemler
Hypergraph-Root her proteini üç tamamlayıcı yolla tanımlamakla başlar. Amino asitlerin evrim boyunca birbirinin yerine nasıl geçtiğini yakalayan geleneksel dizi skorlama şemaları (BLOSUM62 ve konum-spesifik skorlama matrisleri) kullanır. Ardından ProtT5 adlı bir protein dil modelinden elde edilen daha modern bir üçüncü betimlemeyi ekler—bu yazılım milyonlarca protein dizisi üzerinde eğitilmiştir, tıpkı bir metin tahmin motorunun insan dilinde eğitilmesi gibi. ProtT5 her amino asit için yapısal ve işlevsel ipuçlarını kodlayan zengin sayısal "gömüler" üretir. Bu üç bakış açısı bir araya geldiğinde çalışmadaki her proteinin ayrıntılı bir parmak izini verir.
Protein içindeki karmaşık bağlantıları haritalamak
Basit ikili karşılaştırmaların ötesine geçmek için araştırmacılar amino asitlerin bir proteinin 3B yapısında ne kadar yakın olduğunu tahmin etti ve bu bilgiyi, tek bir bağlantının aynı anda iki’den fazla amino asidi bağlayabildiği bir ağ türü olan bir hipergraph oluşturmak için kullandı. Bu yapı-bilinçli ağı işleyen uzmanlaşmış bir sinir ağı, hipergraph konvolüsyonel ağ, protein parmak izlerini daha yüksek düzeyde özelliklere dönüştürdü. Bir çoklu-baş dikkat (multi-head attention) modülü daha sonra bir proteinin hangi bölümlerinin kökle ilişkili olup olmadığını belirlemede en yararlı sinyalleri taşıdığını öğrendi. Son olarak, standart bir sınıflandırıcı bu özütlenmiş özellikleri kökle ilişkili olup olmadığına dair bir olasılık skoruna dönüştürdü. Çok sayıda eğitim çalışması ve dengeli ile dengesiz test setlerinde Hypergraph-Root yüzde 83’ün üzerinde doğruluk ve yaklaşık 0.9 civarında ROC eğrisi altında alan (AUC) elde ederek önceki modelleri açıkça geride bıraktı.
Modelin ortaya koydukları ve neden önemli olduğu
Ham doğruluğun ötesinde model hangi bilgilerin en çok önemli olduğunu gösterdi. ProtT5 dil modelinden gelen özellikler geleneksel dizi ve evrimsel özelliklerden daha fazla katkı sağladı; bu, önceden büyük ölçüde eğitilmiş modellerin eski yöntemlerin kaçırdığı ince biyolojik sinyalleri yakalayabildiğini öne sürüyor. Hipergraph bileşeni de önemli çıktı: bunu kaldırmak ya da daha basit bir grafik modeliyle değiştirmek performansı düşürdü. Araştırmacılar Hypergraph-Root’u daha önce kökle ilişkili olarak etiketlenmemiş proteinlere uyguladıklarında, membran taşınması ve köklerde protein işaretleme gibi bilinen işlevleri kökle ilişkili rolleri güçlü biçimde düşündüren birkaç proteini öne çıkardı. Bu adaylar şimdi deneysel biyologlara laboratuvarda test edilecek net kısa listeler sağlıyor.
Zeki tahminlerden daha dayanıklı ürünlere
Günlük ifadeyle Hypergraph-Root bitki biyolojisi için bir uzman kütüphaneci gibidir: yalnızca bir proteinin "harfleri" verildiğinde, o proteinin büyük olasılıkla köklerde çalışıp çalışmadığını tahmin eder. Dil modeli içgörüleri, evrimsel geçmiş ve karmaşık yapısal ilişkileri birleştirerek önceki tahmin araçlarına göre büyük iyileşme sağlar. Deneylerin yerini almasa da binlerce olasılığı yönetilebilir birkaç adayla sınırlandırarak zaman ve para tasarrufu sağlayabilir. Uzun vadede, bu tür modeller sıcaklık, kuraklık veya kötü toprak koşullarına karşı bitkilerin hayatta kalmasına yardımcı olan kök ilişkili proteinlerin keşfini hızlandırarak değişen iklimde daha dirençli tarıma doğru önemli bir adım atabilir.
Atıf: Chen, L., Xun, X. & Zhou, B. Root-associated protein prediction using a protein large language model and hypergraph convolutional networks. Sci Rep 16, 4876 (2026). https://doi.org/10.1038/s41598-026-35110-7
Anahtar kelimeler: kök ilişkili proteinler, bitki biyoinformatiği, derin öğrenme, protein dil modelleri, ürün dayanıklılığı