Clear Sky Science · tr
Tekrarlanabilir üçlü de novo genoma montajı için asgari sanal veri kümesi
Neden üç kopyalı genomlar önemli
Birçok tarım bitkisi ve diğer organizma insanlar gibi her kromozomdan iki kopya taşımıyor—üç veya daha fazla kopya taşıyabiliyorlar. Bu ekstra kopyaları DNA dizileme verilerinden birleştirmek beklenenden zor; çünkü kopyalar birbirine çok benziyor ama tamamen aynı değil. Bu makale, araştırmacıların genom montajı yazılımlarını gerçekçi bir üç kopyalı (triploid) problem üzerinde test edip karşılaştırmasını sağlayan, küçük ama dikkatle tasarlanmış bir “sanal” veri kümesini tanıtıyor; koşullar tamamen biliniyor ve tekrarlanabilir.
Basit bir vekil genom oluşturmak
Gerçek bir bitki veya hayvandan başlamak yerine, yazar önce temiz bir şablon görevi görecek şekilde bir milyon baz çiftinden oluşan rastgele bir DNA dizisi oluşturuyor. Bu şablon daha sonra üç ayrı versiyona çoğaltılıyor ve triploid bir organizmadaki üç kromozom setini temsil ediyor. Gerçek genomların zaman içinde yavaşça nasıl değiştiğini taklit etmek için çalışmada her kopyaya sabit sayıda küçük değişiklik—tek bazlı yerine koymalar—adım adım ekleniyor. Bu işlemi 100 adım tekrarlamak, neredeyse özdeş olanlardan belirgin ama hâlâ ılımlı farklılıktaki triplet genomlar üretiyor. Bu kontrollü “ayrışma gradyanı” kıyaslama testinin omurgasını oluşturuyor.
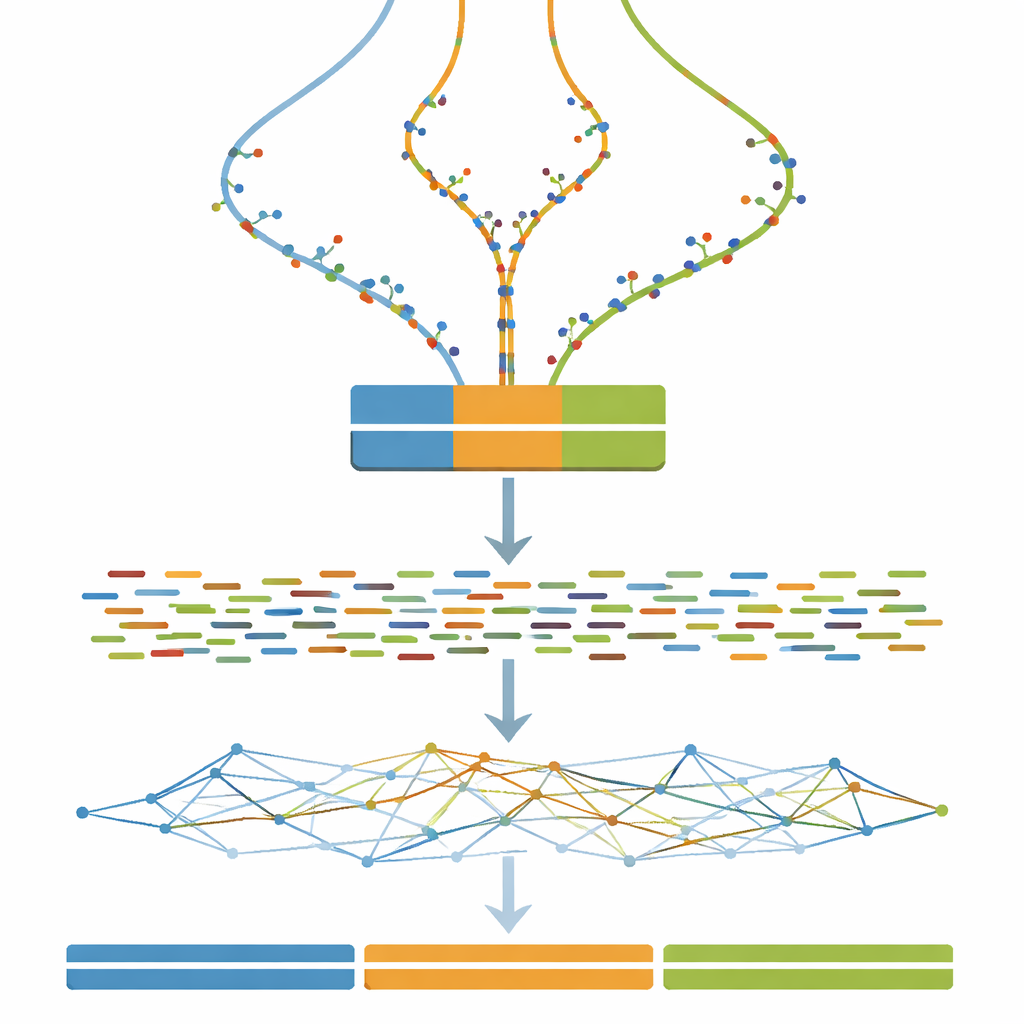
Sanal genomları sanal deneylere dönüştürmek
Her üç kopyalı genom tanımlandıktan sonra bir dizileme makinesinin ne göreceğini taklit etme adımı geliyor. Çalışma, Illumina dizileme makinelerinin ürettiğine benzer kısa çift uçlu DNA parçalarını simüle etmek için yaygın olarak kullanılan yazılımlar kullanıyor ve sabit, nispeten yüksek bir örtme derinliği sağlıyor. İsteğe bağlı temizleme adımları rastgele dizileme hatalarını düzeltme ve örtüşen ok çiftlerini birleştirme gibi yaygın gerçek dünya uygulamalarını taklit ediyor. Sonuç olarak, veri kümesini kullanan herkes yalnızca montaj algoritmalarını değil, aynı zamanda tipik ön işleme seçimlerinin son montajlar üzerindeki etkisini de test edebiliyor.
Montaj stratejilerini stres testine tabi tutmak
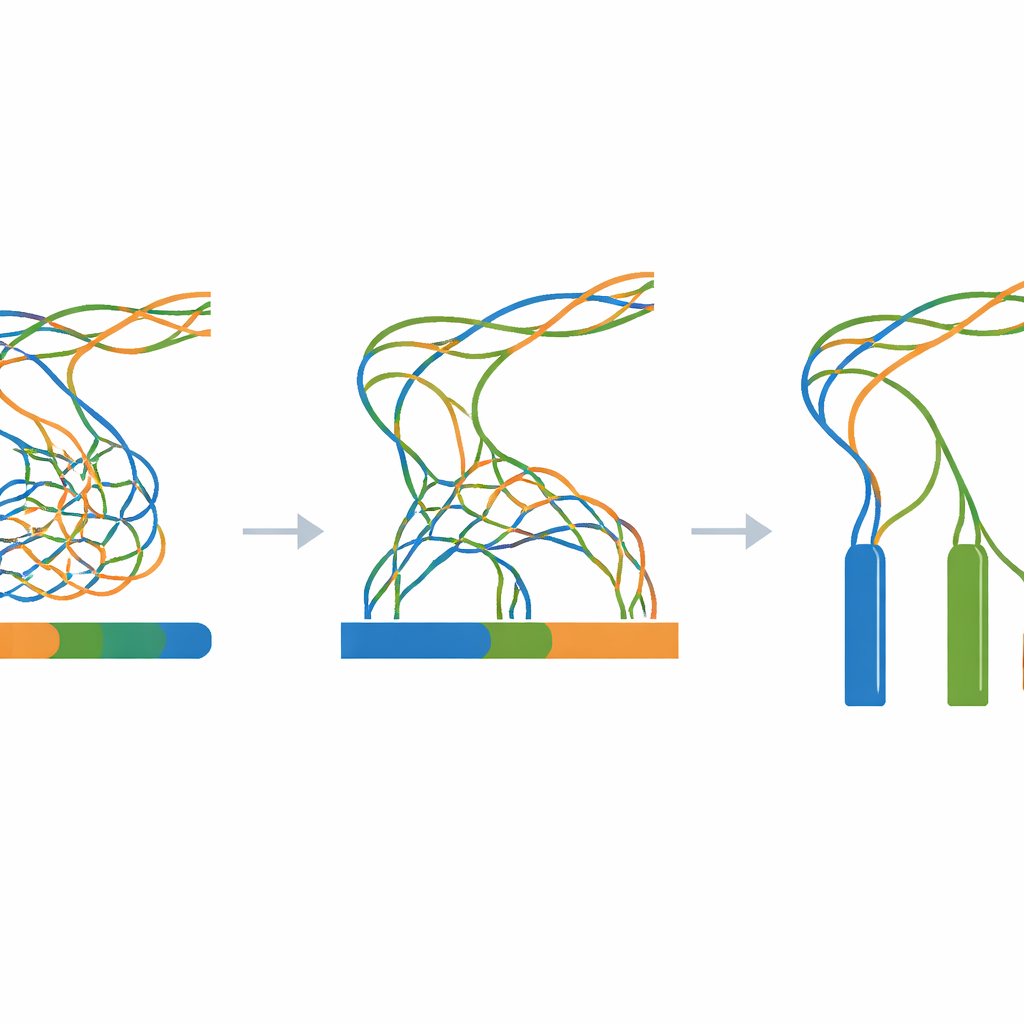
Çalışmanın özü, tüm simüle okların tek bir genom montaj programına beslenip yalnızca bir önemli ayarın değiştirildiği devasa bir deneydir: k-mer boyutu; bu parametre yazılımın genomu yeniden oluştururken okları ne kadar ince parçalara böldüğünü kontrol eder. Ayrışma düzeyi için (0 ile 100 adım arası) ve k-mer boyutu için (geniş bir tek sayılı değer aralığı) her kombinasyon için yeni bir montaj oluşturulur. Bir değerlendirme aracı daha sonra monte edilmiş parçaların sürekliliğini, kaç parça olduğunu ve birleşik uzunluklarının bilinen üç milyon bazlık gerçeğe ne kadar yakın olduğunu ölçer. Bu ölçümler ısı haritaları olarak özetlenir; montajların farklı kopyaları tek bir kopyada nasıl çöktürdüğü, birçok küçük parçaya nasıl ayrıldığı veya üç uzun, doğru kontiguya ne kadar yaklaştığına dair geniş bölgeleri ortaya koyar.
Zor genomlar için şeffaf bir referans
İlk rastgele şablondan son montajlara kadar her aşama sentetik ve betiklenmiş olduğu için—araştırmacılar yalnızca açık kaynak araçları kullanarak herhangi bir standart Linux bilgisayarda tüm iş akışını yeniden oluşturabilirler. Makaledeki Zenodo arşivi şablon genomu, tüm ara mutasyona uğramış diziler, tüm simüle oklar ve her montaj sonucu ile günlükler ve basit yardımcı betikler içerir. Teknik kontroller mutasyon sürecinin beklendiği gibi davrandığını, simüle okların istenen uzunluklara ve örtmeye uygun olduğunu ve montajların beklenen deseni gösterdiğini doğrular: üç kopya neredeyse özdeş olduğunda güçlü aşırı çökme ve kopyalar birbirinden uzaklaştıkça daha net ayrışma.
Bunu basitçe söylemek gerekirse
Gündelik dille, bu makale karışık parça yığınlarından üç benzer talimat kitabını yeniden inşa etmeye çalışan yazılımlar için kontrollü bir test pisti sunuyor. Üç kitabın birbirinden ne kadar farklı olduğunu kademeli olarak artırarak ve yeniden yapılandırma sürecindeki kilit bir ayarı sistematik olarak değiştirerek veri kümesi, mevcut yöntemlerin ne zaman ve nasıl başarısız olduğunu veya başarılı olduğunu görmeyi kolaylaştırıyor. Geliştiriciler yeni algoritmaları ayarlamak için kullanabilir; kullanıcılar ise triploid genomlar için hangi ayarların en iyi çalıştığını daha iyi anlayabilir. DNA kendisi yapay olsa da, çökme, ayrışma ve parametre seçimlerinin etkisi konusundaki öğrendikleri birçok önemli türün karmaşık genomlarını çözme çabalarına doğrudan uygulanabilir.
Atıf: Ootsuki, R. Minimum virtual dataset for reproducible triploid de novo genome assembly. Sci Data 13, 382 (2026). https://doi.org/10.1038/s41597-026-06779-2
Anahtar kelimeler: üç kopyalı genom montajı, poliploidi değerlendirme, sentetik DNA veri kümesi, de novo montaj, k-mer optimizasyonu