Clear Sky Science · tr
DiReG ile doğrudan hücresel yeniden programlamanın haritasında yol almak
Bir Hücre Tipini Başka Birine Dönüştürmek
Bir deri hücresini istenince kalp hücresine veya karaciğer hücresine dönüştürebilmenin mümkün olduğunu hayal edin. Hücrenin doğrudan böyle biçim değiştirmesi, hücresel yeniden programlama olarak adlandırılır ve doktorların yedek doku yetiştirmesine, hastalık modelleri oluşturmasına ve ilaçları daha güvenli şekilde test etmesine olanak tanıyabilir. Ancak bir hücre içindeki doğru moleküler “anahtarları” bulmak, bir kasanın kombinasyonunu tahmin etmek gibidir: olasılıklar binlercedir ve bunları tek tek denemek yavaş ve maliyetlidir. Bu makale, bilim insanlarının seçenekleri daraltmak için bilgisayarları nasıl kullanmaya çalıştığını açıklıyor ve araştırmacıların yeniden programlama reçetelerini daha akıllıca tasarlayıp doğrulamasına yardımcı olan yeni bir çevrimiçi rehber, DiReG’i tanıtıyor.
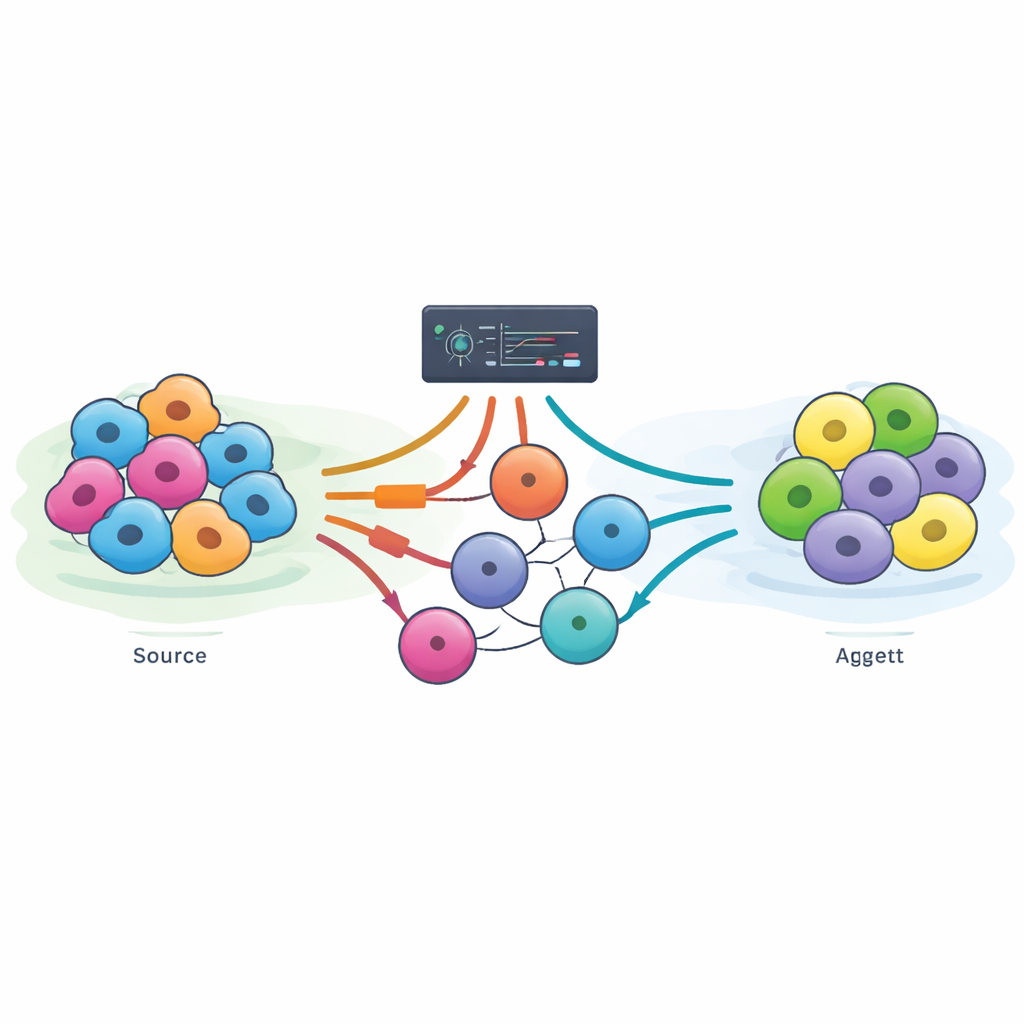
Tesadüften Sistematik Tasarıma
Hücre yeniden programlamanın öyküsü, araştırmacıların tek bir gen olan MyoD1’i bağ dokusu hücrelerine zorla sokmanın onları kas hücresine dönüştürebileceğini keşfetmesiyle başladı. Daha sonra nöronları veya insülin üreten hücreleri yaratabilen diğer kombinasyonlar bulundu ve yetişkin hücreleri kök benzeri bir duruma geri sarabilen dört “Yamanaka faktörü” keşfedildi. Bu atılımlar mümkün olanı gösterdi, ancak bunların bulunma biçimi büyük ölçüde uzman sezgisine ve uzun laboratuvar çalışmalarına dayanıyordu. Doğrudan yeniden programlama—bir olgun hücre tipinden doğrudan başka bir olgun hücre tipine atlama—özellikle zordur çünkü birçok deneme yarıda kalır, kararsız “hibrit” hücreler üretir veya hücrenin önceki kimliğini tamamen silmede başarısız olur.
Bilgisayarlar Reçete Bulucuları Olarak
Son on yılda, hücre kimliğinin başlıca anahtarları olan umut verici transkripsiyon faktörü setlerini seçmeye yardımcı olmak için birkaç hesaplamalı araç oluşturuldu. Makale, büyük gen aktivitesi ve DNA düzenlemesi veri setlerini ele geçirmek için altı önde gelen yöntemi gözden geçiriyor ve bunların bir hücre tipinden diğerine geçişi hangi faktörlerin tetikleyebileceğini önermeye nasıl çalıştığını anlatıyor. Bazıları hangi genlerin açılıp kapandığına odaklanırken, diğerleri devre şeması benzeri düzenleyici ağlar kuruyor; daha yenileri ise birçok kontrol anahtarının bulunduğu DNA erişilebilirliği ve güçlendirici (enhancer) bilgilerini de dahil ediyor. Her ilerleme faydalı ayrıntılar ekliyor, ancak yöntemlerden hiçbiri açık bir üstünlük göstermedi; bunun bir kısmı, yöntemlerin farklı veri setleri ve koşullar altında test edilmesinden kaynaklanıyor ve adil karşılaştırmaları imkânsız kılıyor.
Hücre İçindeki Gizli Karmaşıklıklar
Yazarlar, mevcut tüm araçların birkaç biyolojik nüansı göz ardı ettiğine dikkat çekiyor. Tek bir “gen” birçok hafifçe farklı protein versiyonunda (izoformlar) var olabilir ve bunlar farklı davranır; bugünün modelleri genellikle bunları tek bir birim gibi ele alıyor. DNA üzerindeki kimyasal etiketler, örneğin metilasyon, kontrol proteinlerini engelleyebilir veya çekebilir; buna rağmen çoğu algoritma bir hedef bölgenin kullanışlı olup olmadığını dikkate almıyor. Birçok önemli yardımcı—protein ortakları, aynı bağlanma noktaları için rekabet eden aile üyeleri ve istenmeyen mesajları susturan küçük düzenleyici RNA’lar—de çoğunlukla dışarıda bırakılıyor. Buna ek olarak, çoğu yöntem karışık hücre örneklerinden elde edilen ortalama sinyallere ve yalnızca yaklaşık olarak gerçek protein aktivitelerini izleyen RNA düzeylerine dayanıyor; oysa gerçek değişimi yöneten protein etkinlikleridir.
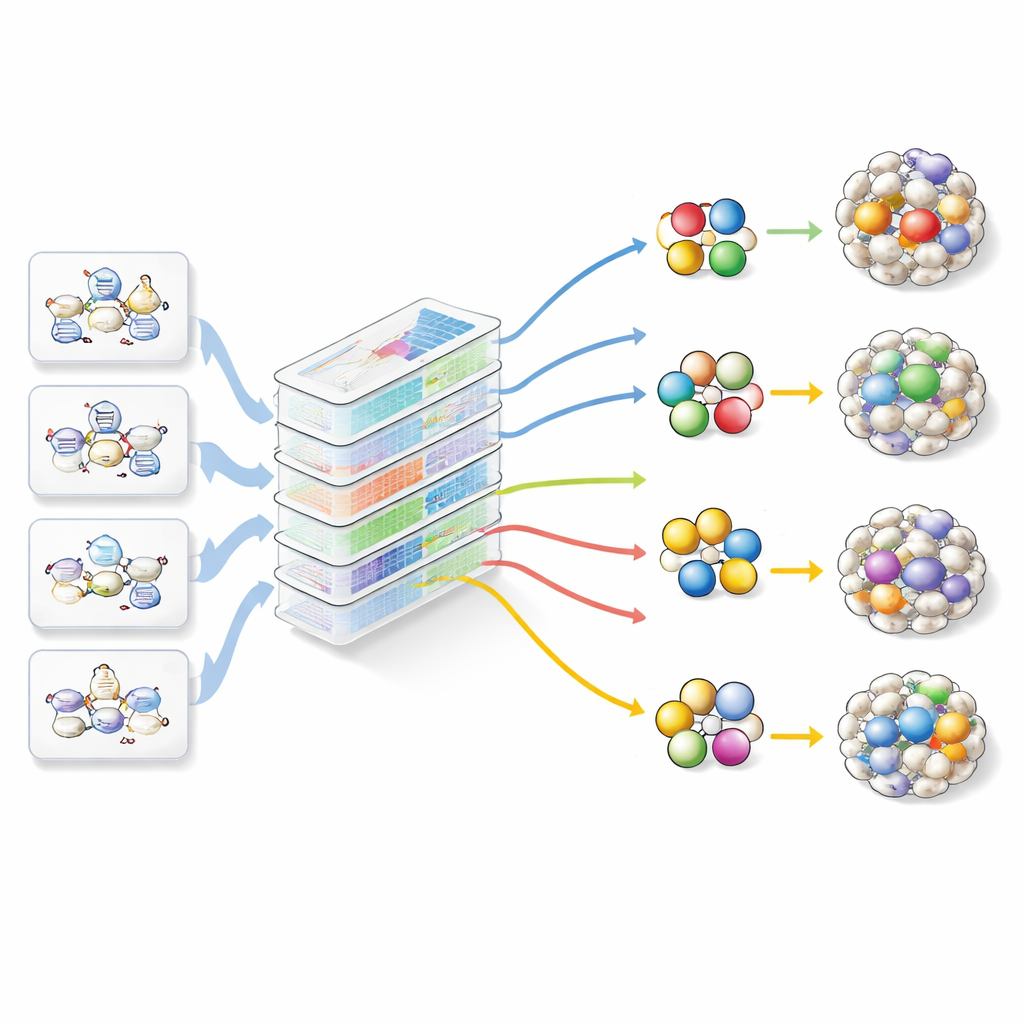
Seçenekleri Gezinmek İçin Yeni Bir Rehber
Bu boşluklara rağmen ilerleme kaydetmek için yazarlar DiReG’i (Direct Reprogramming Guide) geliştirdi; bu web uygulaması her şeyi bilen yeni bir algoritmadan çok bir kontrol merkezi gibi çalışıyor. DiReG var olan büyük araçlardan tahminleri topluyor, açık kromatin verilerinden doğrudan çalışan basit bir motif‑temelli yöntem ekliyor ve tüm bunları yüzlerce yeniden programlama makalesinden oluşan küratörlü bir kütüphane ile bağlıyor. Yerleşik soru‑cevap sistemlerini kullanarak araştırmacılar literatürdeki protokolleri, faktör kombinasyonlarını ve deneysel ayrıntıları hızla bulabiliyor. Ardından aday faktör setlerini DiReG’in analiz alanına taşıyarak, uygulamanın düzenleyici ağlarını çizmesini, etkilenen genlerin istenen dokuya benzer görünüp görünmediğini test etmesini, faktörlerin doğal olarak nerelerde aktif olduğunu kontrol etmesini ve dönüşümü hızlandırabilecek veya engelleyebilecek bilinen etkileşim ortaklarını ve izoformları vurgulamasını sağlayabiliyorlar.
Daha Akıllı Hücre Dönüşümü İçin Bir Adım
Uzman olmayanlar için temel mesaj, bu çalışmanın henüz herhangi bir hücreyi herhangi bir hücreye dönüştürecek tek tuşla çalışan bir reçete sunmadığıdır. Bunun yerine bilinenleri, denenmiş olanları ve hangi genetik anahtarların birlikte çalışma olasılığının daha yüksek olduğunu merkezi, etkileşimli bir harita halinde sunuyor. Araştırmacıların bilgisayar tahminlerini biyolojik bağlamla hızlıca birleştirmesine yardımcı olarak DiReG, çıkmaz deneyleri azaltmayı ve protokol tasarımını daha mantıklı hale getirmeyi amaçlıyor. Yazarlar ayrıca hâlâ eksik olanları—protein formları, kimyasal işaretler, hücreler arası etkileşimler ve gerçek protein etkinliği üzerine daha zengin verileri—sıralıyor. Bu katmanları dolduran yeni teknolojiler geliştikçe, burada sunulan fikirler üzerine inşa edilen gelecek araçlar doğrudan hücresel yeniden programlamayı daha güvenilir, daha güvenli ve klinik uygulamaya daha yakın hale getirebilir.
Atıf: Lauber, M., List, M. Navigating the landscape of direct cellular reprogramming with DiReG. npj Syst Biol Appl 12, 35 (2026). https://doi.org/10.1038/s41540-026-00652-z
Anahtar kelimeler: hücresel yeniden programlama, transkripsiyon faktörleri, hesaplamalı biyoloji, gen düzenleyici ağlar, rejeneratif tıp