Clear Sky Science · tr
SMART: grafik sinir ağları ve metrik öğrenme kullanarak mekansal çok‑omik toplulaştırma
Dokuları Mahalle Haritaları Olarak Görmek
Vücudumuz, genlerin, proteinlerin ve DNA paketlenmesinin belirli konumlarda uyum içinde çalıştığı canlı hücresel mahallelerden oluşur. Yeni mikroskoplar ve sekanslama araçları artık ince doku kesitleri içinde bu moleküler katmanların birçoğunu doğrudan okuyabiliyor; ancak bu çok katmanlı, mekansal verilerin selini organların nasıl düzenlendiğine dair net görüntülere dönüştürmek devasa bir hesaplama zorluğudur. Bu çalışma, bilim insanlarının bu karmaşık sinyalleri farklı hücre topluluklarının nerede yaşadığını ve nasıl düzenlendiklerini gösteren ayrıntılı haritalara birleştirmelerine yardımcı olan SMART adlı bir bilgisayar yöntemini tanıtıyor.
Hücre Mahallelerini Haritalamanın Zorluğu
Modern "mekansal çok‑omik" teknolojiler, RNA, hücre yüzeyindeki proteinler ve DNA’nın ne kadar açık veya kapalı olduğu gibi birden çok moleküler bilgiyi aynı anda ölçebiliyor ve her ölçümün doku kesiti içindeki tam konumunu kaydediyor. Her bir omik türü hücre davranışı hakkında farklı bir bakış açısı sunuyor, ancak bunlar gürültülü, yüksek boyutlu ve doğal olarak birbirleriyle hizalanmış değil. Buna ek olarak, aynı tip hücreler her zaman bir arada kümelenmez; bir organ boyunca dağılmış adacıklar halinde görünebilirler. Mevcut yazılım araçları genellikle mekansal düzeni göz ardı ediyor, farklı omikler arasındaki ilişkiyi fazla basitleştiriyor veya yeni cihazların üretebildiği çok büyük veri setleriyle ölçeklenmekte zorlanıyor.
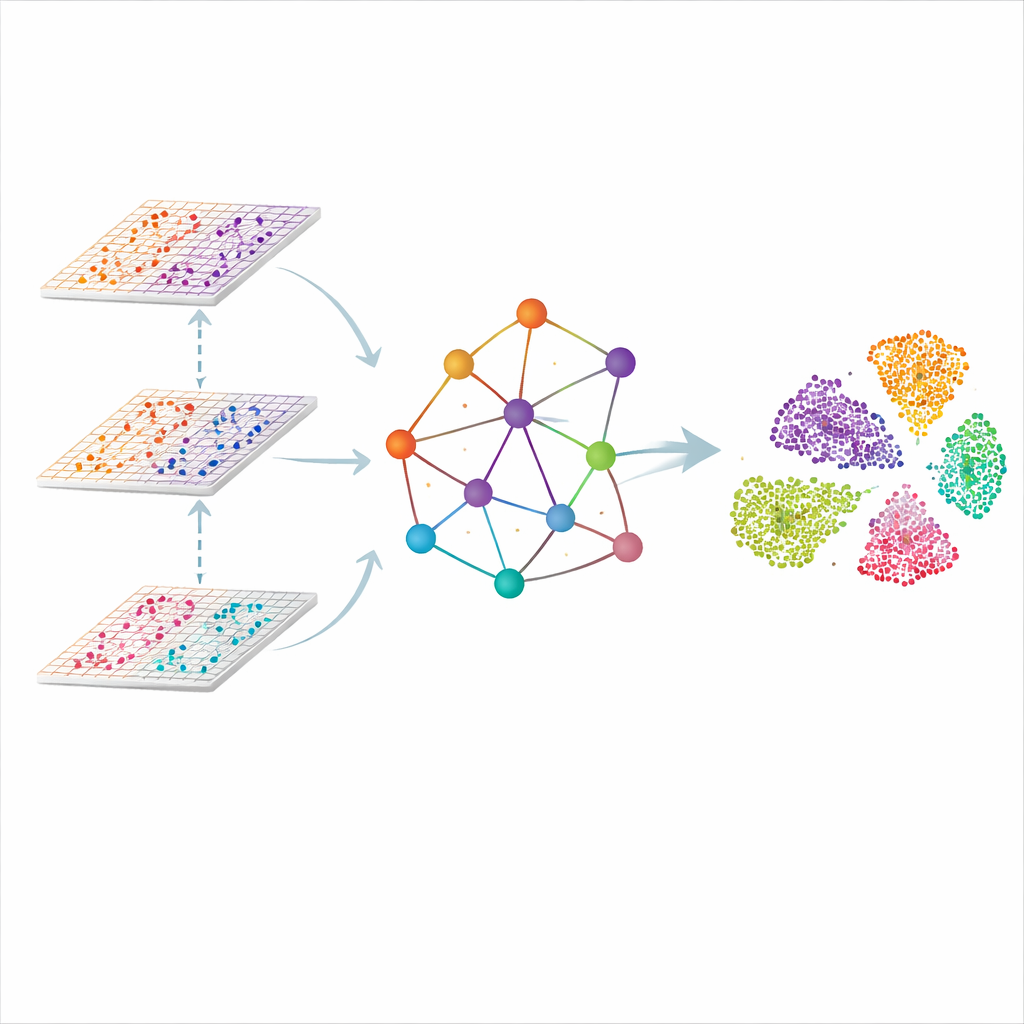
Sadece Hücre Listesi Değil, Dokunun Bir Grafiği
SMART, problemi her ölçüm noktasını dokudaki bir ağ içindeki bir nokta olarak ele alarak yaklaşıyor. Yakın noktalar bağlanarak mekansal bir grafik oluşturuluyor ve her omikten gelen moleküler ölçümler ilk olarak bireysel genlerden ziyade genel desenleri yakalayan daha küçük, koordine özellik setlerine sıkıştırılıyor. Graf için tasarlanmış bir tür sinir ağı sonra bağlantılar boyunca bilgi aktarıyor; böylece her nokta komşularını "dinleyebiliyor" ve aynı zamanda her omikin nasıl katkıda bulunduğunu takip edebiliyor. Sonuç, beyin katmanları ya da lenf düğümündeki zonlar gibi benzer doku bölgelerinin doğal olarak gruplaştığı paylaşılan, düşük boyutlu bir gösterimdir.
Modele Nelerin Benzer Olması Gerektiğini Öğretmek
Salt fiziksel komşuluğu takip etmek yeterli değil, çünkü aynı tip hücreler uzakta olabilir. SMART, yüz tanıma sistemlerinden alınan ikinci bir bileşen ekliyor: üçlülerle metrik öğrenme. Her nokta için yöntem otomatik olarak çok benzer moleküler desenlere sahip başka bir nokta ("pozitif") ve açıkça farklı olan bir diğerini ("negatif") buluyor. Ardından iç gösterimi, pozitiflerin daha yakın çekilmesi ve negatiflerin daha uzak itilmesi yönünde ayarlıyor; bu, dokuda fiziksel olarak uzak olsalar bile gerçekleşiyor. Bu çekişme, SMART’ın her omik katmanının ana ayrıntılarını korumasını zorlayan bir yeniden yapılandırma adımıyla eşzamanlı olarak çalışıyor; böylece mekansal süreklilik moleküler özgüllükle dengeleniyor.
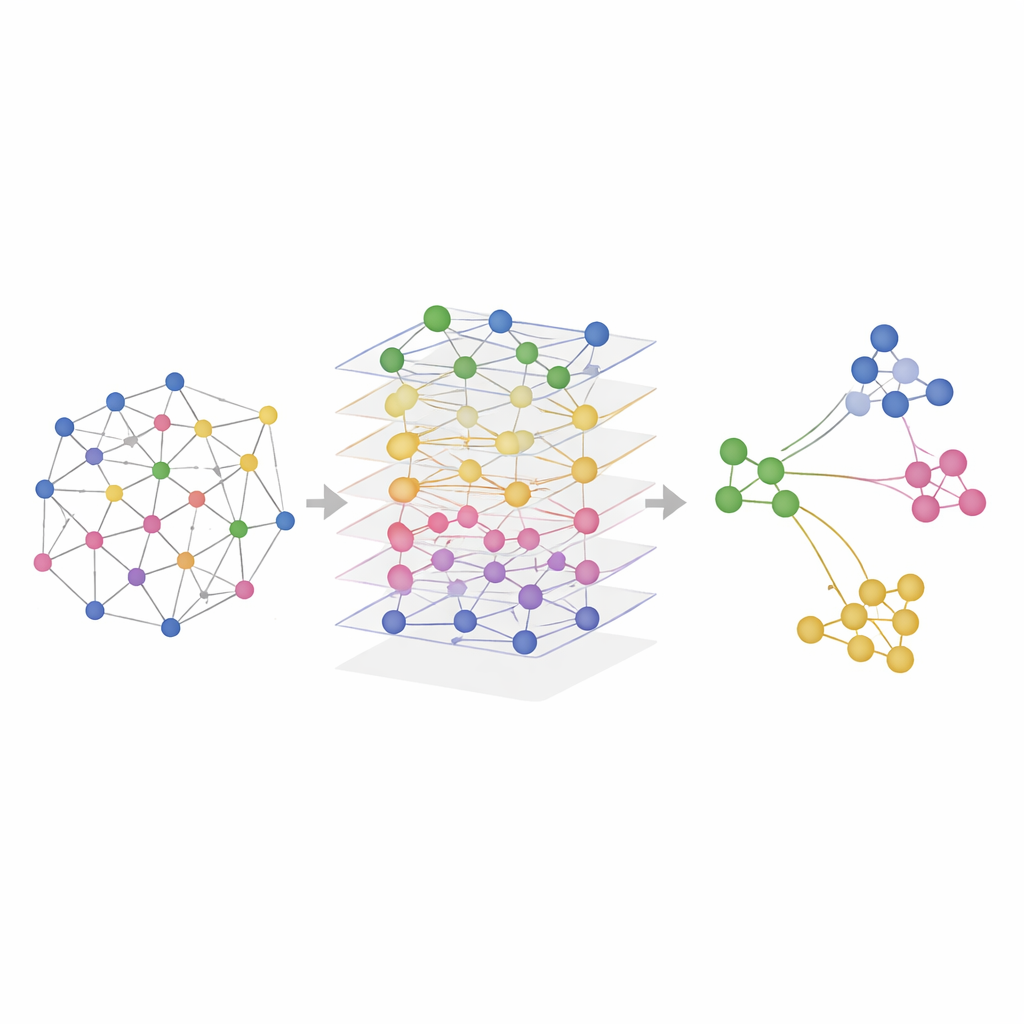
SMART’ı Gerçek Dokularda Test Etmek
Araştırmacılar SMART’ı hem simüle edilmiş verilerde hem de fare beyni, fare dalakları, insan lenf düğümleri ve bademciklerde RNA, proteinler ve kromatin erişilebilirliğinin kombinasyonlarını ölçen gerçek deneylerde test ettiler. Gerçek mekansal bölgelerin bilindiği kontrollü simülasyonlarda SMART, yer‑gerçeği desenlerini en doğru biçimde geri kazandı ve her omik katmanda bulunan ilişkileri korudu. Gerçek veri setlerinde SMART, rekabet eden yöntemlere göre belirli beyin bölgeleri veya lenfoid organlardaki immün hücre zonları gibi ince anatomik yapıların daha keskin biçimde tanımlanmasını sağladı ve hesaplama yükünü düşük tuttu. SMART‑MS adlı ilişkili bir versiyon, aynı organın birden çok doku kesiti arasında hizalama yaparak ve deneyler arasındaki teknik farklılıkları düzelterek aynı fikirleri çoklu kesitlere genişletiyor.
Mekansal Biyolojinin Yeni Dalgası İçin Hızlı Haritalar
Basitçe söylemek gerekirse, SMART moleküler atlasların bir sonraki nesli için bir harita oluşturma motorudur. Doku düzeninin ağ‑tarzı modellenmesini "benzer" sayılması gerekenleri içeren yerleşik bir anlayışla birleştirerek geniş, dağınık mekansal çok‑omik ölçümler koleksiyonlarını organların tutarlı mahalle haritalarına dönüştürebilir. Bu, araştırmacıların belirli hücre tiplerinin ve mikroçevrelerin nerede bulunduğunu, gelişim veya hastalık sırasında nasıl değiştiklerini ve yeni deneysel teknolojilerin nasıl bir araya geldiğini daha kolay görmesini sağlar. Mekansal veriler boyut ve karmaşıklık bakımından büyümeye devam ettikçe, SMART ve SMART‑MS gibi araçlar ham ölçümleri biyolojik içgörülere dönüştürmede kilit rol oynayacaktır.
Atıf: Du, Z., Chen, Q., Huang, W. et al. SMART: spatial multi-omic aggregation using graph neural networks and metric learning. Nat Commun 17, 2876 (2026). https://doi.org/10.1038/s41467-026-70821-5
Anahtar kelimeler: mekansal çok‑omik, graf sinir ağları, doku mikroçevresi, veri entegrasyonu, tek hücre biyolojisi