Clear Sky Science · tr
XL-MSDigger: çapraz bağlama kütle spektrometrisi için derin öğrenme tabanlı, çok yönlü bir çözüm
Proteinlerin Bir arada Nasıl Durduğunu Görmek
Vücudumuzdaki her süreç, proteinlerin yalnızca doğru şekillere bürünmesine değil, aynı zamanda doğru ortakları bulmasına da bağlıdır. Ancak bu moleküler ilişkileri hareket halinde izlemek son derece zordur. Bu çalışma, XL-MSDigger adlı bir yazılım platformunu tanıtıyor; modern yapay zekâyı kullanarak çapraz bağlama kütle spektrometrisinden gelen gürültülü verilerden çok daha temiz sinyaller çıkarıyor ve bilim insanlarının hücre içinde proteinlerin nasıl düzenlendiğini ve kiminle etkileştiğini haritalandırmalarına yardımcı oluyor.
Kalabalık Bir Moleküler Dünyayı Çözmek
Proteinlerin nasıl yapılandığını ve nasıl bağlandıklarını öğrenmek için araştırmacılar sıklıkla çapraz bağlama kütle spektrometrisini kullanır. Bu yaklaşımla, küçük kimyasal “köprüler” proteinlerin birbirine yakın bölümlerini birbirine bağlar. Bağlı parçalar daha sonra peptidlere ayrılır ve bir kütle spektrometresinde tartılır. İlk bakışta, parçaların deseni hangi protein parçalarının mekânda yakın olduğunu ortaya koyar; tıpkı hangi kitap sayfalarının birbirine klipslendiğini bulmak gibi. Ancak uygulamada ortaya çıkan veriler son derece karmaşıktır. Mevcut bilgisayar araçları çoğunlukla yalnızca temel kütle bilgisine bakar ve muazzam olası kombinasyon sayısıyla başa çıkmakta zorlanır; bu da kaçırılan bağlantılara ve yanlış eşleşmelere yol açar.
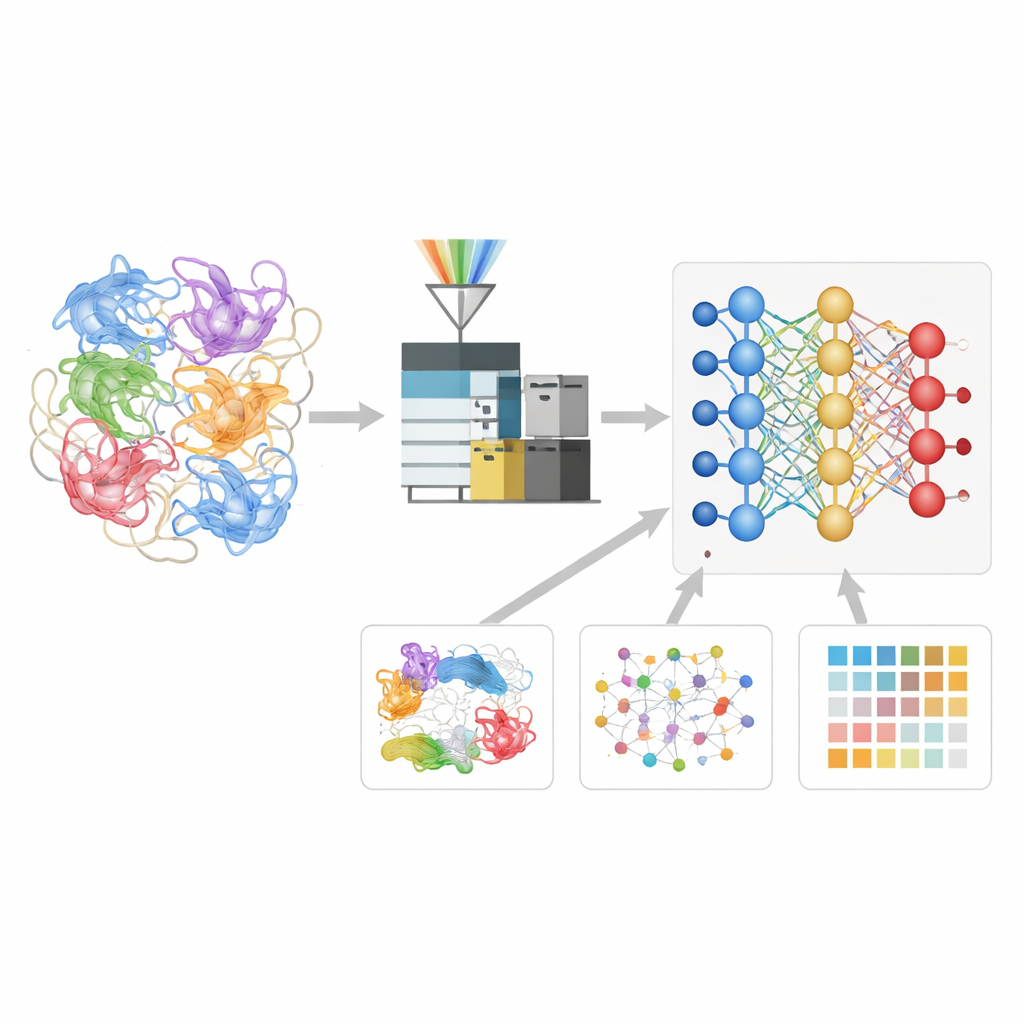
Protein Fragmentlerinin Dilini Bir Sinir Ağına Öğretmek
Yazarlar, bu çapraz bağlama deneylerini daha iyi yorumlamak için Deep4D-XL adlı bir derin öğrenme modeli geliştirdiler. Önce insan hücrelerinden proteinleri çapraz bağlayarak, bunları peptidlere ayırarak ve yalnızca kütlelerini değil, aynı zamanda cihaz içinde ne kadar süre kaldıklarını ve iyon-mobilite odasındaki hareketlerini de kaydederek büyük bir referans seti oluşturdular. Her çapraz bağlı çift model için kodlandı; model hem peptid ortaklarını okumak için ikiz “Siamese” bir tasarım kullanıyor hem de bilgilerini birleştirmek için çapraz-dikkat (cross-attention) adımı uyguluyor. Bundan hareketle ağ, yeni herhangi bir çapraz bağlı peptidin üç ana özelliğini tahmin etmeyi öğreniyor: deneyde ne zaman görünmesi gerektiği, nasıl hareket edeceği ve parçalanma deseninin nasıl olacağı.
Tahminleri Daha Temiz Sinyallere Çevirmek
XL-MSDigger bu tahmin motorunu iki ana veri toplama tarzı için analiz iş akışlarına sarıyor. Geleneksel, hedefe yönelik tarzda cihaz, uçta seçtiği iyonlardan parçacıkları seçici olarak kaydeder. XL-MSDigger, yerleşik arama yazılımlarından gelen ilk eşleşmeleri alır ve her aday için modelin öngördüğü davranışla yeniden değerlendirir. İkinci bir sinir ağı, tahmin ile deneyi bir dizi boyut boyunca karşılaştırır ve geliştirilmiş puanlar atar. Bu yeniden puanlama adımı, maya ve insan örneklerinde farklı proteinler arasındaki güvenle tespit edilen bağlantı sayısını neredeyse iki katına çıkarırken hata oranlarını düşük tutar ve öncekiye göre çok daha fazla protein–protein etkileşimini ortaya çıkarır.
Tarafsız Verilerin Selini Anlamlandırmak
Bu cihazları çalıştırmanın daha yeni bir yolu olan veri-bağımsız edinim (data-independent acquisition), numunedeki neredeyse her şeyin parçalarını kaydederek kapsamı artırır ancak bunaltıcı miktarda veri üretir. Bugüne kadar, ortaya çıkan çapraz bağlantıların kaç tanesinin gerçekten gerçek olduğunu tahmin etmenin iyi bir yolu yoktu. XL-MSDigger, Deep4D-XL’yi kullanarak dikkatle eşleştirilmiş bir “dekoY” kütüphanesi (sahte çapraz bağlantılar) oluşturur ve ardından gerçek ve dekoY girişlerini birlikte analiz eder. Dekoyların ne sıklıkta atlatıldığını görerek yazılım yanlış keşif oranını tahmin edebilir ve başka bir sinir ağını gerçek ile sahte eşleşmeleri ayırmak üzere eğitebilir. Bu yeniden puanlama, güvenilir çapraz bağlı sinyal sayısını yaklaşık beş kat artırır ve gerçek ile dekoy desenleri arasında net bir ayrım üretir.
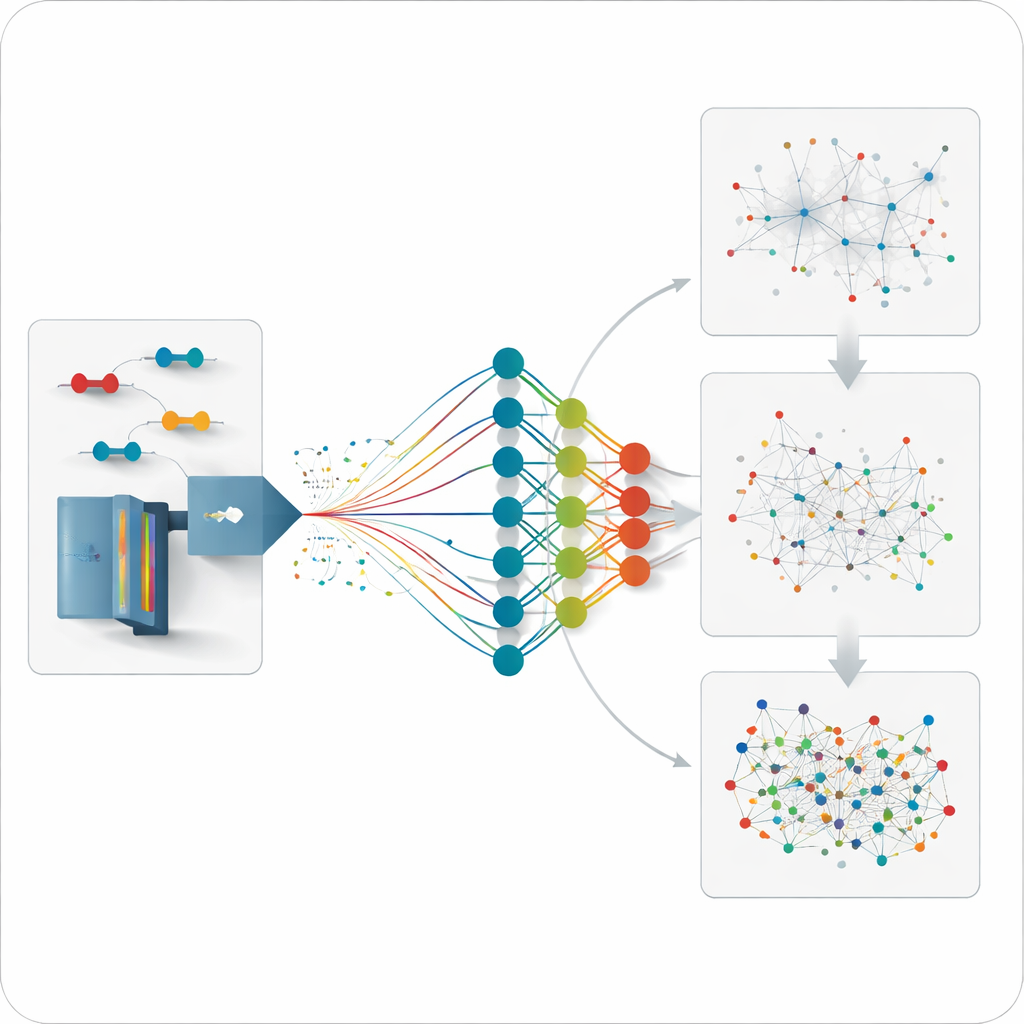
Henüz Ölçülmemiş Olanı Tahmin Etmek
Model herhangi bir makul çapraz bağlı peptidin nasıl davranması gerektiğini öngörebildiği için ekip bir adım daha ileri giderek daha önce doğrudan ölçülmemiş bağlantılar için veri analizleri yapabiliyor. Belirli proteinlere veya etkileşim ağlarına odaklanan orta büyüklükte tahmini kütüphaneler üretiyorlar ve ardından tarafsız verileri bu kütüphanelere karşı tarıyorlar. Bu strateji, tek bir protein içindeki ve önemli şaperon proteinlerin ortakları arasındaki ek bağlantıları ortaya çıkarıyor; bulunan uzaklıklar bilinen üç boyutlu yapılarla iyi uyum gösteriyor. Ayrıca geleneksel, daha sınırlı deneysel kütüphanelerle kaçırılan etkileşimleri, özellikle düşük bolluklu bağlantılarda geri kazanıyor.
Protein Ortaklıklarına Daha Net Bir Pencere Açmak
Uzman olmayanlar için ana mesaj şudur: XL-MSDigger, zaten güçlü bir deneysel yöntemin üzerine yerleştirilmiş yüksek eğitimli bir desen tanıyıcı gibi davranır. Gerçek çapraz bağlı sinyallerin aynı anda birkaç boyutta nasıl görünmesi gerektiğini öğrenerek geniş, dağınık veri setlerini süzebilir, muhtemel sahtekarları eleyebilir ve önceden gizlenmiş gerçek protein bağlantılarını kurtarabilir. Tam, tüm proteom uygulamaları hâlâ yüksek hesaplama gücü gerektirecek olsa da, bu çalışma çapraz bağlama deneylerini derin öğrenmeyle birleştirmenin proteinlerin hücre içinde nasıl düzenlendiğini ve kimlerle buluştuğunu görmemizi büyük ölçüde netleştirebileceğini gösteriyor.
Atıf: Chen, M., Hao, Y., Huang, X. et al. XL-MSDigger: a deep learning-based, versatile solution for cross-linking mass spectrometry. Nat Commun 17, 2554 (2026). https://doi.org/10.1038/s41467-026-69489-8
Anahtar kelimeler: protein etkileşimleri, çapraz bağlama kütle spektrometrisi, derin öğrenme, proteomik, veri-bağımsız edinim