Clear Sky Science · tr
AlphaFold ile intrinsically disordered protein’lerin atomik çözünürlüklü toplulukları
Biçim değiştiren proteinlerin önemi
Hücrelerimiz, asla tek ve sert bir şekle yerleşmeyen proteinlerle doludur. Bu “intrinsically disordered” (içsel olarak düzensiz) proteinler, düzgün katlanmış makinelerden çok gevşek erişte gibi davranır, ancak hücre sinyalleşmesinden nörodejeneratif hastalıklara kadar pek çok süreçte merkezî rol oynarlar. Sürekli hareket edip esnedikleri için, bunların atomik ayrıntıyla tam şekil çeşitliliğini yakalamak son derece zor olup genellikle yıllarca süren deneyler ve yoğun hesaplamalar gerektirir. Bu makale, yapay zekâ ile fiziği birlikte kullanarak bu huzursuz molekülleri çok daha verimli şekilde haritalandırmanın yeni bir yolunu sunuyor.
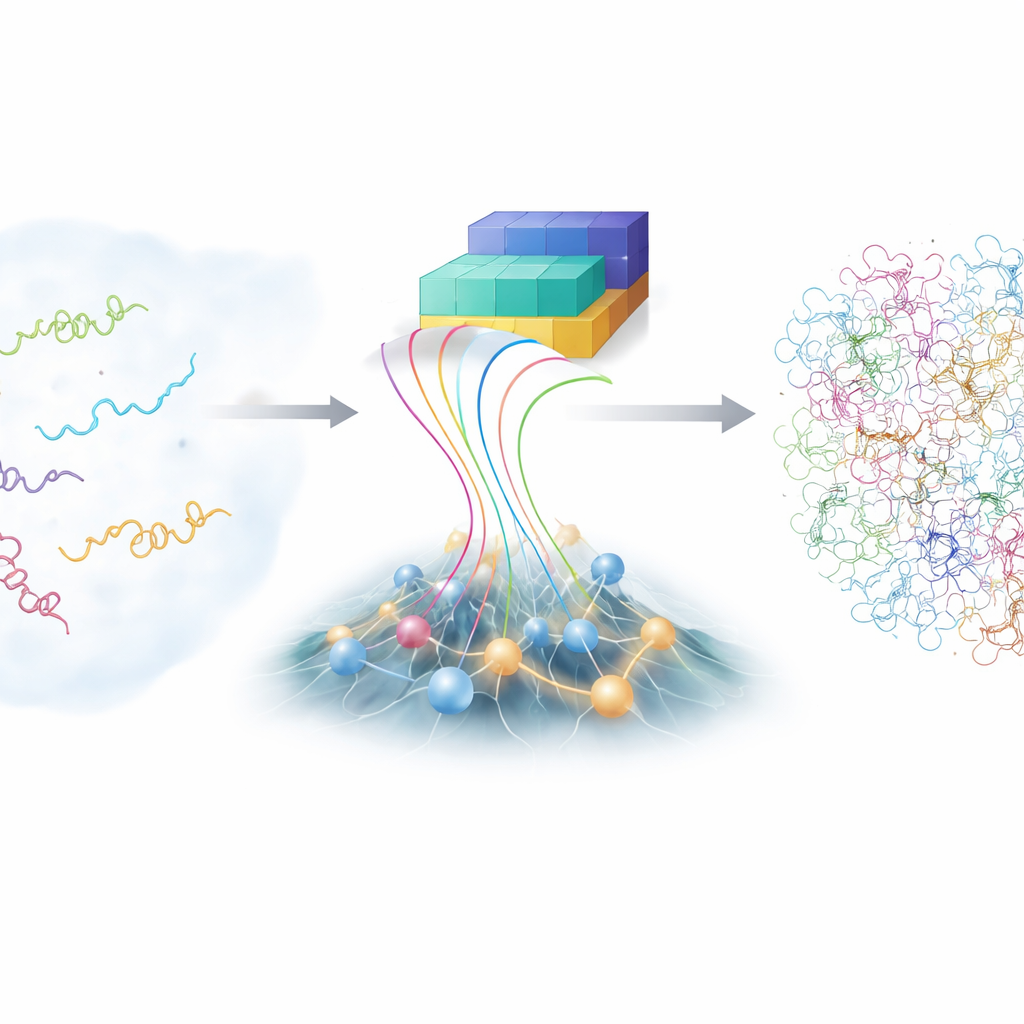
Huzursuz moleküllerin zorluğu
Ders kitaplarındaki tek bir düzenli yapıyı gösteren protein modellerinin aksine, intrinsically disordered proteinler (IDP’ler) olası şekillerin geniş bir alanında gezinir. Bu esneklik, onların birçok farklı partneri tanımasını kolaylaştırırken aynı zamanda incelenmelerini de zorlaştırır. Gelişmiş nükleer manyetik rezonans ve X-ışını saçılması gibi geleneksel laboratuvar teknikleri birçok şeklin ortalamaları hakkında bilgi verir, fakat her bir bireysel formu ortaya koymaz. Tam atomik ayrıntıda bilgisayar simülasyonları teoride bir IDP kıvrılırken her atomu izleyebilir; ancak bu simülasyonlar son derece maliyetli olup hassas fiziksel modellere bağımlıdır. Sonuç olarak, bilim topluluğunun öğrenebileceği sınırlı sayıda doğru, ayrıntılı IDP topluluğu vardır.
Akıllı tahminleri fiziksel kurallarla birleştirmek
Son yıllarda AlphaFold ailesi derin öğrenme araçları, amino asit dizilerinden protein yapılarını tahmin ederek biyolojiyi şaşkına çevirdi. Ancak düzensiz proteinler için AlphaFold’un tipik gücü—tek bir en iyi şekli tahmin etmek—daha az faydalıdır, çünkü IDP’lerin yalnızca bir şekli yoktur. Buna karşın AlphaFold, zincirin farklı bölümlerinin birbirine yakın veya uzak olma olasılığı hakkında zengin bilgiler sağlar. Yazarlar, bu yapay zekâ kaynaklı bilgiyi yumuşak yönlendirme olarak ele alan ve bunu hızlı, fiziğe dayalı bir modelle harmanlayan bAIes adlı yeni bir çerçeve geliştirdiler. Bu fiziksel model kasıtlı olarak bir “rastgele koil” bakış açısından başlar; burada zincir herhangi bir belirli yapıyı tercih etmeden tüm olası bükülme ve burulmaları keşfeder.
Rastgele düğümlenmelerden gerçekçi topluluklara
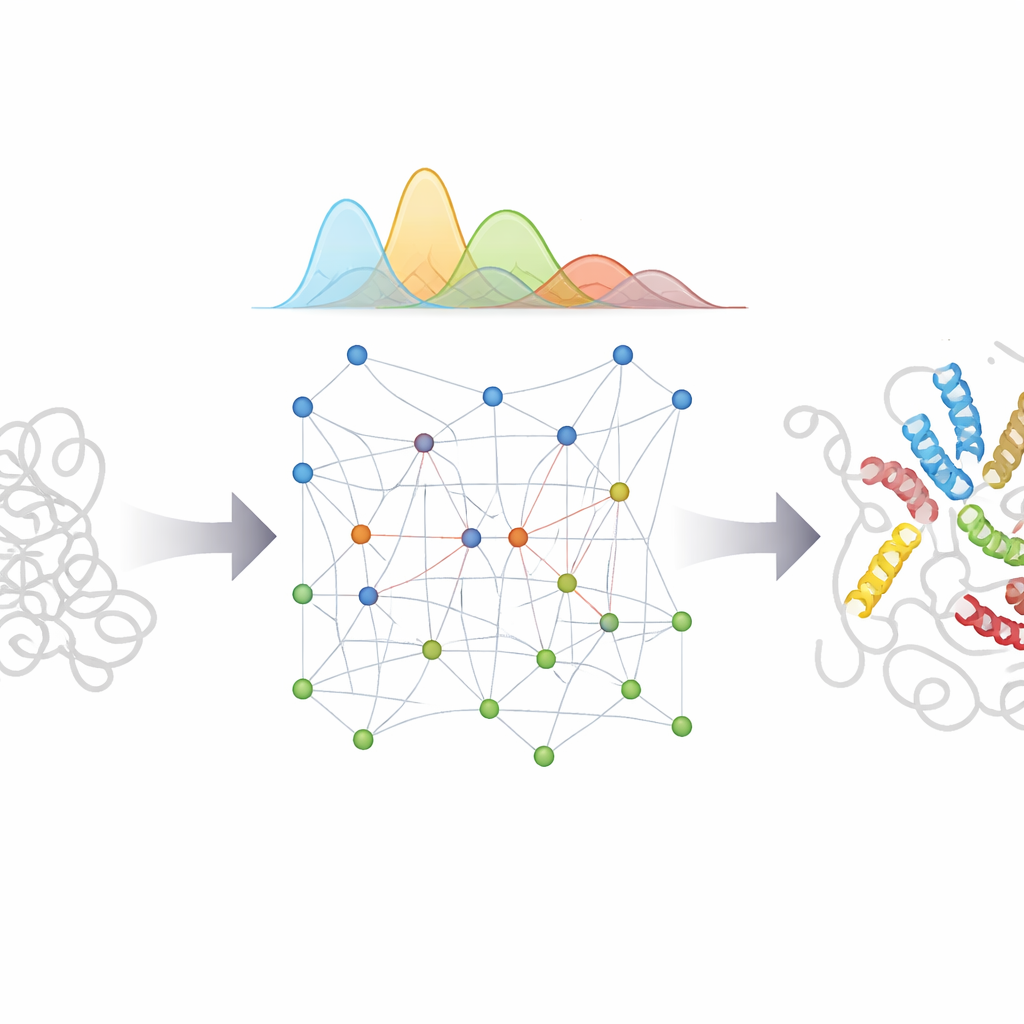
Önce araştırmacılar, tamamen yapısal olmayan bir protein zincirinin davranışını binlerce bilinen protein yapısından çıkarılan istatistiklere dayalı olarak yeniden üreten verimli bir fiziksel model kurdular. Bu model “önbilgi” olarak hizmet eder—eğer başka bir şey bilmiyorsak bir IDP’nin nasıl hareket edeceğine dair temel beklenti. Ardından bAIes, hangi kalıntı çiftlerinin birbirine yakın olma eğiliminde olduğuna dair AlphaFold tahminlerini okur. Proteini tek bir desene zorlamak yerine, bu ipuçlarını yerleşik belirsizlikle nazik mesafe kısıtlamalarına dönüştürür ve zincirin yapay zekânın önerilerini ancak bunlar daha geniş fiziksel resimle tutarlı olduğunda yerine getirmesine izin verir.
Gerçek deneylerle test etmek
Bu yaklaşımın işe yarayıp yaramadığını görmek için ekip, bAIes’i neredeyse tamamen rastgele koillerden geçici heliksler ve birden çok domaine sahip daha karmaşık sistemlere kadar uzanan 21 protein setine uyguladı. Her biri için bilgisayar tarafından üretilen toplulukları yerel ayrıntıları ve küresel boyut ile şekli ölçen geniş yelpazede deneysel ölçümlerle karşılaştırdılar. Alzheimer ile ilişkili peptid Aβ40 gibi çok gevşek proteinler için basit rastgele koil modeli zaten gerçeğe yakındı ve bAIes bu iyi uyumu korudu. Kısmi yapıya sahip proteinlerde bAIes, kısa helikal segmentlerin ve kompakt lekelerin nerede ortaya çıkıp kaybolduğunu doğru şekilde yakalayarak deneylerle uyuşmayı iyileştirdi. Kritik olarak, yöntem AlphaFold çok kendinden emin olup çözelti deneylerinin düzensizlik gösterdiği yerlerde yanlış olarak stabil katlar tahmin etse bile dayanıklılığını korudu; çünkü bAIes yapay zekâ girdisindeki hatalara açıkça izin veriyor.
Mevcut yöntemleri geride bırakmak veya eşleşmek
Yazarlar daha sonra bAIes’i, özel süperbilgisayarlarda çalıştırılan tam atom simülasyonları, proteinleri boncuklara basitleştiren önde gelen kaba taneli modeller ve simülasyon verileriyle eğitilmiş yeni derin öğrenme üreticileriyle karşılaştırdılar. Birden çok testte bAIes, deneysel verileri yeniden üretmede tutarlı şekilde bu yaklaşımlarla eşleşti veya onları geride bıraktı ve tam ölçekli simülasyonlara kıyasla çok daha az hesaplama kaynağı gerektirdi. Ayrıca basit IDP’lerin ötesinde çalıştı; birkaç sert domaini esnek bağlayıcılarla birleştiren proteinleri işleyebildi ve çözeltideki genel şekillerini geri kazandı. Araştırmacılar bAIes topluluklarını daha fazla deneysel veri ile ince ayar yaptıklarında, uyuşma daha da iyileşti ve yöntemin bütünleştirici modelleme için güçlü bir başlangıç noktası olabileceğini gösterdi.
Bu durum biyoloji ve tıp için ne anlama geliyor
AlphaFold’un desen tanıma gücünü özenle tasarlanmış bir fiziksel model ve belirsizliğin Bayesyen ele alınmasıyla birleştirerek, bAIes tek karelik görüntüler yerine düzensiz proteinlerin ayrıntılı “filmlerine” pratik bir yol sunuyor. Bu atomik ayrıntılı topluluklar, esnek bölgelerin partnerleri nasıl tanıdığını, Parkinson ve Alzheimer gibi hastalıklarda yanlış katlanma ve agregasyonun nasıl başladığını ve küçük moleküllerin belirsiz, değişken hedeflere nasıl bağlanabileceğini anlamaya yardımcı olabilir. Yöntem verimli ve açık kaynaklı yazılıma entegre olduğundan, birçok düzensiz protein için gerçekçi topluluklar üretmek, deneyleri yönlendirmek ve yalnızca tek bir yapı değil, yaşamın en esnek moleküllerinin benimseyebileceği şekil yelpazesini tahmin etmeyi amaçlayan gelecekteki yapay zekâ sistemlerini desteklemek üzere yaygın şekilde benimsenebilir.
Atıf: Schnapka, V., Morozova, T.I., Sen, S. et al. Atomic resolution ensembles of intrinsically disordered proteins with Alphafold. Nat Commun 17, 2399 (2026). https://doi.org/10.1038/s41467-026-69172-y
Anahtar kelimeler: intrinsically disordered proteinler, AlphaFold, Bayesyen modelleme, protein toplulukları, yapısal biyoloji