Clear Sky Science · tr
ForkML ile insan hücrelerinde DNA replikasyon çatalı ilerlemesinin otomatik haritalanması
DNA kopyalama hızını izlemenin önemi
Her insan hücresi bölündüğünde, üç milyardan fazla DNA harfini hızlı ve hatasız şekilde kopyalamak zorundadır. Bu kopyalama süreci yavaşlar veya durursa genom zarar görebilir ve kanser ile gelişimsel bozukluklara katkıda bulunabilir. Ancak şimdiye dek bilim insanlarının, bireysel DNA “kopyalama makinelerinin” belirli insan DNA bölgeleri boyunca tam olarak ne kadar hızlı ilerlediğini görmelerini sağlayan basit bir yöntem yoktu. Bu makale, nanopore DNA dizileme ve makine öğrenmesini kullanarak bu görevi benzeri görülmemiş bir ölçekte otomatikleştiren yeni bir teknik olan ForkML’i sunuyor.
Hücudun kopyalama makinelerini dolaylı olarak izlemek
DNA, çift sarmal boyunca hareket eden ve yeni iplikler oluşturan replikasyon çatalı adı verilen küçük moleküler makineler tarafından çoğaltılır. ForkML, araştırmacıların bu çataları iki kısa ve sabit arayla uygulanan zararsız bir kimyasal işaretçi olan BrdU’yu yeni sentezlenen DNA’ya ekleyerek dolaylı yoldan görmelerini sağlar. BrdU, nanopore dizileyicileriyle tek DNA moleküllerinde algılanabildiği için bilim insanları her bir DNA ipliğinde bir çatalın iki darbede geçtiği yerde iki işaretli “şerit” görürler. Şeritler arasındaki mesafeyi ölçüp bilinen zaman aralığına böldüklerinde, genomun o bölgesinde her bir çatalın ne kadar hızlı ilerlediğini hesaplayabilirler. 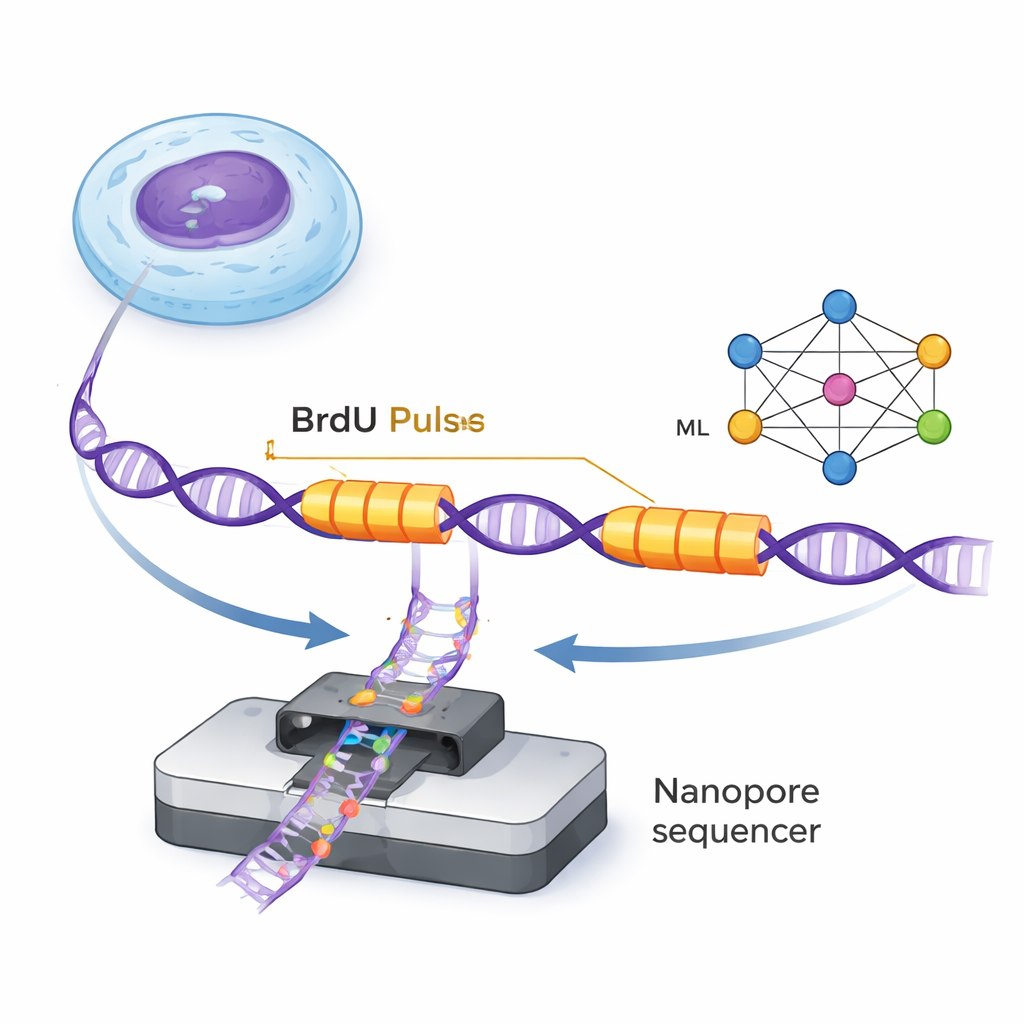
Bilgisayara kimyasal izleri okumayı öğretmek
Yazarların mayada yaptıkları önceki çalışmalarda bu BrdU izleri basit kurallarla tespit edilebiliyordu, ancak insan hücrelerinde sinyaller daha zayıf ve daha karmaşıktır. Uzman insanlar hâlâ karakteristik deseni—darbenin başladığında BrdU’da keskin bir artış ve yıkama sonrası yavaş bir düşüş—tanıyabilir, ancak milyonlarca DNA fragmanı için bunu gözle yapmak imkânsızdır. ForkML bunu, binlerce elle açıklanmış örnek üzerinde eğitilen bir sinir ağı (makine öğrenimi biçimi) ile çözer. Model her DNA bölgesini arka plan, sağa doğru hareket eden veya sola doğru hareket eden çatal olarak sınıflandırmayı ve her BrdU darbesinin başlangıcını yüksek doğrulukla belirlemeyi öğrenir. Bu da tek bir dizileme çalışmasından binlerce bireysel çatal hızının tamamen otomatik haritalanmasını sağlar.
Genom boyunca stres ve farklılıkları ölçmek
ForkML’i insan kolon kanseri hücre hattında kullanarak ekip, her deneyde 2.000’in üzerinde çatal hızı ölçümü elde etti ve tipik bir çatalın dakikada yaklaşık 1.2 kilobaz ilerlediğini buldu; bu, daha önceki düşük verimli yöntemlerle uyumludur. Hücrelere DNA replikasyonunu yavaşlattığı bilinen ilaçlar uyguladıklarında ForkML bu yavaşlamayı açıkça tespit etti ve bunun replikasyon stresini hassas şekilde ölçebildiğini gösterdi. Her çatal referans genoma haritalandığı için yazarlar hızları bir bölgenin hücre döngüsü sırasında normalde ne zaman kopyalandığı, DNA’nın ne kadar sıkı paketlendiği ve ne kadar aktif olarak RNA’ya çevrildiği gibi diğer özelliklerle ilişkilendirebildiler. 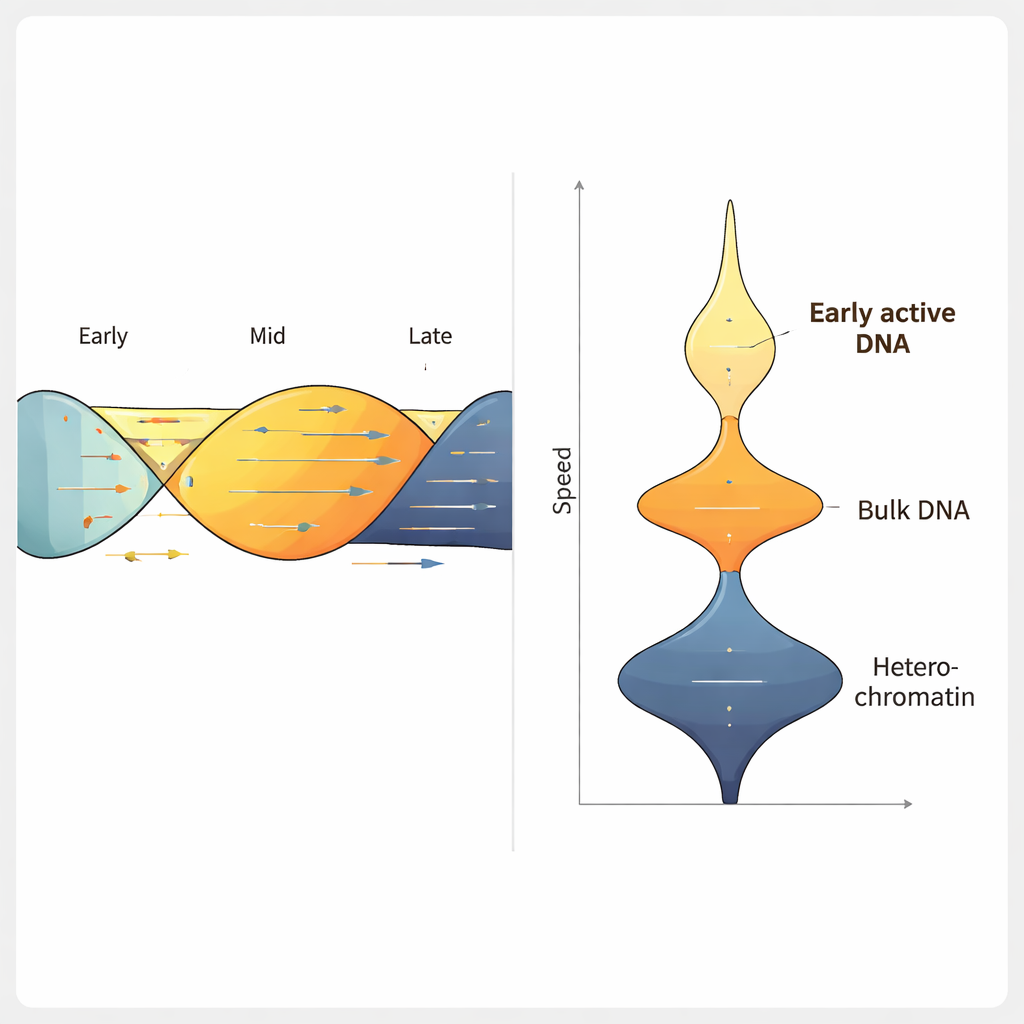
DNA kopyalamanın nerede başladığını ve ipliklerin nasıl farklılaştığını açığa çıkarmak
Hızın ötesinde, ForkML aynı molekül boyunca çatalların ayrıldığı veya birleştiği noktaları tespit ederek DNA replikasyonunun nerede başladığını ve durduğunu da belirler. 20.000’den fazla başlangıç sitesini haritalayarak yazarlar, insan hücrelerinin karma bir strateji kullandığını doğruluyor: bazı kopyalamalar iyi tanımlanmış başlatma bölgelerinde başlarken, çoğu başlangıç genom boyunca dağınık olarak ortaya çıkıyor. Çatal yönünü dizileyicinin hangi DNA ipliğini okuduğu bilgisiyle birleştirerek ForkML, gelen ve geciken iplik sentezinin hızlarını ayırt edebiliyor; bu, geleneksel fiber temelli yöntemlerin yapamadığı bir şeydir. Altı farklı insan hücre hattı—hem normal hem de kanser hücreleri—üzerindeki testler, aynı basit BrdU etiketleme koşullarının geniş çapta uygulanabildiğini ve her durumda sağlam hız tahminleri verdiğini gösterdi.
Klasik bir tekniğin dijital yükseltmesi
Uzman olmayanlar için ForkML, klasik DNA fiber analizinin modern, dijital bir versiyonu olarak görülebilir: benzer bir etiketleme şeması kullanır, ancak manuel mikroskopiyi uzun okuma dizileme ve makine öğrenmesi ile değiştirir. Bu, çok daha yüksek bir verim, her ölçümün genoma doğrudan yerleştirilmesi ve DNA’nın nerede ve ne kadar hızlı kopyalandığına dair daha ayrıntılı bilgiler sağlar. Protokol basit, mevcut nanopore donanımıyla uyumlu ve diğer organizmalara uyarlanabilir olduğundan, ForkML DNA replikasyonunu incelemek için standart bir araç haline gelmeye adaydır. Pratik açıdan, araştırmacılara yerel DNA kopyalama hızını—normal veya stres altında—gen aktivitesi, kromatin durumu ve genomdaki hastalıkla ilişkili değişikliklerle ilişkilendirmek için güçlü bir yol sunar.
Atıf: Rojat, V., Ciardo, D., Tourancheau, A. et al. Automated mapping of DNA replication fork progression in human cells with ForkML. Nat Commun 17, 1975 (2026). https://doi.org/10.1038/s41467-026-68750-4
Anahtar kelimeler: DNA replikasyonu, replikasyon çatalı hızı, nanopore dizileme, BrdU etiketleme, genomikte makine öğrenmesi