Clear Sky Science · sv
Genomisk översikt över antimikrobiell resistens i Indien: fynd från en övervakningsstudie med flera arter
Varför superbuggar i Indien berör oss alla
Antibiotikaresistenta ”superbuggar” är ett växande globalt problem, men vi vet fortfarande förvånansvärt lite om hur dessa mikrober utvecklas och sprids i många delar av världen. Denna studie granskar farliga bakterier från sjukhus i Indien och läser deras hela DNA för att förstå hur de överlistar våra starkaste läkemedel. Resultaten visar inte bara vad som gör dessa mikrober svåra att döda, utan prövar också om snabba DNA‑baserade metoder pålitligt kan ersätta långsammare laboratorietester—en fråga som kan påverka hur infektioner behandlas överallt.
Närmare granskning av sjukhusinfektioner
Forskare samlade in 266 bakterieprover från svårt sjuka patienter på stora sjukhus i norra och västra Indien mellan 2022 och 2024. De flesta prover kom från blod, men även från urin och lunginfektioner, och majoriteten var från intensivvårdsavdelningar där patienterna är mest sårbara. Teamet fokuserade på välkända problemgerm—såsom Escherichia coli, Klebsiella pneumoniae, Acinetobacter baumannii, Pseudomonas aeruginosa, meticillinresistent Staphylococcus aureus (MRSA) och vankomycinresistenta Enterococcus (VRE). För varje prov hade läkare redan utfört standardiserade antibiotikasusceptibilitetstester, där bakterier utsätts för läkemedel i laboratoriet för att se vilka mediciner som fortfarande fungerar. Forskarlaget sekvenserade sedan bakteriernas genom för att kartlägga hela uppsättningen resistensgener och jämförde vad DNA:t ”förutspådde” med vad som faktiskt hände i provrören.
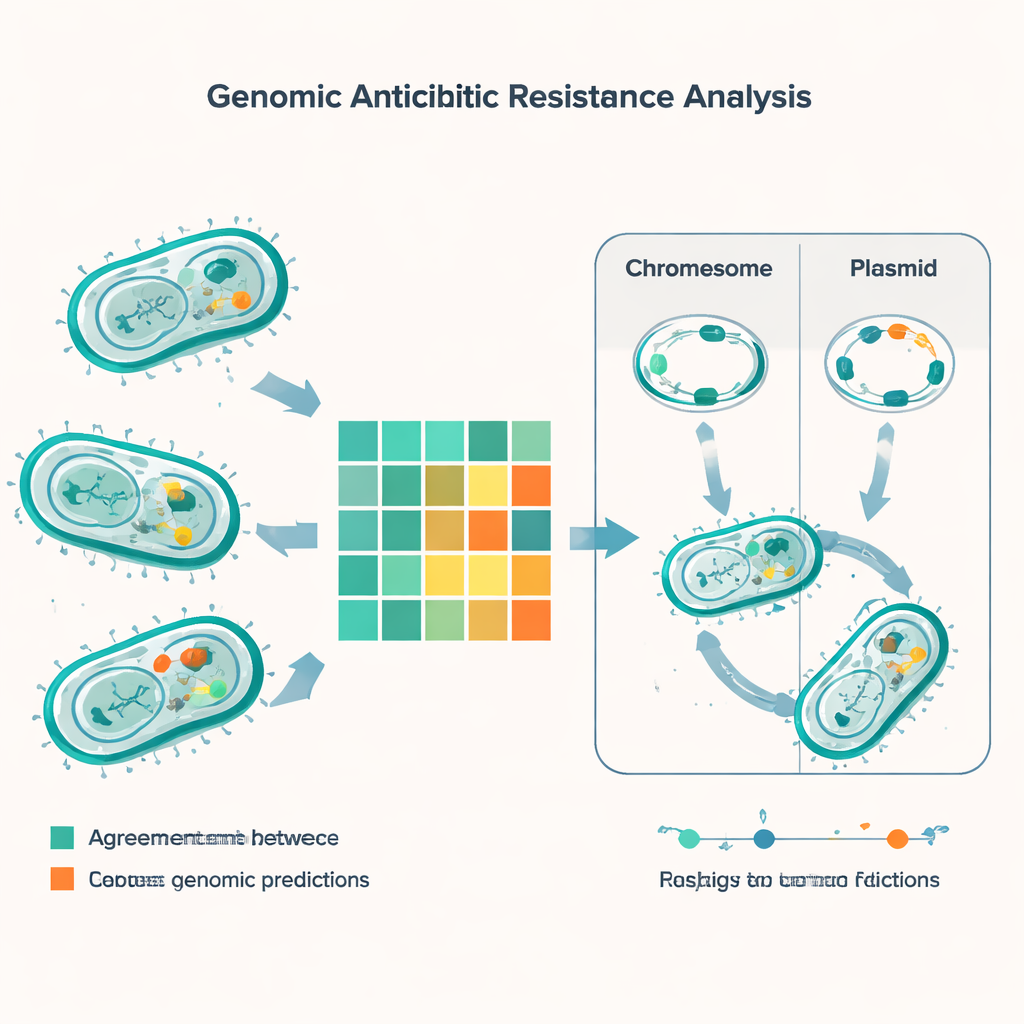
När gener och provrör inte stämmer överens
Genom att jämföra genetiska förutsägelser med laboratorieresultat för 56 olika antibiotika genomförde studien mer än 5 000 jämförelser. I de flesta fall överensstämde den DNA‑baserade metoden och de traditionella testerna, men nästan 600 avvikelser stack ut. Den vanligaste typen av fel var att det genomiska verktyget förutspådde att en bakterie skulle vara resistent när labbet sade att den fortfarande var behandlingsbar. Detta skedde ofta för läkemedel som minocyklin, kolistin och gentamicin, särskilt hos E. coli. Den motsatta typen av fel—där laboratoriet såg resistens men generna inte tydligt förklarade det—var mindre frekvent men mer oroande, eftersom det riskerar att göra att resistens missas. Dessa ”mycket stora” avvikelser visade sig särskilt hos tarmrelaterade bakterier kallade enterokocker, i synnerhet för vanligen använda penicillinlika läkemedel och för kombinationen trimetoprim‑sulfametoxazol.
Dolda arsenaler i bakterie‑DNA
Den genomiska undersökningen avslöjade ett tätt lager av resistensgener över de stora arterna. Var och en av de vanliga gramnegativa patogenerna bar minst en beta‑laktamasgen, som kan bryta ner penicillin och besläktade läkemedel, och många stammar hade flera sådana gener samtidigt. Beryktade aktörer som NDM‑typ karbapenemaser—som neutraliserar reservantibiotika—var utbredda i E. coli, Klebsiella, Acinetobacter och Pseudomonas. Studien fann också gener som hjälper bakterier att överleva kraftfulla ”peptid”‑antibiotika som kolistin, tillsammans med den klassiska mecA‑genen som ger MRSA resistens mot meticillin och vankomycinresistensklyftor i enterokocker. Genom att jämföra DNA‑fingeravtryck kallade sekvenstyper kopplade teamet vissa av dessa resistensgener till kända högrisklinjer av bakterier som redan sprids i Indien och runt om i världen.
Genuppdelning via rörligt DNA
En avgörande del av historien ligger inte bara i vilka gener bakterierna bär, utan var dessa gener finns. Många resistensgener sitter på små DNA‑ringar kallade plasmider, som bakterier kan byta som samlarkort. Med specialiserad programvara förutspådde forskarna cirka 1 400 plasmider i proverna, med särskilt hög mångfald i E. coli och Klebsiella. I dessa arter var en stor andel av resistensgenerna—inklusive flera kritiska beta‑laktamaser—plasmidburna, vilket gör dem lättare att föra vidare mellan stammar och till och med mellan arter. Andra resistensegenskaper var inbyggda i bakteriens kromosomer, vilket innebär att de kan bestå även om plasmider förloras. Teamet katalogiserade också mobila genetiska element—korta DNA‑segment som kan hoppa runt och bära resistensgener med sig—vilket lyfter fram ännu en väg för snabb spridning.
Vad detta betyder för framtida behandlingar
För icke‑specialister är det centrala budskapet att läsning av bakterie‑DNA kan i hög grad stödja kampen mot superbuggar, men tekniken är ännu inte perfekt. De genomiska verktygen tenderade att ”över‑ropa” resistens, vilket är säkrare än att missa en farlig stam men kan få läkare att använda starkare läkemedel än nödvändigt. Samtidigt visade ett mindre antal fall att laboratoriet upptäckte resistens som dagens genkataloger inte fullt ut kunde förklara, vilket understryker viktiga blinda fläckar i vår kunskap. Genom att bygga en detaljerad karta över resistensgener, plasmider och mobila element i indiska sjukhus skapar denna studie en grund för bättre, snabbare DNA‑baserade diagnostik och mer informerad antibiotikaanvändning—inte bara i Indien utan i alla miljöer där superbuggar hotar modern medicin.
Citering: Gheewalla, N., Karthikeyan, V., Jadhav, Y. et al. Genomic landscape of antimicrobial resistance in India: findings from a multi-species surveillance study. npj Antimicrob Resist 4, 13 (2026). https://doi.org/10.1038/s44259-026-00185-9
Nyckelord: antimikrobiell resistens, genomsekvensering, sjukhusinfektioner, läkemedelsresistenta bakterier, plasmidmedierad resistens