Clear Sky Science · sv
Nätverkshierarki-entropi för kvantifiering av grafolikhet
Varför små skillnader i nätverk spelar roll
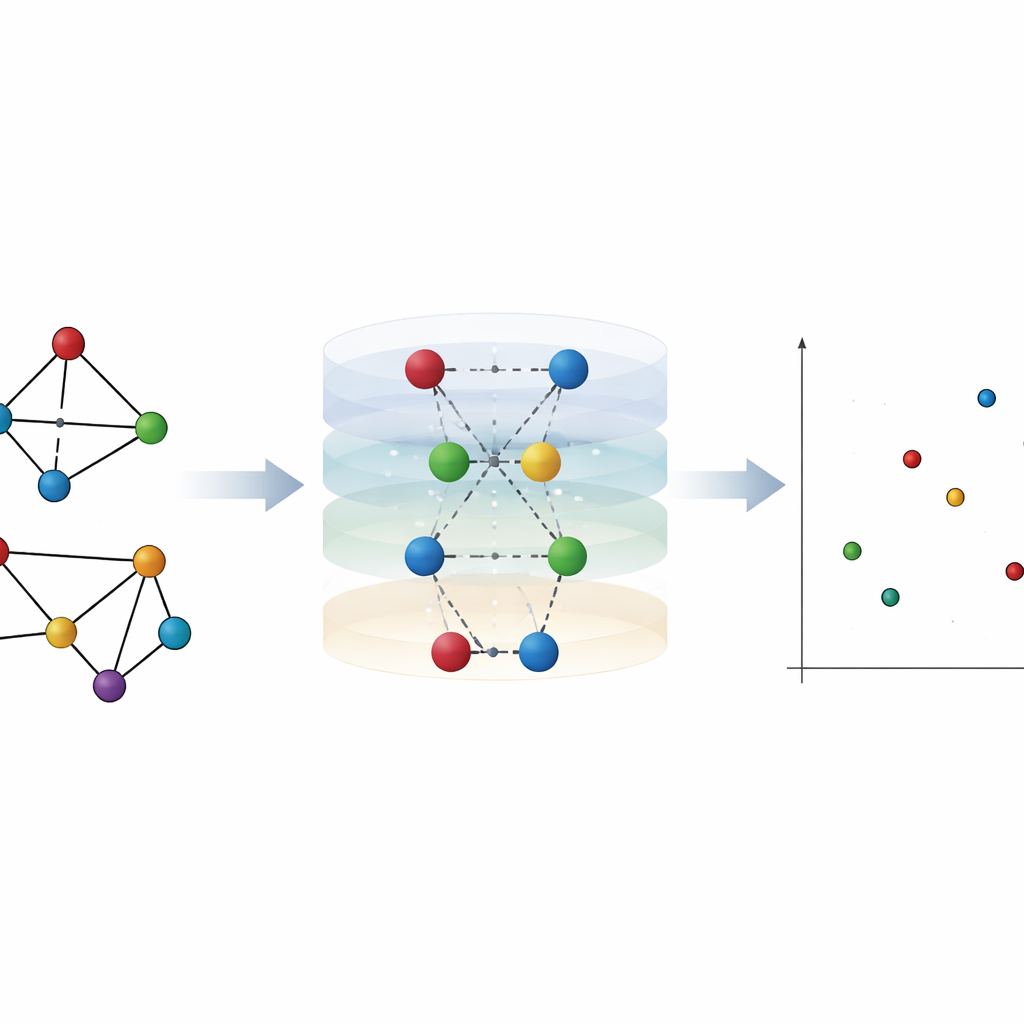
Från vänskapsband i sociala medier till flygrutter och proteinstrukturer kan många system beskrivas som nätverk av noder och länkar. Att avgöra när två sådana nätverk faktiskt skiljer sig åt är dock förvånansvärt svårt, särskilt när de vid första anblick liknar varandra. Den här artikeln introducerar ett nytt sätt att mäta hur olika två nätverk verkligen är genom att uppmärksamma inte bara enskilda punkter (noder) utan också förbindelserna (kanter) och hur de samverkar. Metoden, kallad nätverkshierarki-entropi, kan upptäcka subtila strukturella förändringar som andra verktyg missar och hjälper till att skilja enzymproteiner från icke‑enzymatiska proteiner.
Att betrakta nätverk lager för lager
För att förstå ett nätverk betraktar författarna först hur långt varje nod ligger från varje annan nod i antal steg längs länkar. Runt en vald nod kan andra noder grupperas i lager: omedelbara grannar, grannars grannar och så vidare. Denna "hierarki" kring en nod beskriver hur inflytande eller en infektion kan sprida sig utåt genom nätverket. Vridningen är att två mycket olika nätverk kan dela samma nodnivå-hierarki, så denna vy ensam kan misslyckas med att skilja dem åt. Artikeln visar att klassiska exempel, som Desargues‑ och Dodekaedergraferna, har identiska nodhierarkier trots att deras interna kopplingar skiljer sig.
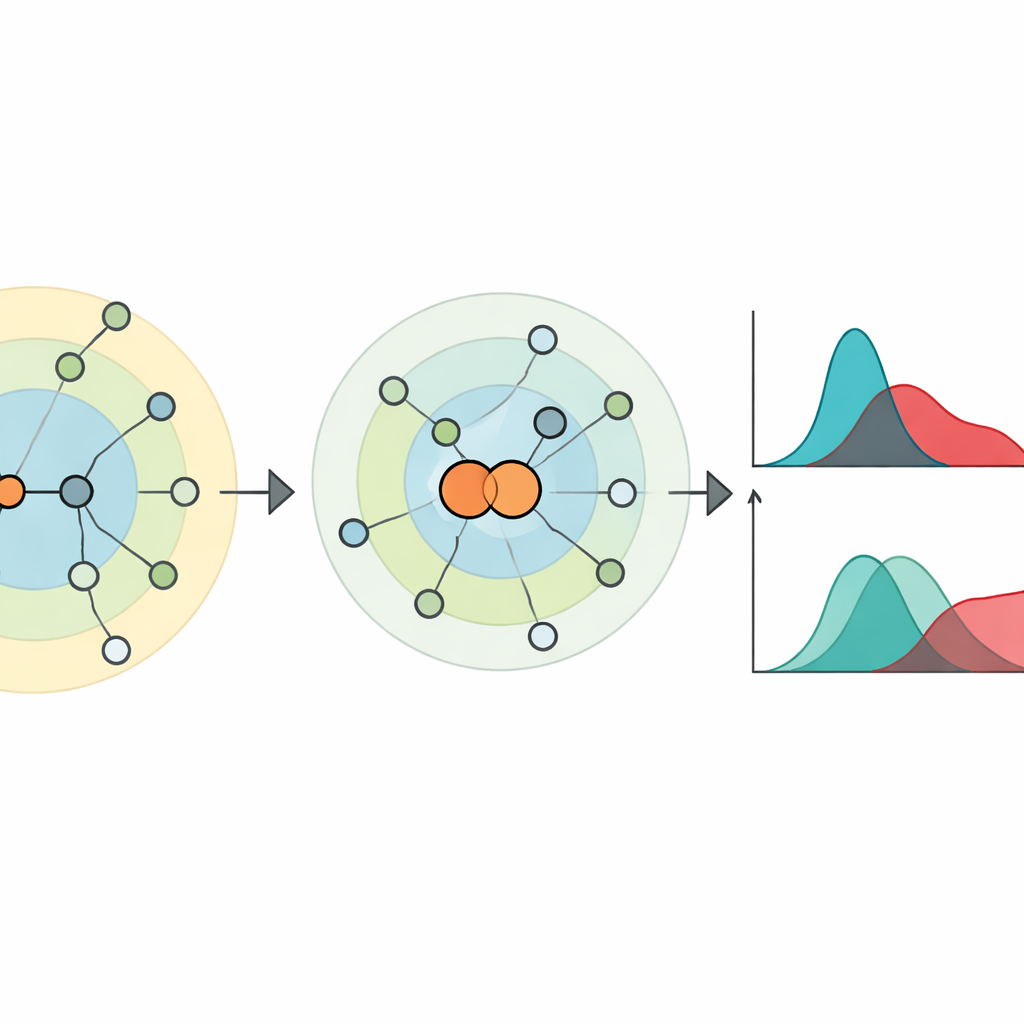
Låta länkarna tala: krympande nodpar
För att fånga vad nodcentrerade vyer missar fokuserar författarna på kanter — förbindelserna mellan noder — och hur de omformar avstånd i nätverket. De introducerar en enkel men kraftfull idé: "krympning av nodpar." Här slås två förbundna noder temporärt ihop till en enda ny nod, samtidigt som deras samlade grannar behålls. Detta avslöjar hur nära varje annan nod är paret jämfört med varje ändpunkt för sig. I termer av spridning efterliknar det effekten av att infektera båda ändarna av en länk samtidigt snarare än att starta från bara en nod. Ur dessa lagerbaserade avståndsmönster definierar de "hierarkicentralitet" för både noder och kanter, vilket visar sig korrelera starkt med hur väl noder eller kanter fungerar som spridare i simulerade epidemier på verkliga nätverk.
Mäta informationsförlust med entropi
Med utgångspunkt i dessa centraliteter definierar författarna två typer av hierarki‑entropi. Kant‑hierarki‑entropi frågar: hur mycket information förlorar vi om vi försöker approximera en kats betydelse endast genom att medelvärdesberäkna betydelsen av de två noder den förbinder? Nod‑hierarki‑entropi ställer motsvarande fråga för noder och deras omgivande kanter. Båda storheterna normaliseras så att de inte beror på det totala nätverksstorleken. Tillsammans bildar de ett tvåtals‑fingeravtryck för varje nätverk. Avståndet mellan två nätverk är sedan helt enkelt det geometriska avståndet mellan deras fingeravtryck. Detta nya mått följer de standardregler som förväntas av ett avstånd och stämmer med intuitiva idéer, till exempel att ge större straff när en förändring bryter sönder ett nätverk.
Se finare struktur och förändring över tid
Författarna testar sitt mått på både artificiella och verkliga nätverk. I syntetiska benchmarks som efterliknar sociala eller teknologiska system kan det nya måttet följa hur nätverk utvecklas när modellparametrar ändras, och det separerar tydligt nätverk med starka gemenskaper från de där gemenskaperna är svagare, även när konkurrerande metoder har svårt. I kontrollerade experiment där nätverk noggrant omblandas för att bevara många gemensamma statistiker — såsom gradsekvenser och till och med avståndsfördelningar — upptäcker hierarki‑entropi‑avståndet fortfarande skillnader som andra populära mått betraktar som försumbar. Det är också skickligt på att gruppera randomiserade versioner av samma nätverk i rätt kategorier, vilket indikerar en skarp känslighet för högre ordningens struktur som går utöver enkla räkningar av länkar och vägar.
Verkliga tillämpningar: rörlighet och proteiner
För att visa praktiskt värde tillämpar författarna sitt avståndsmått på dagliga rörlighetsnätverk mellan hundratals kinesiska städer under de första månaderna av COVID‑19. Med tidig januari som referens visar hierarki‑entropi hur resmönster förändras genom nyårsresandet kring månkalenderns årsskifte, införandet av strikta karantänåtgärder och den gradvisa återhämtningen — i god överensstämmelse med kända policyförändringar och rörlighetsgemenskapsmönster. I en annan tillämpning behandlar de proteinstrukturer som nätverk av aminosyror som kopplas när de ligger nära i rummet. Utan någon inlärning eller handgjorda funktioner uppnår klustring av proteiner med det nya avståndet omkring 75 % träffsäkerhet för att skilja enzymer från icke‑enzymer — konkurrenskraftigt med moderna övervakade neurala nätverksmetoder.
Vad detta betyder i enkla termer
I kärnan visar arbetet att uppmärksamhet på hur noder och länkar tillsammans formar avstånd i ett nätverk ger ett mycket skarpare "fingeravtryck" än att bara betrakta noder. Genom att kvantifiera hur mycket som går förlorat när vi försöker ersätta kanter med deras ändpunkter — eller noder med deras omgivande kanter — lyfter det föreslagna hierarki‑entropi‑avståndet fram subtila strukturella skillnader som starkt påverkar spridning, rörlighet och biologisk funktion. För forskare och analytiker som arbetar med alla slag av nätverksdata erbjuder detta ett praktiskt, allmännt användbart verktyg för att jämföra komplexa system på ett sätt som är både matematiskt välgrundat och nära kopplat till hur processer faktiskt utvecklas i dessa nätverk.
Citering: Mou, J., Wang, L., Zhang, C. et al. Network hierarchy entropy for quantifying graph dissimilarity. Commun Phys 9, 83 (2026). https://doi.org/10.1038/s42005-026-02523-9
Nyckelord: nätverkslikhet, komplexa nätverk, entropimått, epidemisk spridning, proteinstruktur-nätverk