Clear Sky Science · sv
Optimera CRISPR-precision i musembryon via mikrohomoziemedierad ändsammanfogning-dominerande riktning
Varför det spelar roll att göra skarpare genredigerade möss
Genredigeringsverktyg som CRISPR har gjort det anmärkningsvärt enkelt att skapa möss som efterliknar mänskliga sjukdomar, men det finns ett dolt problem: de genetiska förändringarna i den allra första generationen djur är ofta röriga och blandade. Det gör experiment långsammare, mindre tillförlitliga och kräver fler djur. Denna studie presenterar ett sätt att styra CRISPR-klippen i musembryon mot högt förutsägbara utfall, så att de flesta grundar-möss föds med samma väl definierade mutation — vilket ger renare biologi och bättre etik inom genredigeringsforskning.
Utmaningen med rörig DNA-reparation
När CRISPR klipper DNA måste cellen laga brottet med sina egna reparationssystem. Den vanligaste vägen, kallad icke-homolog ändsammanfogning (NHEJ), är snabb men oprecis och ger en röra av små insättningar och borttagningar vid klippstället. En annan väg, mikrohomoziemedierad ändsammanfogning (MMEJ), tenderar att ta bort större DNA-bitar på stereotypa sätt genom att använda korta matchande sekvenser som guide. Båda är mycket effektivare än den precisa men långsamma homologi-drivna vägen. I standard-CRISPR-experiment fokuserar forskare mest på hur kraftfullt ett guide-RNA kan klippa och hur få off-target-ställen det träffar, och uppmärksammar mindre vilken reparationsväg som kommer att gynnas eller vilken exakt mutation som uppstår. Resultatet blir att många grundar-möss bär på ett lapptäcke av olika mutationer i olika celler, vilket tvingar forskare att avla fram nästa generation innan de kan arbeta med en ren, homogen genotype.
En smartare metod för att välja CRISPR-guider
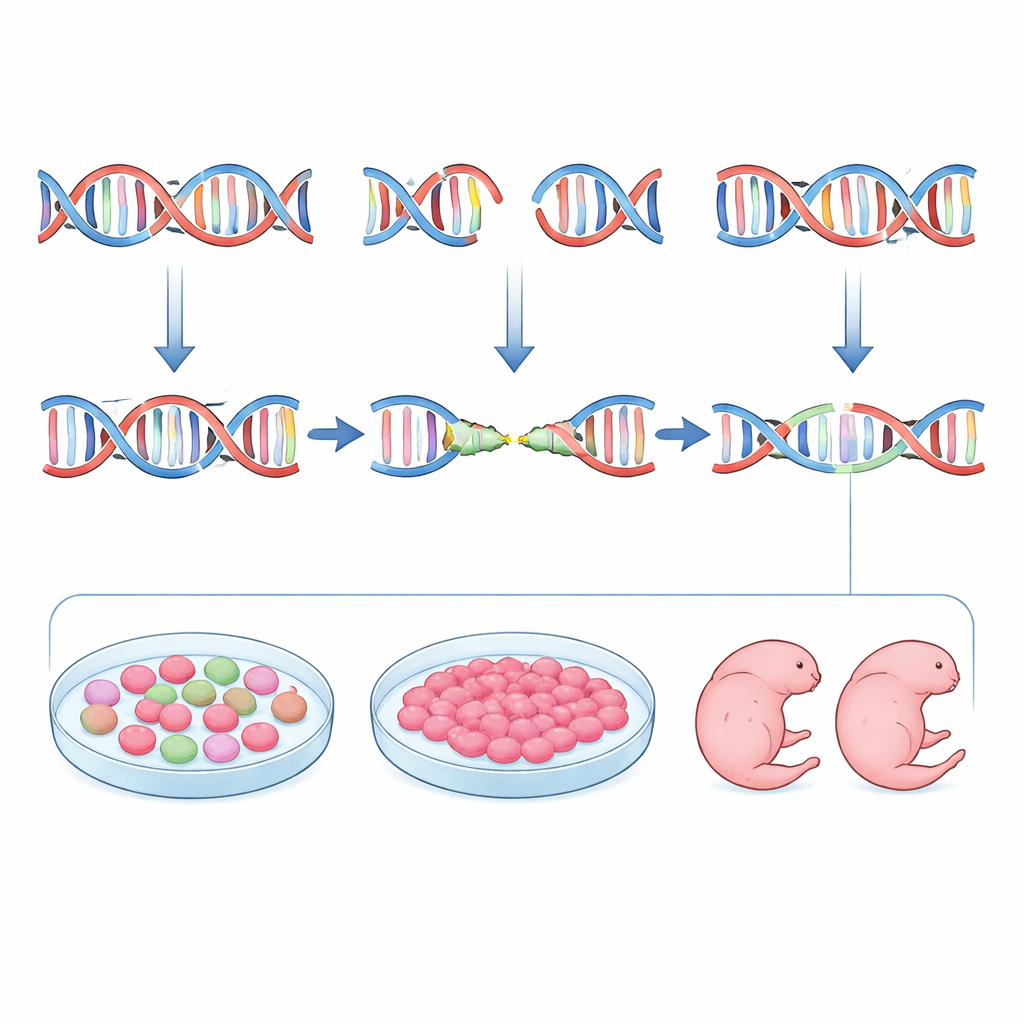
Författarna satte som mål att vända detta genom att designa guider inte bara för effektivitet och säkerhet, utan också för förutsägbarhet. De började med inDelphi, ett maskininlärningsverktyg tränat på stora dataset av CRISPR-inducerade mutationer i odlade celler. inDelphi säger inte bara hur ofta en plats kommer att redigeras; det förutspår hela menyn av möjliga insättningar och borttagningar och hur ofta var och en kommer att förekomma, med särskild uppmärksamhet på mikrohomoziedrivna händelser. Teamet skannade det murina tyrosinas (Tyr)-genen, där förlust av funktion gör djuren albino, och valde guide-RNA för vilka det förutspåddes att gynna starka, upprepbara mikrohomoziemedierade borttagningar samtidigt som off-target-riskerna hölls låga. De redigerade sedan musembryon och mätte de resulterande mutationerna med djup-sekvensering. Överlag dök inDelphis favoritentyp för varje guide upp i embryon i liknande frekvenser som förutspåtts, och guider med starkare mikrohomoziemönster gav verkligen mer enhetliga mutationsmönster.
Använda stamceller som repetitionsscen
Men förutsägelsen i sig räckte inte. När teamet jämförde inDelphi-prognoser med faktiska redigeringsmönster fann de endast måttlig överensstämmelse. För att överbrygga denna klyfta introducerade de ett praktiskt mellansteget: att testa varje guide i musens embryonala stamceller som delar många egenskaper med mycket tidiga embryon. Efter att ha transfecterat dessa celler med CRISPR-komponenter sorterades de redigerade cellerna och målplatserna sekvenserades. Mutationsmönstren i stamcellerna matchade de i embryon mycket närmare än vad datormodellen gjorde. Guider som producerade en enda dominerande deletion i stamceller gjorde vanligtvis samma sak i blastocyster och senare embryostadier. Genom att kombinera inDelphis rangordning med denna stamcells-"generalrepetition" kunde forskarna pålitligt välja guider som driver mikrohomoziemedierad reparation och minimerar mångfalden av mutanta alleler.
Från ögonfärg till saknade lemmar
Författarna testade sin pipeline i levande djur. För Tyr-genen valde de tre guider som representerade hög, medel och låg förutspådd precision och överförde redigerade embryon till fostermödrar. Vid dag 11,5 av utvecklingen undersökte de ögonpigmenteringen och sekvenserade varje embryo individuellt. Den starkt mikrohomoziogynnsamma guiden producerade embryon som mestadels var albino och bar en dominant liten deletion, ofta i båda kopiorna av genen, med mycket liten variation. En mindre optimerad guide gav en blandning av pigmentförlust och partiell pigmentering kopplad till en mer komplex uppsättning mutationer. De tillämpade sedan samma metod på Fgf10-genen, där förlust av funktion ger lemlösa embryon. Genom att välja en guide som förutspåddes — och bekräftades i stamceller — ge en specifik fyrabasonsdeletion med hög sannolikhet att störa genen, genererade de embryon vid dag 15,5 som var enhetligt lemlösa och bar en starkt berikad uppsättning av förväntade deletioner. För båda gener dominerade samma få mutationstyper i inDelphi-prognoser, stamceller, tidiga embryon och senare embryostadier.
Renare genetik med färre djur
I praktiska termer erbjuder studien en ny mall för att designa CRISPR-experiment i möss. Istället för att skynda direkt från en datordesignad guide till embryoredigering förespråkar författarna en integrerad pipeline: använd inDelphi och off-target-verktyg för att välja guider som sannolikt gynnar mikrohomoziemedierade deletioner och ramförskjutningar, testa dessa guider i embryonala stamceller för att bekräfta både effektivitet och enhetlighet i mutationerna, och för vidare endast de bästa presterande till embryoarbetet. Denna strategi ger grundar-möss vars celler övervägande delar samma väl karaktäriserade mutation, vilket gör dem omedelbart användbara för att modellera mänskliga sjukdomar — särskilt de som orsakas av återkommande deletionstyper — samtidigt som antalet djur som måste avlas och screenas minskas. Resultatet är skarpare, mer reproducerbar genetik och en mer etisk väg till kraftfulla sjukdomsmodeller.
Citering: Lkhagvadorj, K., Okamura, E., Taki, T. et al. Optimizing CRISPR precision in mouse embryos via microhomology-mediated end joining-dominant targeting. Commun Biol 9, 371 (2026). https://doi.org/10.1038/s42003-026-09771-z
Nyckelord: CRISPR, musmodeller, genomredigering, DNA-reparation, sjukdomsmodellering