Clear Sky Science · sv
Generativa modeller för celldynamik: från Neural ODEs till flow matching
Att iaktta celler förändras över tid
Varje organ i våra kroppar byggs av celler som en gång såg nästan identiska ut för att sedan successivt anta olika roller. Biologer skulle gärna se varje enskild cell förändras i realtid, men dagens mätmetoder förstör de celler de avläser. Denna översiktsartikel undersöker hur en ny typ av artificiell intelligens-verktyg, så kallade Neural Ordinary Differential Equations, kan hjälpa till att rekonstruera dessa dolda förändringsberättelser från statiska ögonblicksbilder — vilket potentiellt kan förbättra vår förståelse av utveckling, sjukdom och hur behandlingar fungerar.

Från stillbilder till levande filmer
Moderna enkelcellssekvenseringstekniker kan mäta aktiviteten hos tusentals gener i individuella celler och generera enorma tabeller av siffror. Varje rad motsvarar en cell, varje kolumn en gen. Men varje cell mäts bara en gång, så forskare sitter kvar med en samling stillbilder snarare än en film över hur någon enskild cell förändras över tid. Tidiga angreppssätt försökte ordna dessa ögonblicksbilder i en plausibel följd med hjälp av ”pseudotid”, och placera celler längs utvecklingsvägar baserat på hur lika deras genaktivitetsmönster såg ut. Det hjälpte till att avslöja breda riktningar för celldifferentiering men hade svårt när celler delade sig i flera öden eller följde komplexa, loopande banor.
Att beskriva cellförändring som rörelse i ett landskap
För att gå bortom enkla ordningsföljder beskriver forskare celler som punkter som rör sig genom ett landskap: position kodar för det aktuella genaktiveringsläget och ”momentum” speglar hur det läget förändras. Klassiska verktyg såsom RNA-velocity uppskattar vart en cell är på väg genom att jämföra olika former av RNA i den. Andra rekonstruerar vektorfält — kartor av pilar som visar, i varje punkt i detta rum, den troliga riktningen för rörelsen. Dessa metoder började avslöja hur genregulatoriska nätverk driver celler mot specifika öden och hur instabila regioner i landskapet kan signalera kommande beslut. Många av dessa modeller gör dock starka förenklingar om hur gener samverkar och kan ofta inte generera fullt kontinuerliga banor som stämmer med populationsdata vid flera tidpunkter.
Neural ODEs: att lära förändringens lagar
Neural ODEs erbjuder ett flexibelt sätt att lära de underliggande reglerna som styr cellulär rörelse i detta landskap. Istället för att i förväg föreskriva formler lär ett neuralt nätverk en funktion som berättar för dig, för varje celltillstånd, hur det tillståndet kommer att förändras härnäst. En ODE-lösare följer sedan fullständiga banor över tid. Detta ramverk har anpassats till flera uppgifter inom enkelcellsforskning: att härleda utvecklingsvägar, belysa förgreningshändelser, identifiera instabila eller ”primade” tillstånd och till och med rekonstruera genregulatoriska nätverk — orsak-och-verkan-relationerna mellan gener som slår av och på varandra. Genom att uppmuntra de inlärda reglerna att vara enkla och glesa kan vissa metoder föreslå kompaktare regulatoriska diagram som är lättare att tolka och testa experimentellt.
Generativa flöden: att matcha populationer över tid
En annan inriktning behandlar problemet på populationsnivå snarare än att spåra individuella celler. Här är målet att lära hur hela fördelningen av celltillstånd vid en tidpunkt förvandlas till fördelningen vid en senare tidpunkt. Tekniker från optimal transport, som ursprungligen utvecklades för att hitta det billigaste sättet att flytta massa från en form till en annan, har kombinerats med Neural ODEs och närbesläktade ”flow”-modeller. Kontinuerliga normalizing flows och de nyare, mer effektiva ”flow matching”-metoderna lär direkt vektorfält som flyttar en cellpopulation till en annan, utan att kräva dyra omkörningar av simuleringar under träning. Dessa angreppssätt kan hantera ojämn provtagning, brusiga mätningar och även stokastisk (delvis slumpmässig) dynamik, och ger generativa modeller som kan simulera realistiska framtida populationer eller rekonstruera troliga tidigare tillstånd.
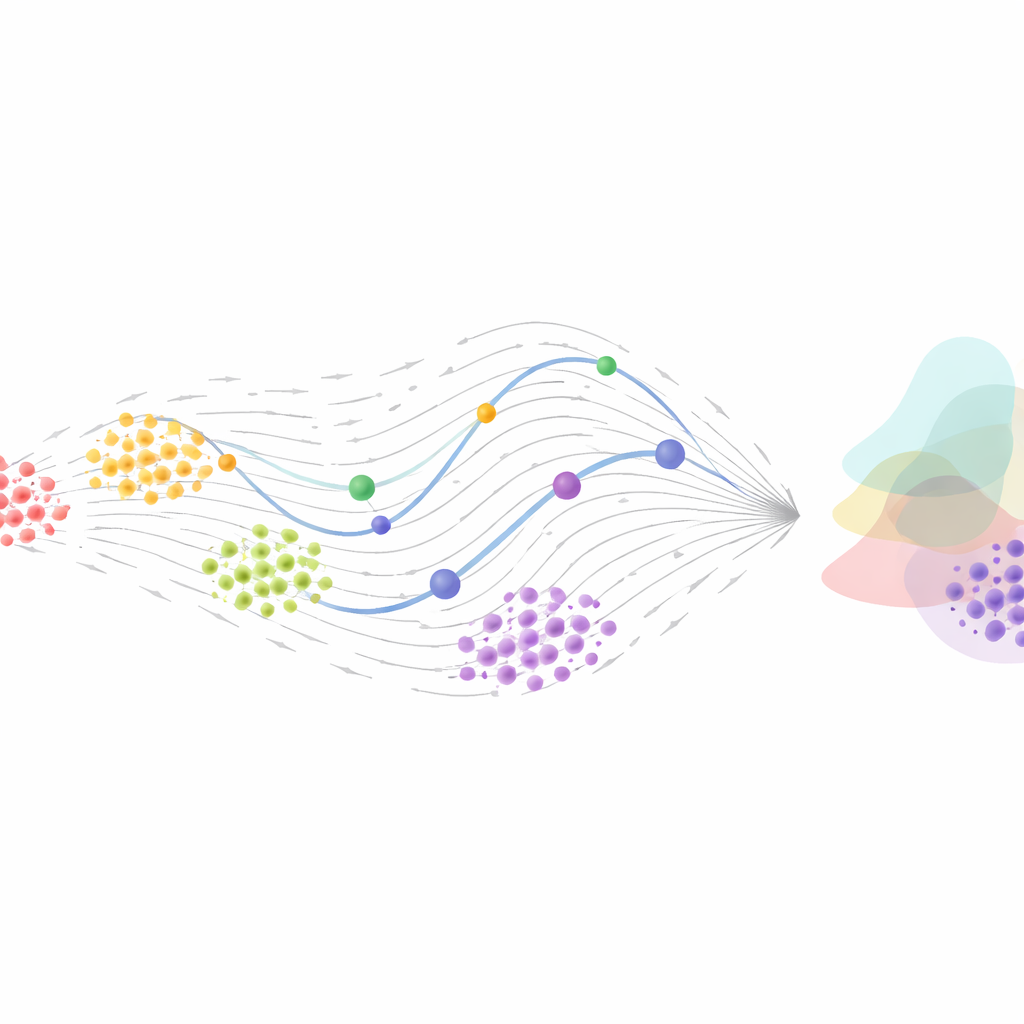
Möjligheter och öppna frågor
Trots sitt löfte står dessa modeller inför viktiga utmaningar. Att skilja verklig orsak-och-verkan från ren korrelation i gennätverk är svårt, särskilt när vissa inflytelserika faktorer är oobserverade. Forskare driver också Neural ODEs att gå bortom att passa den data de ser mot att verkligen lära allmänna lagar som kan förutsäga svar på nya förhållanden, såsom genutslagningar eller läkemedelsbehandlingar. Att hantera brus, slumpmässighet och många överlappande datatyper — som att kombinera genaktivitet med rumslig position eller andra molekylära lager — är fortfarande ett aktivt forskningsområde. Samtidigt tillämpas samma idéer redan utanför genomiken, till exempel på hjärtdynamik, läkemedelsbeteende i kroppen och medicinska tidsseriedata.
Varför detta är viktigt för hälsa och sjukdom
För en icke-specialist är huvudbudskapet att Neural ODEs och flow-matching-modeller låter forskare förvandla statiska cellmätningar till dynamiska berättelser. Istället för att bara veta hur celler ser ut vid några isolerade stadier hjälper dessa verktyg till att härleda hur celler troligen kommer att röra sig genom sitt utvecklingslandskap, vilka brytningar i deras genkretsar som driver dessa rörelser och hur ingrepp kan omdirigera dem. På lång sikt skulle sådana modeller kunna möjliggöra in-silico-experiment som förutser hur en stamcell kan skjutas mot en önskad typ, hur en tumörs cellpopulation kommer att utvecklas under behandling eller hur komplexa terapier påverkar hela cellulära ekosystem — vilket för oss närmare en mekanistisk, prediktiv förståelse av livet på enkelcellsnivå.
Citering: Richter, T., Wang, W., Palma, A. et al. Generative models of cell dynamics: from Neural ODEs to flow matching. Commun Biol 9, 352 (2026). https://doi.org/10.1038/s42003-026-09758-w
Nyckelord: enkelcellsdynamik, neural ODEs, celldifferentiering, generativa modeller, optimal transport