Clear Sky Science · sv
Ultrasnabb och specifik miRNA‑kvantifiering via enmolekylers flourescens‑släckningskinetik
Varför snabba sjukdomstester spelar roll
Att diagnosticera sjukdomar som cancer eller virusinfektioner handlar ofta om att upptäcka mycket små spår av genetiskt material i blod eller andra kroppsvätskor. Dagens guldstandardtester kan vara mycket noggranna men kan också vara långsamma, kostsamma eller ha svårt att hitta mycket sällsynta signaler. Denna studie presenterar en ny mikroskopbaserad metod, kallad Q‑FISH, som kan läsa av dessa genetiska ledtrådar på mindre än en sekund. Om metoden omvandlas till kliniska verktyg kan sådan hastighet och precision göra det lättare att upptäcka sjukdomar tidigare, följa hur behandlingar fungerar och anpassa vården till varje patient.
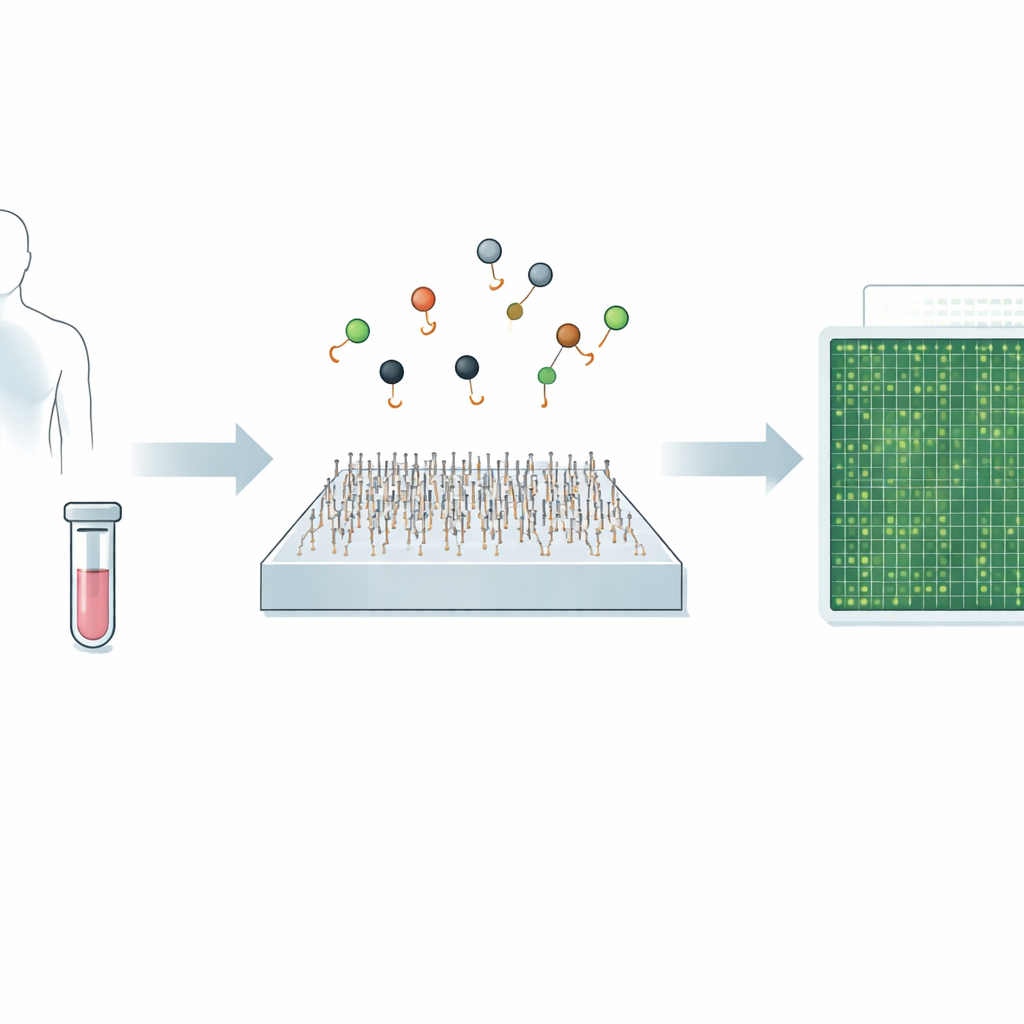
Ett nytt sätt att se små genetiska budskap
Arbetet fokuserar på microRNAs — korta RNA‑fragment som hjälper till att reglera hur våra gener används och som är starkt kopplade till många cancerformer, hjärtsjukdomar, infektioner och hjärnsjukdomar. Eftersom microRNAs är så små och ofta skiljer sig åt bara med en eller två byggstenar kan standardmetoder som PCR och nästa generations sekvensering ha svårt att skilja mycket nära släktingar åt, särskilt när de förekommer på mycket låga nivåer. Nyare enmolekylavbildningsmetoder har förbättrat denna specificitet genom att följa hur individuella prober binder och släpper, men de var fortfarande relativt långsamma och tog ungefär tio minuter för att analysera ett enda mål.
Att betrakta ljusblinkningar för att hitta rätt mål
Q‑FISH vänder problemet genom att utnyttja de korta blinkningarna av ljus från enmolekyler. Metoden använder två korta DNA‑prober som känner igen intilliggande platser på en mål‑microRNA. En probe bär en fluorescerande färg som glöder under en laser, medan den andra bär en ”släckare” som absorberar ljuset när den kommer nära. Den fluorescerande proben binder till målet och sitter kvar länge nog för att synas, medan släckarproben är designad för att binda och lossna mycket snabbt. Varje gång släckaren landar intill färgen sjunker ljusstyrkan plötsligt; när den lämnar hoppar ljuset tillbaka. Genom att spela in dessa snabba på‑/av‑blinkningar från individuella molekyler och analysera hur länge de ljusa respektive dunkla perioderna varar kan systemet avgöra om ett verkligt mål är närvarande.
Från minuter till millisekunder
Eftersom släckarproben inte själv avger ljus kan den användas i mycket högre koncentrationer än fluorescerande prober utan att skapa bakgrundsblänk. Att förkorta släckarproben ökar hur snabbt den släpper, och att höja dess koncentration ökar hur ofta den landar. Tillsammans leder dessa designval till ett dramatiskt språng i hastighet. I tester med en cancerrelaterad microRNA kallad let‑7a nådde Q‑FISH mer än 70 % av sin maximala detektionseffektivitet på bara en sekunds observation. Jämförbara enmolekylsmetoder behövde tiotals till hundratals sekunder för att uppnå liknande prestanda, vilket gör Q‑FISH mer än 600 gånger snabbare i praktiska termer.
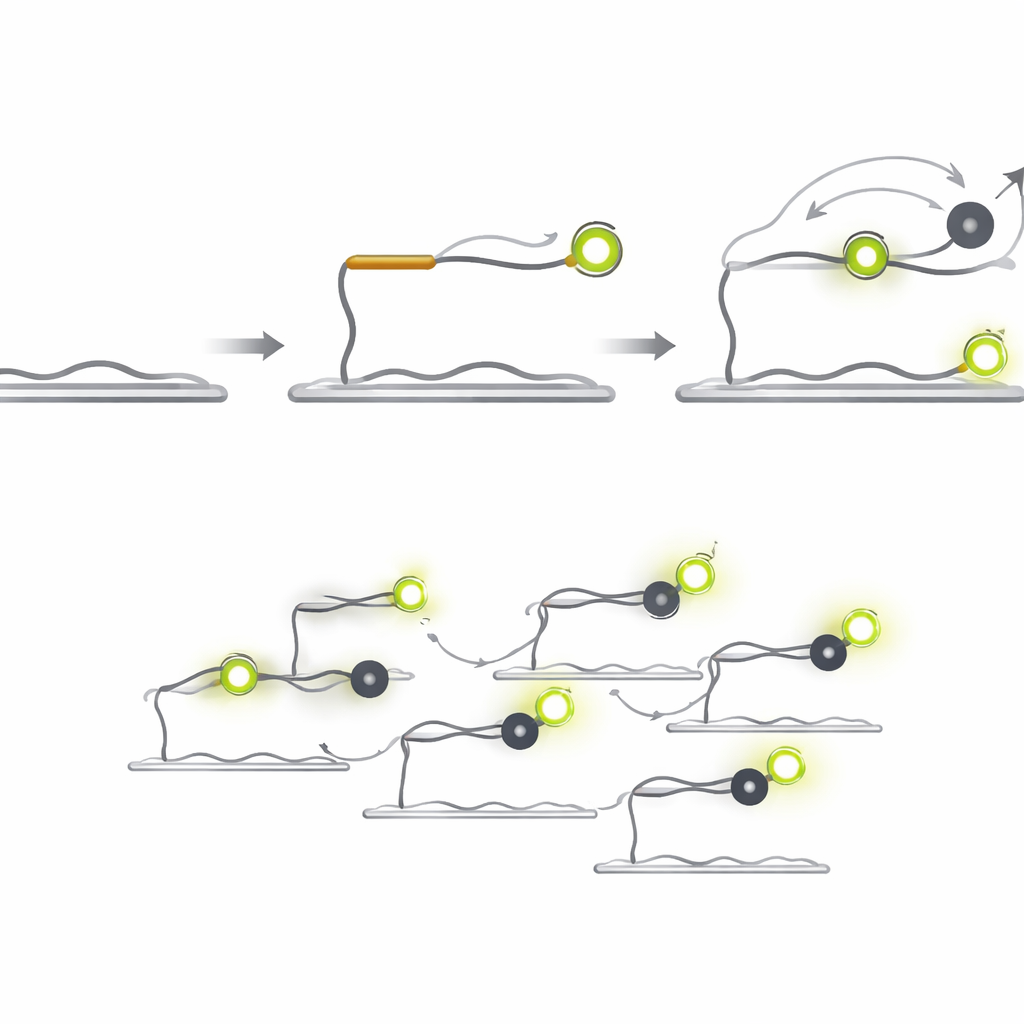
Sortera nästan identiska signaler och mäta verkliga prover
Forskarna visade också att Q‑FISH kan skilja mellan flera medlemmar i let‑7 microRNA‑familjen, som delar nästan samma sekvens men har olika roller i regleringen av cancerkopplade gener. De använde två multiplexstrategier. I den ena infördes olika släckarprober efter varandra, var och en justerad för en något annan microRNA; i den andra var proberna märkta med olika färger och avbildades samtidigt. I båda fallen gjorde avläsningen av blinkmönstren det möjligt för teamet att korrekt identifiera vilken microRNA som var vilken inom ungefär en sekund. Slutligen tillämpade de metoden på total RNA extraherat från mänsklig lever‑ och lungvävnad. Genom att tillsätta kända mängder syntetiska microRNAs och räkna de resulterande fläckarna byggde de kalibreringskurvor och avläste sedan de naturliga nivåerna i vävnaderna, vilket avslöjade tydliga skillnader mellan organen.
Vad detta kan innebära för framtida tester
Sammantaget visar studien att Q‑FISH kan plocka ut specifika microRNAs med mycket hög noggrannhet, även när de är nästan identiska med varandra, och kan göra det i hastigheter som vida överstiger tidigare enmolekylmetoder. Även om experimenten utfördes på förberedda prover med ett specialiserat mikroskop, kan den underliggande idén — att använda snabba ljussläckningsevenemang istället för enbart långsamt bindningsbaserade lägen — anpassas till många typer av genetiska markörer, inklusive tumör‑DNA‑fragment i blod. Med vidare ingenjörskonst och förenklad provberedning skulle detta tillvägagångssätt kunna bidra till att föra snabba, högt multiplexade och extremt känsliga molekylära diagnostiska metoder närmare vardaglig klinisk användning.
Citering: Kim, J., Hohng, S. Ultrafast and specific miRNA quantification via single-molecule fluorescence quenching kinetics. Commun Biol 9, 432 (2026). https://doi.org/10.1038/s42003-026-09714-8
Nyckelord: detektion av microRNA, enmolekylavbildning, molekylär diagnostik, fluorescenssläckning, flytande biopsi