Clear Sky Science · sv
DANST möjliggör celltypsdekonvolution i spatial transkriptomik med djupa domänadversariella neurala nätverk
Att se celler i deras grannskap
Mänsklig vävnad är som trånga städer med många olika celltyper, där varje cell har sin funktion. Nya ”spatiala transkriptomik”-tekniker kan mäta vilka gener som är aktiva över ett vävnadsskikt, men varje mätning blandar ofta signaler från flera intilliggande celler. Denna artikel presenterar DANST, en smart beräkningsmetod som tränger isär dessa blandningar. Genom att ange vilka celltyper som finns och var i organ och tumörer hjälper den forskare att bättre förstå hur vävnader är uppbyggda, hur sjukdomar sprider sig och var behandlingar bäst kan riktas. 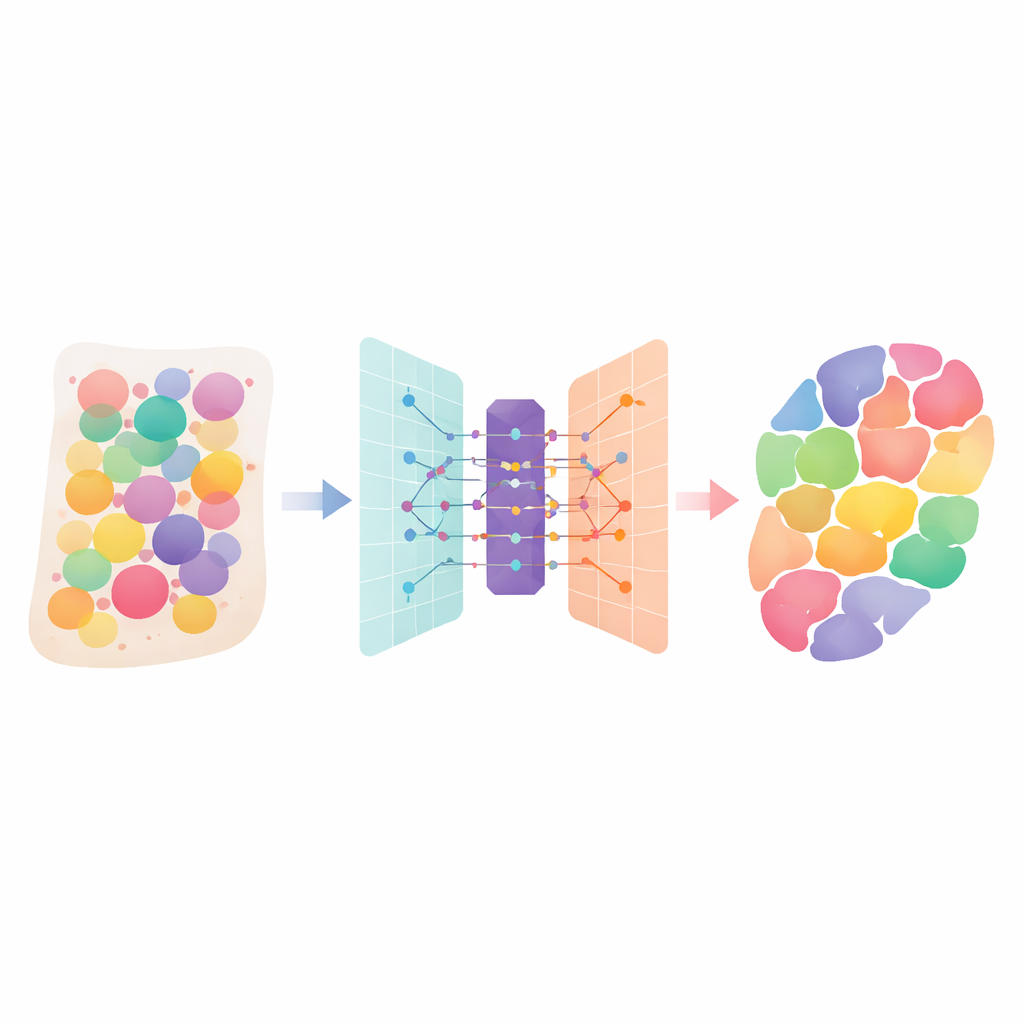
Utmaningen att reda ut cellträngseln
Moderna genavläsningsverktyg kan antingen studera enstaka celler mycket exakt eller fånga hela vävnadens struktur, men sällan båda samtidigt. Populära spatiala tekniker registrerar genaktivitet i relativt stora ”fläckar” som kan omfatta flera celler. Resultatet liknar att höra en kör utan att kunna avgöra vem som sjunger vilka toner. För att tolka detta behöver forskare dekonvolutionsmetoder som uppskattar hur mycket varje celltyp bidrar till varje fläck. Många befintliga tillvägagångssätt använder single-cell-data som referens, men de har svårt eftersom de två datatyperna samlas in i olika experiment och inte matchar perfekt i kvalitet, brus eller upplösning.
Att bygga en bro mellan datavärldar
DANST tar itu med denna mismatch genom att skapa en bro mellan single-cell-data och spatiala data. Först använder den de detaljerade single-cell-profilerna för att simulera många artificiella blandade fläckar med kända celltypsproportioner. Samtidigt grupperar den de verkliga spatiala fläckarna utifrån både deras läge i vävnaden och deras genmönster, och använder avstånden till dessa grupper för att tilldela varje simulerad fläck en ”pseudo”-position. Detta steg skapar en länkad karta där artificiella och verkliga fläckar delar en gemensam spatial ram, vilket gör det möjligt för metoden att lära sig hur blandade signaler bör se ut i specifika grannskap i vävnaden. 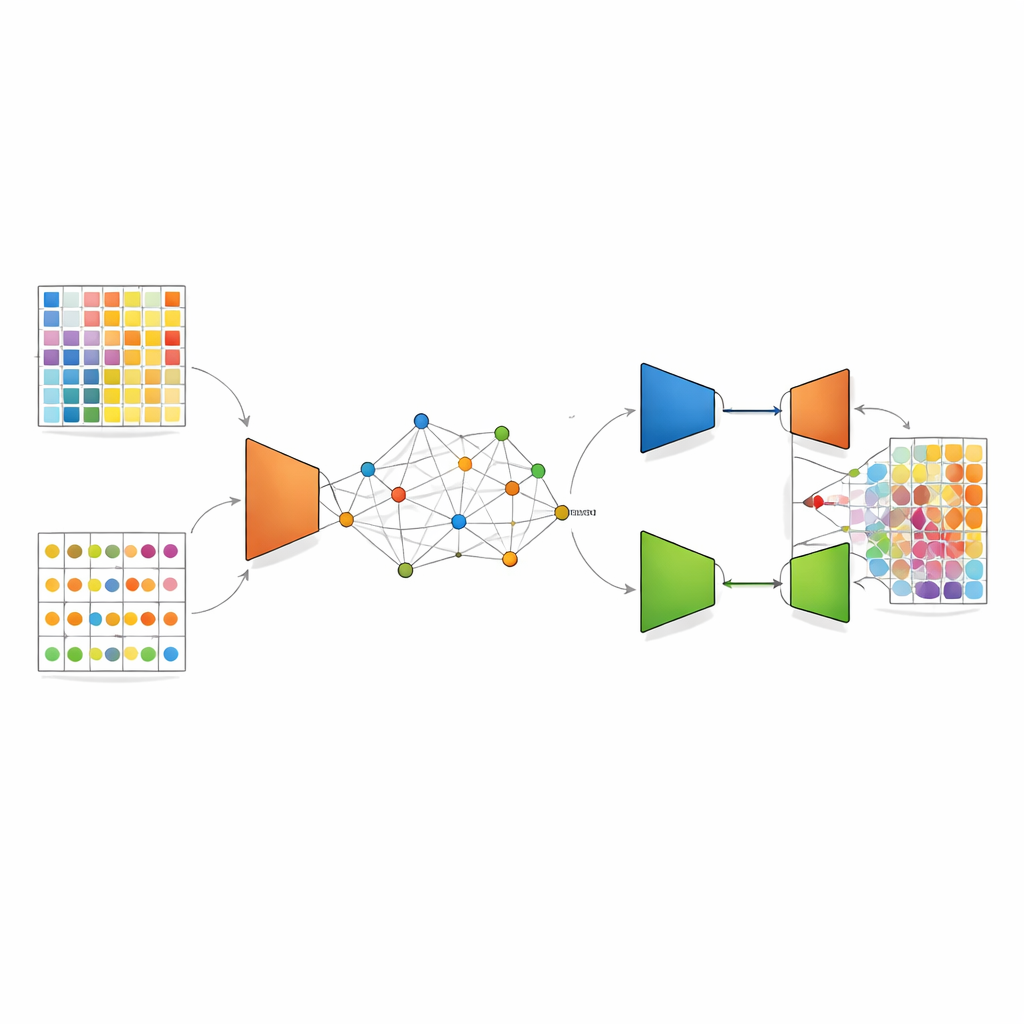
Rensa signaler och alignera domäner
När denna gemensamma karta är på plats använder DANST en typ av djupinlärning som kallas en variational autoencoder. Detta nätverk komprimerar genmönster från både verkliga och simulerade fläckar till en förfinad intern representation och försöker sedan rekonstruera dem, vilket i praktiken avbrusar data och framhäver viktiga egenskaper. Utöver detta lägger författarna till en adversariell komponent: ett andra nätverk försöker avgöra om ett förfinat mönster kommer från verkliga spatiala data eller simulerade data, medan funktionsutdragaren lär sig att lura det. Detta ”dragkamp” driver modellen mot egenskaper som fungerar väl för båda datakällorna, så att kunskap som erhålls från simulerade fläckar med kända celltypsandelar pålitligt kan överföras till verkliga vävnadsfläckar vars sammansättning är okänd.
Testning på hjärtan, hjärnor och tumörer
Teamet testade DANST på både artificiella benchmark-dataset och verkliga biologiska prover från möss och människor. Jämfört med flera ledande metoder återvann DANST celltypsproportioner mer exakt i syntetiska dataset och behöll sin fördel över mycket olika vävnader och plattformar. I ett mus-hjärna-dataset rekonstruerade den tydligt cortex lagerorganisation och motsvarade expertd efinerade anatomiska regioner. I en annan mus-hjärnesektion fångade den fina mönster i områden såsom hippocampus. Mest anmärkningsvärt i mänsklig bröstcancervävnad spårade DANST hur olika immunceller, stödjeceller och hormonkänsliga luminala celler är ordnade i och runt tumörområden. Dessa kartor stämde överens med känd biologI och föreslog kliniskt relevanta egenskaper, såsom hormonavhängighet och potentiellt sämre prognos där vissa immunceller var sällsynta.
Vad detta betyder för biologi och medicin
För en icke-specialist kan DANST ses som en kraftfull tolk som förvandlar suddiga, överlappande signaler till en klar bild av vilka celler som finns var i en vävnad. Genom att pålitligt separera celltyper i rummet ger den forskare en skarpare bild av hur friska organ är organiserade och hur sjukdom förändrar denna organisation. Inom cancer kan detta avslöja hur tumörceller och immunceller interagerar i specifika regioner, vilket kan vägleda riktade behandlingar och hjälpa till att förutsäga patientutfall. I takt med att fler spatiala och single-cell-dataset blir tillgängliga är verktyg som DANST redo att bli oumbärliga för att avkoda de cellulära grannskap som ligger till grund för hälsa och sjukdom.
Citering: Zhang, X., Wu, Z., Wang, T. et al. DANST enables cell-type deconvolution in spatial transcriptomics using deep domain adversarial neural networks. Commun Biol 9, 388 (2026). https://doi.org/10.1038/s42003-026-09659-y
Nyckelord: spatial transkriptomik, celltypsdekonvolution, djuplärande, tumörmikromiljö, single-cell RNA-sekvensering