Clear Sky Science · sv
Molekylära QTL är berikade för strukturella varianter i en kohort med långavläsningsdata från nötkreatur
Varför kos-DNA kan lära oss om komplexa egenskaper
Uppfödare, veterinärer och genetiker vill alla förstå varför vissa djur växer snabbare, motstår sjukdom eller producerar mer mjölk än andra. Mycket av svaret finns i DNA, men våra vanliga verktyg tittar mest på mycket små förändringar i enstaka "bokstäver" i genomet. Den här studien visar att mycket större DNA-förändringar — strukturella varianter — i det fördolda formar hur gener fungerar hos nötkreatur, och att nya långavläsningstekniker slutligen låter oss se deras fulla påverkan.
Att betrakta genomet med en skarpare lins
De flesta genetiska studier förlitar sig på korta DNA-sekvenser, som är billiga och precisa men har svårt i repetitiva eller komplexa områden av genomet. Författarna använde en nyare teknik, långavläsningssekvensering, på 120 tjurar från en mjölkproducerande nötkreatursras. Dessa långa läsningar täcker mycket större DNA-regioner, vilket gör det lättare att upptäcka stora insättningar, borttagningar och omarrangemang som kallas strukturella varianter. Teamet jämförde dessa långläsningar med befintliga kortavläsningsdata från samma djur och fann att långläsningarna avslöjade fler varianter totalt och avsevärt förbättrade täckningen av svåra regioner som X- och Y-kromosomerna.
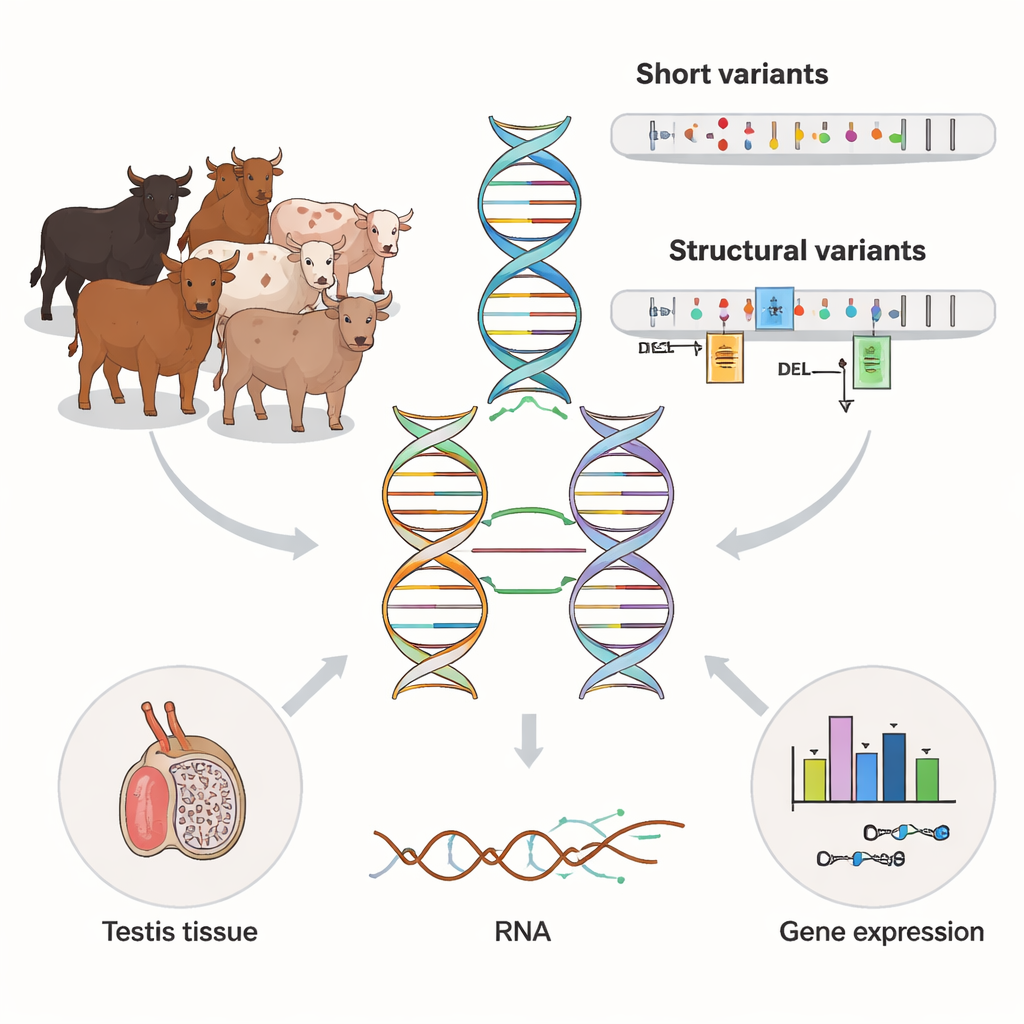
Att upptäcka tusentals dolda DNA-omarrangemang
Med långavläsningsdata katalogiserade forskarna ungefär 24 miljoner små DNA-förändringar och över 79 000 strukturella varianter i tjurarna. Många av dessa större förändringar kopplades till repetitiva DNA-element som kopierar och klistrar in sig själva i genomet. Ungefär en av tio strukturella varianter fanns bara hos ett eller två djur, vilket avslöjar ett rikt förråd av sällsynt variation. Jämfört med ett tidigare nöt-pangenom byggt från högkvalitativa sammanställningar lade den nya datamängden till tiotusentals extra strukturella varianter, särskilt insättningar och komplexa duplikationer som är svåra att upptäcka med äldre metoder. Detta tyder på att långavläsningsstudier fortfarande avslöjar tidigare osynliga lager av genetisk mångfald i boskap.
Koppla DNA-förändringar till genaktivitet
För att se hur dessa DNA-skillnader faktiskt påverkar biologin vände sig teamet till en vävnad som är viktig för hanlig fertilitet: testikeln. För 117 av tjurarna hade de djup RNA-sekvenseringsdata som visar vilka gener som är aktiverade och hur deras budskap splejas. Genom att statistiskt länka genetiska varianter nära varje gen till dess aktivitet identifierade de över 27 000 "molekylära QTL" — genomiska platser som förändrar antingen hur mycket en gen uttrycks eller hur dess RNA sätts ihop. Strukturella varianter framträdde som centrala aktörer: de var mer än dubbelt så vanliga bland toppsignaler för expression och över fem gånger så vanliga bland toppsignaler för splitsning som förväntat av slumpen. I många fall var den mest inflytelserika varianten en stor insättning, borttagning eller duplikation som låg i en promotor, enhancer, exon eller splitsningsställe snarare än en enkeltonsändring.
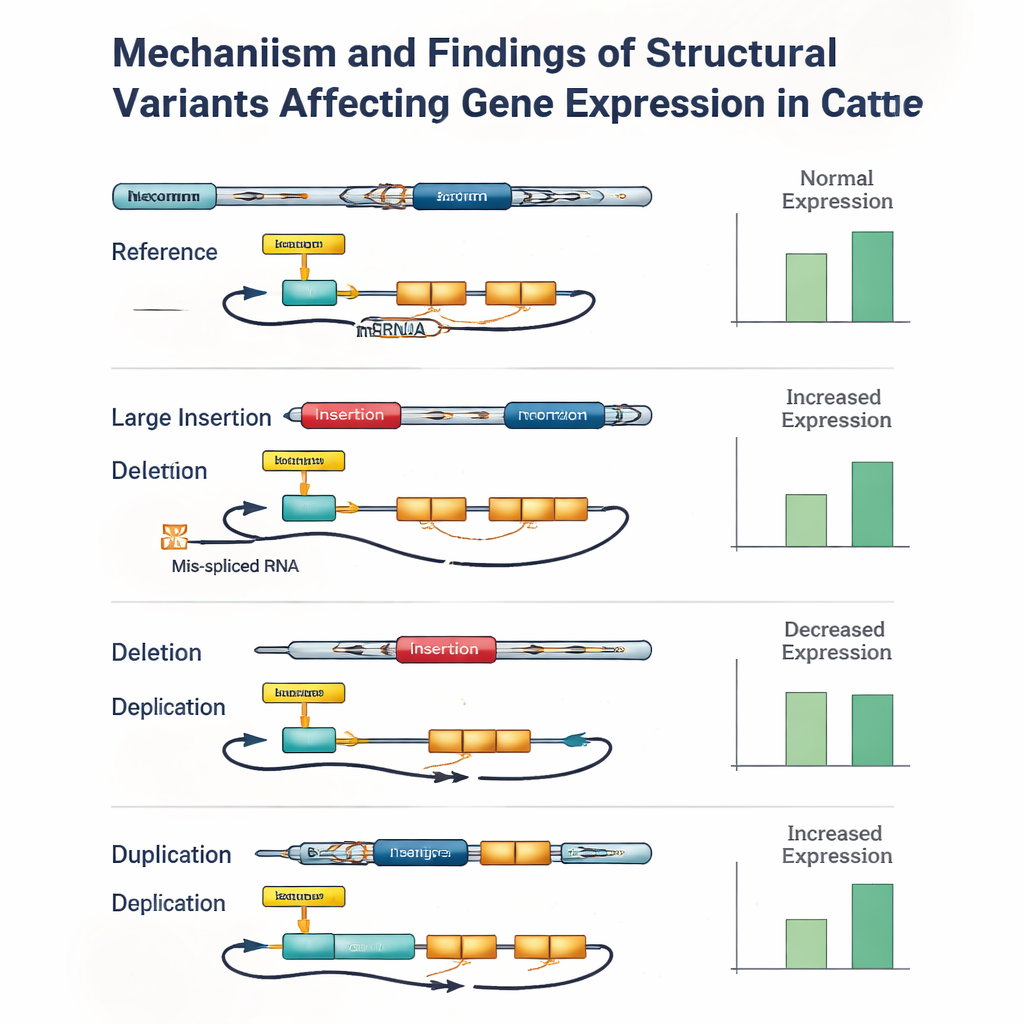
När genotypningsfel döljer viktiga signaler
Studien blottlade dock också gränserna för dagens verktyg. Även med högkvalitativa långläsningar var det utmanande att korrekt tilldela genotyper för strukturella varianter till varje djur, särskilt för stora insättningar och långa duplikationer. Små fel — ibland bara involverande en eller två tjurar — kunde göra att en strukturell variant verkade något mindre statistiskt signifikant än en närliggande liten variant som var i perfekt genetisk låsning med den. När författarna manuellt granskade några av de starkaste signalerna fann de upprepade gånger fall där en strukturell variant inom en gen eller nyckelregulatorisk region var den mest sannolika orsaken till effekten, men genotypningsfel eller saknad data gjorde att en länkad liten variant hamnade högst upp i rangordningen.
Vad detta betyder för avel av nötkreatur och bortom
För icke-specialister är slutsatsen att "stora" DNA-förändringar spelar stor roll. Denna långavläsningsundersökning i nötkreatur visar att strukturella varianter är starkt berikade bland genetiska platser som styr hur gener slås på och splejas, särskilt i reproduktiv vävnad. Samtidigt varnar studien för att dagens analysmetoder fortfarande missar eller felklassificerar många av dessa varianter, särskilt vid måttlig sekvenseringsdjup. När långavläsningssekvensering blir billigare och mer exakt, och bättre mjukvara utvecklas, kommer uppfödare och forskare att kunna spåra ekonomiskt viktiga egenskaper — som fertilitet, sjukdomsresistens och mjölkproduktion — tillbaka till specifika strukturella varianter. Samma principer gäller för människors hälsa och växtförädling: för att fullt ut förstå komplexa egenskaper måste vi se bortom enstaka bokstavsförändringar och omfamna de större omarrangemang som formar genomerna.
Citering: Mapel, X.M., Leonard, A.S. & Pausch, H. Molecular QTL are enriched for structural variants in a cattle long-read cohort. Commun Biol 9, 290 (2026). https://doi.org/10.1038/s42003-026-09596-w
Nyckelord: strukturella varianter, långavläsningssekvensering, nötkreatursgenomik, genuttryck, molekylära QTL