Clear Sky Science · sv
Långvarig exponering för etanol‑nedbrytningsprodukten acetaldehyd ökar strukturella genomiska förändringar men inte bas‑substitutioner
Varför alkoholens dolda biprodukt spelar roll
Många vet att tungt drickande ökar risken för cancer i mun, svalg, magsäck och bröst, men det har varit oklart exakt hur alkohol skadar vårt DNA. Denna studie fokuserar på acetaldehyd, ett mycket reaktivt ämne som kroppen bildar när vi bryter ner alkohol och som även finns i cigarettrök och vissa livsmedel. Med känslig helgenomssekvensering och patientdata visar författarna att acetaldehyd inte öser genomet fullt av små stavfel, som många antagit. I stället ökar det tyst större avbrott och omkastningar i våra kromosomer — förändringar som kan hjälpa friska celler att bli cancerösa.
Närmare titt på vardaglig exponering
Acetaldehyd är klassificerat som en säkerställd mänsklig cancerframkallande substans. Efter en drink, särskilt starka drycker, kan nivåerna tillfälligt nå cancerrelevanta koncentrationer i mun och matstrupe, och mindre mängder cirkulerar i blodet. Vissa personer, särskilt i Östasien, bär varianter av ALDH2‑genen som bromsar nedbrytningen av acetaldehyd och gör att det ansamlas mer. I laboratoriet har det varit svårt att precisera hur acetaldehyd förändrar DNA, delvis eftersom det så snabbt avdunstar från öppna cellkulturer. För att komma runt detta byggde forskarna ett slutet system som håller acetaldehyd på stabila, realistiska nivåer liknande dem som ses i mänskliga vävnader efter alkoholkonsumtion.
Långvarig exponering utan en storm av små mutationer
Teamet exponerade fyra typer av humana celler — inklusive blodceller, bröstceller och två cellinjer från esofaguscancer — för 100 mikromolar acetaldehyd i 30 dagar, en dos som stressade cellerna men som ändå tillät tillväxt. De sekvenserade hela genomet hos individuella efterkommande celler och jämförde med obehandlade kontroller. Över alla celltyper och under normala eller reducerade syreförhållanden ökade acetaldehyd inte antalet "en‑bokstavs" DNA‑ändringar eller små insättningar och deletioner. Inte heller skapade det den kända alkoholkopplade mutationssignaturen kallad SBS16, som setts i låga nivåer i vissa mänskliga tumörer. Med andra ord uppträdde kronisk exponering för acetaldehyd inte som en klassisk kemisk mutagen som strör genomet med små stavfel.
Stora slag mot kromosomerna istället för små fel
Även om småskaliga mutationer knappt förändrades berättade genomet en annan historia. Forskarna fann fler strukturella varianter — stora deletioner och duplikationer av DNA‑sträckor upp till ungefär en miljon baser långa — i de flesta acetaldehydbehandlade cellinjer. Många av dessa deletioner hade korta matchande DNA‑sekvenser vid sina föreningspunkter, ett kännetecken för reparation via icke‑homolog rekombination (non‑homologous end joining), en snabb men felbenägen väg för celler att limma ihop brutna DNA‑ändar. I parallella experiment såg författarna fler sister chromatid exchanges, där motsvarande kromosomer byter segment, och upptäckte direkt bevis för DNA‑brott och aktivering av DNA‑skadesignaler i cellen. Tillsammans tyder dessa resultat på att acetaldehyd utlöser kromosombrott som ibland repareras felaktigt och därigenom omformar genomet.
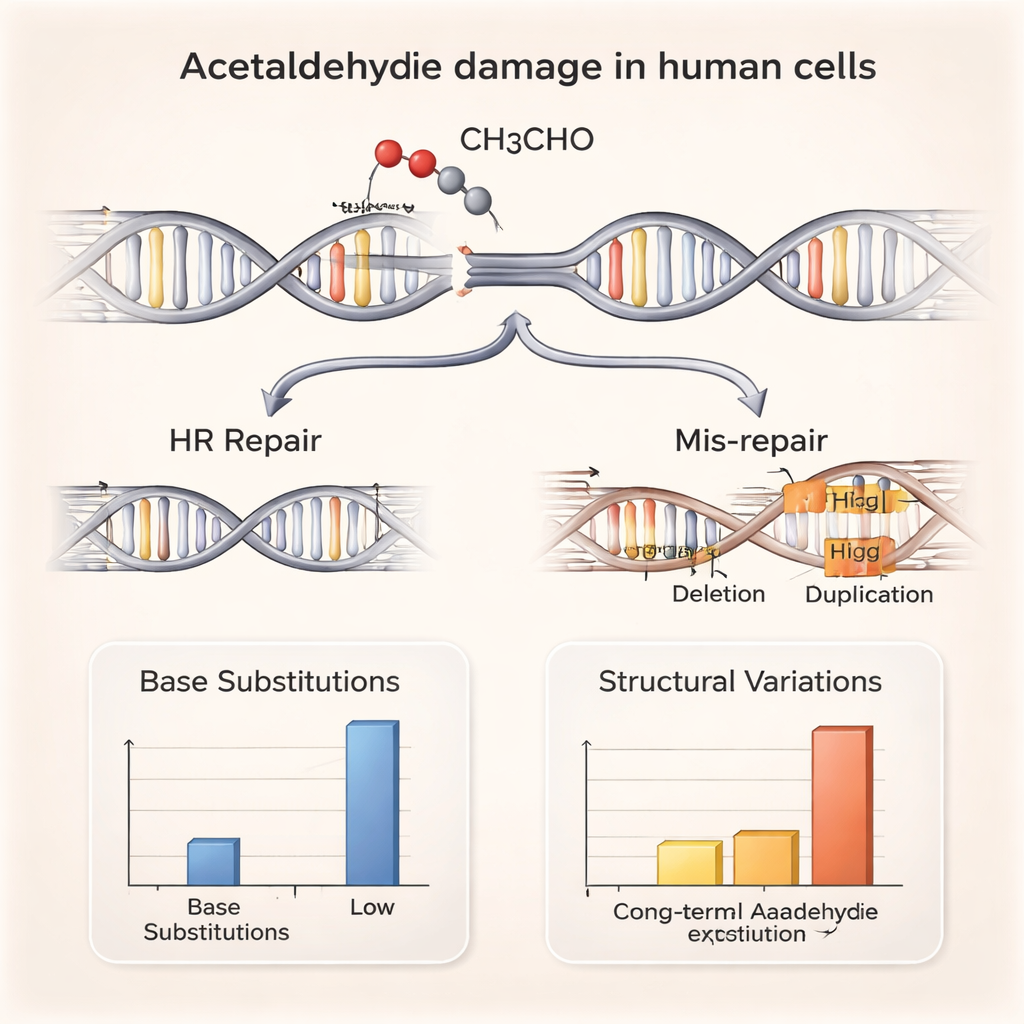
Hur celler hanterar skadorna — och när de inte kan
För att förstå hur celler överlever denna påfrestning testade teamet mutanta cellinjer som saknade specifika DNA‑reparationssystem. Celler som saknade viktiga proteiner i homolog rekombination, en hög‑fidelitetsväg som använder en intakt DNA‑kopia som mall för att reparera brott, var särskilt känsliga för acetaldehyd. Däremot var celler defekta i flera andra reparationsprocesser, inklusive klassisk end‑joining och nukleotid‑excision‑reparation, inte särskilt sårbara. Detta mönster tyder på att många acetaldehyd‑inducerade brott uppstår vid stillastående eller kollapsade DNA‑replikationsgafflar, strukturer som normalt är beroende av homolog rekombination för säker reparation. När detta system försvagas — som hos personer med skadliga BRCA1‑ eller BRCA2‑varianter — kan acetaldehydskador vara svårare att hantera och potentiellt öka cancerrisken.
Bevis från verkliga tumörer
Forskarna vände sig sedan till genomdata från 170 magsäckscancerfall i Japan, där detaljerade uppgifter om alkoholkonsumtion fanns. De såg att tumörer från drickare bar på signifikant fler medelstora deletioner och duplikationer, ungefär mellan 32 000 och 1 miljon DNA‑baser — exakt det storleksintervall som ökade i deras acetaldehydbehandlade celler. Ett liknande mönster visade sig inte i en esofagustyp som inte är starkt kopplad till alkohol. Även om rökning också kan bidra till sådana strukturella variationer, stöder den nära överensstämmelsen mellan laboratorie‑ och patientdata idén att alkohol‑nedbrytningen till acetaldehyd främjar denna särskilda form av genomisk ärrbildning under cancerutveckling.
Vad detta betyder för dem som dricker
För icke‑specialister är huvudbudskapet att alkoholens fara kan ligga mindre i att orsaka oräkneliga små DNA‑felskrivningar och mer i dess förmåga att producera acetaldehyd, som ibland snappar av och omarrangerar stora delar av våra kromosomer. Dessa strukturella förändringar kan störa eller förstärka viktiga gener som styr celltillväxt och därigenom putta celler mot cancer över år av upprepad exponering. Arbetet hävdar inte att någon enstaka drink utlöser cancer, men det fördjupar förståelsen för hur regelbunden alkoholkonsumtion — och faktorer som ALDH2‑ eller BRCA‑varianter — kan samverka på DNA‑nivå. Genom att visa ett specifikt mönster av storskalig skada i stället för en flod av små mutationer hjälper studien att förklara varför alkohol är cancerframkallande och kan vägleda framtida insatser för att identifiera och skydda dem med högst risk.
Citering: Lózsa, R., Szikriszt, B., Németh, E. et al. Long-term exposure to the ethanol-derived metabolite acetaldehyde elevates structural genomic alterations but not base substitutions. Commun Biol 9, 243 (2026). https://doi.org/10.1038/s42003-026-09521-1
Nyckelord: acetaldehyd, alkohol och cancer, DNA‑skada, genomomläggningar, homolog rekombination