Clear Sky Science · sv
Kinic‑index: en AI‑driven prediktiv modell och ramverk för multitarget‑läkemedelsupptäckt för patienter med hepatocellulärt karcinom
Varför denna forskning är viktig
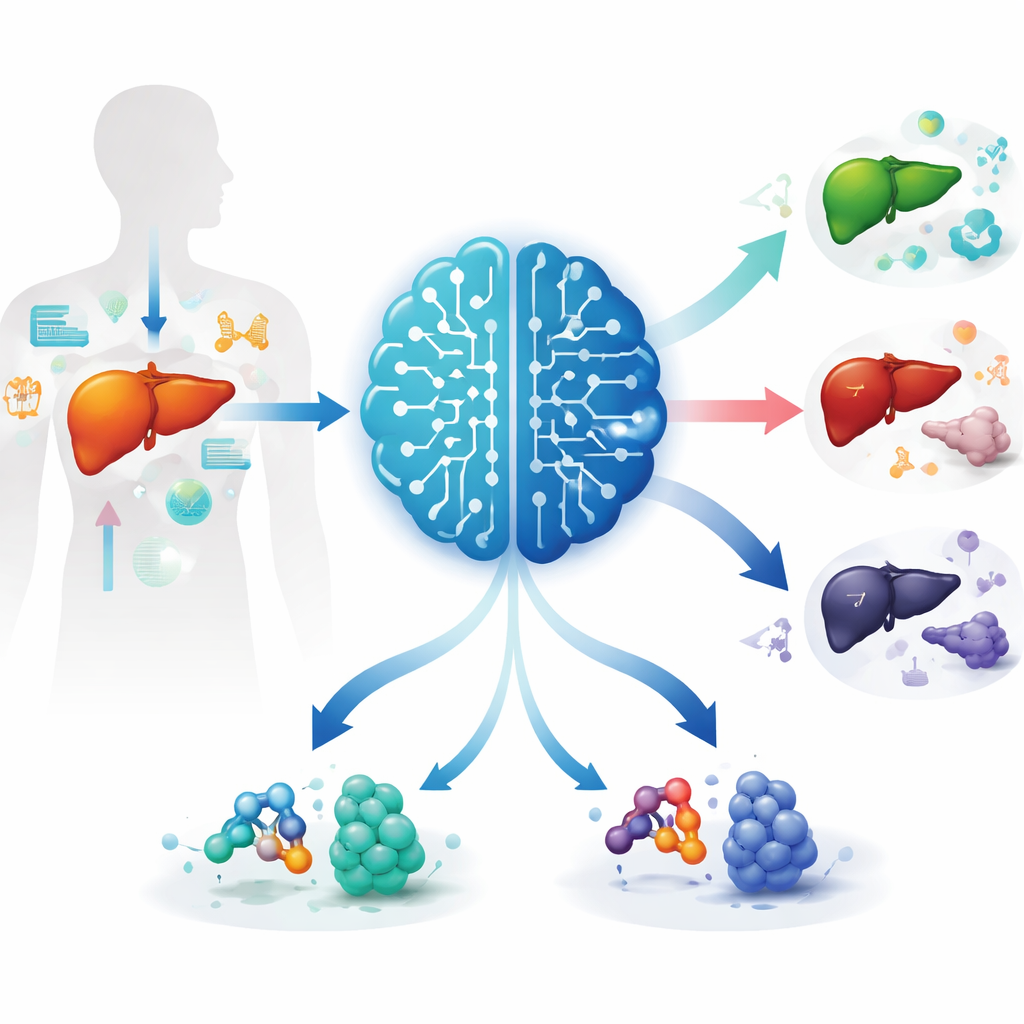
Levercancer hör till de dödligaste cancerformerna globalt, delvis för att tumörer varierar kraftigt mellan patienter och ofta är resistenta mot dagens läkemedel. Denna studie introducerar ett nytt sätt att dela in levercancerpatienter i riskgrupper och samtidigt söka efter nya läkemedel skräddarsydda för deras sjukdom. Med avancerad artificiell intelligens (AI) byggde forskarna ett verktyg kallat Kinic‑indexet som kopplar subtila kemiska märken på proteiner till patientöverlevnad och till lovande läkemedelsmål.
En ny kemisk märkning med stora följder
Att sortera patienter i högre och lägre risk
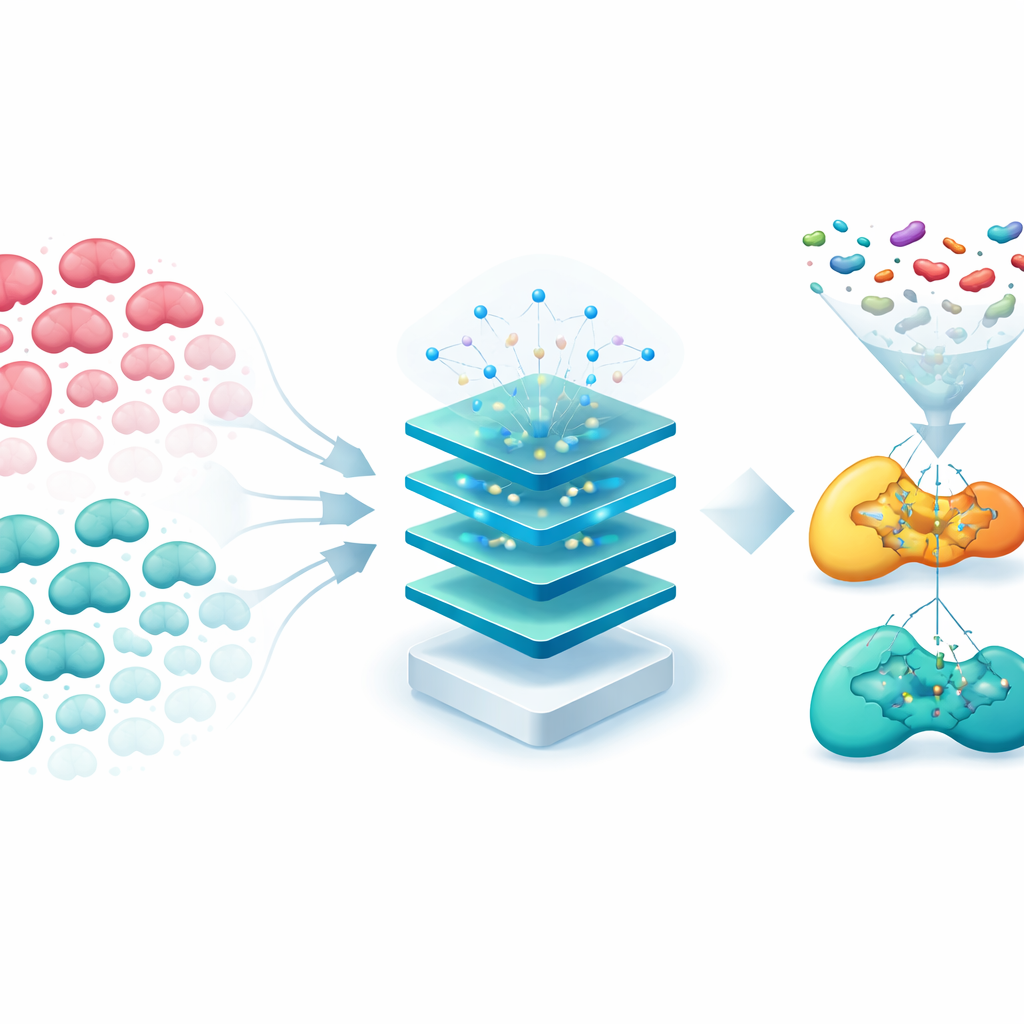
För att göra dessa fynd kliniskt användbara använde forskarna maskininlärning för att gruppera levercancerpatienter baserat på aktiviteten hos isonikotinylation‑relaterade gener. Två huvudundergrupper framträdde. Den ena undergruppen uppvisade starkare aktivitet i vissa gener och hade klart sämre totalöverlevnad. Denna högriskgrupp visade också tecken på en mer aggressiv tumörmiljö: snabbare celldelning, större genetisk instabilitet och en immunprofil som antyder att tumörer kan undgå kroppens försvar. Den andra undergruppen hade mer aktiva avgiftnings‑ och ämnesomsättningsvägar och bättre utfall, vilket tyder på att dessa molekylära mönster kan hjälpa läkare att förutse patienters prognos.
En AI‑poäng som framhäver två nyckelgener
Byggt på dessa mönster skapade forskarna Kinic‑indexet, en AI‑driven poäng som kombinerar flera maskininlärningsmetoder för att förutsäga en patients dödsrisk. De testade över hundra modellkombinationer och valde den som presterade bäst både i en stor cancerdatabas och i en oberoende patientkohort. Poängen visade sig vara en stark och oberoende prediktor för överlevnad, även efter justering för ålder och tumörstadium. Viktigt är att en teknik kallad SHAP, som förklarar hur AI‑modeller fattar beslut, pekade ut två gener — CYP2C9 och G6PD — som mest inflytelserika. Encells‑ och rumsliga analyser visade att båda generna främst är aktiva i maligna leverceller med hög spridningspotential, och att deras aktivitet är tätt kopplad till hur tumörer interagerar med närliggande immunceller och stödjeceller.
Från riskpoäng till kandidatläkemedel
Studien stannade inte vid prognos. Teamet använde ett djupinlärningsramverk kallat GraphBAN för att screena mer än 200 000 kemiska föreningar för deras förmåga att binda till CYP2C9 och G6PD. Därefter tillämpade de ett AI‑verktyg som förutspår hur väl en förening absorberas, metaboliseras och tolereras i kroppen, vilket begränsade listan till bara ett fåtal läkemedelslika molekyler. Datorsimuleringar av dockning föreslog att två kandidater, var och en riktad mot ett av nyckelproteinerna, passar väl in i mycket fördelaktiga fickor på sina mål och bildade stabila komplex över tid. Dessa resultat föreslår konkreta startpunkter för nya läkemedel utformade att störa de metaboliska svagheterna hos levertumörer som Kinic‑indexet lyfter fram.
Vad detta betyder för framtida vård
Enkelt uttryckt visar detta arbete hur AI kan koppla ihop tre avgörande steg i modern cancervård: att förstå hur en ny proteinmärkning formar tumörbeteende, att omvandla den kunskapen till en riskpoäng som skiljer mer sårbara patienter från mer stabila, och att snabbt identifiera nya läkemedelskandidater som träffar rätt molekylära mål. Om fynden bekräftas i ytterligare studier och kliniska prövningar kan Kinic‑indexet hjälpa läkare att identifiera levercancerpatienter som behöver mer intensiv behandling, välja terapier som passar tumörens biologi och vägleda utvecklingen av multitarget‑läkemedel som förutser och motverkar läkemedelsresistens.
Citering: Zhou, J., Jiang, Y., Yu, M. et al. Kinic index: an artificial intelligence-driven predictive model and multitarget drug discovery framework for hepatocellular carcinoma patients. npj Precis. Onc. 10, 132 (2026). https://doi.org/10.1038/s41698-026-01324-1
Nyckelord: hepatocellulärt karcinom, precisionsonkologi, artificiell intelligens, epigenetisk modifiering, läkemedelsupptäckt