Clear Sky Science · sv
AI-driven virtual screening platform identifies novel NSUN2 inhibitor candidates for targeted cancer therapy: a computational drug discovery approach
Nya sätt att överlista envisa cancerformer
Många cancerformer blir dödliga inte bara för att de uppstår, utan för att de lär sig undvika våra bästa läkemedel. Denna studie utforskar ett lovande nytt sätt att stänga ner en nyckelhjälpare för tumörtillväxt, genom att använda artificiell intelligens för att sålla igenom mer än hundra miljoner potentiella läkemedel på en dator innan något blandas i ett riktigt provrör.
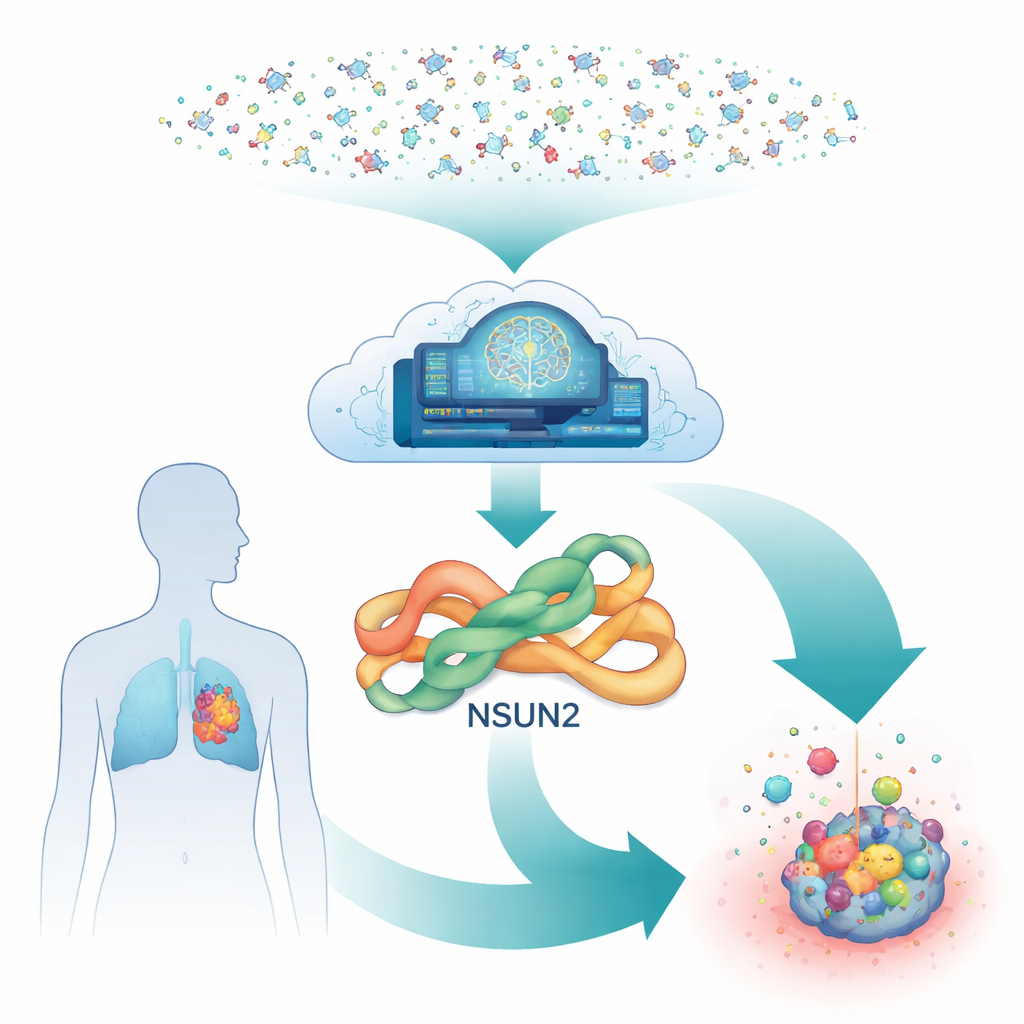
En dold brytare inne i cancerceller
Djupt inne i våra celler fungerar ett enzym kallat NSUN2 som en kemisk markör för RNA, molekylen som hjälper till att omvandla gener till proteiner. Genom att lägga till små kemiska märken på RNA kan NSUN2 göra tillväxtrelaterade budskap mer stabila och lättare att läsa. Många tumörer, inklusive lung-, magsäck-, pankreas- och bröstcancer, höjer NSUN2-nivåerna, vilket ökar deras förmåga att dela sig, sprida sig och motstå riktade läkemedel. Trots dess betydelse finns dock mycket få läkemedelskandidater som säkert kan dämpa NSUN2, särskilt reversibla sådana som inte permanent skadar enzymet.
Låta AI söka i ett hav av molekyler
Traditionell läkemedelsupptäckt skulle ha svårt att testa miljontals molekyler mot NSUN2 i labbet, eftersom varje experiment kräver komplexa blandningar av RNA och hjälpkemikalier. Istället byggde forskarna en helt digital pipeline. De utgick från en predikterad tredimensionell form av mänskligt NSUN2 som genererats av AlphaFold, ett AI-system som revolutionerat strukturbestämning. För att försäkra sig om att modellen var pålitlig, justerade de den mot ett närbesläktat enzym vars struktur är känd från röntgenstudier. Den kritiska fickan där NSUN2 binder sitt naturliga hjälpmolekyl visade sig vara starkt bevarad, vilket gav teamet förtroende för att virtuell dockning av potentiella läkemedel i denna plats skulle vara meningsfull.
Från hundratals miljoner till en handfull
Med målfickan på plats vände sig teamet till en omfattande offentlig databas med köpbara molekyler. De dockade först en träningsuppsättning föreningar i NSUN2-fickan och använde de resulterande poängen för att lära en maskininlärningsmodell vilka former som var mest lovande. Den modellen skannade sedan snabbt omkring 350 miljoner molekyler och flaggade ungefär 101 miljoner som troliga ”träffar”. För att ytterligare begränsa urvalet omdockades den främsta delen med noggrannare beräkningar, och bara de bästa 12 000 med starkt förutsagd bindning behölls. Dessa kördes sedan genom ett batteri av datorbaserade säkerhetskontroller som uppskattade hur kroppen kan absorbera, distribuera, bryta ner och tolerera varje kandidat. Efter dessa filter återstod endast 34 molekyler som såg både potenta och läkemedelsliknande ut.
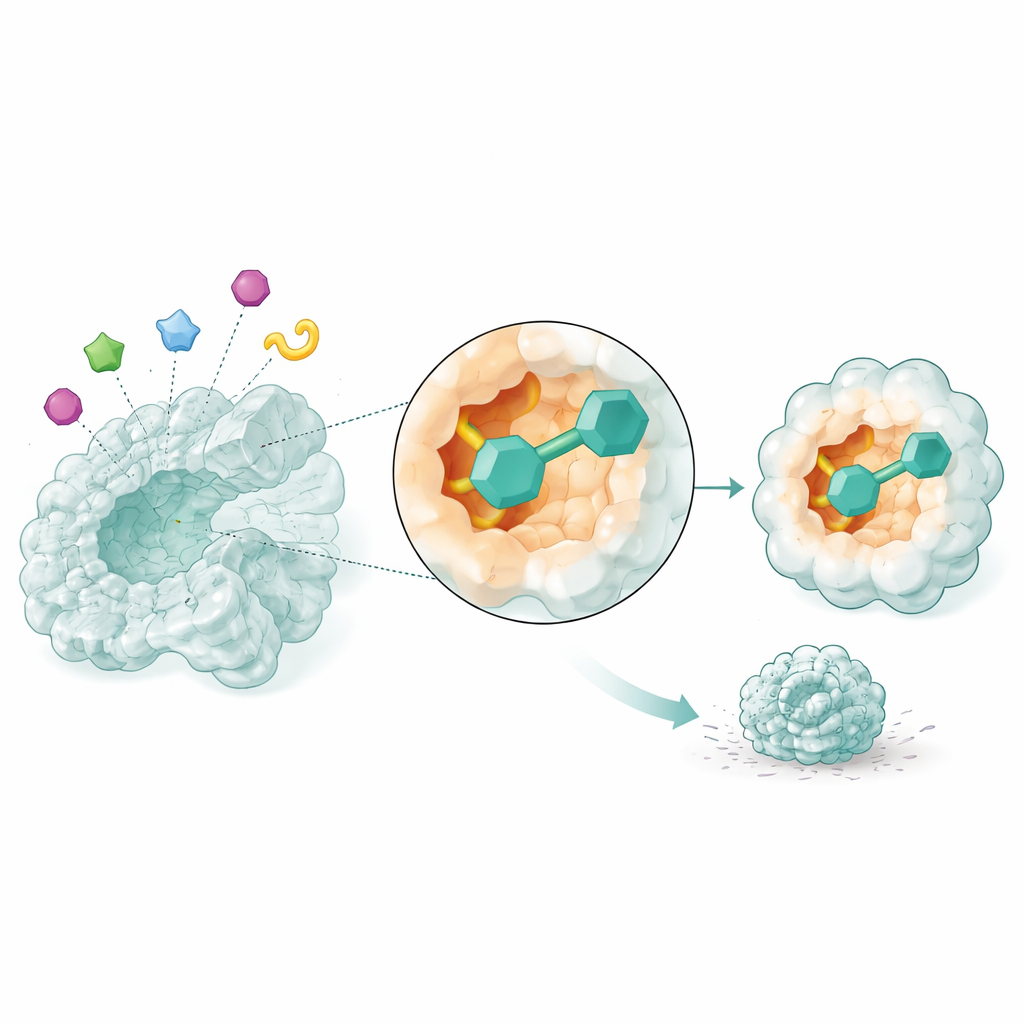
Se kandidatläkemedel i rörelse
Statiska ögonblicksbilder räcker inte för att veta om ett läkemedel verkligen kommer att sitta kvar vid sitt mål. Forskarna använde därför molekylär dynamik-simuleringar, som modellerar hur atomer rör sig över tid, för att observera de mest lovande tre kandidaterna interagera med NSUN2 över 50 miljondels sekund. Två föreningar, identifierade enbart via sina databas-koder, bildade särskilt stabila komplex: enzymstrukturen förblev kompakt, dess nyckelregioner förblev stadiga snarare än sladdriga, och de små molekylerna höll en tät passform inne i fickan samtidigt som de bildade bestående kontakter. Dessa simuleringar tyder på att de två föreningarna pålitligt skulle kunna blockera NSUN2:s aktivitet i verkliga celler.
Vad detta kan innebära för framtida behandlingar
Även om alla resultat i detta arbete bygger på beräkningar och fortfarande måste bevisas i labbet, levererar studien en kort lista med realistiska utgångspunkter för nya NSUN2-blockerande läkemedel. Eftersom NSUN2 hjälper cancerceller att stabilisera tillväxt- och överlevnadssignaler, skulle sådana läkemedel kunna försvaga tumörer och potentiellt återkänsliggöra dem för befintliga riktade terapier, särskilt i lungcancer som blivit resistent. Lika viktigt visar studien upp ett generellt recept för att använda AI och fysikbaserad modellering för att snabbt och billigt utforska enorma kemiska rum, vilket erbjuder en kraftfull genväg mot nästa generation av precisionsbehandlingar mot cancer.
Citering: Yu, S., Peng, Q., Wei, W. et al. AI-driven virtual screening platform identifies novel NSUN2 inhibitor candidates for targeted cancer therapy: a computational drug discovery approach. npj Precis. Onc. 10, 98 (2026). https://doi.org/10.1038/s41698-026-01296-2
Nyckelord: NSUN2, epitranskriptomik, AI virtuell screening, cancer drug discovery, RNA-metylering