Clear Sky Science · sv
Morfologisk‑biokemisk och molekylär identifiering av isolat av Bacillus licheniformis och Bacillus cereus från sorghum (Sorghum bicolor L.) rhizosfär
Vänliga mikrober vid roten av en tålig gröda
Sorghum är ett tåligt sädesslag som föder miljontals människor, särskilt där värme och torka gör jordbruk svårt. Men sorghum står inte ensam i näringsfattiga jordar: dess rötter omges av små jordlevande partner som kan hjälpa den hitta näring, bekämpa sjukdomar och klara av stress. Denna studie undersöker vilka bakterier som lever runt sorghumrötter i östra Indien och granskar två viktiga hjälpande arter från släktet Bacillus, och visar hur noggrant detektivarbete i laboratoriet kan avslöja vilka de är och hur de förhåller sig till sina många släktingar.

Grävandet i livet runt rötterna
Forskarna samlade jord som fastnat på rötterna från flera sorghumvarianter odlade på tre olika platser runt Bhubaneswar, Indien, inklusive en stadspark, en försöksstation och ett universitetsområde. Från dessa rotnära (rhizosfär) jordprover använde de standardiserade odlingstekniker för att växa bakterier på näringsrika plattor, och valde sedan kolonier som skilde sig i färg, form och struktur. En första granskning i mikroskop och Gramfärgning visade att de flesta av de 13 isolaten var stavformade bakterier med tjocka cellväggar, ett kännetecken för Bacillus och närstående släktingar, tillsammans med några sfäriska former och ett tunnväggigt, Gramnegativt isolat.
Test av vad mikroberna kan göra
För att gå bortom utseendet gjorde teamet enkla biokemiska tester som avslöjar hur varje mikrob hanterar syre, bryter ner vissa molekyler och fermenterar sockerarter. Till exempel visar tillsats av väteperoxid om cellerna producerar katalas, ett enzym som skyddar dem mot reaktiva syreföreningar, medan andra tester upptäcker bildning av syra eller förmåga att spjälka aminosyran tryptofan. Mönster i dessa reaktioner hjälpte till att begränsa varje isolats sannolika identitet. Två stavformade stammar, märkta AG3 och AG11, utmärkte sig: båda tolererade syre väl, hanterade skadliga biprodukter effektivt och visade en liknande fermentationsprofil typisk för Bacillus‑arter som trivs i växtrötter.
Avläsning av bakteriernas genetiska streckkod
Där många Bacillus‑arter ser och beter sig lika vände forskarna sig till deras DNA för ett mer precist svar. De fokuserade på 16S rRNA‑genen, en vida använd genetisk ”streckkod” för bakterier. Efter att ha extraherat DNA från AG3 och AG11 kopierade de denna gen med polymeraskedjereaktion och bekräftade på en gel att fragmenten hade förväntad längd. Teamet läste därefter gensekvenserna med Sangersekvensering och jämförde dem med tusentals kända sekvenser i det offentliga NCBI‑databasen. Matchningarna var tydliga: AG3 stämde nästan perfekt överens med Bacillus licheniformis, medan AG11 var en exakt match med Bacillus cereus. Båda är vanliga i jordbrukets jordar och är kända för starka interaktioner med växter, ibland för att främja tillväxt och ibland, i fallet B. cereus, för att kunna innebära hälsorisker i andra sammanhang.
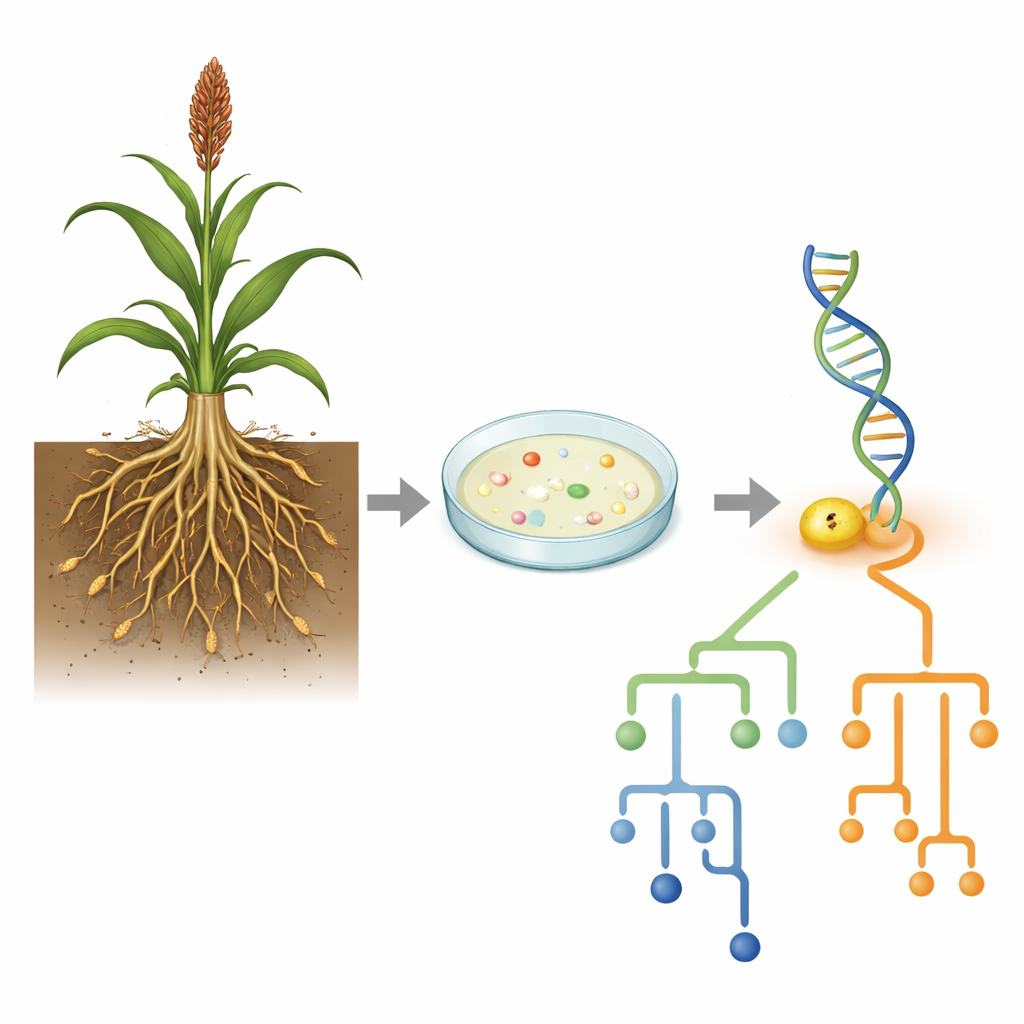
Placering av de nya fynden i livets träd
Att veta närmaste match är bara en del av berättelsen; författarna ville också se var dessa isolat hamnar i det bredare bakterieträdet. De byggde fylogenetiska träd genom att rada upp 16S‑sekvenserna från AG3 och AG11 med flera dussin närstående stammar och använda statistiska modeller för att uppskatta hur snabbt olika positioner i genen förändrats över tid. Bacillus licheniformis AG3 klustrade tätt med en stor grupp liknande stammar, men visade stor variation i hur snabbt olika delar av genen utvecklats, vilket antyder regioner under olika evolutionära påfrestningar. Däremot hamnade Bacillus cereus AG11 i en distinkt undergrupp inom B. cereus‑komplexet, med mer jämnt förändringstakt i genpositionerna. Dessa mönster tyder på att även inom ett släkte kan olika linjer följa skilda evolutionära vägar samtidigt som de fyller liknande nischroller i jordar.
Vad detta betyder för framtidens jordbruk
Studien visar att sorghumrötter i en enda region hyser en mångfald av bakterier och att kombinationen av enkla mikroskop‑ och kemiska tester med DNA‑sekvensering är ett kraftfullt sätt att peka ut nyckelspelare som B. licheniformis och B. cereus. För icke‑specialister är huvudbudskapet att grödors hälsa och avkastning inte bara beror på frön och jord, utan också på dessa dolda mikrobpartner. Även om detta arbete ännu inte direkt testade hur de identifierade stammarna påverkar sorghumtillväxt, kartlägger det vilka mikrober som finns och hur de förhåller sig till varandra — avgörande steg för att utforma säkra, riktade mikrobiella inokulanter som skulle kunna hjälpa bönder att odla mer motståndskraftig sorghum med färre kemiska insatser.
Citering: Jurry, A.G., Sahoo, J.P., Sharma, S.S. et al. Morpho-biochemical and molecular identification of Bacillus licheniformis and Bacillus cereus isolates from sorghum (Sorghum bicolor L.) rhizosphere. Sci Rep 16, 8983 (2026). https://doi.org/10.1038/s41598-026-42932-y
Nyckelord: sorghum, rhizosfärsbakterier, Bacillus licheniformis, Bacillus cereus, växttillväxtfrämjande