Clear Sky Science · sv
En automatiserad bildanalys‑pipeline för bredfältig optisk redoxavbildning av patient‑härledda cancerorganoider
Varför den här canceravbildningsstudien är viktig
Att hitta rätt läkemedel för en persons cancer är fortfarande en långsam, slumpartad process. Denna studie tar sig an problemet genom att kombinera små laboratorieodlade tumörer från patienter — så kallade organoider — med en snabb, kamerabaserad metod för att iaktta hur deras energianvändning förändras när läkemedel tillsätts. Författarna visar hur en ny automatiserad datorpipeline kan sålla igenom stora bildstackar från mikroskop, följa hundratals organoider över flera dagar och avslöja vilka behandlingar som fungerar — allt mycket snabbare och mer tillförlitligt än vad en människa kan göra manuellt.
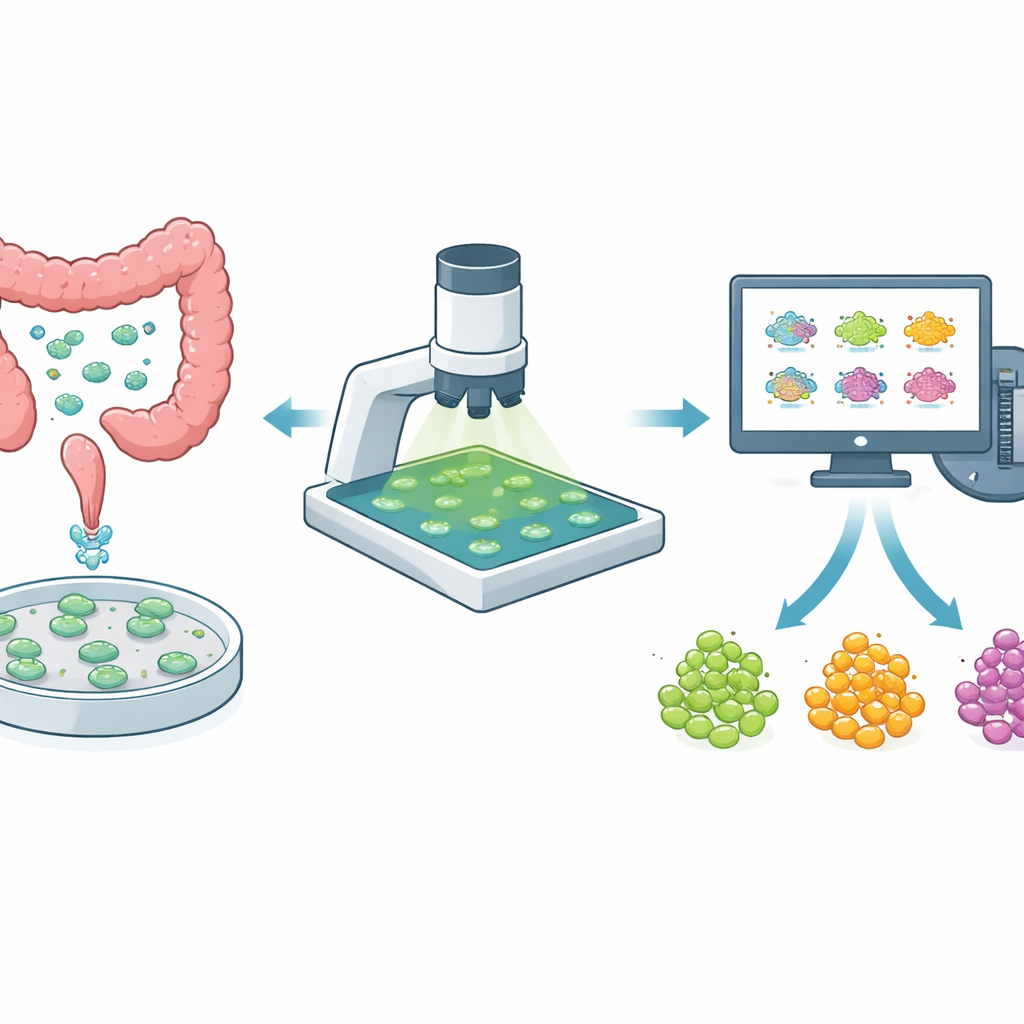
Mini‑tumörer i en skål som testplattform
I stället för att lita enbart på cancerceller odlade som plana lager använder forskare nu ofta tredimensionella organoider framställda direkt från en patients tumör. Dessa mini‑tumörer bevarar bättre blandningen av celltyper och de dolda fickorna med läkemedelsresistenta celler som finns i kroppen. Vid kolorektal cancer, där tumörer varierar kraftigt mellan personer och även inom samma patient, är organoider ett kraftfullt sätt att testa hur väl nya och befintliga läkemedel fungerar. Men för att vara användbara för att vägleda behandling måste organoidtester vara både skonsamma — så att samma organoid kan observeras över tid — och tillräckligt snabba för att screena många läkemedel och doser.
Att iaktta tumörens ”bränsleförbrukning” med ljus
Teamet använder en teknik som kallas optisk redoxavbildning, som utnyttjar den svaga naturliga glöden från molekyler inne i cellerna som är involverade i energiproduktion. Genom att belysa med specifika färger och samla in den emitterade glöden kan ett enkelt bredfältsmikroskop fånga en karta över hur ”oxiderad” eller ”reducerad” varje organoid är — ett ögonblicksbild av dess metaboliska tillstånd. Till skillnad från mer komplexa avancerade mikroskop använder denna uppställning standardkomponenter som många labb redan har, vilket gör den relativt lätt att ta i bruk. Förändringar i denna redoxsignal dyker ofta upp tidigare än förändringar i organoidstorlek eller celldöd, vilket gör den till ett tidigt varningstecken på om ett läkemedel hjälper eller misslyckas.
Att förvandla råa bilder till tillförlitliga siffror
Tidigare betydde analys av dessa bilder att en person var tvungen att rita konturer runt varje organoid, välja bakgrundsområden med ögat och sedan försöka spåra vilken organoid som var vilken över flera dagar. Denna långsamma, felbenägna metod lämpade sig inte för stora läkemedelsscreeningar. Författarna skapade en helhetsautomatisk pipeline som utför tre svåra uppgifter: att exakt skilja varje organoid från omgivningen, tilldela varje organoid en konsekvent identitet över flera dagar och uppskatta bakgrundssignalen på ett sätt som undviker mänsklig partiskhet. De finjusterade ett befintligt verktyg baserat på artificiell intelligens (Cellpose) för att känna igen organoider även när de varierar i form, storlek och fokus, och byggde sedan en spårningsalgoritm som linjerar upp bilder tagna vid olika dagar och matchar organoider baserat på hur deras former och positioner överlappar.
Zooma in på den mest aktiva kanten
Organoider har distinkta zoner: en död eller döende kärna, en lugn mellanzon och en livlig ytterkant där cellerna aktivt växer och ofta är mest känsliga för behandling. Pipelinén skär automatiskt ut denna tunna yttre ring — kallad ledande kant — för varje organoid och beräknar dess redoxvärde. Genom att följa samma organoids ledande kant över tre dagars behandling med olika doser av läkemedlet romidepsin kan programvaran upptäcka subtila skiften i metabolismen. Författarna visar att denna organoid‑för‑organoid‑spårning minskar variabiliteten jämfört med att slå ihop alla organoider, vilket ökar den statistiska styrkan att se läkemedelseffekter även när svaren skiljer sig mellan mini‑tumörerna.
Snabbare, mer robusta insikter om läkemedelssvar
Forskarna testade sin pipeline på bilder från två olika mikroskopsystem och fann att de automatiskt genererade konturerna nära motsvarade expert‑ritade konturer, och att spårningen överensstämde med manuell spårning över 94 procent av tiden. När de jämförde övergripande mått på läkemedelssvar matchade den automatiserade metoden känsligheten hos det manuella tillvägagångssättet samtidigt som analyssituationen kortades med mer än hundrafalt — från många timmars mänskligt arbete till bara några minuters datorbearbetning. För labb som arbetar med patient‑härledda organoider innebär detta att de realistiskt kan analysera stora bildsamlingar och kartlägga hur varje mini‑tumör reagerar på behandling. På lång sikt kan sådan automatiserad analys hjälpa till att föra organoid‑baserad läkemedelsprovning närmare kliniken och stödja mer personanpassad och effektiv cancerbehandling.
Citering: Hsu, A., Samimi, K., Gillette, A.A. et al. An automated image analysis pipeline for wide-field optical redox imaging of patient-derived cancer organoids. Sci Rep 16, 9757 (2026). https://doi.org/10.1038/s41598-026-40249-4
Nyckelord: kolorektal cancer, patient‑härledda organoider, optisk redoxavbildning, automatiserad bildanalys, läkemedelssvar