Clear Sky Science · sv
Implementering av genomisk övervakning av SARS-CoV-2 under covid-19-pandemin genom ett akademiskt–folkhälsosamarbete i sydöstra Michigan
Varför det spelar roll att spåra varianter nära hemmet
Under covid-19-pandemin hörde de flesta av oss om nya varianter via nationella rubriker. Viruset spreds dock inte på samma sätt överallt. Denna artikel beskriver hur forskare, sjukhus och folkhälsomyndigheter i sydöstra Michigan byggde ett lokalt system för att i realtid följa hur coronaviruset utvecklades. Genom att läsa virusets genetiska kod från tusentals prov kunde de se vilka varianter som spreds, var de etablerade sig och vilka samhällen som drabbades hårdast — information som kan leda till snabbare och mer riktade insatser vid framtida utbrott.
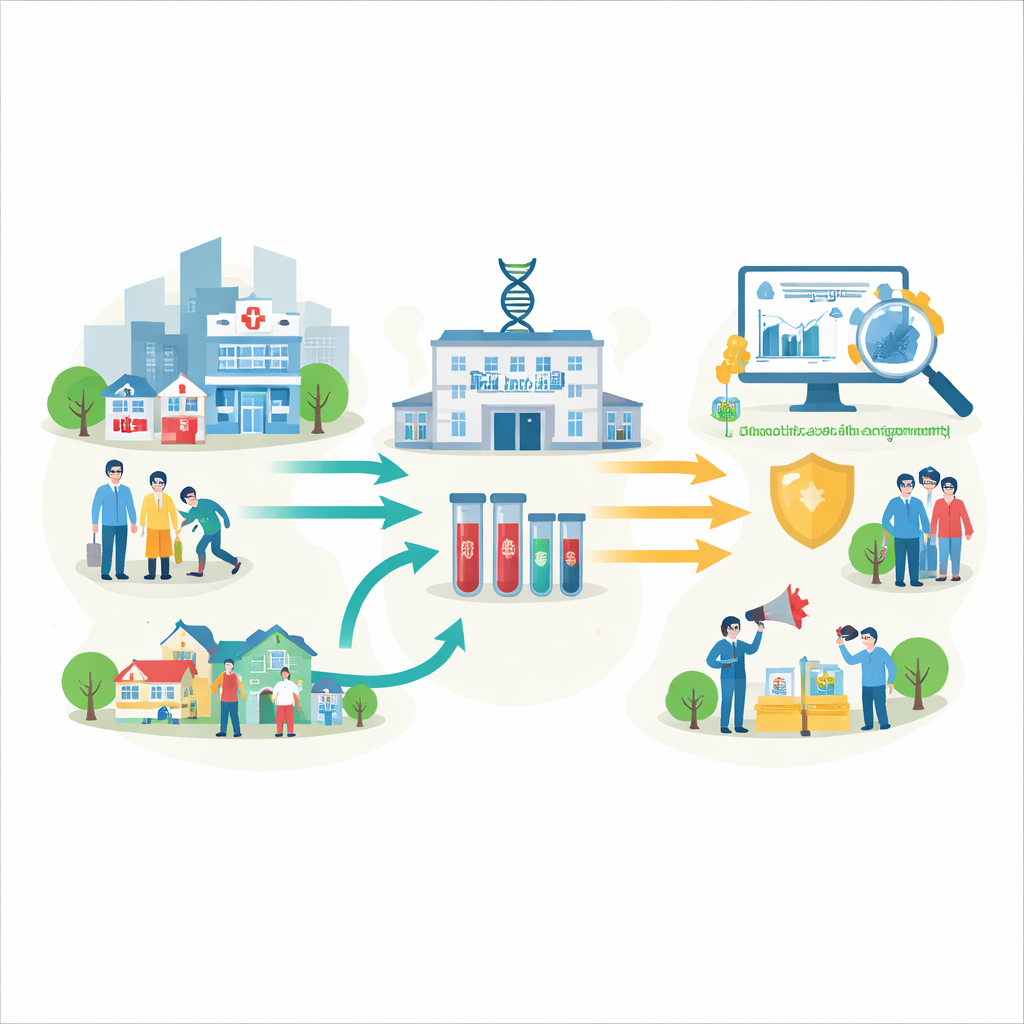
Att bygga ett lokalt tidigt varningssystem
Teamet förenade Wayne State University, Detroit Health Department, Henry Ford Health, en flotta av mobila vårdenheter och delstatens hälsodepartement. Deras gemensamma mål var att skapa ett regionalt ”tidigt varningssystem” för covid-19 baserat på virusets genetiska fingeravtryck. Sjukhus, offentliga kliniker och mobila enheter samlade näsprov från personer som testat positivt. Dessa prover streckkodades, förvarades säkert i ett centralt biobank och skickades vidare till ett universitetslaboratorium utrustat för storskalig testning. Noggrant utformade dataavtal och integritetsskydd gjorde det möjligt att koppla varje virussekvens till grundläggande uppgifter om patienten och deras område utan att avslöja identiteter.
Från prov till genetisk karta
I laboratoriet värmebehandlade teknikerna proverna i biosäkerhetsskåp, extraherade det virala genetiska materialet och bekräftade infektion med ett standardiserat PCR-test. Samma material kördes sedan i högkapacitetsmaskiner som läste hela SARS-CoV-2:s genom för varje patient. Kraftfulla datorer jämförde dessa sekvenser med referensgenom och använde specialiserad programvara för att placera varje virus i en känd variantgrupp. Denna process förvandlade råa svabbprov till organiserade genetiska data — som visade vilka versioner av viruset som cirkulerade, när de dök upp och hur de förändrades över tid.
Var och hos vem viruset slog hårdast
Mellan början av 2022 och mitten av 2024 samlade programmet in över 7 500 prover och lyckades sekvensera mer än 6 200 av dem, de flesta från patienter inom Henry Ford Health-systemet. Dessa fall kom från nästan 300 postnummer över sydöstra Michigan. Omikron var med stor marginal den dominerande varianten och stod för ungefär två tredjedelar av de sekvenserade infektionerna, och variantmönstret stämde väl överens med vad som observerades i delstatsdata. Äldre vuxna förekom oftare i datamängden och hade högre dödlighet, vilket speglar deras större risk för svår sjukdom. Infektioner var något vanligare bland kvinnor, men dödsfall var något vanligare bland män. När forskarna jämförde mönster efter ras och bostadsområde fann de att svarta invånare hade högre infektions- och dödlighet än vita invånare — men när man tog hänsyn till infektion, ålder och variant var det bostadsområdets socioekonomiska nackdel, inte ras ensam, som bäst förklarade den ökade dödsrisken.

Att följa hur viruset förändras över tid och rum
Eftersom varje virus bar en tidsstämpel och en plats kunde teamet rita kartor och tidslinjer över pandemin i deras region. De såg tidiga vågor dominerade av äldre linjer, följt av en kort topp av Delta-varianten och sedan en lång period där Omikron och dess avknoppningar tog över. Omikron visade den största geografiska spridningen, även till norra delar av delstaten, men de högsta infektionsnivåerna klustrade sig i och runt Detroit-storstadsområdet. När forskarna jämförde sina data med nationella och globala databaser fann de stark överensstämmelse i övergripande varianttrender men också tydliga tecken på lokala avvikelser och provtagningsluckor, vilket understryker varför regional övervakning tillför värde utöver nationella siffror.
Vad denna modell betyder för framtiden
Enkelt uttryckt visar denna artikel att en stad och dess kringliggande samhällen kan bygga sin egen ”genetiska radar” för att spåra ett virus, även under en snabb förlöpande kris. Programmet i sydöstra Michigan kopplade ihop sjukhus, mobila kliniker och folkhälsomyndigheter till ett fungerande system som kunde se farliga varianter anlända, följa deras spridning och koppla dem till verkliga utfall som sjukhusinläggning och dödsfall. Författarna erkänner visserligen begränsningar — såsom ojämn provtagning och fokus på ett vårdsystem — men hävdar att den grundläggande modellen är hållbar och anpassningsbar. Med tillräckligt stöd skulle liknande partnerskap kunna användas för att övervaka influensa, RSV, Mpox eller nästa okända patogen, och ge lokala beslutsfattare en tidigare och tydligare bild av problem innan de utvecklas till en fullskalig nödsituation.
Citering: Raychouni, R., Zhang, X., Bauer, S.J. et al. Implementation of SARS-CoV-2 genomic surveillance during the COVID-19 pandemic through an academic–public health collaboration in southeast Michigan. Sci Rep 16, 8680 (2026). https://doi.org/10.1038/s41598-026-39974-7
Nyckelord: SARS-CoV-2-varianter, genomisk övervakning, COVID-19-epidemiologi, folkhälsodata, Detroit Michigan