Clear Sky Science · sv
Uppmärksamhetsstyrd förbättrad dekonvolution möjliggör referensfri uppskattning av celltyper i spatial transkriptomik
Se celler på plats
Modern biologi kan läsa av aktiviteten hos tusentals gener samtidigt, inte bara i isolerade celler utan direkt i tunna vävnadsskivor. Denna "spatiala transkriptomik" avslöjar var olika celler finns och interagerar, men varje mätning blandar ofta signaler från många närliggande celler. Studien presenterar en ny beräkningsmetod, kallad AGED, som kan reda ut dessa blandningar och uppskatta vilka celltyper som finns var — utan att behöva en separat, noggrant matchad single-cell-referensdatamängd. 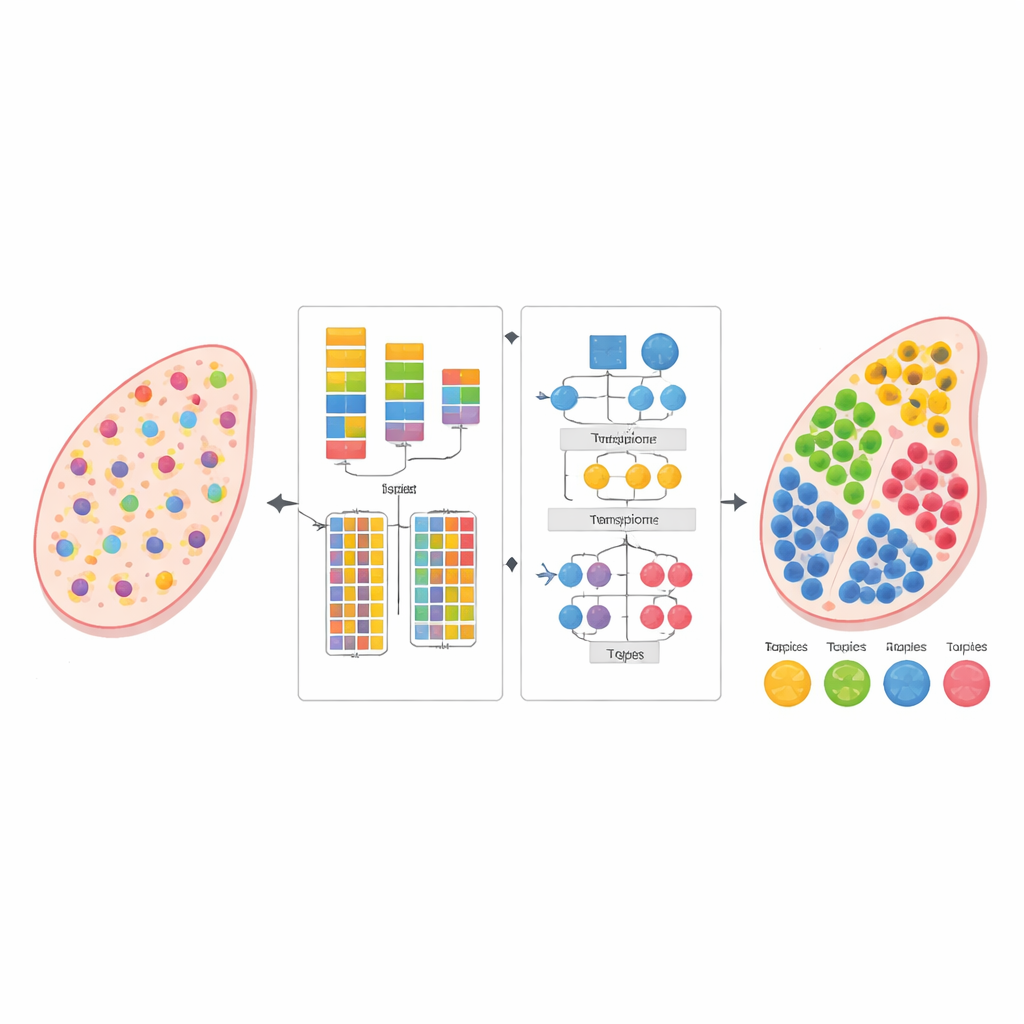
Varför kartläggning av celler i vävnad är svårt
Plattformar för spatial transkriptomik mäter genaktivitet över ett rutnät av fläckar som läggs över en vävnadsskiva. Eftersom de flesta fläckar fångar flera celler samtidigt måste forskare matematiskt dela upp de blandade signalerna för att återfå de underliggande celltyperna och deras andelar. Befintliga verktyg förlitar sig ofta på externa single-cell-referensatlaser för samma vävnad. Sådana atlaser kan saknas för ovanliga vävnader, särskilda sjukdomstillstånd eller ovanliga experimentuella förhållanden, och även när de finns kan de vara ofullständiga eller inte helt matcha provet, vilket inför bias. Referensfria metoder undviker detta beroende, men nuvarande angreppssätt har svårt med komplexa spatiala mönster, subtila genrelationer och utmaningen att bestämma hur många distinkta celltyper man ska leta efter från början.
En tvåstegsstrategi för att reda ut blandningar
Författarna utformade AGED som ett tvåstegsramverk som kombinerar idéer från statistik och modernt djuplärande. I första steget testar metoden ett spann av möjligheter för hur många celltyper som kan finnas i vävnaden. Den använder ett snabbt uppmärksamhetsbaserat neuralt nätverk, känt som en Performer, för att lära sig kandidatdekompositioner och poängsätter dem sedan med flera kriterier samtidigt: hur väl modellen rekonstruerar de observerade gentranskripten, hur tydligt de infererade cellgrupperna skiljer sig åt och hur diversifierade dessa grupper är. En kurvanpassningsprocedur hittar en "armbågspunkt" där tillägget av fler celltyper ger liten nytta, vilket låter metoden automatiskt välja ett lämpligt antal i stället för att förlita sig på användarens gissning.
Vägledd uppmärksamhet för att fånga biologin
När antalet celltyper är bestämt förfinar AGED i andra steget lösningen med en rikare uppmärksamhetsbaserad arkitektur. Den utgår från en statistisk topic-modell som behandlar varje vävnadsfläck som en blandning av dolda "teman" — här motsvarande celltyper — och varje celltyp som ett karaktäristiskt genmönster. Dessa initiala teman ger global struktur. Modellen lägger sedan flera uppmärksamhetsmekanismer ovanpå: en kopplar de statistiska temana till det neurala nätverket, en annan samlar information från närliggande fläckar i fysisk rymd, och en tredje länkar teman direkt till gener. Ett styrsystem låter modellen avgöra, för varje fall, hur mycket den ska lita på de statistiska förhandsmönstren kontra den lokala datan. Ytterligare begränsningar uppmuntrar till glesa lösningar, vilket speglar den biologiska verkligheten att de flesta vävnadsplatser domineras av bara några få huvudcelltyper. 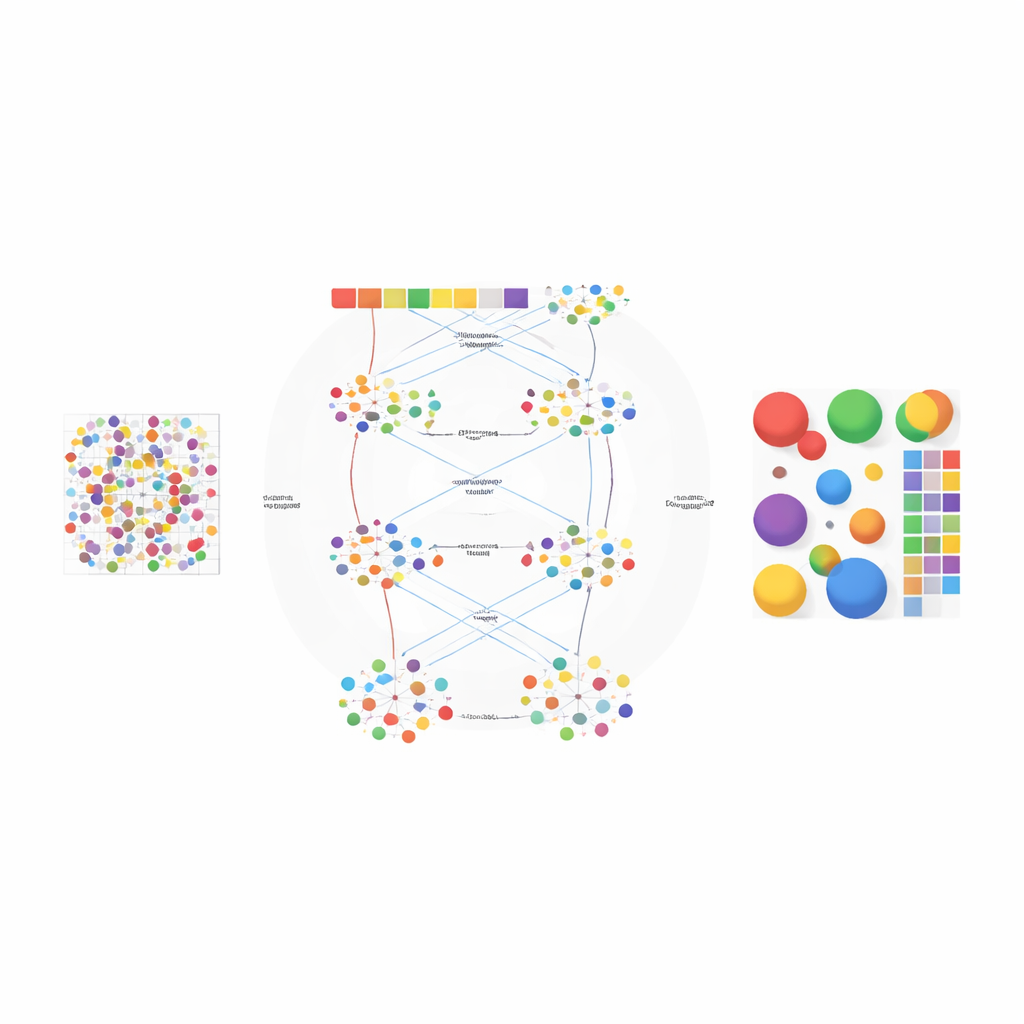
Att sätta metoden på prov
Forskarna utvärderade AGED på flera typer av data. I simulerad musluktlobsvävnad återhämtade metoden fyra kända anatomiska lager och matchade de verkliga cellkompositionerna närmare än vida använda referensbaserade och referensfria verktyg, med både hög korrelation med marksanningen och låg rekonstruktionsfel. I mänsklig pankreas ductal adenocarcinom valde AGED automatiskt en lösning med tjugo celltyper som stämde överens med patologannoterade regioner som tumör, gång och normal pancreas, och överträffade andra metoder på ett strukturellt likhetsmått som jämför de infererade kartorna med den synliga vävnadsstrukturen. I mänsklig thymusvävnad separerade AGED korrekt viktiga cellpopulationer och fångade ett biologiskt förväntat negativt förhållande mellan två specialiserade epitelcelltyper — ett mönster som konkurrerande metoder misslyckades med att reproducera. Ytterligare analyser på andra dataset och i single-cell-liknande upplösning stödde vidare metodens robusthet.
Vad detta betyder framöver
För en icke-specialist kan AGED ses som en smart avblandningsmotor för komplexa vävnader: den lär sig hur många distinkta cellgemenskaper som finns, var de är lokaliserade och vilka gener som definierar dem, allt från den spatiala datan själv. Genom att väva ihop tolkbara statistiska modeller med flexibla uppmärksamhetsbaserade neurala nätverk erbjuder ramverket både noggrannhet och insikt, även när ingen lämplig referensatlas finns. Det gör det till ett praktiskt verktyg för att utforska vävnadsorganisation i hälsa och sjukdom, från hjärnskikt till tumörer och immunceller, och pekar mot en bredare strategi för att använda förhandskunskap för att styra kraftfulla men ogenomskinliga maskininlärningsmodeller i biologin.
Citering: Yang, X., Wang, Y. & Chen, X. Attention-guided enhanced deconvolution enables reference-free cell type estimation in spatial transcriptomics. Sci Rep 16, 8097 (2026). https://doi.org/10.1038/s41598-026-39703-0
Nyckelord: spatial transkriptomik, dekonvolution av celltyper, djuplärande, vävnadsarkitektur, referensfri analys