Clear Sky Science · sv
Att integrera djupinlärning med fysikbaserad modellering möjliggör högprecisionsprediktion av antikropp–antigen-gränssnitt
Varför detta spelar roll för framtida läkemedel
Antikroppar är vårt immunsystems och många moderna läkemedels styrda missiler. För att designa bättre antikroppar måste forskare veta exakt hur en antikropp griper sitt mål, antigenet. Att bestämma dessa strukturer experimentellt är långsamt och kostsamt. Denna studie visar hur en kombination av djupinlärning och klassisk fysikbaserad modellering kraftigt kan förbättra datorbaserade prediktioner av var en antikropp och ett antigen möts, vilket potentiellt kan påskynda design och screening av antikroppar.
Att hitta handskakningszonen
Antikroppar känner igen sina mål med små flexibla slingor i spetsarna, kallade bindningsregioner, som tillsammans bildar en kontaktyta. Dessa slingor kan böjas och vridas, och motsvarande yta på antigenet är ofta utspridd och grund snarare än att bilda en djup ficka. Denna flexibilitet och finkänslighet gör dockningsproblemet—att lista ut hur de två formerna passar ihop—extremt svårt för datorer. Traditionella dockningsprogram testar många relativa positioner mellan de två proteinerna och poängsätter dem med fysiska principer som elektrostatisk attraktion och hur vatten trängs undan, men utan biologiska ledtrådar hamnar de ofta i felaktiga lösningar.
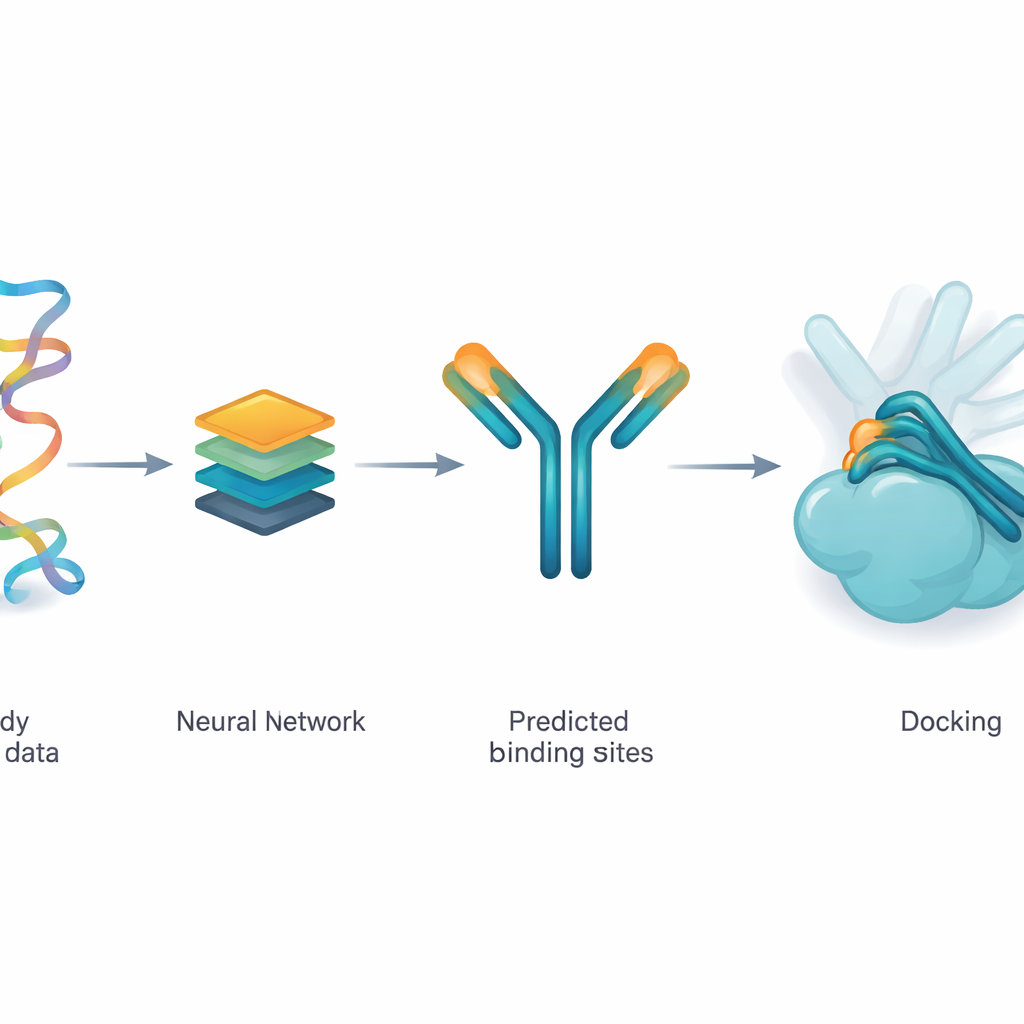
Att lära ett nätverk föreslå sannolika kontaktställen
Författarna använder en djupinlärningsmodell kallad ParaDeep för att gissa vilka aminosyror på en antikropp som mest sannolikt kommer att röra antigenet. ParaDeep gör detta enbart utifrån antikroppens sekvens—ordningen av dess byggstenar—istället för att kräva en full 3D-struktur. Den läser tung- och lättkedjornas sekvenser tillsammans, kodar deras kemiska och positionella egenskaper och använder attention-mekanismer för att framhäva rester som ser ut att vara bra kandidater för bindning. Varje position tilldelas en sannolikhetspoäng; de över en tröskel behandlas som en predikterad kontaktzon som kan kartläggas tillbaka på antikroppsstrukturen.
Att styra en fysikmotor istället för att ersätta den
I stället för att använda djupinlärning för att generera fullständiga antikropp–antigen-komplex från grunden matar teamet ParaDeeps predikterade kontaktrester in i en befintlig fysikbaserad dockningsmotor kallad PyDockWEB. Detta dockningsprogram provtar tusentals möjliga sätt som antikroppen och antigenet kan mötas och poängsätter dem med en energifunktion. I den nya ramen fungerar de predikterade kontaktresterna som mjuka restriktioner: de biasar sökningen så att många provade orienteringar för dessa rester nära antigenets yta. Viktigt är att den underliggande fysiska poängsättningen och behandlingen av proteinerna som styva kroppar förblir oförändrade, vilket gör processen transparent och relativt lätt att köra.
Hur mycket bättre blir prediktionerna?
Forskarna testade sitt hybrida tillvägagångssätt på 50 kända antikropp–antigen-komplex från en kurerad databas. För varje fall jämförde de standard “blind” dockning med dockning styrd av ParaDeeps restriktioner. De mätte lokal gränssnittsnoggrannhet (hur nära den predikterade kontaktregionen var verkligheten), övergripande formlikhet och en kombinerad kvalitetspoäng som ofta används för att bedöma dockningsmodeller. Över detta dataset minskade den styrda metoden fel vid bindningsstället kraftigt, försköt de övergripande strukturerna närmare de verkliga komplexen och flyttade många prediktioner från uppenbart felaktiga till medel- eller högkvalitativa kategorier. Nästan hälften av de styrda modellerna hamnade i högkvalitetsintervallet, jämfört med ungefär en fjärdedel för blind dockning.
Vad gör att vissa träffar är lättare än andra
Teamet undersökte också varför vissa komplex drog större nytta än andra. De fann att att förutsäga fler kontaktrester inte automatiskt gav framgång; vad som spelade roll var att placera restriktionerna i rätt område, inte deras antal. Gränssnitt som var mer vattenälskande och innehöll fler flexibla coil-segment tenderade att docka bättre, sannolikt eftersom de gynnades av PyDockWEBs fokus på elektrostatik och var lättare att alignera utan stora formförändringar. När forskarna upprepade några misslyckade fall med “oracle”-kontaktinformation hämtad direkt från experimentella strukturer förbättrades de flesta av dessa fall, vilket bekräftar att noggrann lokalisering av kontaktytan är en nyckelingrediens—men styv kroppsdockning har fortfarande begränsningar när stora formjusteringar krävs.
Vad detta betyder framöver
I praktiska termer visar detta arbete att ge ett fysikbaserat dockningsprogram en smart ledtråd om var en antikropp sannolikt griper sitt mål kan förbättra träffsäkerheten avsevärt, utan att göra processen till en ogenomskinlig svart låda. Den kombinerade ParaDeep–PyDockWEB-pipelinen ersätter inte mer avancerade flexibla eller generativa metoder, men erbjuder ett praktiskt sätt att använda sekvensbaserade djupinlärningssignaler för att vägleda välkända, tolkbara dockningsverktyg. När antikroppsupptäckt och ingenjörsarbete genererar allt större sekvensbibliotek kan sådana hybrida angreppssätt hjälpa forskare att snabbt filtrera kandidater som är strukturellt förenliga med ett önskat mål, vilket gör vägen från sekvens till användbar antikropp snabbare och bättre underbyggd.
Citering: Kodchakorn, K., Udomwong, P., Pamonsupornwichit, T. et al. Integrating deep learning with physics based modeling enables high precision antibody antigen interface prediction. Sci Rep 16, 8134 (2026). https://doi.org/10.1038/s41598-026-39466-8
Nyckelord: antikropps-dockning, djupinlärning, paratop-prediktion, protein–protein-interaktioner, antikroppsdesign