Clear Sky Science · sv
CiCLoDS: Gemensam cellklustring och genval för enkelcells spatial transkriptomik
Att hitta grannskap i cellernas stad
Moderna mikroskop kan nu avläsa vilka gener som är aktiva i hundratusentals celler samtidigt som varje cell behåller sin ursprungliga plats i vävnaden. Denna "spatiala transkriptomik"-revolution är som att förvandla en suddig stadskarta till en gatunivåvy av varje hus. Men det finns en hake: kartorna innehåller mätvärden för tusentals gener per cell, mycket mer än vad forskare enkelt kan tolka eller ha råd att mäta i uppföljande experiment. Denna studie introducerar CiCLoDS, en ny metod som hittar meningsfulla cellulära grannskap och samtidigt väljer en liten, tolkbar lista av gener som definierar dessa grannskap.
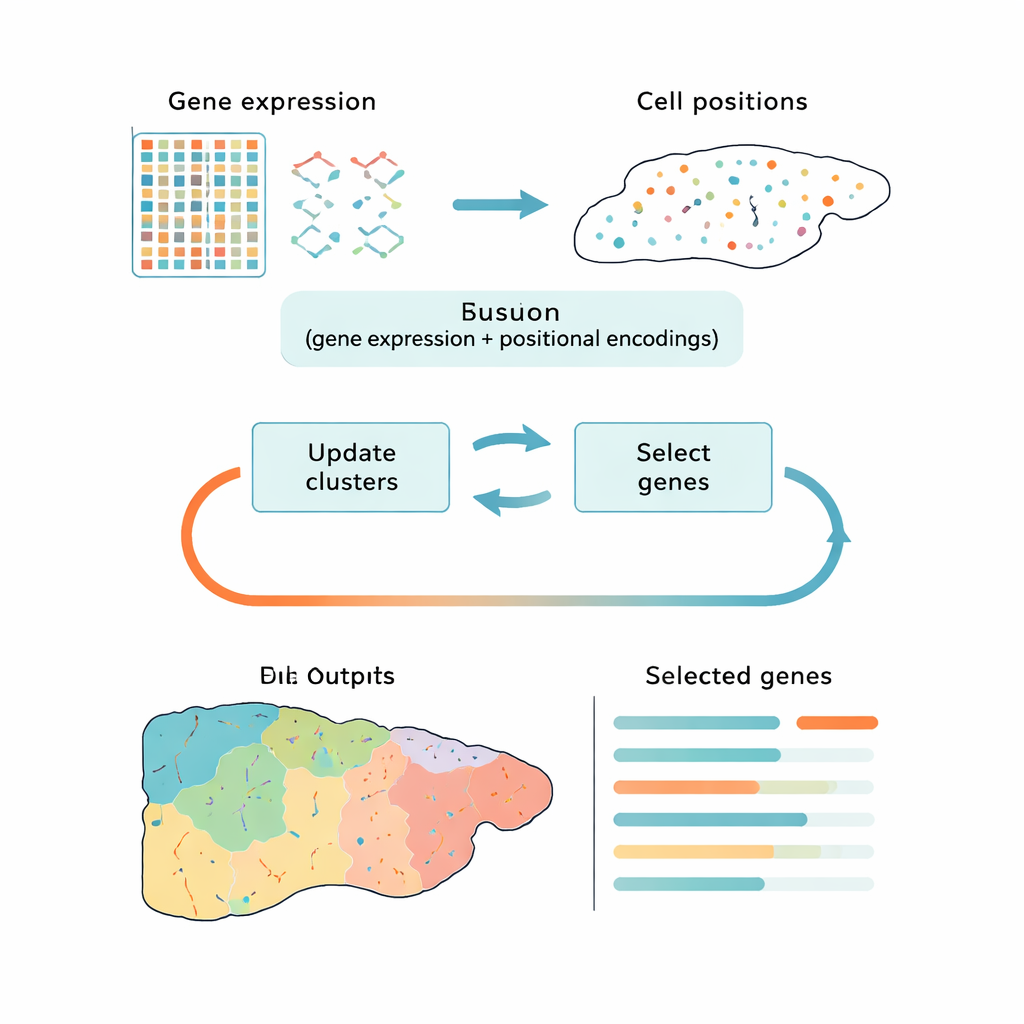
En smartare väg att krympa big data
De flesta nuvarande verktyg hanterar denna utmaning i två åtskilda steg: först reducerar de datan till en enklare form, sedan grupperar de celler i kluster. Populära tillvägagångssätt som principal component analysis (PCA) bevarar övergripande variation men kan fokusera på tekniskt brus eller generiska cellcykelsignaler snarare än de biologiska skillnader som är viktiga. Andra metoder använder djupinlärning för att hitta mönster, men de fungerar som svarta lådor och säger inte tydligt vilka gener som är viktigast. CiCLoDS tar en annan väg. Den behandlar genval och klustring som ett gemensamt problem under en användardefinierad "budget" för hur många gener som kan behållas. I praktiken frågar den: vilken begränsad uppsättning gener förklarar bäst hur celler faller in i distinkta grupper, givet både deras genaktivitet och, när det är tillgängligt, deras fysiska position i vävnaden?
Från matematik till kartor över verkliga vävnader
Författarna anpassar en familj av matematiskt transparenta tekniker som kallas subspace clustering till spatial transkriptomiks realiteter, där dataset kan innehålla över en miljon celler. CiCLoDS arbetar på en enkel cell‑per‑gen-tabell, tilldelar celler till kluster samtidigt som den poängsätter varje gen för hur mycket den hjälper till att separera dessa kluster. Den kan också väva in spatial information genom att lägga till positionella "kodningar" som beskriver var varje cell sitter i vävnaden, utan att förändra den grundläggande optimeringen. På stora muslever‑ och mänskliga kolon‑dataset framtagna med högupplösta bildplattformar kör CiCLoDS på minuter på standarddatorer och producerar kompakta genpaneler—i storleksordningen några tiotals till några hundra gener—som ändå fångar den rika strukturen i ursprungsdatan.
Avslöja dolda zoner och blodkärl
När CiCLoDS tillämpades på muslever undersökte teamet om metoden kunde återskapa kända "zonations"‑mönster—gradvisa skiften i hepatocytfunktion från ena sidan av lobulen till den andra. Jämfört med PCA och ett ledande genvalverktyg kallat geneBasis producerade CiCLoDS renare spatiala zoner med skarpare gränser och betydligt färre felaktigt tilldelade regioner, vilket syntes i kvantitativa mått som mäter överensstämmelse med en referenskarta. Anmärkningsvärt är att när den fick använda fler gener återupptäckte CiCLoDS peri‑portal‑liknande och peri‑central‑liknande hepatocytgrupper som nära matchade expertdefinierade referenskluster, trots att den inte informerades om den nyckelbiomarkören AXIN2 eller fick uttryckliga spatiala koordinater. När spatiala kodningar lades till lärde sig CiCLoDS också genpaneler som var stärkta för cell‑yta‑ och kärlrelaterade funktioner och kunde noggrant skilja verkliga blodkärl från bildartefakter—något enklare metoder antingen misslyckades med eller endast uppnådde med mer ad hoc‑justeringar.
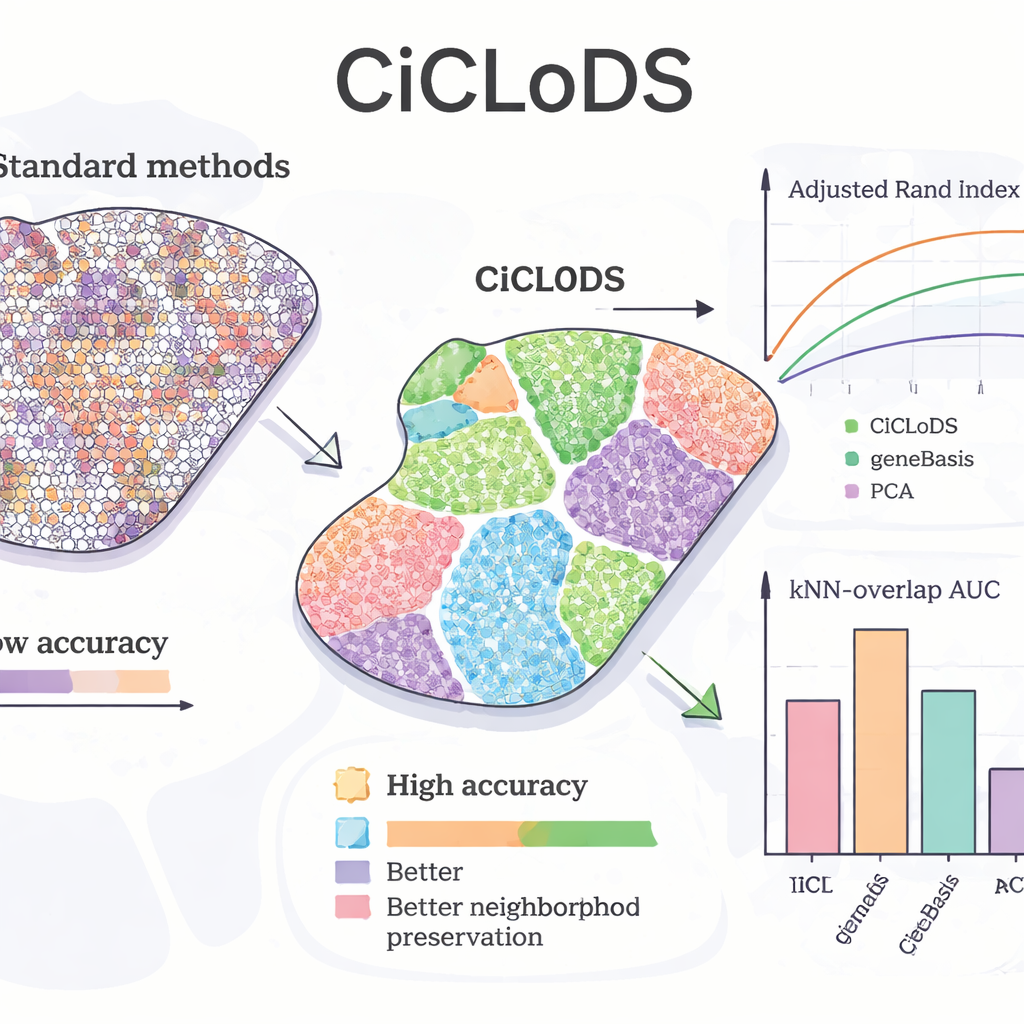
Generaliserar över hjärnor och förbättrar andra metoder
För att testa om CiCLoDS står sig över mycket olika vävnader och individer analyserade författarna mänskliga dorsolaterala prefrontala cortexprover från tre donatorer. Här presterade CiCLoDS i nivå med eller bättre än specialiserade spatiala metoder som BayesCafe och BayesSpace, särskilt på ett svårt prov där de andra verktygen kämpade. Studiet lyfter också fram en "hybrid" användning: köra CiCLoDS först för att få stabila kluster och sedan mata in dessa i BayesSpace. Denna warm‑start‑strategi ökade den övergripande noggrannheten och producerade hjärnlager‑mönster som bäst matchade expertannoteringar, vilket visar att CiCLoDS både kan stå på egen hand och göra efterföljande probabilistiska modeller mer tillförlitliga.
Varför detta är viktigt för biologi och medicin
För icke‑specialister är huvudpoängen att CiCLoDS förvandlar överväldigande cellulära kartor till kortfattade, biologiskt meningsfulla sammanfattningar. Istället för att arbeta med tusentals brusiga mätvärden får forskare en hanterbar lista med gener och tydliga spatiala kluster som speglar verklig vävnadsorganisation—metabola zoner i levern, blodkärl och deras nischer, samt lagerstrukturer i hjärnan. Eftersom genbudgeten styrs av användaren och beräkningarna är lätta, kan CiCLoDS hjälpa till att utforma målinriktade genpaneler för framtida experiment, vägleda tolkningen av komplexa spatiala dataset och ge robusta startpunkter för mer avancerad modellering. I en tid där flaskhalsen inte längre är datainsamling utan förståelse, lovar verktyg som CiCLoDS att göra högdimensionella vävnadskartor både praktiska och insiktsfulla.
Citering: Wang, N., He, Y., Ray, E. et al. CiCLoDS: Joint cell clustering and gene selection for single-cell spatial transcriptomics. Sci Rep 16, 5356 (2026). https://doi.org/10.1038/s41598-026-39168-1
Nyckelord: spatial transkriptomik, cellklustring, val av genpanel, vävnadsarkitektur, analys på enkelcellsnivå