Clear Sky Science · sv
Nya markörgener för samtidig upptäckt av Salmonella, EHEC O157:H7 och Cronobacter
Varför detta spelar roll för vardaglig livsmedelssäkerhet
Från salladsblad till hamburgare och modersmjölksersättning kan de livsmedel vi litar på ibland hysa farliga bakterier. Tre av de mest oroande förövarna — vissa stammar av E. coli, Salmonella och en mindre känd bakterie kallad Cronobacter — kan orsaka allvarlig sjukdom, särskilt hos små barn och sårbara vuxna. Denna studie visar hur forskare använder massiva DNA-databaser och smarta laboratorietester för att upptäcka alla tre hoten samtidigt, snabbt och noggrant, innan förorenad mat når ditt bord.
Dolda faror i vanliga livsmedel
Matförgiftningar har ökat under det senaste decenniet, delvis drivet av globala leveranskedjor och volymen av processade och färdigförpackade livsmedel. EHEC O157:H7, en mycket toxiskt variant av E. coli, kan ge blodig diarré och njursvikt. Salmonella orsakar miljontals fall av matförgiftning varje år, och Cronobacter, även om den är mindre känd, kan vara dödlig för nyfödda, särskilt i samband med pulverbaserad modersmjölksersättning. Traditionella laboratoriemetoder fokuserar ofta på en organism i taget och kräver dagars odling, vilket fördröjer utredningar av utbrott och rutinmässig screening. Författarna ville ta fram snabbare DNA-baserade tester som kan flagga för dessa tre patogener tillsammans i ett enda, effektivt förfarande.
Att hitta ”streckkoder” i ett hav av DNA
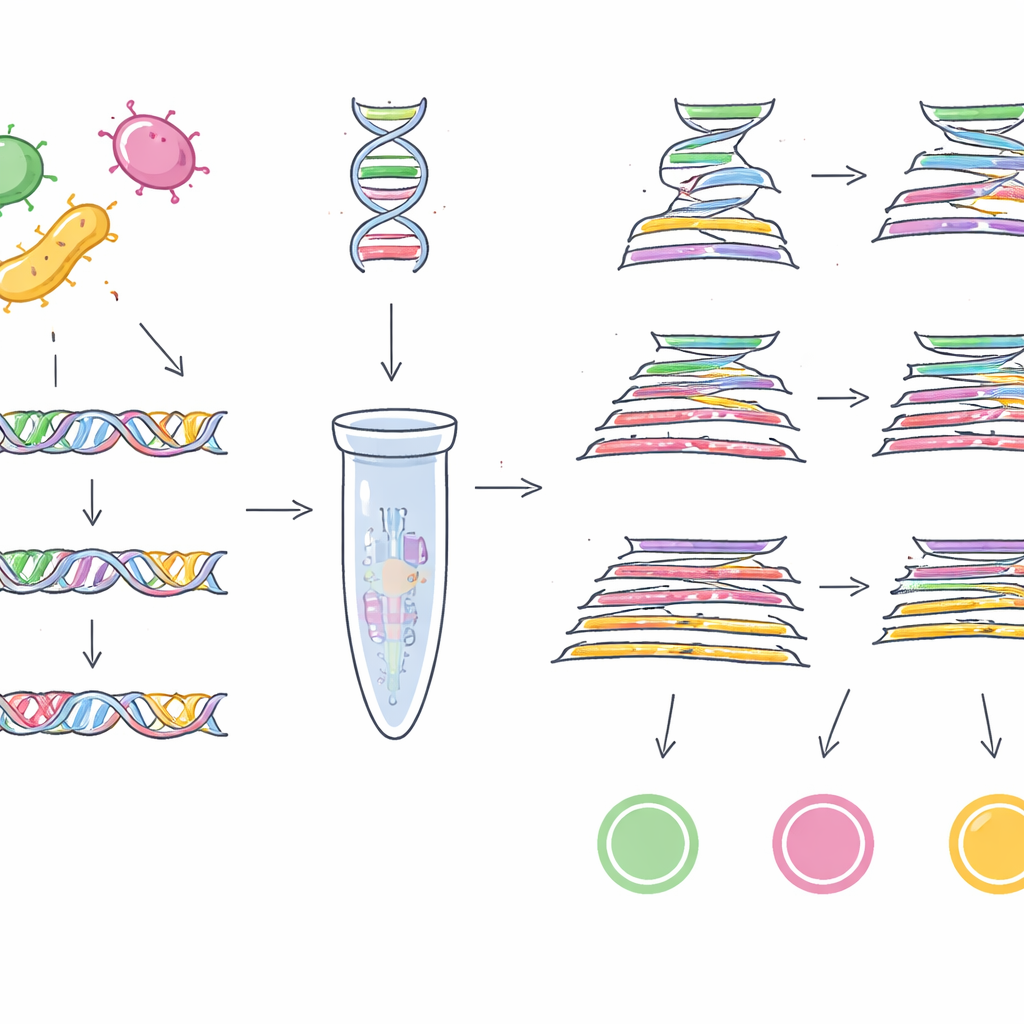
För att göra detta behövde teamet först tillförlitliga genetiska ”streckkoder” — korta DNA-sekvenser som finns i nästan alla stammar av en målbakterie men saknas hos andra. Istället för att söka i några få genom utnyttjade de en enorm offentlig samling på 1,46 miljoner bakteriegenom från 50 olika släkten. För EHEC O157:H7 jämförde de tusentals E. coli-genom och sållade igenom mer än 100 000 tilläggsgene-familjer för att hitta DNA-sekvenser som är unika för denna farliga undergrupp. Efter flera filtreringsrundor och korskontroller mot över en miljon icke-E. coli-genom landade de i en gen kallad z0340 som en mycket specifik markör för EHEC O157:H7. Med en liknande strategi på mer än en halv miljon Salmonella-genom och nästan en miljon andra bakteriegenom identifierade de en annan gen, sbcC, som en pålitlig markör för Salmonella-gruppen som helhet.
Att omvandla markörer till tester i verkligheten
Med dessa två nya streckkoder i hand — plus en Cronobacter-specifik gen, ygcB, som gruppen tidigare upptäckt — designade forskarna laboratorietester som kan upptäcka alla tre patogener samtidigt. De byggde multiplex PCR-assays, som fungerar som molekylära kopieringsmaskiner riktade mot specifika DNA-segment, och en mer känslig TaqMan kvantitativ PCR-version som mäter hur mycket mål-DNA som finns i realtid. När dessa tester utmanades med 23 stammar av de tre patogenerna och 100 stammar av andra vanliga bakterier identifierade de endast de avsedda målen varje gång, och visade 100 % specificitet. Den grundläggande multiplex PCR kunde detektera så lite som 1 pikogram DNA per mikroliter, medan TaqMan-versionen nådde ner till 0,5 pikogram, vilket indikerar hög känslighet.
Att pröva metoderna på mat
Laboratorienoggrannhet är bara användbar om testen fungerar i röriga, verkliga prov. För att kontrollera detta förorenade forskarna avsiktligt sallad, malet kött och pulverbaserad modersmjölksersättning med kända mängder EHEC O157:H7, Salmonella eller Cronobacter. Efter standardiserade berikningssteg för att låta eventuella bakterier multiplicera tillämpade de sina multiplex PCR- och TaqMan qPCR-assays. I samtliga fall upptäckte metoderna den införda patogenen korrekt och gav inga falska larm i negativa kontroller. Prestandan var konsekvent över alla tre livsmedelstyper, vilket tyder på att fett, växtkomponenter eller komplexa ingredienser inte märkbart störde detektion.
Begränsningar och framtida förbättringar
Trots de starka resultaten påpekar författarna att deras valideringspanel fortfarande representerar endast en liten del av den mikrobiella mångfald som finns i naturen. Till exempel testade de endast en EHEC O157:H7-stam i laboratoriet, även om deras genombaserade screening omfattade tiotusentals sådana stammar. De arbetade också med relativt höga nivåer av kontaminering jämfört med de extremt låga bakteriemängder som ändå kan orsaka sjukdom. Framtida arbete behöver testa många fler verkliga isolat, undersöka naturligt kontaminerade livsmedel och lägga till interna kontroller för att skydda mot ämnen i mat som kan hämma DNA-amplifiering.
Vad detta betyder för konsumenter
I praktiska termer visar denna studie att noggrant utvalda DNA-streckkoder kan låta livsmedelslaboratorier screena efter flera högriskpatogener samtidigt, med hög noggrannhet och på kortare tid än traditionella kulturbaserade metoder. Genom att utvinna data från miljoner genom identifierade forskarna tre genetiska signaturer — en för EHEC O157:H7, en för Salmonella och en för Cronobacter — som verkar vara både mycket specifika och stabila. De resulterande testerna kan stärka rutinövervakningen av livsmedel som sallad, kött och modersmjölksersättning och upptäcka kontaminering tidigare och mer tillförlitligt. Utöver dessa tre patogener kan samma genom-först-tillvägagångssätt användas för att designa snabba tester för många andra farliga mikrober och erbjuda ett kraftfullt nytt verktyg för att göra den globala livsmedelsförsörjningen säkrare.
Citering: Zhang, H., Xiong, P., Lu, Z. et al. Novel marker genes for simultaneous detection of Salmonella, EHEC O157:H7, and Cronobacter. Sci Rep 16, 9362 (2026). https://doi.org/10.1038/s41598-026-38990-x
Nyckelord: födoämnesburna patogener, multiplex PCR, genomiska markörer, Salmonella och EHEC, Cronobacter-detektion