Clear Sky Science · sv
Ny konvolutionsneural nätverk för bakterieidentifiering i konfokala mikroskopidata
Varför det är viktigt att upptäcka mikrober snabbare
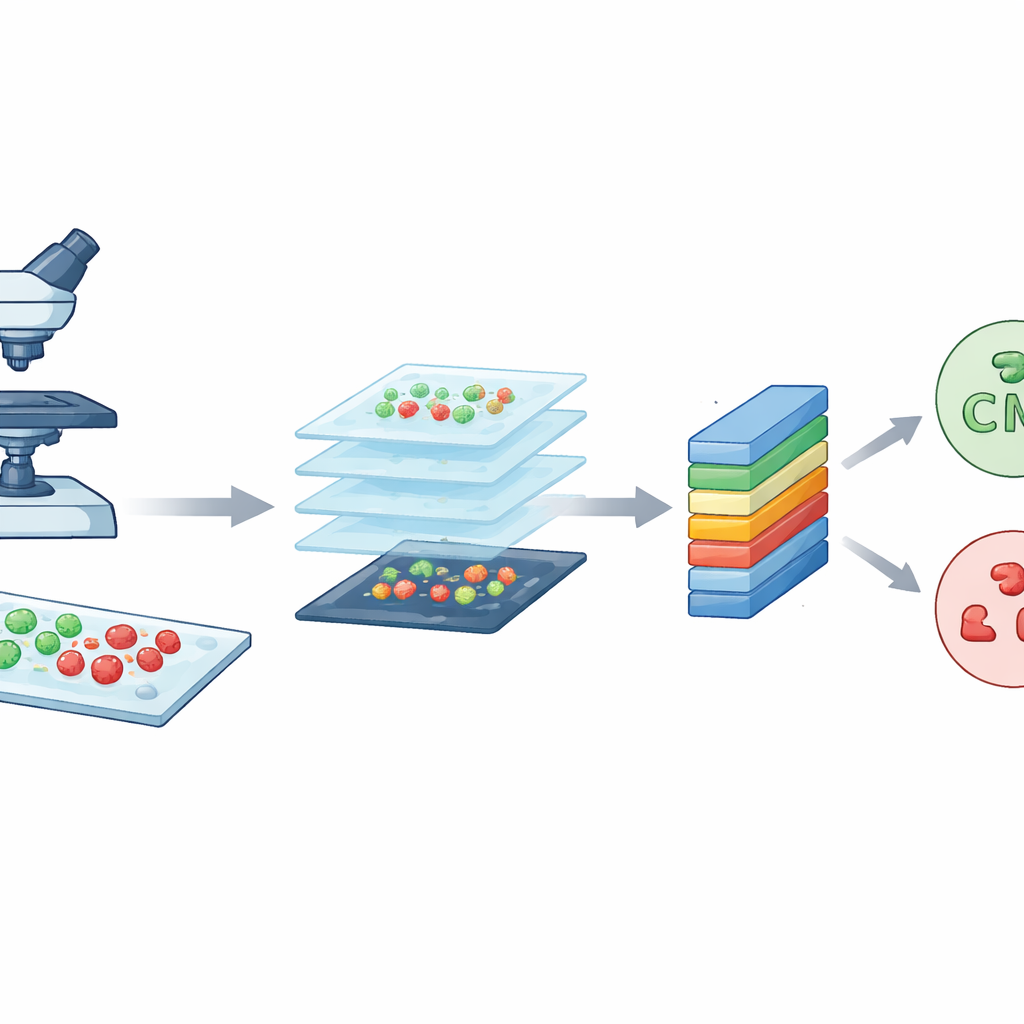
När läkare försöker fastställa vilka bakterier som orsakar en infektion är tid en kritisk faktor. Traditionella laboratorietester kan ta många timmar eller till och med dagar, och de kräver högt utbildade experter som granskar mikroskopbilder med ögat. Denna studie presenterar ett nytt datorvisionssystem, kallat CM-Net, som automatiskt kan läsa specialiserade mikroskopbilder och snabbt skilja mellan två vanliga, medicinskt viktiga bakterier, samtidigt som det identifierar vilka celler som är levande eller döda. Arbetet pekar mot en väg för snabbare och mer tillförlitliga diagnostikmetoder som en dag skulle kunna användas på sjukhus och forskningslaboratorier världen över.
Att förvandla lysande mikrober till användbara bilder
Forskarna började med ett kraftfullt avbildningsverktyg känt som konfokalmikroskop med laserscanning. Enkelt uttryckt använder detta mikroskop en fokuserad laser och fluorescerande färgämnen för att få bakterier att glöda i olika färger beroende på om de är levande eller döda. Levande celler framträder som gröna, medan döda celler visas som röda. Genom att skanna igenom provet i mycket tunna lager bygger mikroskopet upp skarpa, detaljerade bilder av bakterierna på glasobjektglass. Teamet arbetade med två välkända arter som ofta orsakar sjukhusinfektioner: stavformiga Escherichia coli och runda Staphylococcus aureus. Dessa högkvalitativa bilder utgör råmaterialet som CM-Net måste lära sig att tolka.
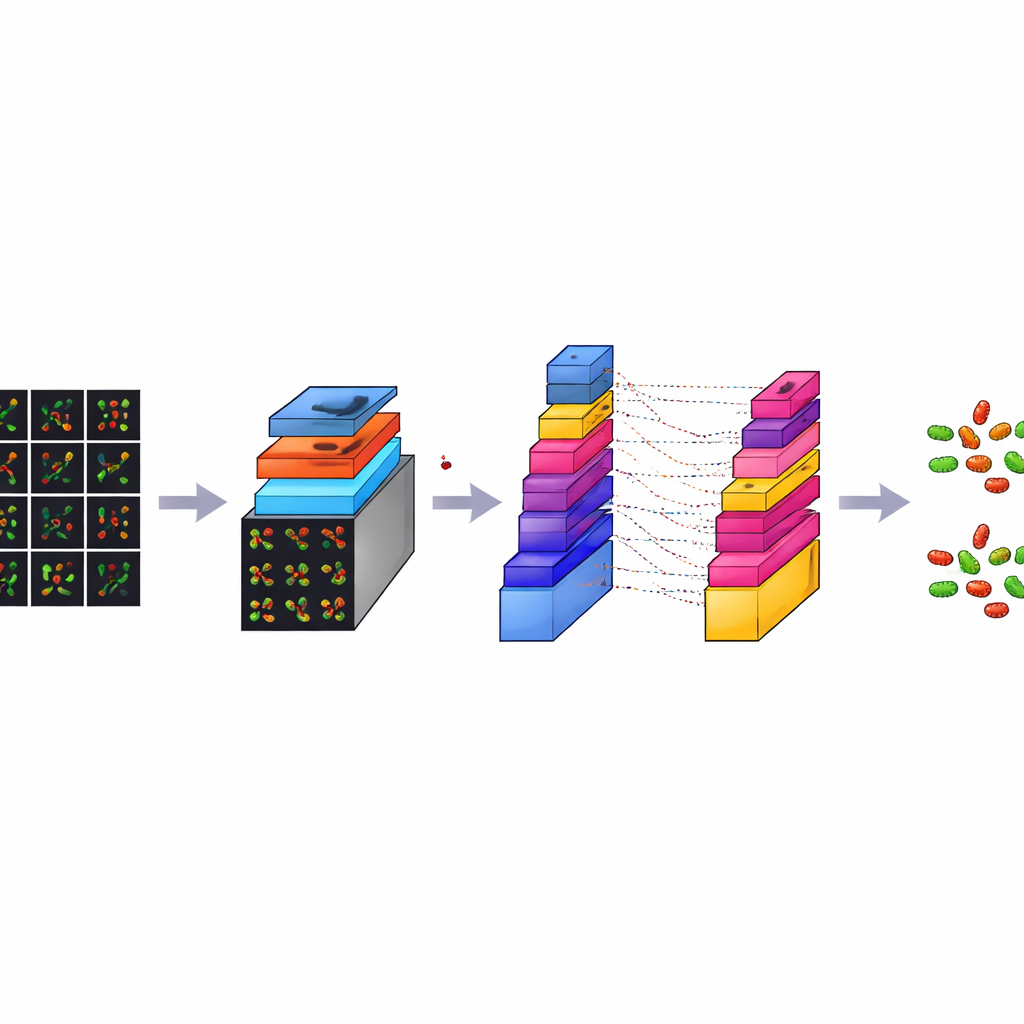
Att skapa många små kakor från stora bilder
Även om varje konfokal bild är rik på detaljer är den också mycket stor, ungefär 3000 gånger 3000 pixlar. Att träna en dator direkt på sådana enorma bilder skulle vara långsamt och kräva överdriven beräkningskapacitet. För att lösa detta skar teamet varje stor bild i många mindre kvadratiska kakor, vardera 224 gånger 224 pixlar, en standardstorlek inom bildanalys. Denna process, som kan ses som dataaugmentation, både minskar den tekniska bördan och multiplicerar antalet träningsexempel. Från en ursprunglig uppsättning av 300 bilder per bakterietyp genererade de totalt 7 066 kakor. Dessa kakor fångar lokala mönster av former, färger och texturer från olika områden på objektglassarna och ger modellen en varierad och balanserad uppsättning exempel att lära sig från.
Hur den digitala observatören lär sig se
CM-Net är en noggrant utformad djupinlärningsmodell byggd specifikt för bakteriemikroskopi, snarare än anpassad från allmänna fotodatabaser. Den är en typ av konvolutionsneuronätverk, en klass av program som är särskilt bra på att hitta mönster i bilder. CM-Net bearbetar varje kaka genom en serie steg. Tidiga steg letar efter enkla visuella ledtrådar som kanter och fläckar; djupare steg kombinerar dessa till mer komplexa mönster som särskiljer stavar från klot och levande från döda celler. Nätverket använder tekniker som batchnormalisering, vilket håller dess interna signaler välbalanserade, och en avklippt form av dess aktiveringsfunktion, som förhindrar extrem respons som kan destabilisera inlärningen. Senare lager kondenserar den extraherade informationen och fattar ett slutgiltigt beslut om bakterietyp och celltillstånd.
Bättre än populära färdiga modeller
För att bedöma CM-Nets prestanda tränade och testade författarna modellen 30 gånger, varje gång med en ny uppdelning av data i tränings- och testgrupper. De mätte noggrannhet, hur ofta modellen hade rätt totalt; sensitivitet, hur väl den upptäckte varje mål; specificitet, hur väl den undvek falska positiva; samt flera andra standardmått. CM-Net uppnådde i genomsnitt cirka 96 % noggrannhet, med sensitivitet och specificitet också runt 96 %, och en stark balans mellan de två klasserna. Det krävde dessutom färre interna parametrar och mindre minne än flera allmänt använda förtränade modeller, inklusive GoogLeNet, MobileNetV2, ResNet18 och ShuffleNet, samtidigt som det var snabbare att köra. Visualiseringsverktyg visade att CM-Net fokuserar sin uppmärksamhet på själva bakteriekropparna i bilderna snarare än på slumpmässiga bakgrundsdetaljer, vilket stöder idén att det lär sig biologiskt meningsfulla ledtrådar.
Vad detta betyder för framtida laboratoriearbete
I vardagliga termer visar studien att ett specialbyggt djupinlärningssystem kan lära sig att «läsa» komplexa mikroskopbilder av bakterier på ett korrekt, effektivt sätt som ligger i linje med vad mänskliga experter värdesätter. För tillfället har CM-Net tränats på endast två bakteriearter och på data från en enda typ av mikroskop, så mer arbete krävs innan det kan användas som ett generellt diagnostiskt verktyg. Författarna planerar att utöka det till fler arter, olika celltillstånd och större, mer varierade dataset. Ändå tyder resultaten på att system som CM-Net så småningom skulle kunna hjälpa laboratorier att identifiera infektioner snabbare, vägleda behandlingsbeslut och öppna för automatiserad analys av mikrobiologi-experiment för användare utan specialiserad avbildningskompetens.
Citering: Al-Jumaili, A., Al-Jumaili, S., Alyassri, S. et al. Novel convolutional neural network for bacterial identification of confocal microscopic datasets. Sci Rep 16, 8123 (2026). https://doi.org/10.1038/s41598-026-38861-5
Nyckelord: bakteriebildklassificering, konfokalmikroskopi, djupinlärning, konvolutionsneuronätverk, medicinsk diagnostik