Clear Sky Science · sv
Genomsekvensering av Bacillus daqingensis och Alkalicoccus luteus avslöjar taxonomiska insikter och adaptiva mekanismer
Liv i salta miljöer
Från saltsjöar till alkaliska jordar trivs vissa mikrober i miljöer som skulle torka ut och döda de flesta andra livsformer. Denna studie dyker ner i DNA:t hos två sådana saltälskande bakterier för att förstå hur de överlever extrema förhållanden och för att klargöra var de faktiskt hör hemma i livets träd. Genom att jämföra deras genom i detalj visar forskarna att vad som tidigare antogs vara skilda bakteriella arter i själva verket är samma slags organism, och de avslöjar de molekylära knep dessa mikrober använder för att klara intensiv saltstress.
Varför dessa saltälskare är viktiga
Bakterierna i centrum för detta arbete namnattes ursprungligen Bacillus daqingensis och Alkalicoccus luteus. Båda isolerades från salta, alkaliska miljöer som sodasjöar och saltsjordar, där det mesta liv har svårt att överleva. Forskare misstänkte att Bacillus daqingensis kanske i själva verket tillhör släktet Alkalicoccus, men dess fullständiga genomsekvens saknades, vilket lämnade dess officiella status i limbo. Genom att sekvensera och analysera de kompletta genomen hos dessa mikrober och jämföra dem med närbesläktade arter, ämnade författarna att lösa detta taxonomiska pussel och samtidigt ta reda på hur medlemmar av släktet Alkalicoccus klarar sig under så hårda förhållanden.
Läsning och jämförelse av mikrobiella genom
Teamet odlade bakterierna i laboratoriet, extraherade deras DNA och sekvenserade det med höggenomströmningsmetoder. De sammanfogade sedan de miljontals små DNA-fragmenten till nästan kompletta genomkartor och kontrollerade deras kvalitet. Både Bacillus daqingensis och Alkalicoccus luteus visade sig ha liknande stora genom på cirka 3,4 till 3,5 miljoner baspar, med nästan identiskt genetiskt innehåll och mycket hög fullständighet. En viktig genetisk markör, den 16S rRNA-genen, var i praktiken densamma i båda organismerna: en jämförelse visade 99,8 procent identitet mot tidigare laboratoriemätningar och, avgörande nog, var 16S-sekvenserna från de två stammarna en perfekt 100 procentig överensstämmelse med varandra.
Avkodning av överlevnad i salt och stress
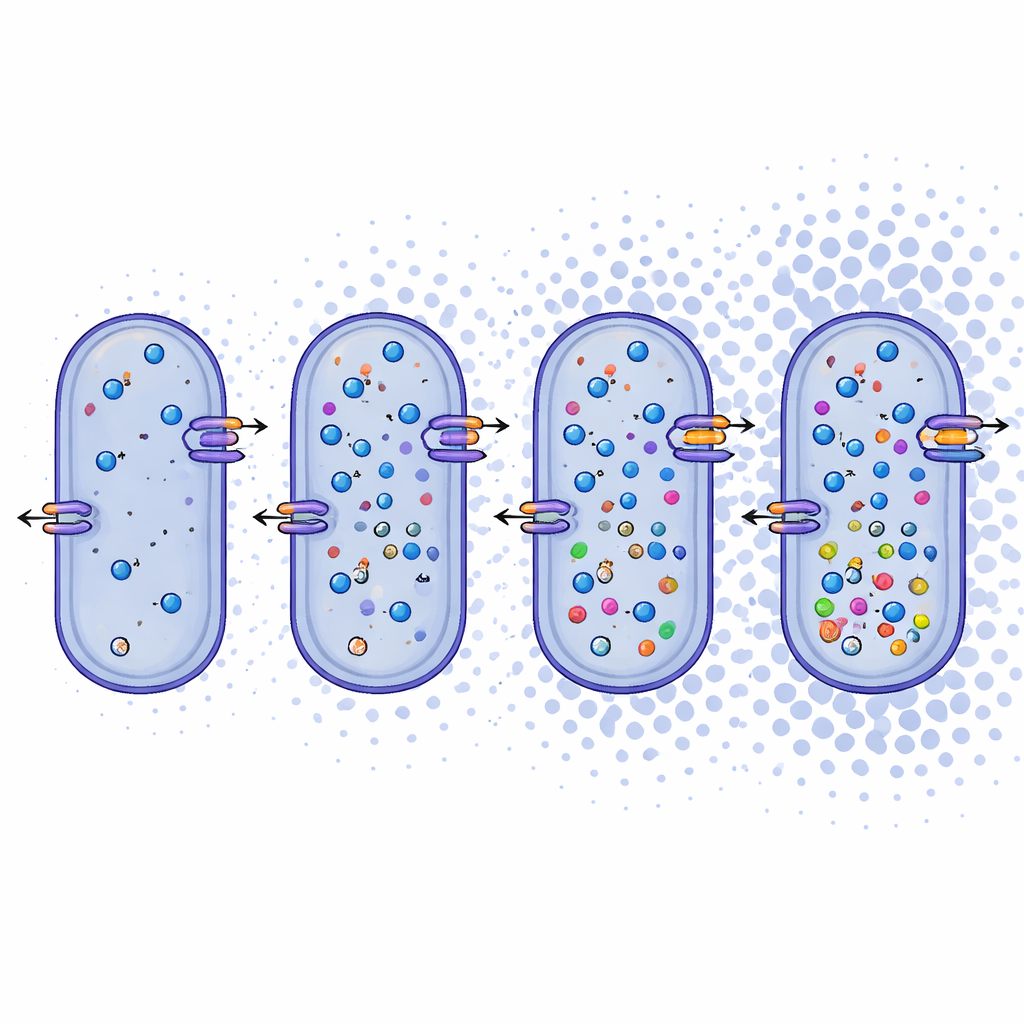
Bortom namnen undersökte forskarna vad genomen avslöjar om hur dessa mikrober försörjer sig. De fann att Bacillus daqingensis och samtliga undersökta Alkalicoccus-arter delar kärnmetaboliska vägar, inklusive vanliga rutter för nedbrytning av socker och en modifierad cykel kallad glyoxylatshunten som hjälper till att bevara kol vid stress. Mest slående är att genomen bär på ett rikt verktygslåda för att hantera hög salthalt. Bakterierna verkar använda två kompletterande taktiker: ”salt-in”-system som flyttar oorganiska joner som natrium och kalium över cellmembranet, och ”salt-out”-system som bygger upp eller importerar små organiska molekyler, såsom betain, ectoin och vissa aminosyror, vilka fungerar som inre puffrar mot uttorkning. Gener för jontransportörer, antiportare och biosyntes av dessa kompatibla osmolytter finns över hela släktet, vilket pekar på en robust, flexibel respons mot osmotisk stress.
Bevisa vem som är vem
För att avgöra den taxonomiska frågan jämförde författarna hela genomer med flera numeriska mått som nu är standard inom mikrobiell systematik. Average nucleotide identity (ANI) mäter hur lika DNA-sekvenserna är över genomet, medan average amino acid identity (AAI) gör samma sak på proteinnivå. Mellan Bacillus daqingensis och Alkalicoccus luteus nådde ANI 98,2 procent och AAI 98,5 procent — långt över de vanliga gränser som används för att definiera samma art och även samma släkte. Fylogenetiska träd byggda från många gener, tillsammans med jämförelser av delade proteinkluster, visade att dessa två stammar grupperar tätt tillsammans och delar fler genkluster med varandra än med någon annan Alkalicoccus-art. Traditionella egenskaper som cellform, fettsyraprofiler och nyckelbiokemiska reaktioner var också i huvudsak identiska mellan dem.
Vad detta betyder för mikrobiella namn
Sammanvägt pekar alla bevislinjer mot att Bacillus daqingensis inte representerar en distinkt bakterieform. Istället tillhör den släktet Alkalicoccus och är samma art som Alkalicoccus luteus, tidigare känt som Bacillus luteus. Författarna föreslår formellt den nya kombinationsbeteckningen Alkalicoccus daqingensis och behandlar den tillsammans med det äldre Bacillus-namnet som senare synonymer till Bacillus luteus/Alkalicoccus luteus. För icke-specialister är slutsatsen att noggrann genomsekvensering kan avslöja när olika etiketter används för i praktiken samma mikroba, vilket hjälper till att städa upp namnsystemet. Samtidigt betonar arbetet hur dessa saltälskande bakterier förlitar sig på en kombination av jonpumpar och skyddande molekyler för att överleva i miljöer som annars skulle vara för salta för liv.
Citering: Narsing Rao, M.P., Wang, Kk., Zhu, Ky. et al. Genome sequencing of Bacillus daqingensis and Alkalicoccus luteus reveals taxonomic insights and adaptive mechanisms. Sci Rep 16, 9720 (2026). https://doi.org/10.1038/s41598-026-38640-2
Nyckelord: halofila bakterier, genomsekvensering, mikrobiell taxonomi, anpassning till saltstress, Alkalicoccus luteus