Clear Sky Science · sv
Automatiserad och robust icke-rigid registrering av sekventiella mikroskopiska snitt med PiCNoR
Se vävnader i 3D utan att förlora detaljerna
Modern biologi förlitar sig ofta på att omvandla tunna vävnadsskivor till kompletta 3D-bilder av organ och hjärnor. Men när varje mikroskopiskt snitt skärs, färgas och avbildas kan det tänjas, slitas eller förskjutas. Om dessa snitt inte är korrekt uppradade kan den resulterande 3D-bilden bli missvisande. Denna artikel presenterar en ny datorbaserad metod kallad PiCNoR som hjälper forskare att linjera sådana bilder mer exakt och automatiskt, så att fina strukturer i embryo och hjärnor bevaras i 3D-rekonstruktioner.
Varför det är så svårt att rada upp snitten
För att bygga en 3D-vy avbildar forskare långa serier av ultratunna snitt tagna från samma vävnadsprov. I teorin borde varje skiva passa perfekt över den föregående, som kort i en prydligt staplad kortlek. I verkligheten kan varje snitt deformeras på lite olika sätt under skärning och färgning. Färger kan variera, delar kan tänjas ut och strukturer kan förskjutas. Traditionella ”rigida” justeringsmetoder antar att varje helt snitt bara förskjuts eller roteras, vilket ofta inte räcker. Mer flexibla, ”elastiska” metoder finns, men de kan vara långsamma, kräva noggrann fininställning av experter eller vara känsliga för bildens ljusstyrka, som kan variera mellan snitten.
Ett nytt sätt: lokala bitar som samarbetar
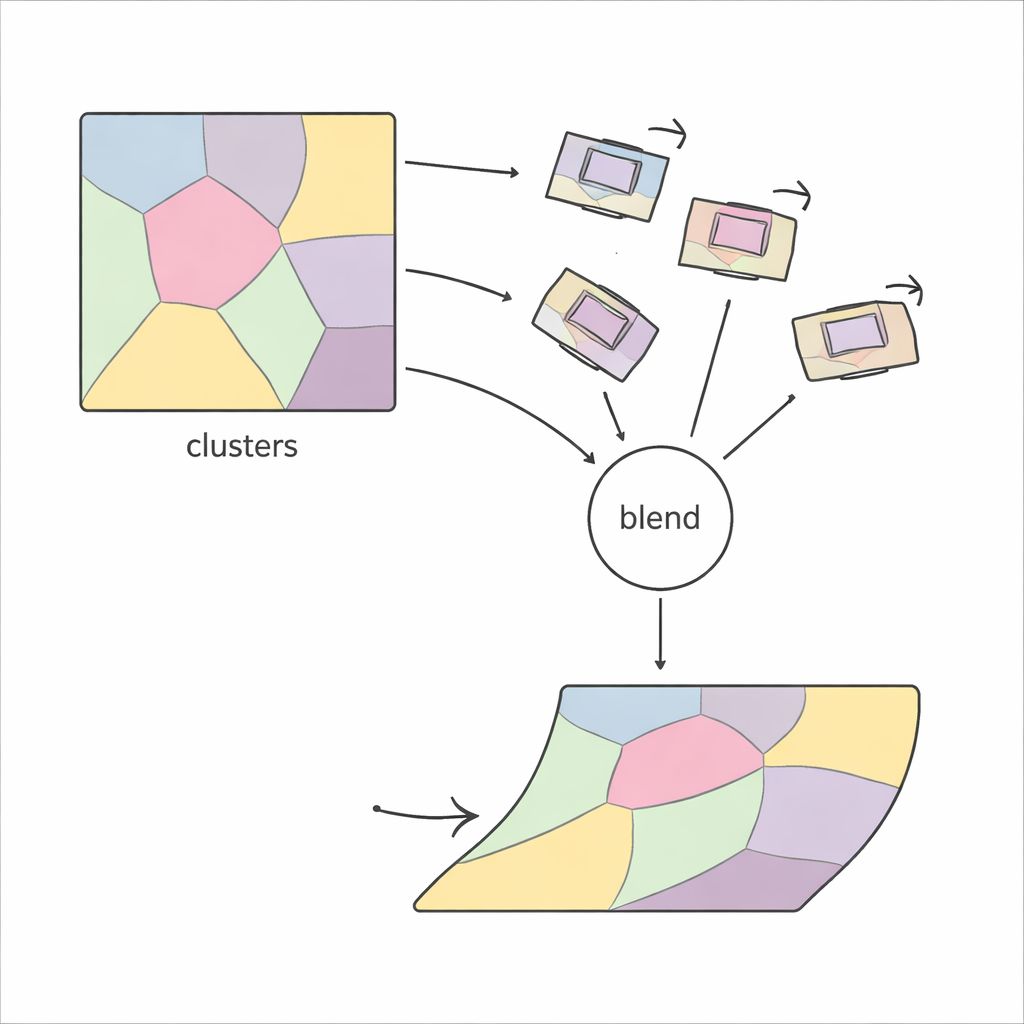
PiCNoR tar ett annat, mer lokalt grepp om problemet. Istället för att försöka böja hela bilden på en gång delar metoden först upp varje snitt i många regioner baserat på bildens mönster av särdrag. Inom varje region hittar metoden matchande punkter mellan två intilliggande snitt med robusta detektorer och uppskattar hur den regionen måste rotera och förskjutas för att linjeras upp. Dessa lokala rörelser kontrolleras sedan för rimlighet och kombineras varsamt, så att varje pixel i snittet får en rörelse som mjukt blandar information från angränsande regioner. Resultatet är en flexibel, ”icke-rigid” justering som ändå beter sig på ett kontrollerat och realistiskt sätt.
Låta data välja rätt komplexitet
En nyckelutmaning i alla regionbaserade metoder är att avgöra hur många regioner som ska användas: för få gör att metoden inte kan korrigera fina deformationer; för många gör den instabil och långsam. Tidigare angreppssätt förlitade sig ofta på prov och fel, där man upprepade gånger kontrollerade resultatets visuella kvalitet. PiCNoR undviker denna manuella justering genom att använda ett statistiskt verktyg kallat Bayesian information criterion, som automatiskt balanserar mängden detaljer mot risken för överanpassning. I praktiken innebär detta att algoritmen kan bestämma själv hur många regioner som behövs för ett givet dataset, utan mänsklig övervakning, vilket sparar tid och minskar bias.
Hålla resultaten tillförlitliga och effektiva
Inte alla uppskattade lokala rörelser är pålitliga—vissa kan vara förvrängda av brus eller dåliga matcher. PiCNoR hanterar detta genom att representera varje region som en nod i en graf, där intilliggande regioner påverkar varandra. Rörelser som ser orealistiska ut vad gäller rotation eller förskjutning ersätts med ett viktat medelvärde av mer tillförlitliga rörelser intill. En kompakt matematisk representation hjälper till att kombinera dessa rörelser effektivt. Slutligen beräknas varje pixels förflyttning som en sannolikhetsviktad blandning av regionernas rörelser, vilket säkerställer att övergångarna mellan regioner förblir jämna, utan plötsliga knölar eller veck i vävnaden.
Bevisa att det fungerar på verkliga biologiska data
Forskarna testade PiCNoR på tre mycket olika dataset: humana embryosnitt från Kyoto-samlingen, en elektronmikroskopisk stapel av ett bananfluganervkordon och en ny ljusmikroskopisk stapel från hippocampus i råtthjärnan. I dessa exempel gav PiCNoR konsekvent bättre överlappning mellan snitten än standardmetoder som är rigida och många av de vanligt använda icke-rigida metoderna. Den bibehöll kontinuiteten hos känsliga strukturer i 3D-vyer och undvek de överdrivna deformationer som ibland ses med andra verktyg. Viktigt är att den gjorde detta med färre lokala regioner än vissa konkurrenter och med beräkningskostnader som förblev praktiska för stora staplar.
Vad detta betyder för framtidens 3D-mikroskopi
För icke-specialister är slutsatsen att PiCNoR erbjuder ett mer pålitligt sätt att omvandla staplar av 2D-mikroskopbilder till trogna 3D-rekonstruktioner. Genom att automatiskt välja hur detaljerad justeringen bör vara och genom att skydda mot dåliga lokala korrigeringar bevarar metoden vävnadens verkliga former samtidigt som den håller bearbetningstiden rimlig. Detta gör det enklare för biologer och patologer att lita på vad de ser i 3D, vare sig de studerar hur ett embryo utvecklas eller hur hjärnceller är ordnade, och lägger grunden för mer exakt, automatiserad analys av komplexa mikroskopiska dataset.
Citering: Adi, P.M., Shabani, H. & Mansouri, M. Automated and robust nonrigid registration of serial section microscopic images using PiCNoR. Sci Rep 16, 7559 (2026). https://doi.org/10.1038/s41598-026-38548-x
Nyckelord: 3D-mikroskopi, bildregistrering, hjärnavbildning, histologi, icke-rigid justering