Clear Sky Science · sv
Cancerklassificering med radiomik i kontrollerade prekliniska modeller
Avläsa cancer från skanningar och blod
Modern cancervård förlitar sig i ökande grad på datorer för att sålla i medicinska bilder och laboratorietester efter mönster som människor har svårt att upptäcka. Denna studie ställer en enkel men viktig fråga: om vi vill avgöra vilken typ av cancer en patient har, är det bättre att läsa ut dold information från deras skanningar eller från deras blod? Genom noggrant kontrollerade experiment på möss jämförde forskarna dessa två angreppssätt direkt för att se vilket som ger mer tillförlitliga svar.
Vad det innebär att göra ett ”virtuellt biopsi”
Radiomik är en snabbt växande teknik som behandlar varje medicinsk skanning som en rik datakälla istället för bara en bild. Särskild programvara går igenom tredimensionella CT-bilder av en tumör och omvandlar dem till hundratals numeriska egenskaper som beskriver dess form, ljusstyrka och finfördelade textur. I princip kan dessa mönster återspegla tumörens biologi på ett sätt som liknar en biopsi, men utan nålar eller kirurgi — ett så kallat ”virtuellt biopsi”. Förespråkarna hoppas att radiomik kan hjälpa till att klassificera cancer, bedöma hur aggressiv den är och vägleda behandlingsval. Men det finns bekymmer: resultaten kan vara svåra att reproducera, lätt förväxlas av tekniska snedheter och svåra för läkare att tolka.
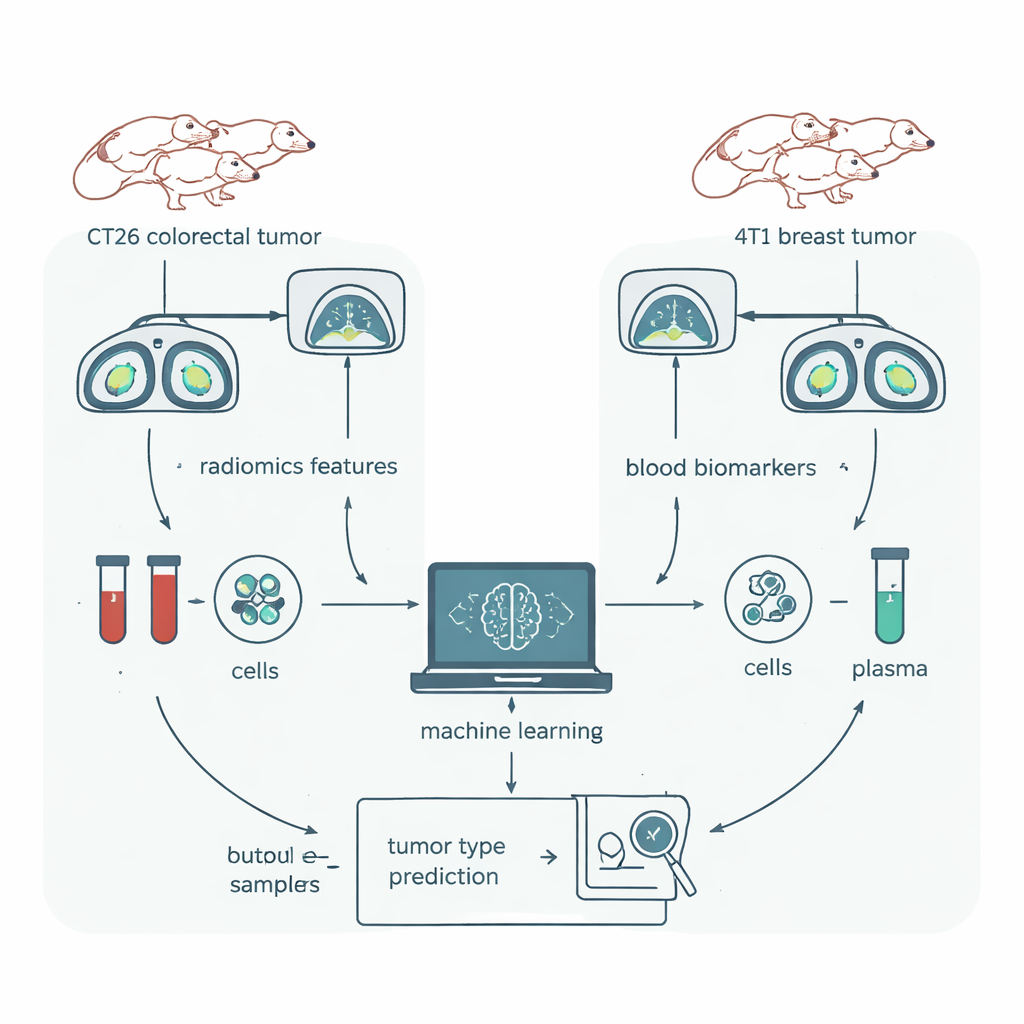
Ett rättvist huvud‑mot‑huvud‑test i möss
För att ge radiomik ett rigoröst test vände sig teamet till en modell med möss där nästan allt kunde kontrolleras. Grupper av genetiskt identiska möss fick implantation av en av två tumörtyper: CT26, en modell för kolorektal cancer, och 4T1, en modell för bröstcancer. Alla djur var av samma stam, kön och liknande ålder, hölls i samma miljö och skannades i samma CT‑maskin. Tumörerna ritades noggrant ut i 3D‑programvara och ett populärt radiomik‑paket extraherade 1 409 numeriska egenskaper från varje skanning. Parallellt tog forskarna blod från samma djur och mätte immuncellstyper och dussintals proteiner — biomarkörer som deras tidigare arbete redan visat kunde särskilja dessa cancermodeller nästan perfekt.
Komprimera tusentals bilddetaljer till en användbar signal
De flesta av de råa bildegenskaperna visade sig vara ovidkommande: vissa varierade knappt mellan mössen och många var nästan duplicerade. Efter flera rundor av statistisk filtrering återstod endast 18 icke‑redundanta radiomiska egenskaper, som huvudsakligen beskrev subtila texturmönster snarare än enkel storlek eller form. Teamet använde sedan en standardmetod inom maskininlärning, Random Forest, för att se hur väl dessa raffinerade bildegenskaper kunde skilja de två tumörtyperna åt. De använde också visualiseringsverktyg för att undersöka om data naturligt bildade separata kluster för varje cancertyp utan att känna till etiketterna i förväg.
Blodsignaler slår bildsignaler
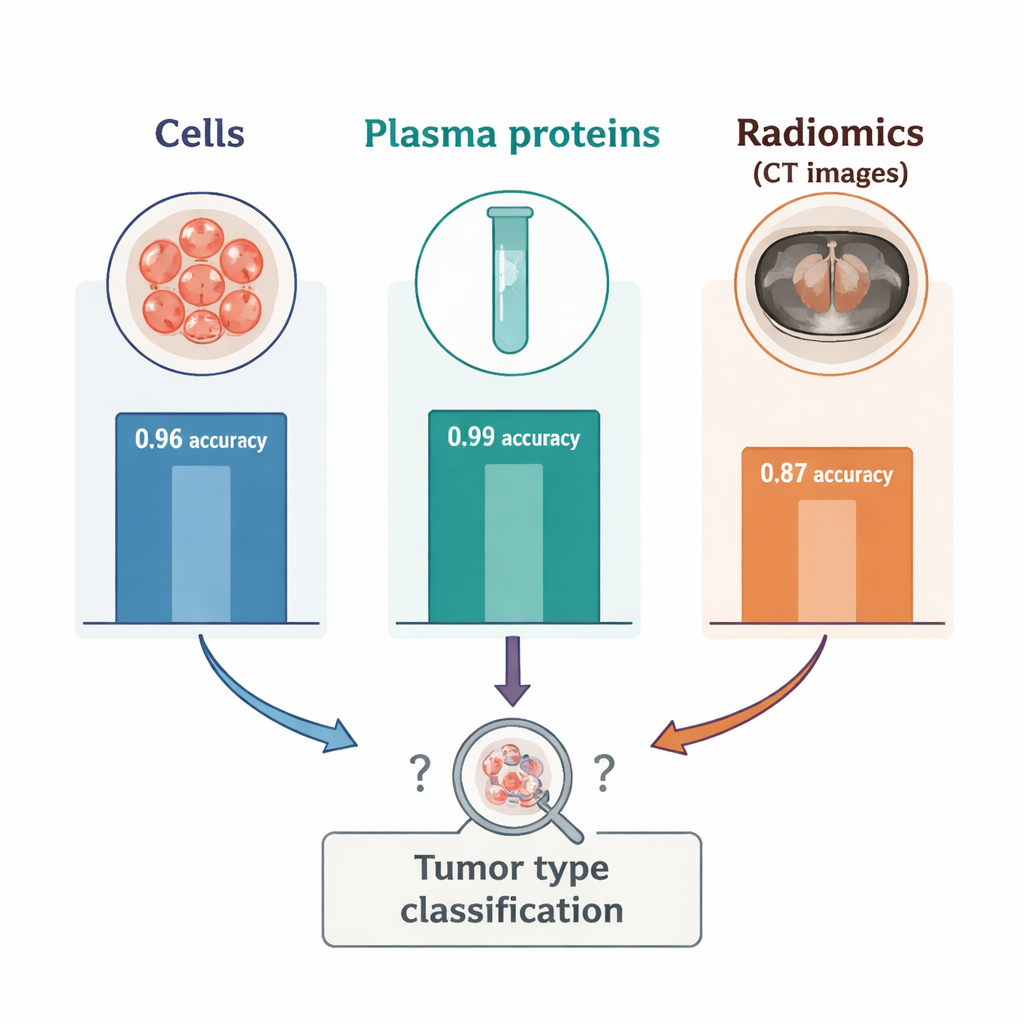
Kontrasten mellan blod och bildgivning var slående. När forskarna reducerade blodcell- och plasmaproteindata till två dimensioner bildade de två tumörtyperna tydligt separerade kluster, vilket bekräftade att blodet fångade starka, tumörspecifika signaler. I radiomikdatan framträdde dock tre blandade kluster, som vardera innehöll en blandning av de två cancerformerna och antydde att andra, okända faktorer formade bilderna. I övervakade tester klassificerade radiomik ensamt tumörtyp med en noggrannhet på cirka 87 procent — bra, men märkbart sämre än 96 procent från immuncellsräkningar och 99 procent från plasmaproteiner. Att lägga till radiomik till blodmarkörerna förbättrade inte prestandan; i vissa kombinationer minskade det något noggrannheten. En ytterligare experiment visade att användning av endast en liten sfärisk region inuti tumören, i stället för att rita hela massan, gjorde att radiomiken presterade ännu sämre, vilket understryker hur känsliga dessa egenskaper är för hur tumören avgränsas på skanningen.
Vad detta betyder för framtida cancertester
För en lekman är slutsatsen tydlig: medan avancerad bildanalys kan ge vissa användbara ledtrådar, presterade den i denna studie sämre än relativt enkla blodtester när det gällde att skilja mellan två cancertyper. Även i en strikt kontrollerad laboratoriemiljö med identiska möss och standardiserad avbildning verkade små tekniska skillnader och komplexiteten i bildbehandlingen sudda ut den radiomiska signalen. Författarna sluter sig till att radiomik ännu inte är redo att fungera som en fristående, högt pålitlig cancerklassificerare. I stället menar de att starkare standardisering av avbildning, bättre konturverktyg och tydligare kopplingar mellan bildmönster och underliggande biologi kommer att behövas innan virtuella biopsier på ett tillförlitligt sätt kan vägleda kliniska beslut tillsammans med, eller istället för, väletablerade blodbiomarkörer.
Citering: Drover, K., Davis, D.A.S., Gosling, K. et al. Cancer classification with radiomics in controlled preclinical models. Sci Rep 16, 6647 (2026). https://doi.org/10.1038/s41598-026-37757-8
Nyckelord: radiomik, cancerbiomarkörer, medicinsk avbildning, maskininlärning inom onkologi, blodtester för cancer