Clear Sky Science · sv
DNA-konjugering på funktionaliserade plastytor för sekventiell, iterativ sekvensering av enskilda molekyler
Lagra morgondagens data i små trådar
Föreställ dig att säkerhetskopiera dina foton, böcker eller vetenskapliga register i en form som kan bestå i århundraden och rymmas i en prick mindre än ett sandkorn. DNA — samma molekyl som bär våra gener — framstår som en stark kandidat för ultratät, långtidsbeständig datalagring. Denna artikel undersöker ett nytt sätt att ”parkera” DNA-data säkert på insidan av vanliga plastprovrör, och sedan läsa ut dem om och om igen utan att förstöra de ursprungliga molekylerna.
En ny sorts data-“tummivisare”
Dagens hårddiskar och flashminnen slits ut, och de rymmer långt mindre information per gram än vad DNA potentiellt kan göra. Forskare har redan visat hur digitala filer kan översättas till sekvenser av DNA-”bokstäver”. Men varje gång dessa DNA-strängar kopieras eller sekvenseras förbrukas en del av ursprungsmaterialet, ungefär som bläcket som bleknar när du fotokopierar en sida för många gånger. I denna studie gjorde författarna det enkla plast-PCR-röret — redan standard i biologiska laboratorier — till en återanvändbar fysisk lagringsenhet. De kemiskt fäste DNA-strängar med inbäddad data på rørets inre yta, så att DNA:t sitter fast medan kopior upprepade gånger görs och läses. 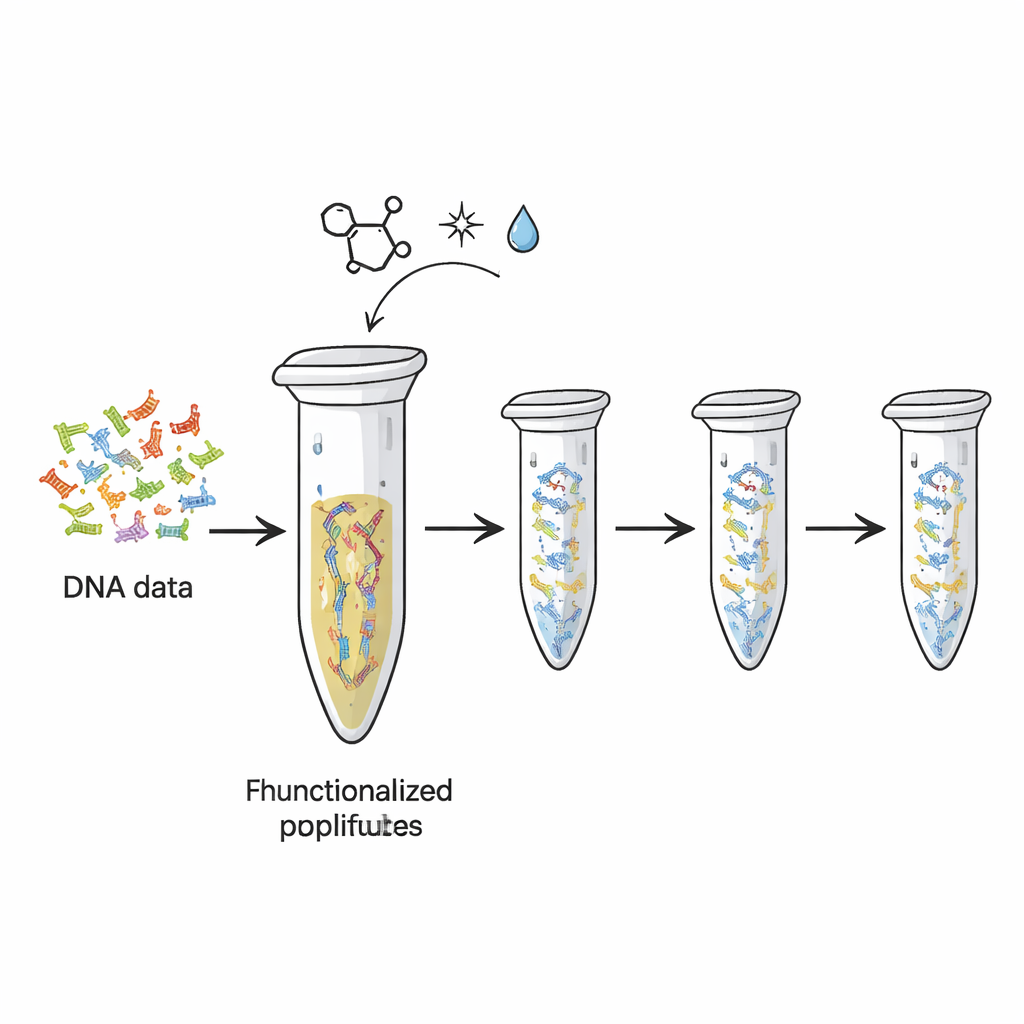
Klicka fast DNA på plast
Teamet förlitade sig på en typ av mycket specifik ”click-kemi” — en uppsättning reaktioner uppskattade för att de är snabba, pålitliga och skonsamma. Först lade de till särskilda kemiska svansar på ändarna av DNA-strängarna som representerar olika data-”filer”. Dessa svansar, baserade på en molekyl kallad TCO, är designade för att låsa fast vid matchande grupper (MTz) som har graftats på plastytan i provröret. När de möts bildar de en stabil kovalent bindning och limmar effektivt DNA:t mot plasten. Tester med ett kontroll-DNA-fragment visade att efter inkubation hade nästan allt DNA försvunnit från lösningen, vilket indikerar att det nu var immobiliserat på rörväggen. Plattformen kunde hålla i storleksordningen hundratals femtomol DNA, vilket pekar på god kapacitet för praktiska dataset.
Hämta digitala ”filer” på begäran
För att undersöka om detta ytbundna DNA fortfarande fungerade som ett användbart arkiv kodade forskarna text och annan data i en samling av cirka 15 000 korta DNA-strängar, grupperade i 18 ”filgrupper”. Varje grupp kunde selektivt kopieras med sitt eget par av primrar — korta startsekvenser som dirigerar kopieringsmaskineriet till rätt mål. Teamet utförde upprepade standard-PCR-reaktioner i samma rör, varje gång valde de en annan filgrupp att amplifiera. Efter varje körning tog de bort den kopierade DNA:n, rengjorde röret med enzymer som bryter ner kvarvarande produkter i lösningen, och gick vidare till nästa fil. Nanopore-sekvensering av det kopierade materialet visade att de flesta filgrupper återfanns med hög noggrannhet, och korskontaminering från tidigare körningar var mycket låg, vanligtvis omkring 1 procent eller mindre.
Hitta ett skonsammare sätt att läsa
Det fanns dock en hake: när de upprepade PCR i samma rör upp till 18 gånger minskade mängden återvunnet DNA stadigt. PCR förlitar sig på snabba upp- och nedkylningar, och författarna drog slutsatsen att de upprepade höga temperaturerna skadade det immobiliserade DNA:t eller dess förbindelse till plasten, även om kontrolltester antydde att DNA:t inte bara sköljdes av i lösning. För att lösa detta vände de sig till recombinase polymerase amplification (RPA), en nyare metod som fungerar vid en enda, relativt låg temperatur nära kroppstemperatur. Genom att använda RPA på nykomponerade DNA-belagda rör frågade de återigen alla 18 filgrupper i sekvens. Denna gång var avkastningen hög — omkring 60 ng/µL — och visade inte samma nedåtgående trend. Mönstret av vilka strängar som favoriserades eller missgynnades under kopiering överensstämde också väl med vad som sågs när DNA:t var fritt i lösning. 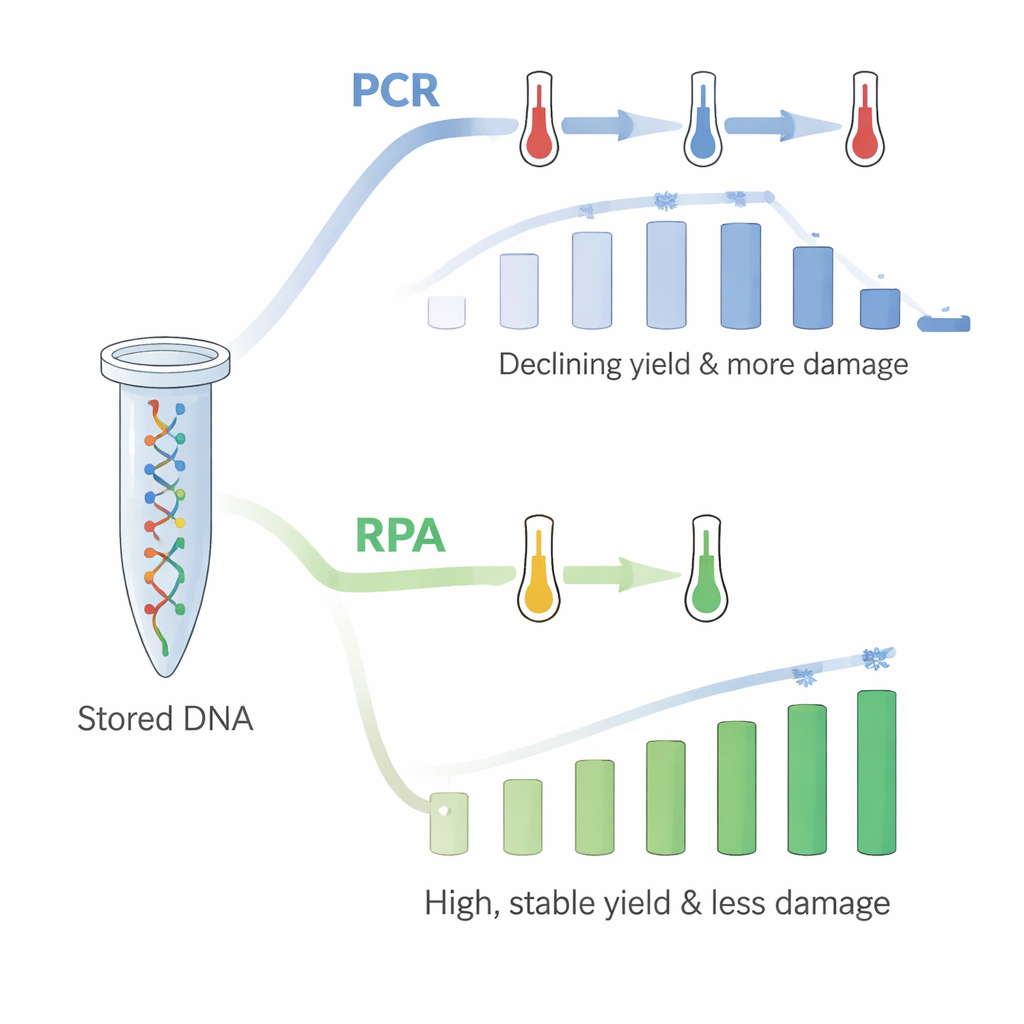
Mot portabel, långlivad DNA-minne
Genom att kombinera robust click-kemi med lågtemperaturkopiering av DNA pekar detta arbete på ett praktiskt sätt att förvandla enkla plastprovör till återanvändbara DNA-datakartridges. DNA:t förblir fysiskt låst vid röret, där det upprepade gånger kan frågas efter specifika ”filer” utan att förbruka de ursprungliga molekylerna, särskilt när man använder den skonsammare RPA-metoden. För icke-specialister är huvudbudskapet att DNA inte bara är livets kod — det kan också fungera som ett kompakt, hållbart lagringsmedium för digital information. Metoder som denna för oss närmare en framtid där dina långtidskopior kanske inte ligger på snurrande skivor, utan i noggrant designade molekyler som vilar tyst på en laboratoriehylla.
Citering: Roy, S., Ji, H.P. & Lau, B.T. DNA conjugation on functionalized plastic surfaces for sequential, iterative single molecule sequencing. Sci Rep 16, 6467 (2026). https://doi.org/10.1038/s41598-026-37575-y
Nyckelord: DNA-datalagring, click-kemi, konjugering på plastyta, recombinase polymerase-amplifiering, nanopore-sekvensering