Clear Sky Science · sv
Snabb, träningsfri kvantifiering och spårning av organoider med OrganoSeg2
Varför små laborativt odlade vävnader spelar roll
I laboratorier runt om i världen odlar forskare numera miniatyrversioner av mänskliga vävnader som kallas organoider. Dessa små, tredimensionella cellklumpar kan efterlikna hur riktiga organ eller tumörer beter sig, vilket gör dem till kraftfulla verktyg för att studera sjukdom och testa behandlingar. Men det finns en flaskhals: forskare kan samla tusentals mikroskopbilder i låg förstoring av organoider och ändå ha svårt att mäta hur var och en växer, förändrar form eller dör över tid. Denna artikel presenterar OrganoSeg2, en omarbetad programvara som omvandlar dessa enkla, grå bilder till rika, tillförlitliga mätningar av varje enskild organoid—utan att kräva artificiell intelligens‑träning eller dyra bildinställningar.
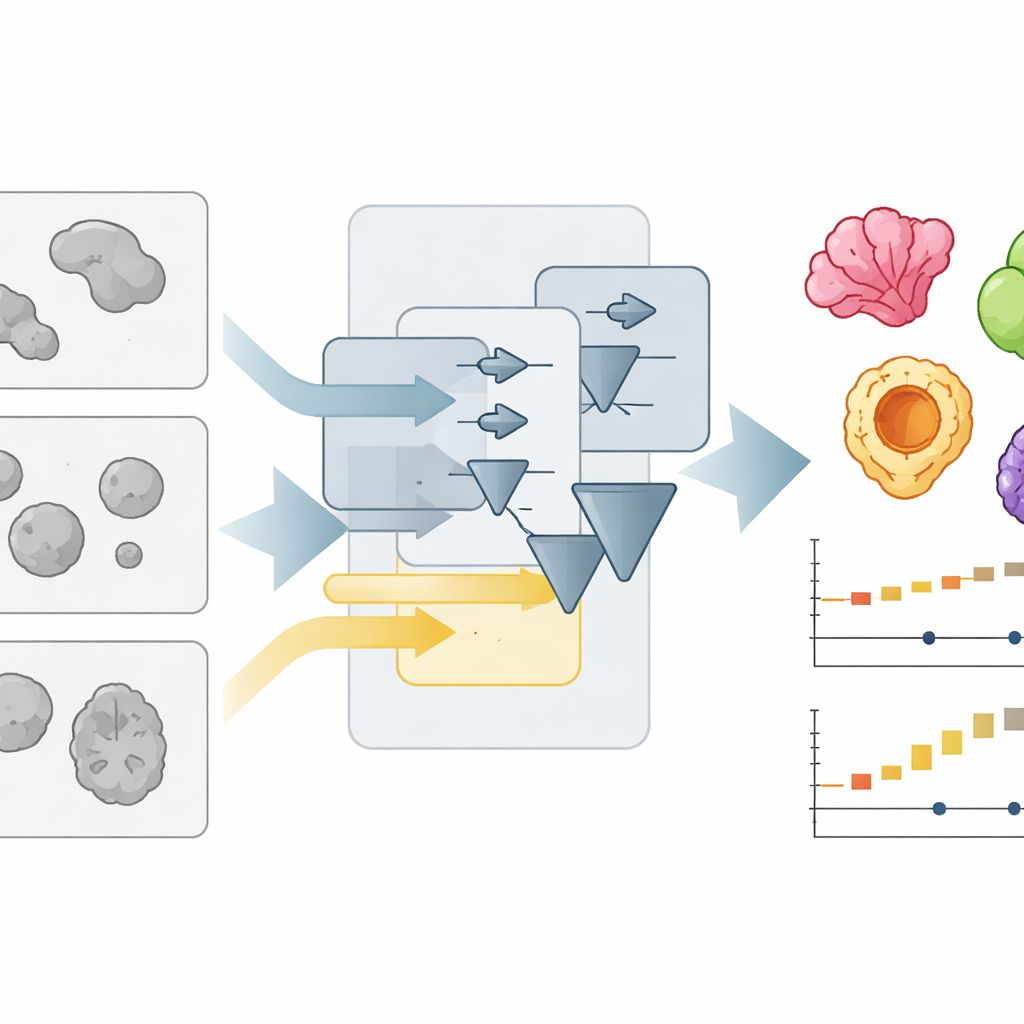
Ett nytt sätt att läsa trånga mikroskopbilder
Organoider avbildas vanligtvis med enkla brightfield‑mikroskop som visar dem som svaga, överlappande fläckar. Att automatiskt avgränsa varje fläck—"segmentera" bilden—är mycket svårare än det ser ut, särskilt när laboratorier använder olika odlingsformat, belysning eller objektiv. Författarna skapade tidigare OrganoSeg, ett program som klarade grundläggande segmentering men som blev långsamt och otympligt när bildsamlingarna växte till hundratals bilder. Med OrganoSeg2 byggde de om programvaran från grunden i ett modernt gränssnitt, förenklade intern kod och exponerade flera dolda inställningar så att användare kan finjustera hur programmet separerar organoider från bakgrund, delar på angränsande objekt och ignorerar artefakter i bildkanterna. Appen sparar nu dessa val som metadata så att analyser blir reproducerbara och delbara.
Snabbare arbete utan att tumma på detaljer
Förutom flexibilitet lade teamet stor vikt vid hastighet och användarupplevelse. I tidigare versioner beräknade programmet automatiskt varje möjlig mätning för varje organoid, även när bara några behövdes. OrganoSeg2 beräknar istället endast vad användaren väljer och organiserar relaterade beräkningar så att tidskrävande steg återanvänds effektivt. Det minskar också hur mycket information som ritas på skärmen, visar etiketter bara vid behov och lägger till tangentbordsgenvägar och interaktiva verktyg för snabb borttagning av skräp eller icke‑organoidobjekt. Dessa designval minskar vanliga operationer—som segmentering av bilder, visning av konturer och export av data—med ungefär en faktor tio, vilket gör det praktiskt att hantera stora, flisade bilder och långa tidsförloppsexperiment på en vanlig dator.
Slår high‑tech‑konkurrenter på verkliga data
För att testa hur väl OrganoSeg2 fungerar jämförde författarna det med flera andra segmenteringsverktyg, inklusive djupinlärningssystem som måste tränas på manuellt märkta exempel. De satte ihop bilduppsättningar från sex olika källor—såsom kolon, lunga, pankreas, hjärna och bröstorganoider, samt embryoidkroppar—där mänskliga experter redan hade spårat organoidernas gränser. Med en standardiserad noggrannhetspoäng som mäter hur mycket de automatiska konturerna överlappar de manuella, matchade eller överträffade OrganoSeg2 specialiserade verktyg i de flesta dataset och ledde tydligt fältet på utmanande bröstcancerbilder fulla av löst material och ovanligt formade organoider. Anmärkningsvärt nådde OrganoSeg2 denna prestanda utan att behöva tiotusentals träningsexempel och körde åtminstone lika snabbt som sina konkurrenter, även de baserade på artificiell intelligens.
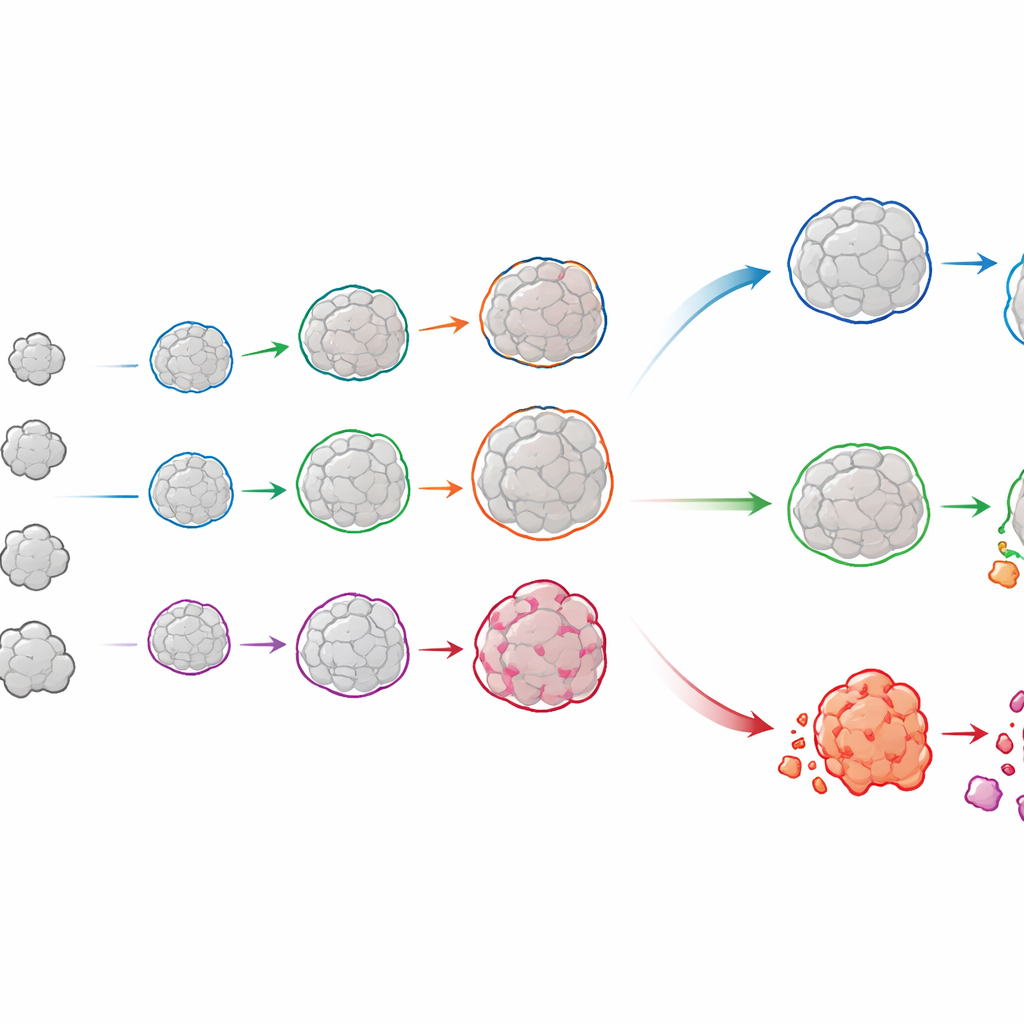
Följa varje organoids livshistoria
OrganoSeg2 gör mer än att rita konturer i enstaka ögonblicksbilder. Det kan alignera bilder tagna vid olika dagar och länka samma organoid över tid, och bygger därigenom en tillväxthistoria för var och en. När författarna tillämpade detta på organoider odlade direkt från patienters luminala brösttumörer såg de att individuella organoider sällan växte jämnt; många avstannade eller nådde platåer, vilket speglar hur riktiga tumörer innehåller en blandning av snabb‑ och långsamt växande regioner. Genom att passa dessa banor till en enkel tillväxtmodell kunde teamet kvantifiera både hur snabbt varje organoid expanderade och hur stor den sannolikt skulle bli. Jämförelser av dessa mönster mellan patienter visade att tumörer med liknande total tillväxt kan dölja mycket olika blandningar av underliggande beteenden—skillnader som kan vara viktiga för att förutsäga behandlingssvar.
Se cancerceller leva och dö under strålning
Programmet länkar också brightfield‑bilder med fluorescerande färgämnen som indikerar cellhälsa. I nya experiment utsatte författarna bröstcancerorganoider för stråldoser liknande de som används kliniskt och färgade dem med en levande‑cellsmarkör som lyser upp vid programmerad celldöd, samt en andra färg som visar döda celler vid slutlig tidpunkt. OrganoSeg2 använde brightfield‑bilden för att definiera organoidens form och mätte sedan de fluorescerande signalerna inom varje organoid över många dagar. Detta gjorde det möjligt för teamet att spåra, organoid för organoid, när strålning utlöste död och hur starkt. Några patienters organoider svarade knappt, medan andra visade hög känslighet även vid lägre doser, vilket understryker hur varierande tumörsvar kan vara.
Vad detta innebär för framtida forskning och vård
Sammantaget visar arbetet att noggrann, justerbar bildbehandling kan konkurrera med eller överträffa komplexa djupinlärningsmetoder för ett brett spektrum av organoidbilder, samtidigt som den förblir transparent och lätt att finjustera. OrganoSeg2 förvandlar enkla, lågförstorade filmer av organoider till detaljerade register över hur varje liten vävnad växer och överlever under olika förhållanden. För grundforskare erbjuder det ett robust sätt att dissekera den dolda mångfalden inom organoidkulturer. För cancerstudier i synnerhet öppnar det dörren för att använda patient‑härledda organoider inte bara för ja‑eller‑nej läkemedelsskärmar, utan för rika, tidsupplösta mätningar av tillväxt och celldöd som en dag kan hjälpa till att anpassa behandlingar mer precist.
Citering: Wells, C.J., Labban, N., Showalter, S.L. et al. Fast learning-free organoid quantification and tracking with OrganoSeg2. Sci Rep 16, 7928 (2026). https://doi.org/10.1038/s41598-026-37526-7
Nyckelord: organoider, bildanalys, cancerforskning, mikroskopi, strålningsrespons