Clear Sky Science · sv
Utveckling och preliminär utvärdering av realtids‑PCR‑tester för sex mjölksyrabakterier
Vänliga bakterier bakom vardagens livsmedel
Många av de livsmedel som fyller butikshyllorna — från yoghurt och ost till inlagda grönsaker och fermenterade grönsaker — får sin smak och sina möjliga hälsofördelar från vänliga bakterier som kallas probiotika. Men för att kunna använda dessa ”goda bakterier” säkert och pålitligt måste tillverkarna vara helt säkra på vilka bakteriearter som faktiskt finns i produkterna. Denna studie beskriver nya laboratorietester som snabbt och noggrant kan identifiera sex lovande probiotiska bakterier som används i livsmedel, och som hjälper till att överbrygga klyftan mellan modern mikrobiologi och de vardagslivsmedel vi äter.
Varför dessa probiotiska bakterier är viktiga
De sex bakterier som står i centrum för arbetet tillhör alla den bredare gruppen mjölksyrabakterier, som länge använts vid fermentering. Nyare forskning antyder att de kan göra mycket mer än att bara göra mjölk eller kål syrlig. Vissa stammar av Ligilactobacillus agilis och Ligilactobacillus salivarius kan hjälpa till att stå emot skadliga tarmbakterier, dämpa inflammation och stödja en sund tarmbarriär. Limosilactobacillus fermentum har kopplats till förbättrad blodtryckskontroll och antioxidantiska effekter i djurstudier. Lactobacillus johnsonii verkar bidra till att balansera tarmens mikrobiota på sätt som kan skydda flera organ. Pediococcus pentosaceus och Weissella cibaria visar potential för att sänka kolesterol, bekämpa förruttnelse och till och med stödja munhälsa. Med ett sådant spektrum av möjliga fördelar är livsmedelsindustrin angelägen om att använda dessa arter mer, men endast om de kan identifieras med säkerhet.
Utmaningen att skilja på snarlika mikrober
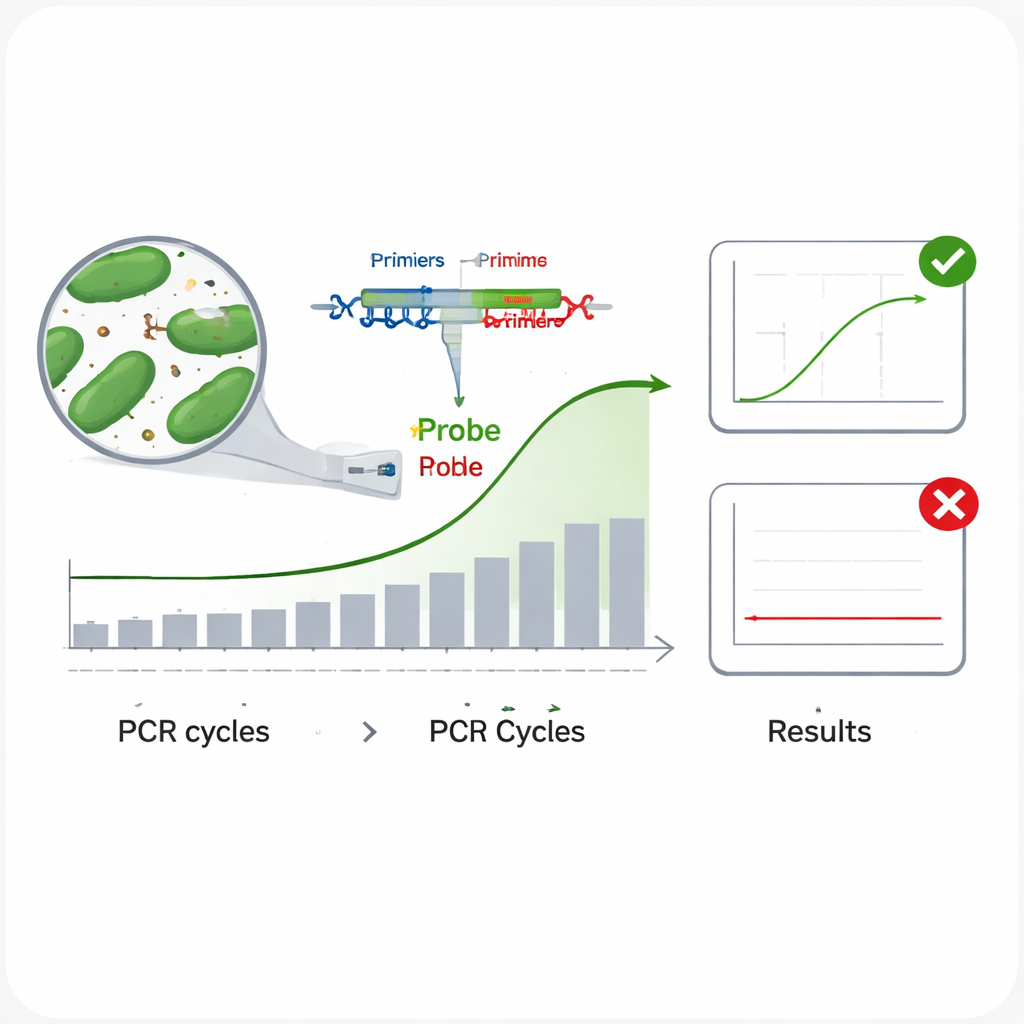
Traditionella metoder för att identifiera bakterier — att odla dem i labbet och göra biokemiska tester — är långsamma och arbetsintensiva. Moderna DNA‑baserade metoder, särskilt realtids‑PCR, går betydligt snabbare. Vid realtids‑PCR riktar sig korta DNA‑stycken kallade primrar och en fluorescerande probe mot ett unikt avsnitt av en mikrobs genetiska kod; när rätt mikroorganism finns närvarande upptäcker apparaten en ljussignal när DNA kopieras cykel efter cykel. Problemet är att nära släkt bakterier kan dela mycket likt DNA, så vanliga genetiska regioner som 16S rRNA‑genen ibland inte räcker för att skilja arter åt. Det kan leda till tester som missar målet (falskt negativa) eller reagerar på fel art (falskt positiva), vilket är oacceptabelt för märkning och säkerhet.
Design av skarpare molekylära ”streckkoder”
För att övervinna detta genomgick forskarna fullständiga genomsekvenser för att hitta korta DNA‑regioner som var både högt bevarade inom varje målarter och tydligt olika andra bakterier. För var och en av de sex probiotiska arterna utformade de ett matchat set av primrar och en probe med noggrant anpassad längd, basammansättning, smältpunkt och minimal benägenhet att veckas eller binda till varandra. Datorbaserade kontroller med BLAST‑databasen och sekvensjusteringsprogram bekräftade att de valda DNA‑regionerna var stabila inom arten men skilde sig från icke‑mål. Teamet arbetade sedan fram en standardiserad reaktionsblandning och ett uppvärmningsprogram så att alla tester kan köras under konsekventa och praktiska förhållanden i samma typ av realtids‑PCR‑maskin.
Sätta de nya testen på prov
Forskarna utvärderade därefter hur väl varje assay fungerade i praktiken. För att testa inklusivitet — om ett test kan upptäcka många olika stammar av samma art — körde de varje assay på flera DNA‑prover från dess målorganism. I samtliga fall gav alla testade stammar en tydlig amplifikationskurva, vilket tyder på låg risk att missa riktiga mål. För att kontrollera specificitet — att assayen ignorerar icke‑målade arter — utsatte de varje test för DNA från 13 andra tarmbakterier, inklusive närbesläktade mjölksyrabakterier och vanliga tarmmikrober som Escherichia coli. Ingen av dessa gav utslag, vilket indikerar mycket låg risk för falsklarm. Teamet undersökte också amplifikationseffektiviteten genom att köra en serie tiodubbelutspädningar av DNA och bekräftade att samtliga sex assay kopierade sina mål med ungefär 95–100 % effektivitet, nära idealet. Slutligen mätte de precision genom att upprepa körningar på två DNA‑nivåer och fann att små variationer mellan upprepningar och mellan separata experiment höll sig väl under accepterade gränser.
Vad detta betyder för framtidens livsmedel
Enkelt uttryckt har författarna byggt sex finjusterade DNA‑”fingeravtrycks”tester som snabbt, noggrant och pålitligt kan skilja viktiga probiotiska arter åt. De varnar visserligen för att bredare tester på fler stammar, fler icke‑målade arter och ytterligare PCR‑instrument fortfarande behövs innan rutinmässig industriell användning, men de tidiga resultaten är uppmuntrande. För konsumenter bidrar framsteg som dessa till att säkerställa att livsmedel som marknadsförs innehållande specifika probiotika verkligen innehåller rätt mikrober, vilket i sin tur stödjer ärlig märkning, bättre kvalitetskontroll och mer trovärdig forskning om hur dessa små samarbetspartner påverkar vår hälsa.
Citering: Li, SJ., Cui, B., Li, W. et al. Development and preliminary evaluation of real-time PCR assays for six lactic acid bacteria. Sci Rep 16, 6165 (2026). https://doi.org/10.1038/s41598-026-37047-3
Nyckelord: probiotika, mjölksyrabakterier, realtids‑PCR, livsmedelsmikrobiologi, mikrobiell identifiering