Clear Sky Science · sv
Integrerad BSI-bakterieidentifierare-på-chip med approximativ k-mer-ökning
Varför snabbare upptäckt av mikrober spelar roll
För patienter som får livräddande stamcellstransplantationer kan infektioner i blodomloppet omvandla återhämtningen till en medicinsk nödsituation inom några timmar. Läkare vet att varje minut räknas, men dagens laboratorieverktyg för att hitta de skyldiga bakterierna kan vara långsamma eller kräva kraftfulla datorer. Denna studie presenterar en liten, energieffektiv datorchip—kallad PC-CAM—som snabbt kan skanna DNA från patientprover och flagga farliga bakterier i realtid, potentiellt vid sjukhussängen.
Infektionsrisken efter en tarmräddande behandling
Vissa transplantationspatienter utvecklar en svår komplikation där de donerade immuncellerna angriper patientens tarm. En lovande behandling är fekal mikrobiotaöverföring, där friska tarmmikrober från en donator introduceras till patienten. Medan detta kan rädda tarmen medför det ibland en extra fara: skadliga bakterier från tarmen kan ta sig ut i blodomloppet och orsaka livshotande infektioner. För att behandla dessa infektioner effektivt måste läkare snabbt identifiera vilka bakteriearter som finns närvarande, men traditionella tester kan ta timmar till dagar och kan missa okända stammar.
Från långsam genom-montering till snabba DNA-fragment
Moderna DNA-sekvenserare kan läsa genetiskt material direkt från blod- eller avföringsprov nästan i realtid. Flaschenhalsen är inte längre att läsa DNA:t, utan att tolka det. Konventionella metoder försöker först rekonstruera hela genom från miljontals korta DNA-fragment och sedan matcha dessa sammanfogade genom mot ett referensbibliotek—en beräkningsintensiv process. Författarna ersätter detta med en enklare strategi: de delar upp DNA i korta bitar av fast längd, kallade k-merer, och söker efter dessa bitar direkt i en databas med kända bakteriesekvenser. Istället för att kräva en perfekt bokstav-för-bokstav-match tolererar deras system ett visst antal skillnader, vilket gör det möjligt att hantera oundvikliga fel i DNA-sekvensering och naturliga mutationer. 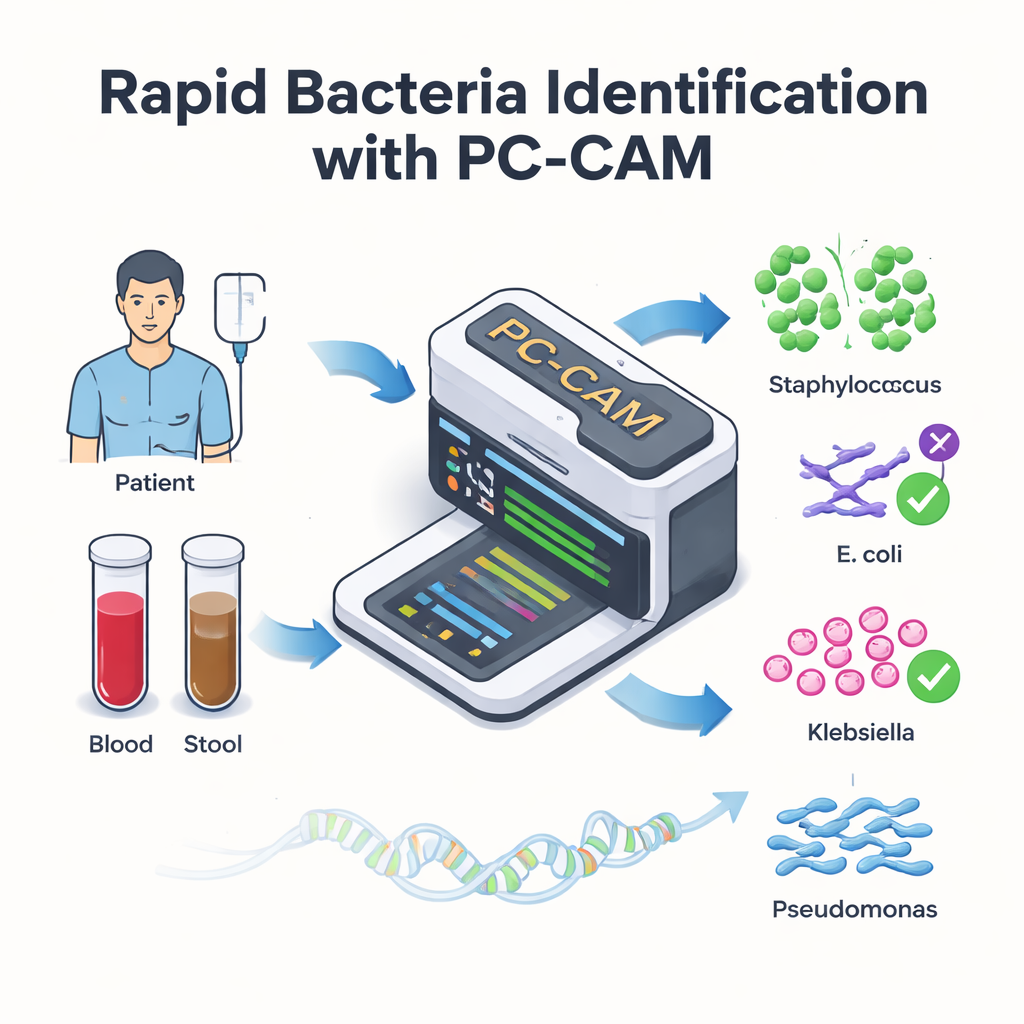
En smart minneskrets byggd för DNA-sökning
I hjärtat av PC-CAM finns en specialiserad typ av minne kallad innehålls-adresserbart minne (content-addressable memory), som kan jämföra inkommande data mot allt det lagrar samtidigt. Forskarna designade en "approximativ sökning"-version av detta minne (ACAM) som kan ställas in för att acceptera närliggande träffar snarare än exakta. Varje kort DNA-fragment kodas och lagras som en rad i detta minne. När ett nytt fragment från ett patientprov anländer aktiverar chippet en sökledning genom alla rader samtidigt och mäter hur snabbt små elektriska signaler urladdas. Genom att justera två styrspänningar sätter systemet en tröskel för hur många avvikelser det tolererar, vilket i praktiken bestämmer hur förlåtande matchningen ska vara. Denna hårdvarunivåjämförelse gör att chippet kan sålla igenom mönster mycket snabbare och med mindre energi än en allmän dator.
Hur väl chippet hittar verkliga bakterier
Teamet testade PC-CAM på verkliga dataset från patienter som genomgått fekal mikrobiotaöverföring och jämförde bakterier upptäckta i deras blod och avföring med resultaten från en fullständig, programvarubaserad genomanalys. Även när chippet bara lagrade en liten, noggrant utvald delmängd av DNA-fragment från varje bakteriegenom, stämde det i stora drag överens med den mer beräkningsintensiva metoden och identifierade korrekt viktiga patogener hos flera patienter. I utökade experiment med simulerade DNA-avläsningar från olika bakterier och olika felhastigheter ökade chippets känslighet (dess förmåga att fånga verkliga träffar) när det tilläts tolerera fler skillnader, medan specificiteten (dess förmåga att undvika falska larm) minskade vid mycket höga toleransnivåer. Författarna visar att enkla efterbearbetningssteg—såsom att kräva flera överensstämmande fragment eller att förkasta svaga träffar—kan minska dessa falska positiva. 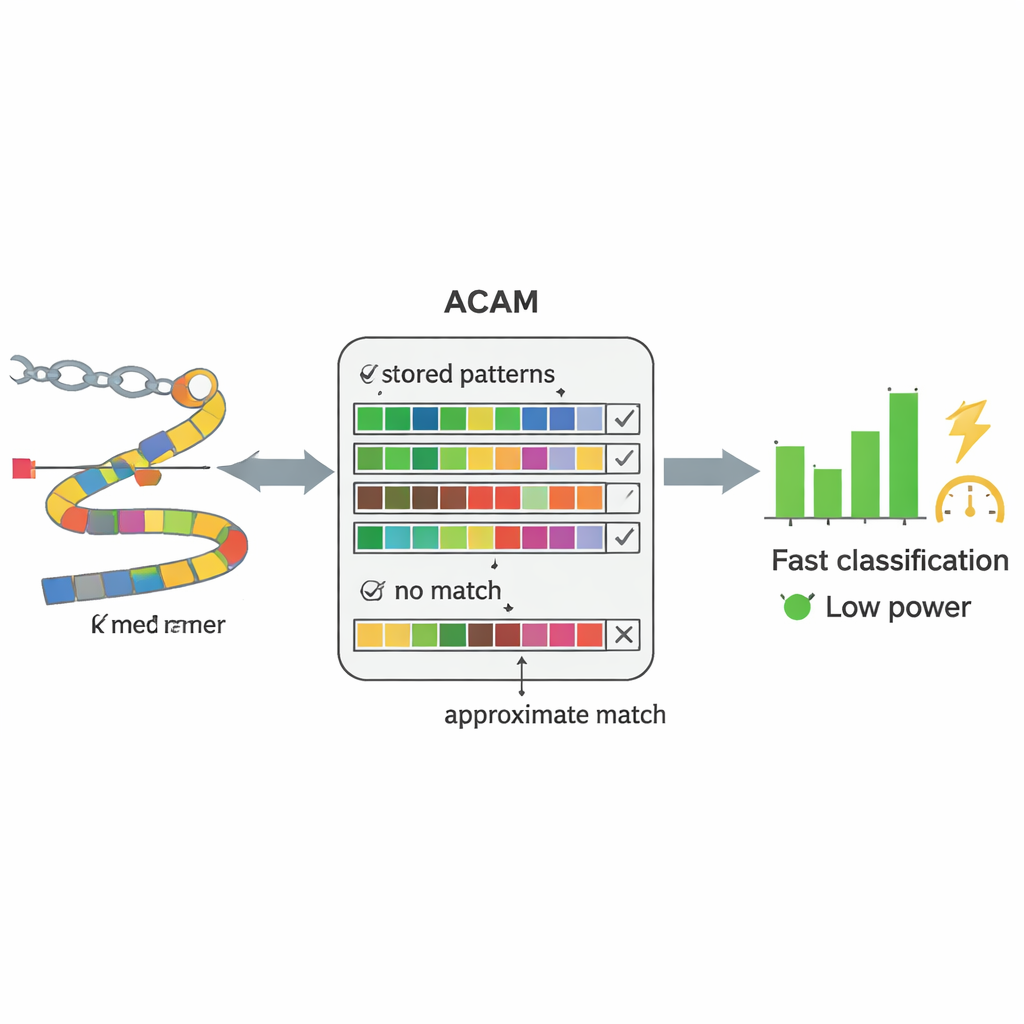
Liten hårdvara med hög hastighet och låg effekt
PC-CAM integrerar ACAM-minnet med en liten RISC-V-processor på ett chip bara några kvadratmillimeter stort, tillverkat i en standard 65-nanometerteknik. Mätningar på verklig hårdvara visar att det kan klassificera ungefär 960 000 korta DNA-avläsningar varje sekund samtidigt som det förbrukar omkring 1,27 milliwatt effekt—mindre än många digitala armbandsur. Jämfört med ett ledande programvaruverktyg som körs på en avancerad stationär processor var chippet ungefär 1 900 gånger snabbare för denna typ av klassificeringsuppgift. Även om dess noggrannhet är måttligt reducerad genom att lagra en förtunnad version av varje genom, menar författarna att denna kompromiss är acceptabel när hastighet och effekt är de primära begränsningarna, till exempel i akutvård eller bärbara enheter.
Vad detta betyder för patienter och mer därtill
Enkelt uttryckt visar studien att ett litet, lågkonsumerande chip kan fungera som en specialiserad sökmotor för bakteriellt DNA och upptäcka farliga mikrober i blod- eller avföringsprov nästan omedelbart. Medan det inte ersätter fullständig genetisk analys i ett stort laboratorium, kan det ge snabb, direkt vägledning om vilka bakterier som finns närvarande och hjälpa läkare att välja antibiotika tidigare och mer träffsäkert. Samma angreppssätt kan utsträckas till övervakning av antibiotikaresistens, kontroll av livsmedel och vatten för kontaminering eller bevakning av grödor för sjukdom—allt med kompakt hårdvara som flyttar avancerad DNA-analys från datacentret närmare där besluten måste fattas.
Citering: Garzón, E., Galindo, V., Harary, Y. et al. Integrated BSI bacteria identifier-on-chip using approximate k-mer matching. Sci Rep 16, 5722 (2026). https://doi.org/10.1038/s41598-026-36497-z
Nyckelord: blodförgiftning, snabb patogendetektion, DNA-sekvensering, lab-on-a-chip, mikrobiom