Clear Sky Science · sv
Fullängds-transkriptommontering och utveckling av SSR-markörer för Spinibarbus hollandi med PacBio SMRT-sekvensering
Varför en anspråkslös flodfisk spelar roll
Längs floderna i södra Kina simmar Spinibarbus hollandi, en karpliknande fisk uppskattad både som matfisk och som prydnadsfisk. Uppfödare vill föda upp den mer effektivt, men fisken växer långsamt, blir könsmogen sent och producerar relativt få ägg. Studien som beskrivs här använder moderna DNA- och RNA-sekvenseringsverktyg för att bygga en detaljerad genetisk ”delkatalog” för denna art. Denna genetiska information kan så småningom hjälpa avelsarbetare att välja tåligare, snabbare växande fiskar och stödja bevarandet av vilda populationer.
Att omvandla många vävnader till en genetisk karta
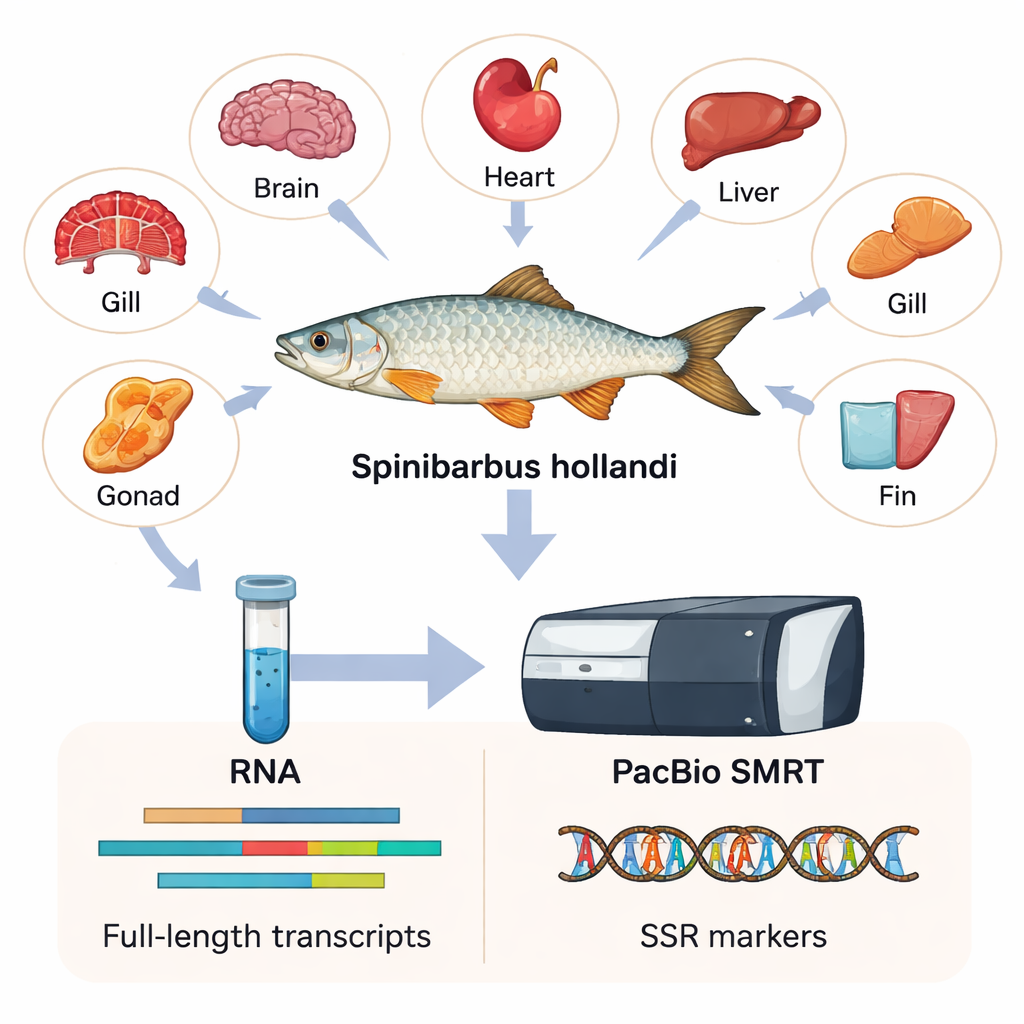
För att fånga så mycket genetisk information som möjligt samlade forskarna sex olika vävnader — hjärta, gälar, hjärna, fenor, lever och gonad — från vuxna hanar och honor. Från dessa vävnader extraherade de RNA, molekylen som bär kopior av aktiva gener i cellerna. Med en teknik kallad PacBio SMRT, som läser mycket långa sträckor av RNA-kopior, monterade de det första fullängds-transkriptomet för S. hollandi. Enkelt uttryckt byggde de en högupplöst katalog över 15 197 distinkta gener och 23 403 transkriptsekvenser, de flesta mycket längre och mer kompletta än vad äldre kortläsningsmetoder kunde producera.
Vad generna avslöjar om fisken
Nästa steg var att ta reda på vad dessa gener faktiskt gör. De jämförde varje sekvens med stora publika databaser som grupperar gener efter funktion. Mer än 95 % av generna kunde matchas till kända poster, en mycket hög träffprocent som tyder på god datakvalitet. Många gener hamnade i kategorier kopplade till grundläggande cellulära aktiviteter som ämnesomsättning, signalöverföring och utveckling, och liknade mest gener från andra karfamiljsfiskar. Detta bekräftar att det nya transkriptomet är biologiskt trovärdigt och utgör en grund för att hitta gener kopplade till egenskaper som tillväxthastighet, stresstolerans och reproduktion hos S. hollandi.
Dolda kontrollnivåer i RNA
Utöver att identifiera gener undersökte forskarna också hur dessa gener styrs. De hittade 373 fall av alternativ splitsning, där samma gen klipps och sätts ihop på olika sätt för att skapa olika RNA-meddelanden. Det vanligaste mönstret behöll delar av RNA som ofta tas bort i andra arter, vilket antyder ett speciellt sätt denna fisk finjusterar sina proteiner. De upptäckte också 2 397 långa icke-kodande RNA — RNA-molekyler som inte bildar proteiner men kan reglera när och var andra gener aktiveras. Tillsammans visar dessa fynd att S. hollandi använder ett rikt spektrum av RNA-nivåkontroller som kan påverka tillväxt, könsmognad och anpassning till lokala miljöer.
Att bygga DNA-landmärken för avel och bevarande
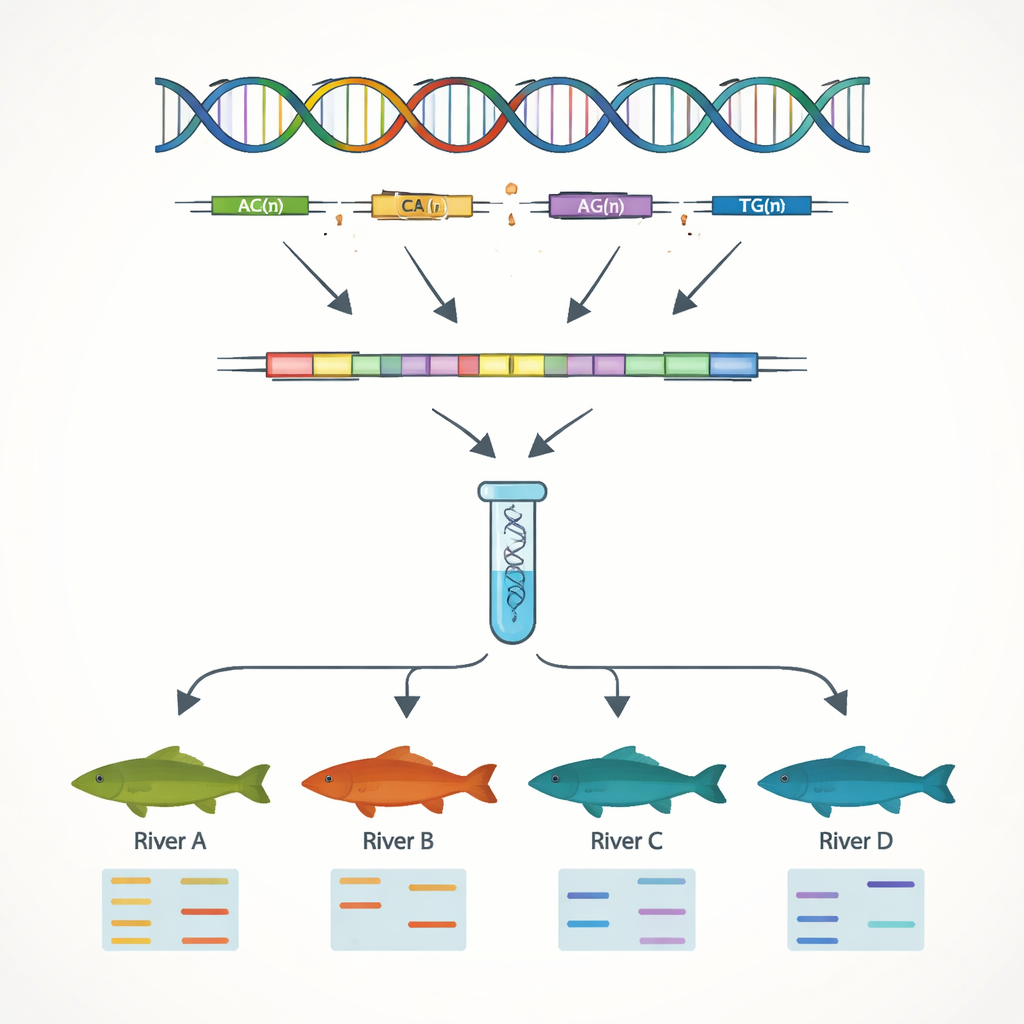
Ett huvudmål med arbetet var att utveckla enkla DNA-markörer som kan särskilja individer och populationer. Med fokus på gensekvenserna sökte författarna efter enkla sekvensrepetitioner, eller SSR — korta DNA-motiv som ”AC” eller ”AAT” upprepade många gånger i följd. Dessa sträckor tenderar att variera mellan individer, vilket gör dem användbara som genetiska streckkoder. De identifierade 7 449 sådana SSR-ställen och designade dussintals korta DNA-primers för att amplifiera dem i laboratoriet. Tretton av dessa markörer visade sig vara mycket variabla och tillförlitliga när de testades på 51 fiskar från fyra flodsystem. Med endast dessa 13 markörer kunde teamet tydligt upptäcka genetiska skillnader mellan populationer från Yangtze-floden och de från Pearl River, vilket speglar bergskedjor som begränsar naturlig blandning mellan avrinningsområden.
Vad detta betyder för fiskodlare och floder
För icke-specialister är huvudpoängen att författarna har skapat en detaljerad, högkvalitativ genetisk referens för S. hollandi och ett set praktiska DNA-markörer. Detta verktygslåda kommer att hjälpa forskare att identifiera gener bakom långsam tillväxt eller låg fertilitet, bistå uppfödare i att välja avelsdjur med önskvärda egenskaper och låta konservatörer övervaka genetisk mångfald över flodsystem. Även om mer arbete krävs för att koppla specifika gener till prestation i dammar eller i det vilda, lägger denna studie den molekylära grunden för att omvandla en traditionell flodfisk till en modern, hållbart förvaltad akvakultursart.
Citering: Li, S., Lai, J., Wu, M. et al. Full-Length transcriptome assembly and SSR marker development for Spinibarbus hollandi using PacBio SMRT sequencing. Sci Rep 16, 5629 (2026). https://doi.org/10.1038/s41598-026-36468-4
Nyckelord: Spinibarbus hollandi, fisktranskriptom, PacBio-sekvensering, mikrosatellitmarkörer, akvakulturgenetik