Clear Sky Science · sv
ONCOPLEX: en onkologi-inspirerad hypergrafmodell som integrerar varierad biologisk kunskap för förutsägelse av cancerdrivande gener
Varför denna forskning är viktig
Cancer drivs av ett fåtal kraftfulla genetiska förändringar gömda bland tusentals ofarliga varianter. Att hitta de verkligt farliga ”drivande” generna är avgörande för bättre diagnostik och riktade behandlingar, men det är som att lokalisera ett par ringledare i en enorm, brusig folkmassa. Denna studie presenterar ONCOPLEX, ett nytt ramverk inom artificiell intelligens som betraktar gener inte en och en, utan i kontexten av de biologiska vägar de verkar i tillsammans, vilket ger ett skarpare sätt att peka ut de gener som faktiskt driver tumörer.
Att se cancergener i deras biologiska grannskap
De flesta nuvarande metoder granskar cancergenom för mutationer som förekommer ovanligt ofta eller som sticker ut i enkla gen-nätverk. Dessa angreppssätt hjälper, men biologin är sällan så enkel. Gener verkar oftast i grupper inom vägar som styr celltillväxt, DNA-reparation och många andra processer. ONCOPLEX omfamnar denna komplexitet genom att representera gener som punkter och vägar som större överlappande grupper som kan innehålla många gener samtidigt. Denna typ av struktur, känd som en hypergraf, låter modellen beakta relationer mellan flera gener direkt istället för att bryta ner dem i många separata par.
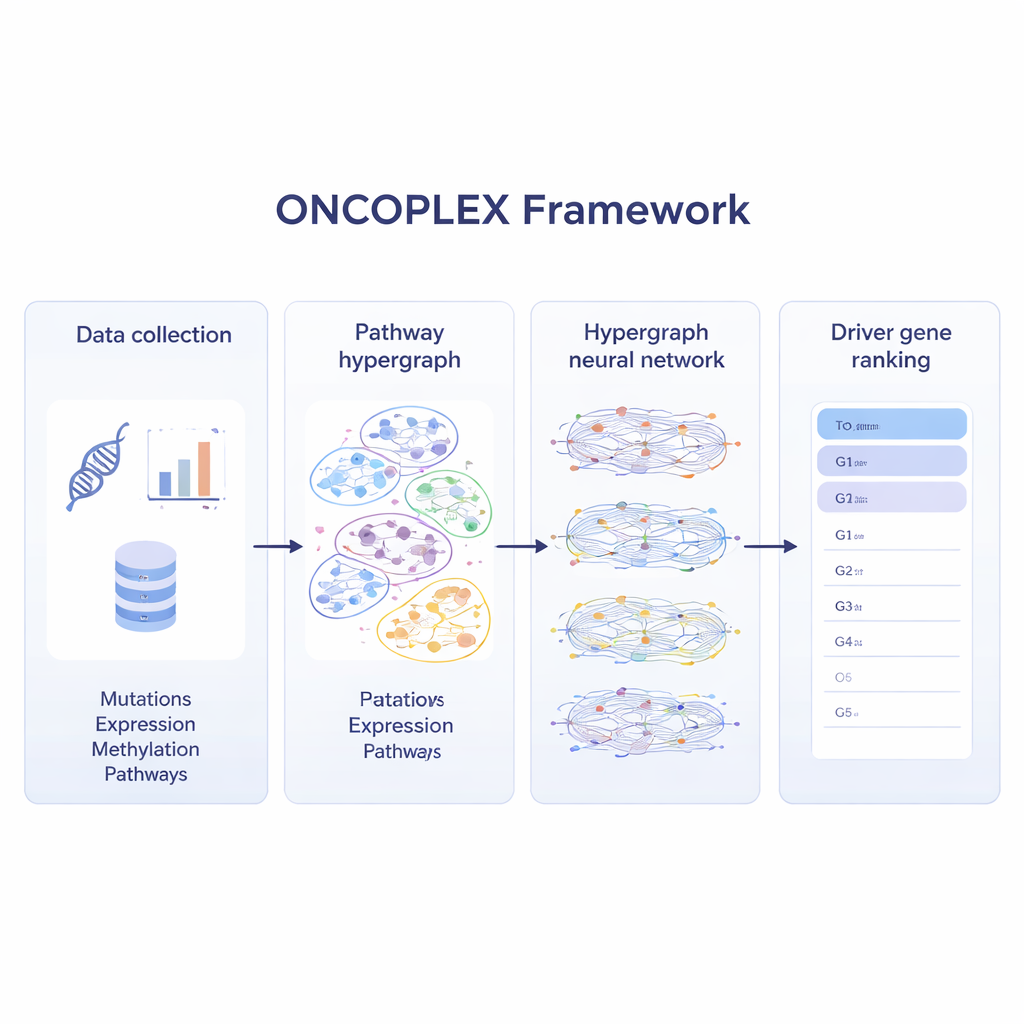
Att blanda många lager av cancerdata
För att utnyttja moderna cancer-dataset maximalt kombinerar ONCOPLEX flera typer av information om varje gen. Den använder mutationsfrekvenser, förändringar i genaktivitet, kemiska taggar på DNA (metylering) och ett rikt set biologiska egenskaper såsom evolutionär konservering och funktionella annotationer. Dessa egenskaper knyts till varje gen i hypergrafen. Ett specialiserat neuralt nätverk för vidare information genom vägarna, så att varje gens representation formas både av dess egna data och av beteendet hos de gener den samarbetar med. Modellen tränas med hjälp av gener som redan är kända som cancerdrivare, samtidigt som den lär från många oetiketterade gener som kan vara viktiga men ännu inte erkända.
Bättre än befintliga verktyg över många cancerformer
Forskarna testade ONCOPLEX på data från The Cancer Genome Atlas, både genom att slå ihop många tumörtyper och genom att undersöka 11 enskilda cancerformer, inklusive bröst-, lung-, lever-, urinblåse- samt huvud- och halscancer. De jämförde det med flera ledande graf- och hypergrafbaserade metoder. I samtliga fall var ONCOPLEX bättre på att särskilja kända drivargener från de betydligt vanligare icke-drivarna och på att ranka sannolika drivare högt i sina listor. Dess fördel var särskilt tydlig bland de högst rankade generna, där korrekt identifiering är mest värdefull för uppföljande experiment och klinisk översättning.
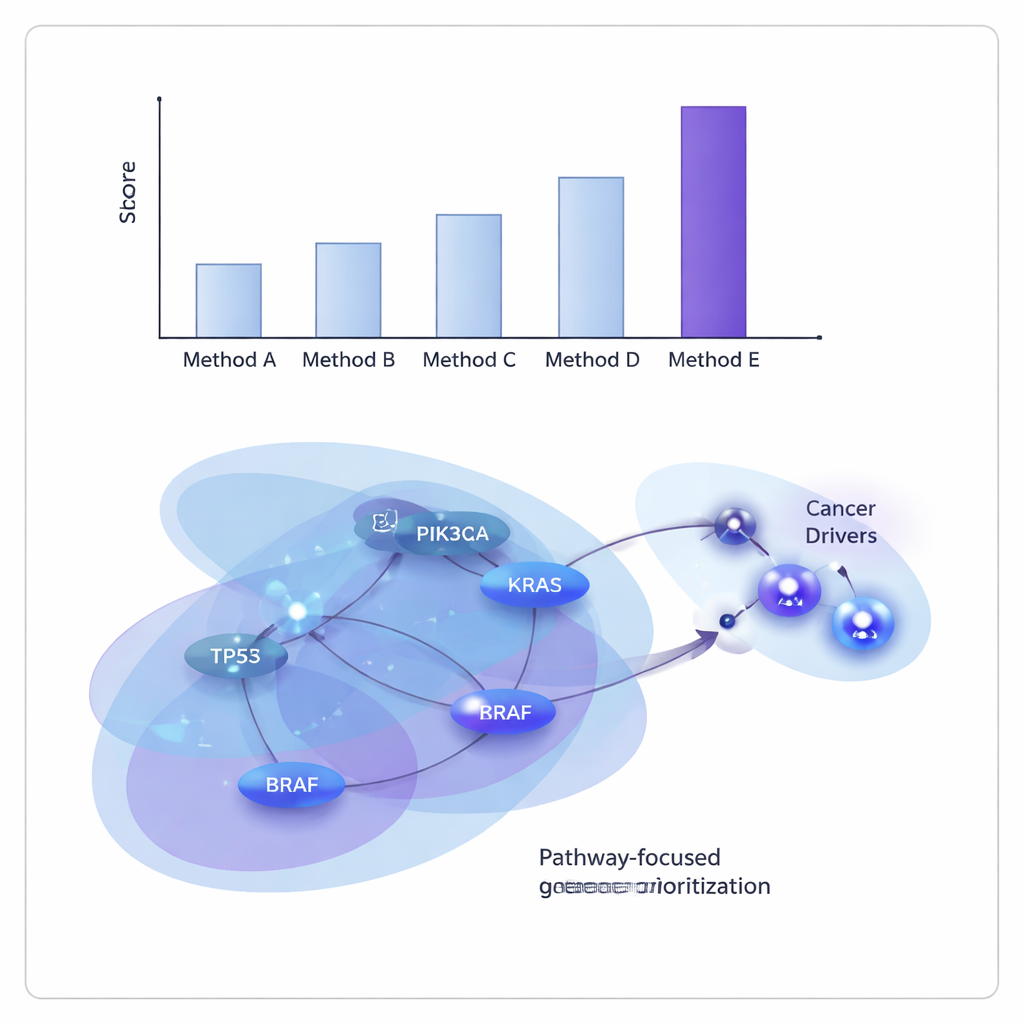
Avslöjar gemensamma och cancerspecifika bovar
Utöver rena prestationssiffror återfann ONCOPLEXs rankade genlistor många välkända cancergener, såsom KRAS, BRAF och medlemmar i PI3K–AKT-signalvägen, vilket bekräftar att modellen fångar etablerad biologi. Den framhöll också lovande kandidater som ännu inte är fastställda som drivare i vissa cancerformer, inklusive gener som GRB2 och MAPK3 i bröstcancer och SHC1 i magsäckscancer. När teamet analyserade de högst rankade generna med vägberikningsanalyser fann de starka signaturer av välkända cancervägar, inklusive ErbB-signalering och PI3K–AKT–mTOR, samt immunsrelaterade vägar, vilket tyder på att ONCOPLEX zoomar in på nätverk som har klinisk betydelse.
Styrkor, begränsningar och vad som kommer härnäst
Genom att visa att rikare biologiska egenskaper stadigt förbättrar dess förutsägelser demonstrerar ONCOPLEX värdet av att förena många datakällor inom ett vägcentrerat ramverk. Samtidigt blottlägger studien en begränsning: eftersom många cancerformer delar ett stort antal vägar tenderar modellen ibland att favorisera vitt verkande ”pan-cancer”-gener framför sådana som verkligen är specifika för en tumörtyp. Författarna föreslår att framtida arbete bör förfina hur väginformation används så att gemensamma och cancerspecifika signaler kan skiljas åt tydligare.
Vad detta betyder för patienter och kliniker
För icke-specialister är huvudpoängen att ONCOPLEX erbjuder ett mer biologiskt realistiskt sätt att söka efter gener som driver cancer. Genom att betrakta gener i sällskap med de de hör ihop med—inom vägar istället för isolerat—förbättrar det vår förmåga att upptäcka både välkända och tidigare förbisette drivare, även i cancerformer där kunskapen i dag är begränsad. Denna typ av verktyg kan hjälpa forskare att prioritera vilka gener som ska studeras i laboratoriet, vägleda jakten på nya läkemedelsmål och i slutändan stödja mer precisa, vägmedvetna behandlingsstrategier inom onkologi.
Citering: Alotaibi, E.M., Alkhnbashi, O.S. & Tran, V.D. ONCOPLEX: an oncology-inspired hypergraph model integrating diverse biological knowledge for cancer driver gene prediction. Sci Rep 16, 5164 (2026). https://doi.org/10.1038/s41598-026-36127-8
Nyckelord: cancerdrivande gener, hypergraf-neurala nätverk, multi-omik-integration, väganalys, precision-onkologi