Clear Sky Science · sv
Haplotypnivåanalys av miljö-DNA-metabarcoding avslöjade biogeografin och fylogeografin hos sötvattensfiskar i Koreanska halvön
Läsa floder genom osynliga ledtrådar
Floder och bäckar kan se klara ut för blotta ögat, men de är fulla av mikroskopiska spår av liv. Den här studien visar hur forskare kan läsa det osynliga genetiska »bläcket« i vatten för att upptäcka vilka fiskar som lever var, hur deras populationer är besläktade över Koreanska halvön och till och med om vissa fiskar har förflyttats av människor från en region till en annan. Arbetet är en försmak av hur bevarandebiologer snart kan övervaka biodiversitet och skydda sällsynta arter utan att sätta ett enda nät.
Fiska med DNA, inte nät
I stället för att fånga fisk samlade forskarna enkla enlitersflaskor med vatten från tre små bäckar—Seom, Gilan och Oshipcheon—var och en belägen i en annan biogeografisk region i Sydkorea. I dessa prover sökte de efter miljö-DNA (eDNA): små fragment av genetiskt material som fiskar avger via hud, avföring och slem. Med en teknik kallad metabarcoding amplifierade och sekvenserade de en kort bit fisk-DNA och jämförde sedan miljontals avläsningar med referensdatabaser för att identifiera vilka arter—och till och med vilka genetiska varianter, eller haplotyper—som fanns i varje bäck.
Vilka lever var i Koreas bäckar?
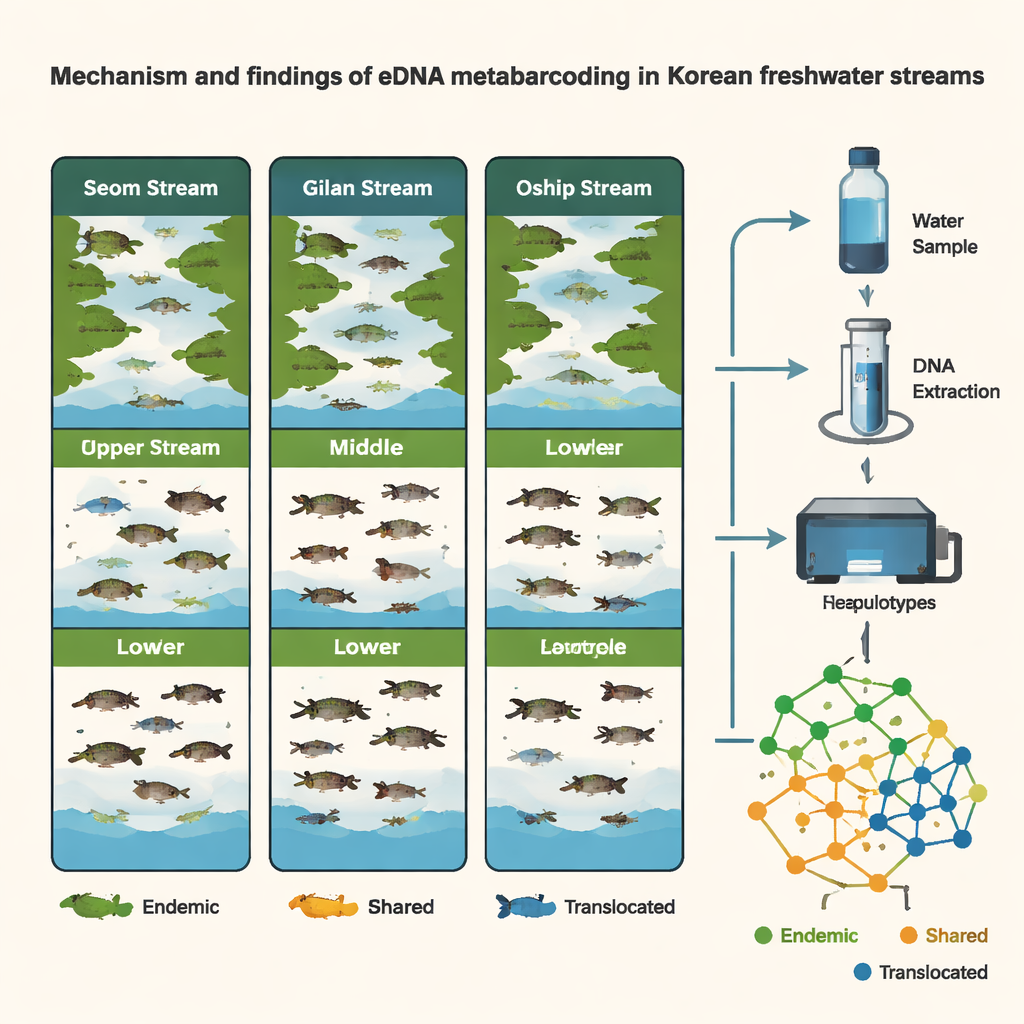
Från endast 54 vattenprov tagna på nio platser upptäckte teamet 107 distinkta DNA-varianter som representerade 76 fiskarter—ungefär en tredjedel av alla sötvattensfiskar kända från Korea. Seom-bäcken, en lägre liggande flod kopplad till Gula havet, hyllade den rikaste fiskfaunan med 49 arter. Gilan och Oshipcheon, högre och brantare biflöden som rinner mot olika kuster, hade vardera 28 arter. Många fiskar delades mellan bäckarna, men nästan 30 arter var endemiska för Koreas sötvattensmiljöer, och varje bäck hade också sin egen unika uppsättning arter. Övergripande överensstämde mönstren med långtidskännedom att Koreas sötvattensliv är uppdelat i tre huvudregioner av bergskedjor och geologisk historia.
Genetiska fingeravtryck och dolda förflyttningar
Eftersom forskarna arbetade på haplotypnivå—de finfördelade »smakerna« av DNA inom en art—kunde de göra mer än att lista arter; de kunde jämföra populationer. Flera vanliga inhemska fiskar visade tydliga genetiska skillnader mellan regioner, vilket indikerar långvarig separation och begränsad naturlig blandning över halvön. Samtidigt blottlade DNA-data sannolika fall av människors hjälp vid förflyttning. För arter såsom Pungtungia herzi, Coreoleuciscus splendidus och Nipponocypris koreanus matchade haplotypmönstren i den östra Oshipcheon-bäckenet starkt dem från västliga eller södra floder, vilket tyder på tidigare utsättning eller translokation. Genom att virtuellt rekonstruera »släktträd« för dessa DNA-varianter kunde teamet härleda sannolika käntregioner för förflyttade fiskar—vilket erbjuder en form av genetisk rättsmedicin för flodförvaltning.
Säsonger, habitat och rörliga mål
Studien följde också hur fiskcommunityn förändrades över tid och rum. Genom att jämföra prover insamlade i sen vinter (mars) och sommar (augusti) fann forskarna högre artdiversitet på sommaren och tydliga säsongsförskjutningar, särskilt i Seom-bäckenet. I Oshipcheon framträdde och försvann eDNA från vandrande arter—såsom lax och andra fiskar som rör sig mellan flod och hav—på sätt som överensstämde med deras kända livscykler. Överraskande nog visade riffles, runs och pooler inom varje plats inte starka skillnader i fisk-DNA, sannolikt eftersom vattenflödet blandar eDNA lateralt över dessa små kanaler. Istället kom de största kontrasterna mellan olika avsnitt av bäckarna (övre, mellersta, nedre) och mellan de tre bäckarna själva, vilket understryker hur viktigt det är var längs en flod prover tas.
Vad detta betyder för att skydda sötvattensliv
Enkelt uttryckt visar denna forskning att en flaska flodvatten kan avslöja en detaljerad ögonblicksbild av vem som lever i bäcken, hur lokala fiskpopulationer är besläktade över stora regioner och om människor har förändrat dessa mönster genom att flytta fiskar. För bevarande innebär det att förvaltare snabbt kan övervaka sällsynta och endemiska arter, upptäcka invasiva och förflyttade fiskar och följa säsongsförändringar i vandrande populationer utan omfattande fältarbete eller att skada djur. Medan eDNA ännu inte kan ersätta traditionella genetiska studier, erbjuder det ett kraftfullt, lågpåverkan verktyg för att övervaka sötvattensbiodiversitet i en värld som värms upp och är starkt förvaltad—och för att säkerställa att Koreas unika flodfiskar fortsätter att frodas i sina naturliga hem.
Citering: Amin, M.H.F., Kim, A.R., Jang, J.E. et al. Haplotype-level analysis of environmental DNA metabarcoding revealed the biogeography and phylogeography of freshwater fishes in Korean Peninsula. Sci Rep 16, 6955 (2026). https://doi.org/10.1038/s41598-026-36043-x
Nyckelord: miljö-DNA, sötvattensfisk, biodiversitet, koreanska floder, bevarandegenetik