Clear Sky Science · sv
Förbättring av bioinformatisk ingenjörskonst genom att använda grafens terapeutiska egenskaper för kliniskt godkända antitoxinläkemedel vid zoonoser
Varför detta är viktigt för framtida mediciner
Anthrax ses ofta som en gammal lantbrukssjukdom, men den utgör fortfarande ett hot mot boskap, människor i utvecklingsregioner och till och med nationell säkerhet eftersom dess sporer kan vapeniseras. Behandling av anthrax förlitar sig på ett litet antal kraftfulla antibiotika och antitoxinläkemedel. Denna studie ställer en till synes enkel fråga med stora konsekvenser: kan vi använda idéer från nätverksmatematik — grafteori — för att läsa av formen hos dessa läkemedel och snabbt förutsäga viktiga fysiska egenskaper som påverkar hur de beter sig i kroppen? Om svaret är ja kan samma angreppssätt påskynda sökandet efter nästa generations antitoxinläkemedel.
Från dödliga sporer till läkemedelsritningar
Anthrax orsakas av Bacillus anthracis, en bakterie som bildar tuffa sporer och främst smittar betande djur som nötkreatur och får, men som också kan hoppa över till människor. När den väl kommit in i kroppen kan den angripa huden, lungorna eller tarmen, med symtom som spänner från influensaliknande till plötslig, livshotande sjukdom. Läkare förlitar sig i dag på ett begränsat urval kliniskt godkända läkemedel — såsom ciprofloxacin, penicillin‑baserade föreningar och flera tetracyklinlika antibiotika — för att stoppa infektionen och dess toxiner. Var och en av dessa läkemedel är en tredimensionell härva av atomer. Hur dessa atomer är förbundna styr grundläggande egenskaper som molekylvikt, hur lätt en tablett löser sig i vatten och hur den rör sig i kroppen. Att förstå sambanden mellan struktur och beteende är avgörande för att säkert modifiera gamla läkemedel eller uppfinna nya. 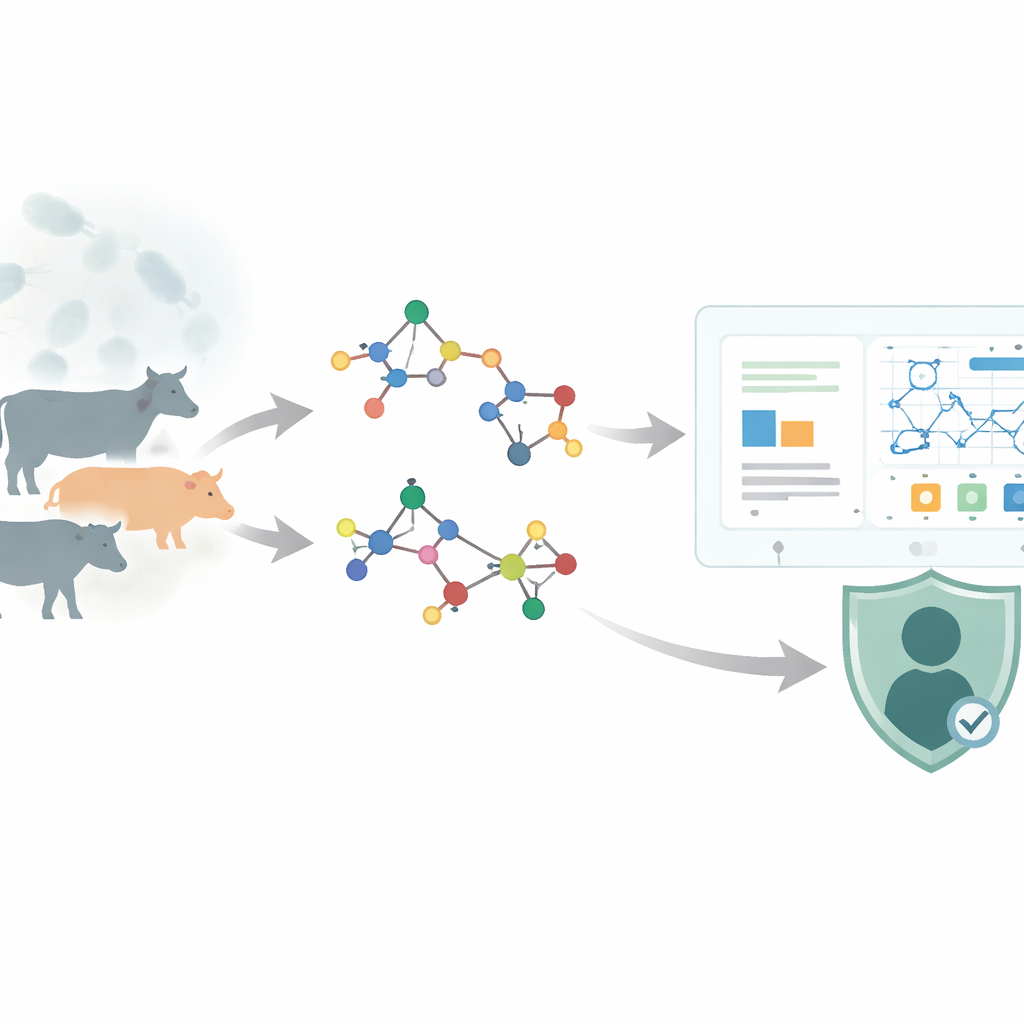
Att omvandla molekyler till nätverk av punkter och linjer
Författarna använder kemisk grafteori, ett fält som behandlar en molekyl som ett nätverk: atomer blir punkter och bindningar blir linjer. Från detta nätverk beräknar de numeriska sammanfattningar kallade topologiska index, som fångar mönster av förgrening och konnektivitet. I detta arbete fokuserar de på en familj av "omvända" index — varianter av klassiska mått såsom Zagreb‑ och atom‑bindningskonnektivitetsindex — och på ett kompakt algebraiskt objekt kallat M‑polynom, som kodar hur starkt olika kopplingsmönster representeras i ett läkemedels struktur. För fjorton godkända anthrax‑relaterade läkemedel använde de Python‑verktyg (RDKit och NetworkX) för att bygga graferna, beräkna M‑polynomen och härleda en panel av omvända index. De samlade sedan experimentellt uppmätta egenskaper från PubChem‑databasen: smält‑ och kokpunkt, vattenslöslighet, molekylvikt, densitet och andra deskriptorer som påverkar hur ett läkemedel absorberas, distribueras, metaboliseras och utsöndras.
Att matcha strukturmönster med mätbara egenskaper
Med båda uppsättningarna siffror i hand — de grafbaserade indexen och de verkliga egenskaperna — genomförde teamet regressionsanalys, ett sätt att passa matematiska kurvor till data. Vägledda av formerna på sina M‑polynomytor testade de två familjer av modeller: logaritmiska kurvor, som växer snabbt och sedan planar ut, och kubiska kurvor, som kan böja sig mer dramatiskt. För varje index och varje egenskap utvärderade de hur väl en given kurva förklarade data (med hjälp av det välkända R²‑statistiken) och hur stabil prediktionen förblev när datapunkter systematiskt lämnades ut (med en striktare korsvalideringsmått kallat Q²). 
Vad som fungerade, vad som misslyckades och varför det spelar roll
Det mest slående mönstret var att inte alla egenskaper var lika lärbara från struktur. För termodynamiska egenskaper som smältpunkt eller den fettälskande måtten LogP presterade de omvända indexen dåligt: modellernas R²‑värden förblev låga, vilket signalerar i huvudsak ingen prediktiv kraft. I kontrast visade flera index — särskilt ett mått kallat Modifierat andra Zagreb‑index (mM2) och ett omvänt atom‑bindningskonnektivitetsindex — mycket starka samband med molekylvikt, en grundläggande måttstock för molekylstorlek. En enkel logaritmisk modell som kopplade mM2 till molekylvikt uppnådde både hög passform och stark korsvaliderad prediktiv förmåga (R² omkring 0,97 och Q² omkring 0,99), även efter att författarna noggrant testade mot överanpassning och slumpmässighet med leave‑one‑out‑tester, analys av applicerbarhetsdomänen och Y‑randomisering. Mer komplexa kubiska modeller passade de befintliga data nästan för väl men misslyckades i dessa stabilitetstester, vilket illustrerar hur lätt små dataset kan vilseleda när överkomplicerade formler används.
Hur detta hjälper utformningen av bättre antitoxinläkemedel
För icke‑specialister är huvudbudskapet att författarna har byggt ett snabbt, matematiskt grundat sätt att uppskatta ett anthraxläkemedels molekylvikt direkt från mönstret av dess atomkopplingar — utan att behöva full experimentell karaktärisering. Molekylvikt är inte en måttstock för hur väl ett läkemedel dödar bakterier, men det är ett centralt filter i läkemedelsdesign kopplat till hur bra en förening kan absorberas, distribueras och utsöndras från kroppen. Genom att identifiera vilka grafbaserade index som pålitligt följer molekylstorlek, och vilka som inte meningsfullt förutsäger mer subtila egenskaper som smältpunkt eller fettlöslighet, skärper detta arbete verktygslådan för datorstödd läkemedelsdesign. I framtiden skulle liknande grafteoretiska modeller kunna hjälpa forskare att snabbt sålla stora bibliotek av kandidat‑antitoxinmolekyler, och utesluta de vars storlek eller komplexitet ligger utanför önskvärda områden långt innan kostsamma laboratorietester påbörjas.
Citering: Imran, M., Aqib, M., Malik, M.A. et al. Enhancing bioinformatics engineering by utilizing graph therapeutic properties for clinically approved antitoxin drugs in zoonotic diseases. Sci Rep 16, 8590 (2026). https://doi.org/10.1038/s41598-026-36036-w
Nyckelord: anthraxläkemedel, kemisk grafteori, topologiska index, QSPR‑modellering, prediktion av molekylvikt