Clear Sky Science · sv
IL2Pepscan: Ett maskininlärningsramverk för att förutsäga IL‑2‑inducerande peptider och deras identifiering över globala virusproteom
Att lära immunsystemet med små proteinfragment
Moderna vacciner och cancerterapier förlitar sig alltmer på att fintjustera immunsystemet i stället för att bomba sjukdomen med breda läkemedelsangrepp. Denna studie undersöker hur små proteinfragment, kallade peptider, kan väljas för att slå på en kraftfull immunsignal, interleukin‑2 (IL‑2). Genom att använda avancerade datormodeller söker författarna både i kända immundata och i proteinkatalogerna för tusentals virus efter peptid‑"nålar" i ett molekylärt höstack som kan hjälpa till att utforma bättre vacciner och immunterapier.
Varför IL‑2 är viktigt för hälsa och sjukdom
IL‑2 är en liten signalsubstans som fungerar som en tillväxtfaktor för nyckelceller i immunsystemet, kända som T‑celler. När dessa celler först möter ett hot — till exempel ett virus eller en cancercell — kan de frisätta IL‑2, vilket uppmuntrar T‑cellerna att multiplicera sig, specialisera sig och skapa minne mot angriparen. IL‑2 hjälper också till att upprätthålla regulatoriska T‑celler som förhindrar att immunsystemet vänder sig mot kroppens egna vävnader. På grund av denna dubbla roll har IL‑2 använts som läkemedel mot vissa cancerformer, som melanom, och studeras även för autoimmuna sjukdomar. Men att ge IL‑2 direkt kan vara påfrestande för patienter, så intresset växer för att utforma säkra peptider som får kroppen att producera IL‑2 på ett mer kontrollerat och målinriktat sätt.
Att lära sig "smaken" hos IL‑2‑inducerande peptider
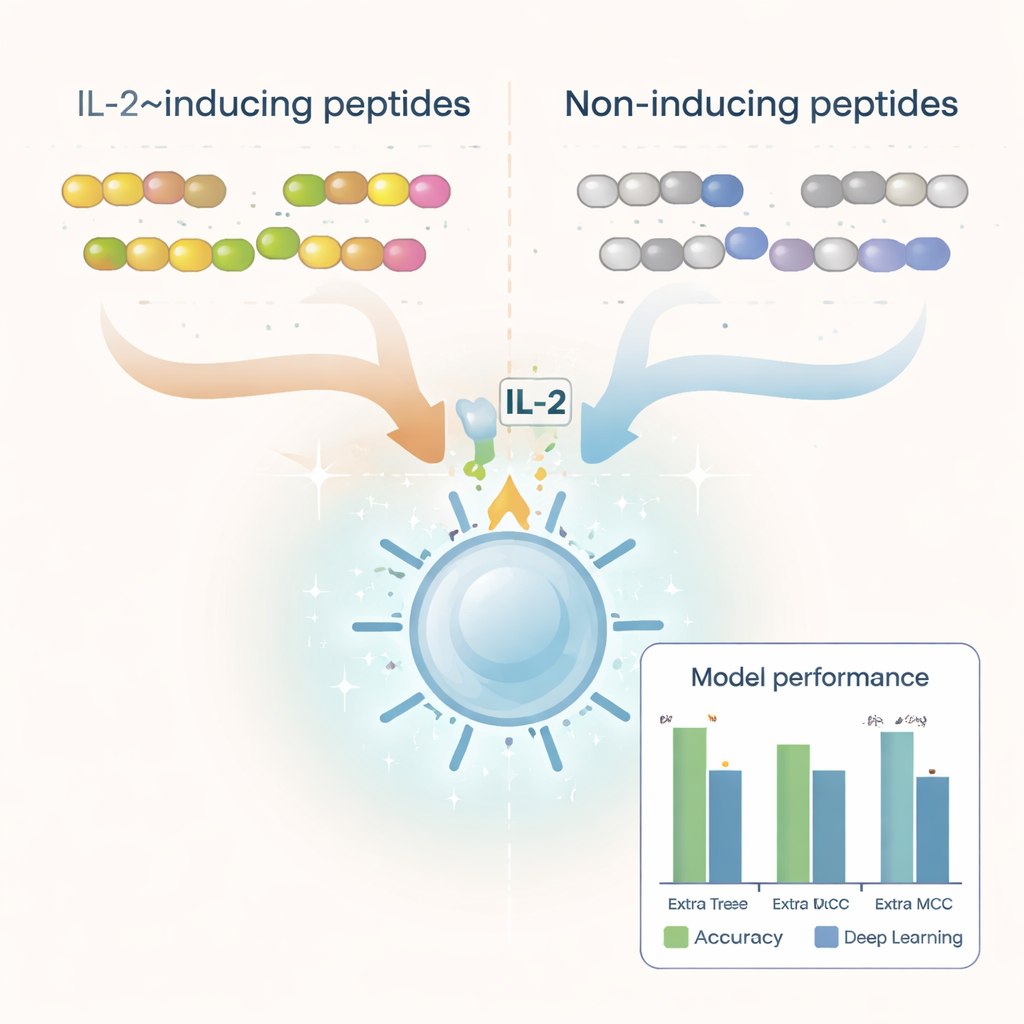
Forskarna började med tusentals peptidsekvenser som redan testats i laboratoriet och märkts som antingen IL‑2‑inducerande eller inte. De rensade datasetet för att ta bort dubbletter, ovanliga byggstenar och peptider som var för korta eller för långa, och sattes samman över 6 000 välkarakteriserade exempel. Genom att undersöka de aminosyror som bygger upp dessa peptider fann de tydliga skillnader mellan de två grupperna. IL‑2‑inducerande peptider tenderade att vara rikare på hydrofoba, eller vattenavvisande, aminosyror som leucin och alanin, medan icke‑inducerande peptider drog mot mer polära och laddade rester. Vissa korta mönster, eller motiv, såsom "LEGS" och "ALEG", förekom endast i IL‑2‑inducerande peptider och antydde strukturella signaturer som kan hjälpa till att utlösa immunsvar.
Träna maskiner att upptäcka immunstärkande mönster
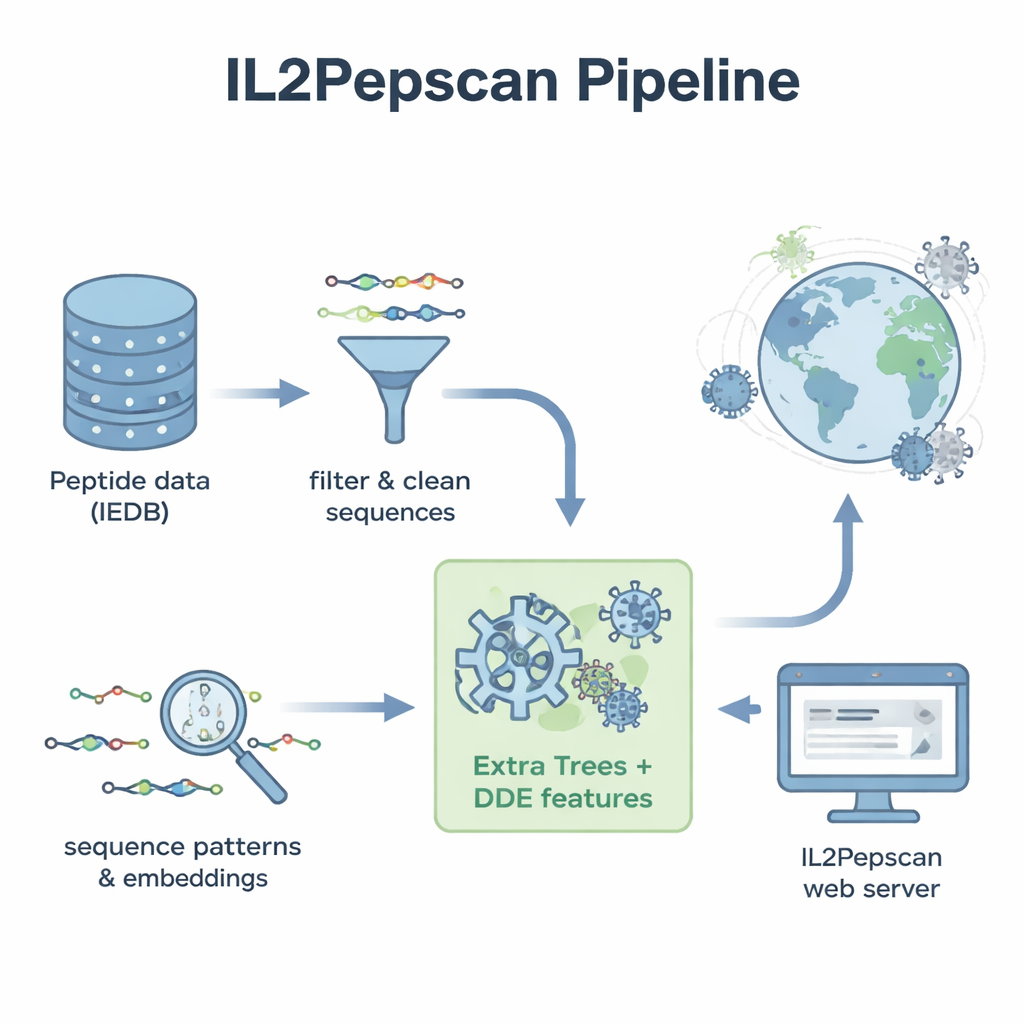
För att omvandla dessa mönster till ett praktiskt förutsägelseverktyg konverterade teamet varje peptid till numeriska beskrivningar som fångar dess sammansättning och aminosyraordning. De testade en rad maskininlärningsmetoder — inklusive populära algoritmer som random forests, support vector machines och boosted trees — tillsammans med djupinlärningsarkitekturer som ofta används för språk‑ och bilduppgifter. De använde också en stor protein‑"språkmodell" kallad ProtBERT, ursprungligen tränad på hundratals miljoner proteinsekvenser, och finjusterade den för att bättre känna igen IL‑2‑relaterade signaler. Efter omfattande tester med korsvalidering och en oberoende testmängd var den främsta presterande modellen Extra Trees kombinerad med ett funktionsset känt som dipeptidavvikelse från förväntat medelvärde (DDE). Denna modell nådde nära 80 % noggrannhet och en stark korrelationspoäng, och överträffade flera djupinlärningsmetoder.
Skanna den virala världen efter dolda immutriggare
Beväpnade med sin bästa modell kastade författarna ett mycket bredare nät. De samlade referensproteinsekvenser från mer än 14 000 virus, skar dessa proteiner i cirka 156 miljoner överlappande peptider och bad modellen förutspå vilka som kunde inducera IL‑2. Bland de högst rankade kandidaterna fanns peptider från välkända virusfamiljer, inklusive flavivirus som West Nile, Zika, gulfeber och hepatit C, samt från influensa och SARS‑CoV‑2. Många lovande peptider kom från virusets hölje‑ eller nukleokapsidproteiner — samma typer av proteiner som andra studier visat kan framkalla IL‑2‑svar i djur. Modellen flaggade också potentiella IL‑2‑inducerande peptider kodade av bakteriofager, virus som infekterar bakterier, vilket antyder en ännu bredare landskap av immunrelevanta sekvenser.
Från algoritm till tillgängligt verktyg
För att göra sitt arbete användbart utanför datorsalen byggde författarna en publik webbserver kallad IL2Pepscan. Forskare kan klistra in peptid‑ eller proteinsekvenser på webbplatsen för att uppskatta deras IL‑2‑inducerande potential, designa nya varianter genom att mutera positioner, skanna hela proteiner efter heta punkter eller söka efter kända IL‑2‑kopplade motiv. Även om studien ännu inte experimentellt bekräftar varje förutspådd peptid, tyder överensstämmelsen med befintliga laboratoriefynd på att IL2Pepscan på ett tillförlitligt sätt kan begränsa antalet kandidater för vidare testning. För icke‑specialister är slutsatsen att vältränade algoritmer kan sålla igenom enorma biologiska dataset för att peka ut små proteinfragment som en dag kan hjälpa vacciner och immunterapier att locka immunsystemet till ett kraftfullare — och mer precist — svar.
Citering: Arora, P., Abhigyan, R., Periwal, N. et al. IL2Pepscan: A machine learning framework for predicting IL-2 inducing peptides and their identification across global viral proteomes. Sci Rep 16, 6701 (2026). https://doi.org/10.1038/s41598-026-35977-6
Nyckelord: interleukin-2, peptidvacciner, maskininlärning, virusproteom, immunterapi