Clear Sky Science · sv
Att reda ut direkta och pleiotropiska SNP-effekter i alfalfaväxter (Medicago sativa L.) med hjälp av orsaksdiagraminlärning
Varför detta spelar roll för jordbruk och mat
Alfalfan är en central gröda i modern jordbruksekonomi: den föder mjölkkor och bidrar till friska jordar. Trots det har förädlingen av bättre alfalfa — plantor som klarar vintern, står emot skador och ger foder av hög kvalitet — försvårats av den stora genetiska komplexiteten. Denna studie presenterar ett nytt sätt att gå från långa, förvirrande listor med DNA-markörer till tydliga orsak-och-verkan-kartor som visar vilka delar av genomet som faktiskt driver viktiga stjälkegenskaper, och vilka som bara följer med i förbifarten.
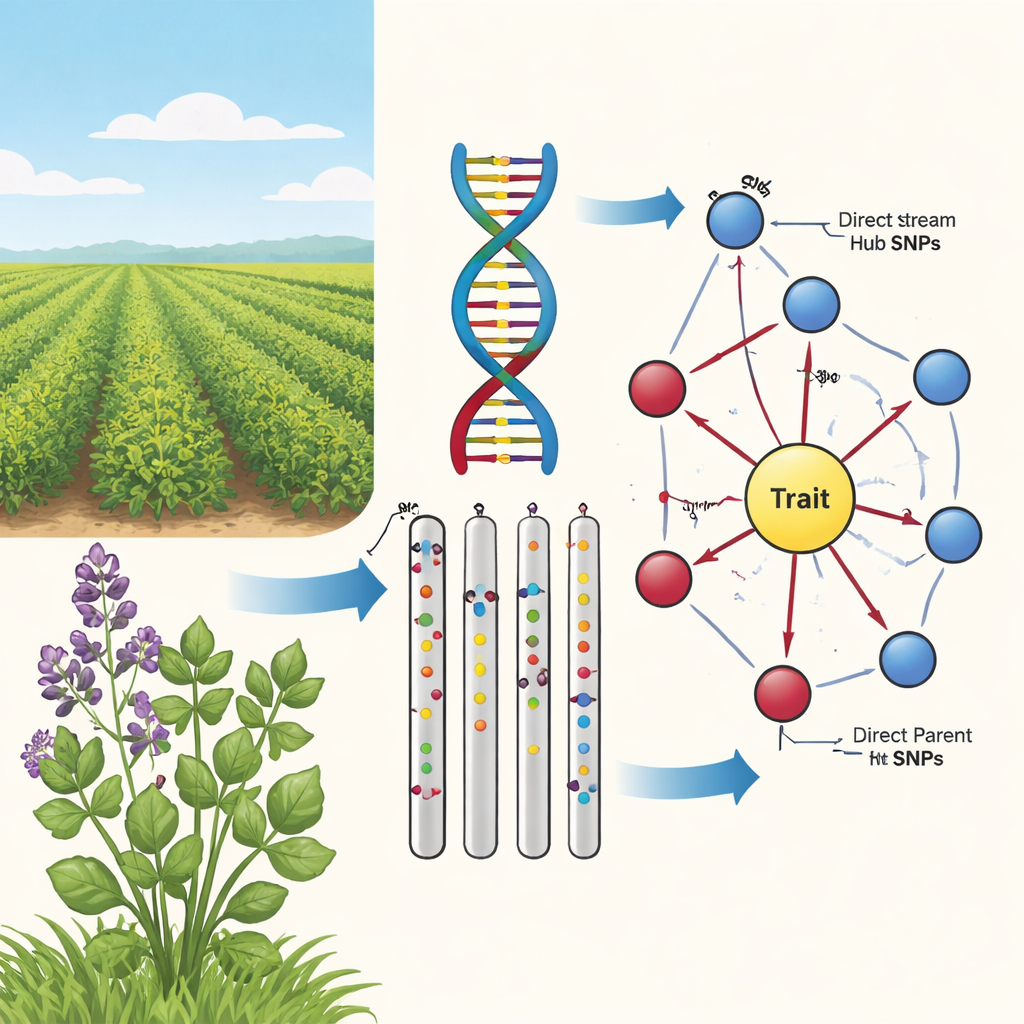
Från lösa samband till orsak och verkan
Traditionella genome-wide association-studier skannar genomet efter DNA-variationer, så kallade SNP:er, som tenderar att förekomma tillsammans med en egenskap, till exempel stjälkfärg eller överlevnad under vintern. I alfalfa är situationen dock särskilt invecklad: den har fyra kopior av varje kromosom, stora DNA-segment rör sig tillsammans och populationerna är genetiskt blandade. Det skapar en "korrelationsdimma" där många markörer ser viktiga ut men bara några få verkligen påverkar egenskapen. Författarna menar att förädlarna behöver mer än enkla statistiska samband; de behöver veta vilka markörer som ligger på de verkliga kausala vägarna från genotype till synliga växtegenskaper.
Hur den nya ramen fungerar
Forskarna byggde en tvåstegsmetod som kombinerar modern maskininlärning med idéer från kausal grafteori. Först använde de en teknik kallad Double Machine Learning för att skärma av cirka 2 400 SNP:er i 500 alfalfagenotyper. Detta steg tar bort påverkan från dolda faktorer som familjebakgrund och geografi, genom att använda huvudkomponenter av genomet som proxyvariabler. Resultatet är en renare bild av vilka markörer som fortfarande visar en direkt effekt på egenskaper som stjälkfärg efter att dessa förväxlande influenser räknats bort. I denna filtrerade bild framträdde starka, stabila signaltoppar främst på kromosomerna 2 och 4, och nyckelmarkörer uppvisade effektskattningar vars konfidensintervall tydligt uteslöt noll, vilket tyder på verklig kausal påverkan.
Att omvandla markörer till genetiska vägnät
I andra steget använde teamet en algoritm för kausal grafinlärning, känd som PC-algoritmen, för att koppla de mest lovande markörerna till ett riktat nätverk. I dessa diagram representerar noder SNP:er och egenskapen, och pilar visar den mest sannolika riktningen för påverkan. Genom att ta bort kanter som strider mot grundläggande biologiska principer (till exempel kan inte egenskaper ändra den underliggande DNA) och bara behålla SNP:er som matar in i egenskapen, fick författarna kompakta, biologiskt rimliga kartor. Dessa "solros"-nätverk visar en lagerstruktur: en innering av Direkta Förälder-SNP:er som kopplar direkt till egenskapen, och en ytterring av Upstream-Hub-SNP:er som påverkar flera föräldrar men inte rör egenskapen direkt.
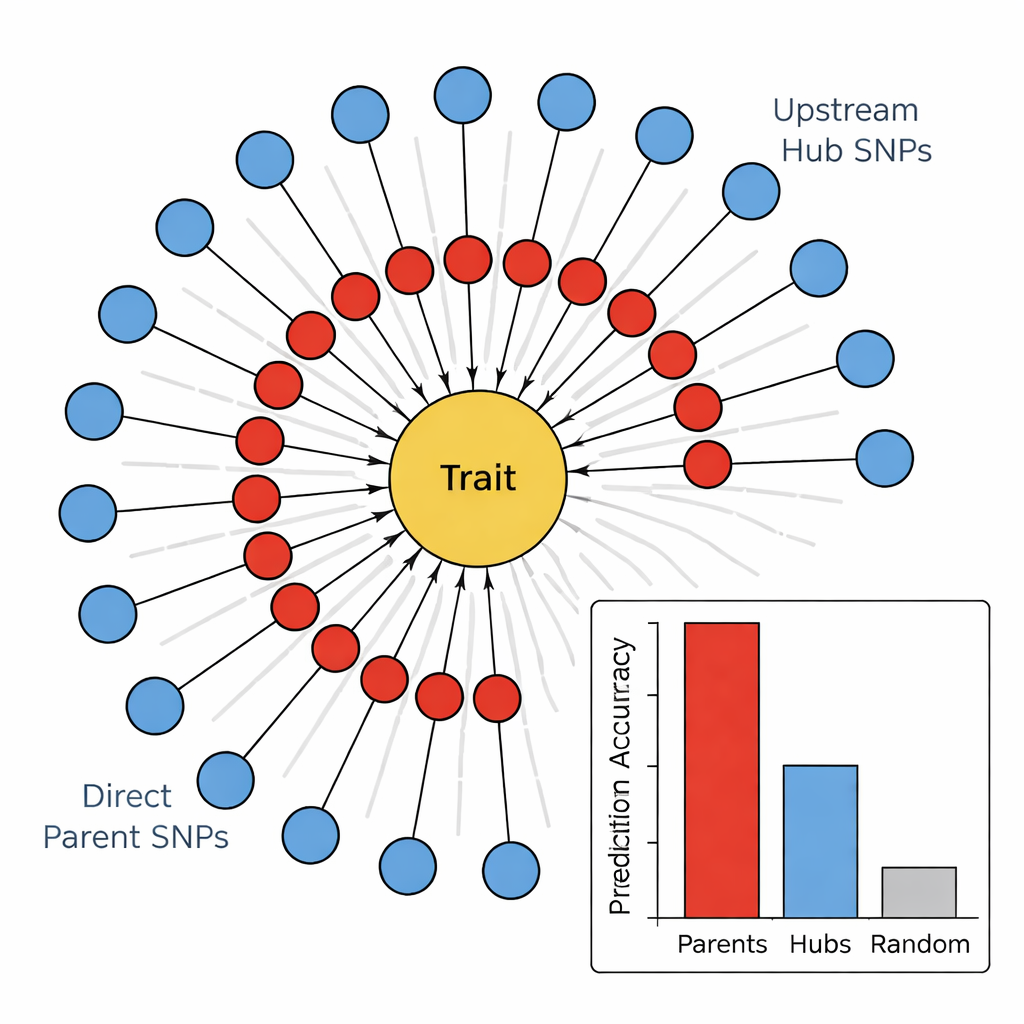
Utförare kontra regissörer i genomet
För att testa om denna hierarki var meningsfull jämförde författarna hur väl olika grupper av markörer kunde förutsäga fyra stjälkrelaterade egenskaper: stjälkfärg, stjälkfyllnad, stjälkstyrka och vinterstressskador. För alla egenskaper var Direkta Förälder-SNP:erna konsekvent de bästa prediktorerna, och förklarade ofta flera gånger mer variation än antingen slumpmässiga markörer eller Upstream-Hubs. I kontrast visade hubbarna svag eller till och med negativ prediktiv kraft, trots att de var högt sammankopplade i nätverket. När teamet kopplade dessa SNP:er till kända gener framträdde ett mönster: Direkta Föräldrar matchade ofta enzymer eller strukturella proteiner som agerar direkt på cellväggar, pigment eller skadereparation, medan hubbarna oftare motsvarade transkriptionsfaktorer och regulatoriska proteiner som brett justerar många vägar samtidigt.
Vad detta innebär för framtida alfalfaförädling
För förädlare och genetiker erbjuder studien ett sätt att skära igenom brusiga associationsresultat och fokusera på DNA-förändringar som verkligen påverkar specifika egenskaper. Författarna visar att kombinationen av dekonfunderad screening och kausala grafer kan fungera som ett inbyggt skydd mot överanpassning, och förvandla långa kandidatlistor till små, tolkbara nätverk i linje med känd biologi. Praktiskt innebär det att Direkta Förälder-SNP:er blir högprecision-märkare för att välja plantor med bättre stjälkar eller vinteröverlevnad, medan Upstream-Hubs pekar ut huvudomkopplare som kan omforma bredare stressresponser, men med potentiella kompromisser. Denna strukturella bild av genomet lägger grunden för mer pålitlig genomisk selektion i komplexa grödor och för att integrera framtida lager av data, såsom genuttryck och metabolism, i koherenta orsak-och-verkan-modeller för växtprestanda.
Citering: Lee, Y., Medina, C.A. & Xu, Z. Disentangling direct and pleiotropic SNP effects in alfalfa (Medicago sativa L.) using causal graph learning. Sci Rep 16, 5216 (2026). https://doi.org/10.1038/s41598-026-35876-w
Nyckelord: alfalfagenetik, orsaksdiagraminlärning, genomisk selektion, växtförädling, polyploida grödor