Clear Sky Science · sv
Strukturerade dissociativa PCA-metoder för dekomponering av högdimensionell neuroavbildningssignal
Lösa upp hjärnans dolda signaler
Moderna hjärnskanningar kan spela in aktivitet från hundratusentals platser varje sekund, men att förvandla denna ström av siffror till tydliga och meningsfulla nätverk är extremt svårt. Olika hjärnprocesser överlappar ofta i rum och tid, ungefär som flera radiostationer som sänder på närliggande frekvenser. Denna artikel presenterar nya matematiska verktyg som hjälper till att separera dessa intrasslade signaler på ett renare sätt, vilket lovar skarpare kartor över hjärnfunktion både för grundforskning och kliniska studier.
Varför vanliga metoder inte räcker till
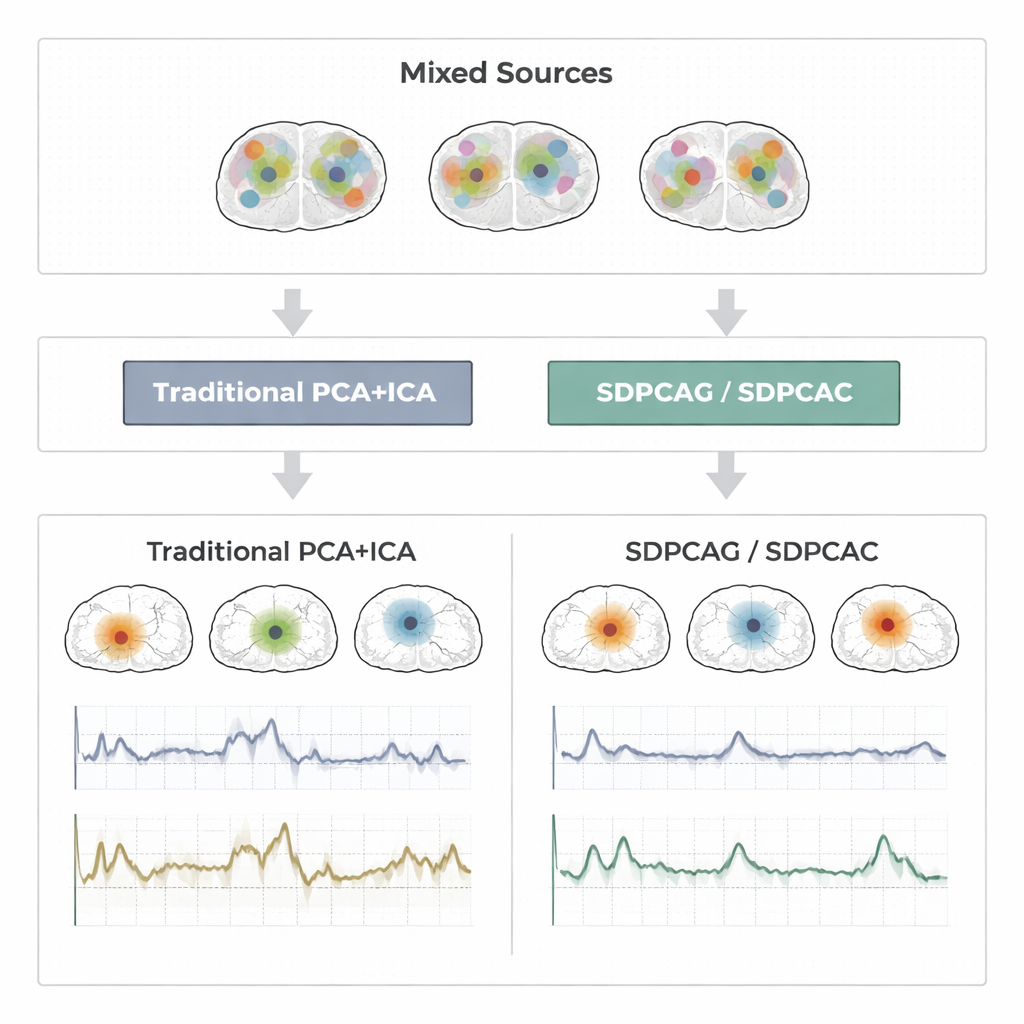
I årtionden har forskare förlitat sig på tekniker kallade principal component analysis (PCA), sparsam PCA och independent component analysis (ICA) för att komprimera och separera funktionell MRI-data (fMRI). PCA hittar mönster som förklarar det mesta av variationen i data, men varje mönster blandar information från nästan varje hjärnplats, vilket gör tolkningen svår. Sparsam PCA försöker åtgärda detta genom att tvinga varje mönster att använda endast en delmängd av platser, och ICA går längre genom att anta att de underliggande hjärnsignalerna är statistiskt oberoende. I praktiken överlappar verkliga hjärnnätverk och påverkar varandra. När det händer bryter antagandena om oberoende och sparsitet samman. Resultatet kan bli fragmenterade kartor och brusiga tidsserier som inte längre överensstämmer med hur hjärnnätverk faktiskt beter sig.
Ett nytt sätt att skilja signaler åt
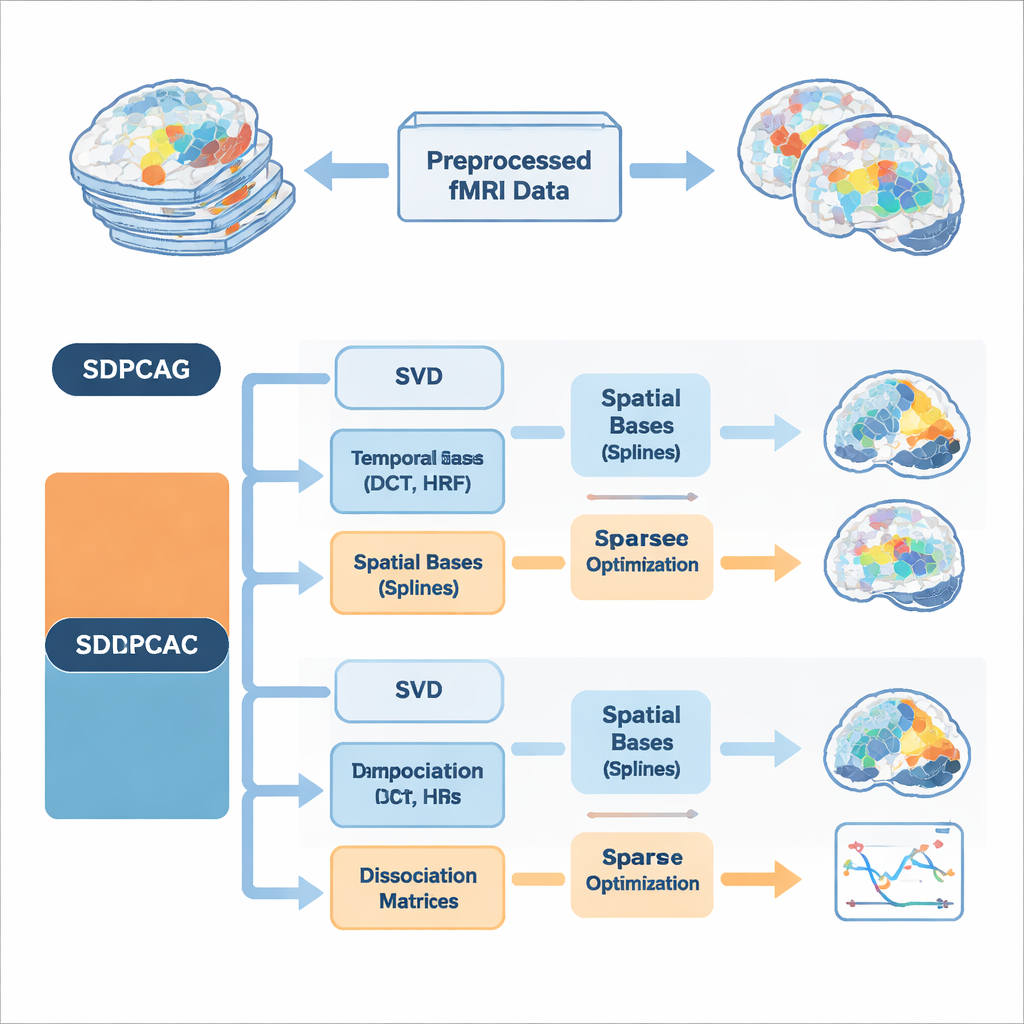
Författarna föreslår ett enhetligt ramverk kallat strukturerad dissociativ PCA, implementerat i två algoritmer med namnen SDPCAG och SDPCAC. Istället för att behandla rum och tid separat omformar metoden hela fMRI-datasetet genom en enda, omsorgsfullt utformad dekomposition. Den börjar från en standard låg-rank uppdelning av data och inför sedan speciella "dissociationsmatriser" som omviktar och roterar både spatiala kartor och tidsförlopp tillsammans. Samtidigt representerar den dessa komponenter med uppsättningar av jämna byggstenar: kosinuslika temporala vågor, modeller av hjärnans blodflödessvar på neural aktivitet, och jämna spatiala kurvor kallade splines. Genom att lära sig hur man kombinerar dessa byggstenar samtidigt som sparsitet upprätthålls — endast de viktigaste delarna behålls — kan metoden reda ut överlappande nätverk utan att påtvinga orealistisk oberoende.
Bygga in kunskap om hjärnan från början
En viktig nyhet är att algoritmerna bakar in förhandskunskap om hjärnsignaler direkt i dekompositionen, istället för att rätta till saker i efterhand. På den temporala sidan använder de diskreta kosinusfunktioner för att uppmuntra släta tidsförlopp och inkluderar standardmodeller av det hemodynamiska svaret, den fördröjda blod-oxygeneringssignalen som mäts med fMRI. På den spatiala sidan hjälper splinebaser att föredra sammanhängande, koherenta aktiveringsmönster istället för utspridda prickar. Ytterligare begränsningar styr hur många temporala och spatiala baskomponenter varje komponent får använda, vilket minskar överanpassning till brus och speglar idén att verkliga hjärnnätverk är relativt kompakta i både rum och tid. Två kompletterande optimeringsstrategier presenteras: SDPCAG uppdaterar hela matriser i block, medan SDPCAC förfinar en komponent i taget med hjälp av residualfel, vilket byter något högre kostnad mot mer flexibla justeringar.
Sätta metoden på prov
För att bedöma hur väl dessa idéer fungerar kör författarna omfattande tester på tre typer av data: noggrant utformade syntetiska fMRI-signaler med känd sanning; ett block-design motorexperiment från Human Connectome Project; och en händelse-relaterad fingerknäppningsstudie från ett oberoende laboratorium. I dessa inställningar jämför de SDPCAG och SDPCAC med ledande alternativ som kombinerar straffade matrisdekompositioner, sparsam PCA, ICA och dictionary learning. De mäter hur nära de återvunna tidsförloppen matchar kända uppgiftsmönster, hur väl spatiala kartor överensstämmer med etablerade vilotillståndsnätverk, och hur noggrant källor återvinns under varierande brusnivåer. De nya metoderna ger konsekvent renare, mer lokaliserade hjärnkartor och mindre brusiga tidsserier, och behåller stark prestanda även när data är kraftigt korrupta. En av algoritmerna, SDPCAG, förbättrar källåtervinningsnoggrannheten med ungefär 22 % jämfört med en stark konkurrerande metod, samtidigt som den körs snabbare än sin mer detaljerade syster SDPCAC.
Vad detta betyder för hjärnforskningen
Enkelt uttryckt erbjuder detta arbete ett bättre sätt att "avblanda" signalerna i fMRI-data. Genom att gemensamt modellera rum och tid, använda realistiska priorer om hur hjärnaktivitet och blodflöde beter sig, och upprätthålla smart sparsitet, producerar SDPCAG och SDPCAC hjärnnätverk som både är skarpare i bilderna och sannare mot sina underliggande tidsförlopp. Detta kan leda till mer pålitlig upptäckt av uppgiftsrelaterade aktiveringar och mer precis kartläggning av vilotillståndsnätverk, vilket i sin tur stödjer studier av tillstånd som Alzheimers sjukdom, psykiatriska störningar och andra hjärnsjukdomar. Även om det fortfarande finns utrymme att snabba upp och utöka tillvägagångssättet — till exempel för multibortsstudier eller multimodal avbildning — representerar det ett betydande steg mot att omvandla högdimensionell skanningsdata till tillförlitliga, tolkbara bilder av den arbetande mänskliga hjärnan.
Citering: Khalid, M.U., Nauman, M.M., Rehman, S.U. et al. Structured dissociative PCA methods for high dimensional neuroimaging signal decomposition. Sci Rep 16, 6911 (2026). https://doi.org/10.1038/s41598-026-35764-3
Nyckelord: fMRI-signaldekomponering, sparsam PCA, kartläggning av hjärnnätverk, blind källseparation, vilotillståndsconnectivitet