Clear Sky Science · sv
Klassificering av vita blodkroppar med anpassat djupt neuralt nätverk och visualisering av bildfunktioner med värmekartor
Varför smartare blodtester spelar roll
Ett rutinblodprov kan avslöja tidiga tecken på infektion, allergi eller till och med cancer — men i dag bygger mycket av den insikten fortfarande på experter som noggrant undersöker celler i ett mikroskop. Denna process är långsam, kostsam och inte alltid tillgänglig i mindre kliniker eller på landsbygdssjukhus. Den här artikeln beskriver ett kompakt artificiellt intelligenssystem som kan känna igen olika typer av vita blodkroppar i mikroskopbilder med hög noggrannhet, vilket potentiellt kan ge snabbare och mer tillförlitlig blodanalys till fler patienter.
Kroppens små försvarare
Vita blodkroppar är kroppens främsta försvarslinje mot bakterier och andra hot. De finns i flera huvudvarianter, vardera med olika uppgifter: vissa angriper bakterier, andra bekämpar parasiter, reagerar vid allergier eller hjälper till att koordinera långsiktigt immunförsvar. Läkare tittar ofta både på antalet och typen av dessa celler för att ställa diagnos och följa behandlingar. I dag görs detta vanligen antingen genom manuell räkning i mikroskop — en skicklig men tidskrävande uppgift — eller med stora automatiserade maskiner som många mindre laboratorier inte har råd med.
Från manuell räkning till digitala ögon
Under det senaste decenniet har forskare vänt sig till datorseende och maskininlärning för att automatisera identifiering av vita blodkroppar. Enkla program kan mäta former och färger, medan mer avancerade system använder djupt lärande som kan fånga komplexa mönster direkt från bilder. Många kraftfulla djuplärande-modeller är dock stora och kräver betydande beräkningskraft och minne, och kan drabbas av träningsproblem som att signaler försvagas inuti nätverket. Det begränsar deras användning i små kliniker, mobila hälsodevices eller sjukhus med begränsade resurser.
En slimmad men kraftfull digitalt mikroskop
Författarna presenterar en strömlinjeformad djuplärande-modell som de kallar ett anpassat djupt neuralt nätverk, eller CDNN. Den är speciellt utformad för att känna igen vita blodkroppar i mikroskopbilder. Modellen tränades och testades på två välkända dataset med blodcellbilder: ett stort och något obalanserat dataset (Raabin WBC) med fem typer av vita blodkroppar, och ett annat mindre men jämnt balanserat dataset (BCCD) med fyra typer. Innan träning ändrades alla bilder i storlek, deras ljusstyrka normaliserades och de modifierades lätt — roterades, speglades och skjuvades — för att efterlikna naturlig variation och minska överanpassning, vilket uppstår när en modell memorerar träningsexempel istället för att lära sig generella mönster.
Inuti modellens ”tankeprocess”
CDNN byggs upp av en serie byggstenar som hjälper den att lära sig effektivt samtidigt som den förblir kompakt. Dessa byggstenar inkluderar ”residuala” kopplingar som låter information passera förbi vissa lager, vilket förhindrar att träningssignaler försvagas när de färdas genom nätverket. Modellen ökar gradvis antalet interna filter när bilderna går igenom den, vilket fångar både fina detaljer och bredare former av cellkärnor och omgivande material. Trots att den har betydligt färre justerbara parametrar än välkända bildmodeller som VGG16 eller ResNet-50 uppnår CDNN mycket hög noggrannhet: cirka 98 % på Raabin-datasetet och nästan 99,6 % på BCCD-datasetet, och överträffar därmed många större toppmoderna metoder.
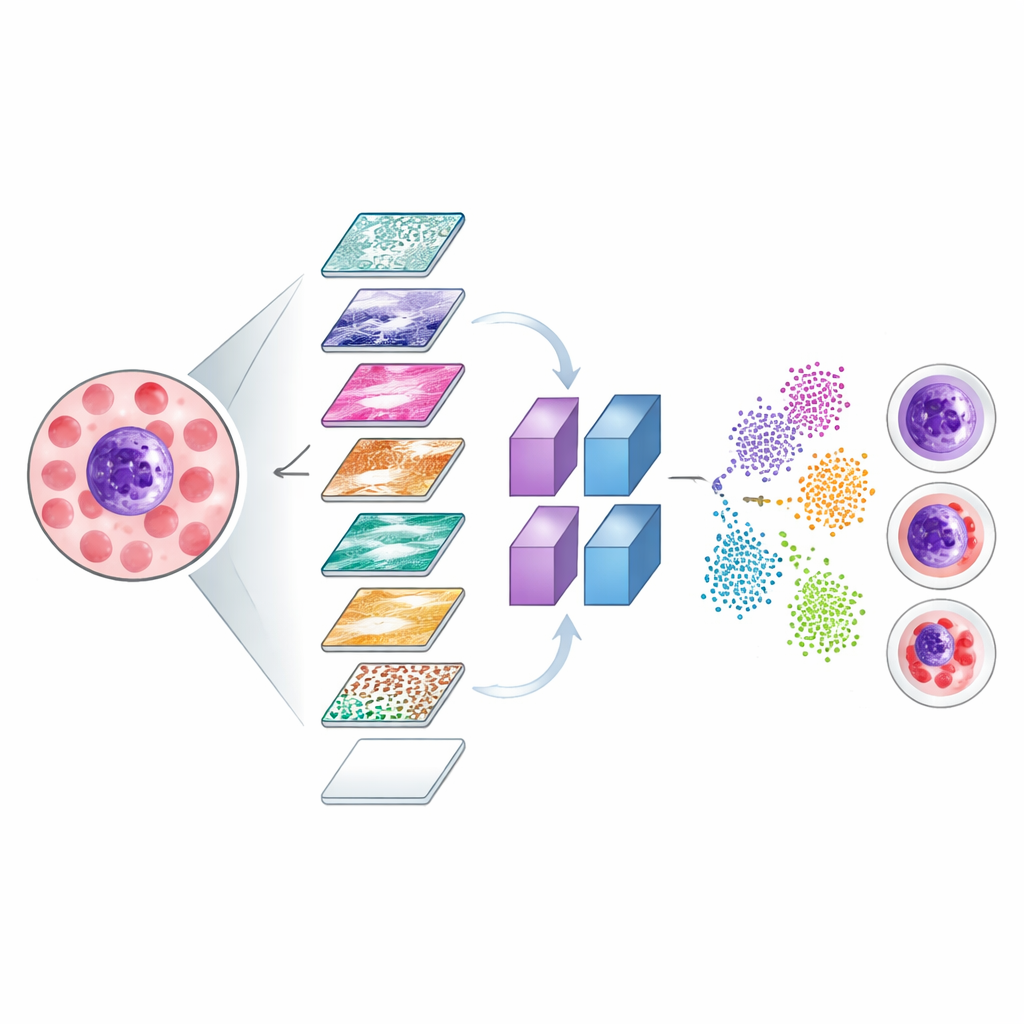
Göra osynliga beslut synliga
För att säkerställa att systemet fokuserar på medicinskt meningsfulla delar av bilderna använde forskarna två visualiseringsverktyg, kända som Grad-CAM och LIME. Dessa metoder genererar färgade värmekartor som markerar vilka regioner av en cellbild som mest påverkade modellens beslut. De ljusa zonerna i dessa kartor visade sig ofta överensstämma med viktiga strukturer som cellens kärna och omgivande cytoplasma, snarare än irrelevant bakgrund. Teamet undersökte också hur nätverket internt separerar olika celltyper genom att projicera dess interna signaler till en tvådimensionell karta, där korrekt klassificerade celler bildar tydliga kluster och felklassificerade fall kan inspekteras för att förstå var modellen har svårigheter.
Vad detta kan innebära för patienter
Kort sagt visar detta arbete att en väl utformad, relativt liten AI-modell kan sortera vita blodkroppar i mikroskopbilder med noggrannhet i nivå med eller bättre än många stora, komplexa system. Eftersom modellen är kompakt och effektiv lämpar den sig bättre för användning i mindre laboratorier, point-of-care-enheter eller till och med bärbar utrustning, vilket potentiellt för dialogen om högkvalitativ blodanalys närmare patienten. Ytterligare tester i verkliga kliniska miljöer krävs fortfarande, men angreppssättet pekar mot snabbare, mer tillgängliga och mer transparenta verktyg som kan hjälpa patologer att ställa diagnoser och upptäcka problem tidigare.
Citering: Karaddi, S.H., Bitra, H., Bairaboina, S.S.R. et al. White blood cell classification using custom deep neural network and visualizing features of the images using heatmaps. Sci Rep 16, 9311 (2026). https://doi.org/10.1038/s41598-026-35138-9
Nyckelord: vita blodkroppar, medicinsk bildbehandling, djupt lärande, bloddiagnostik, neurala nätverk