Clear Sky Science · sv
En fysik‑informerad grafneuralt nätverk för att approximera dockningsbaserad bindningsaffinitet för DYRK2 i omställning av Alzheimer‑läkemedel
Varför detta är viktigt för Alzheimer
Alzheimers sjukdom ökar globalt, men de flesta nuvarande läkemedel lindrar bara symtomen istället för att stoppa sjukdomen. Att testa nya mediciner i laboratoriet är långsamt och kostsamt, särskilt för mindre studerade hjärnproteiner som kan vara viktiga för minne och nervcellernas hälsa. Denna studie undersöker en smart genväg: att använda en fysik‑medveten artificiell intelligensmodell för att förutsäga hur väl befintliga Alzheimer‑läkemedel kan binda till ett illa utforskat protein kallat DYRK2, vilket potentiellt öppnar nya behandlingsvägar.
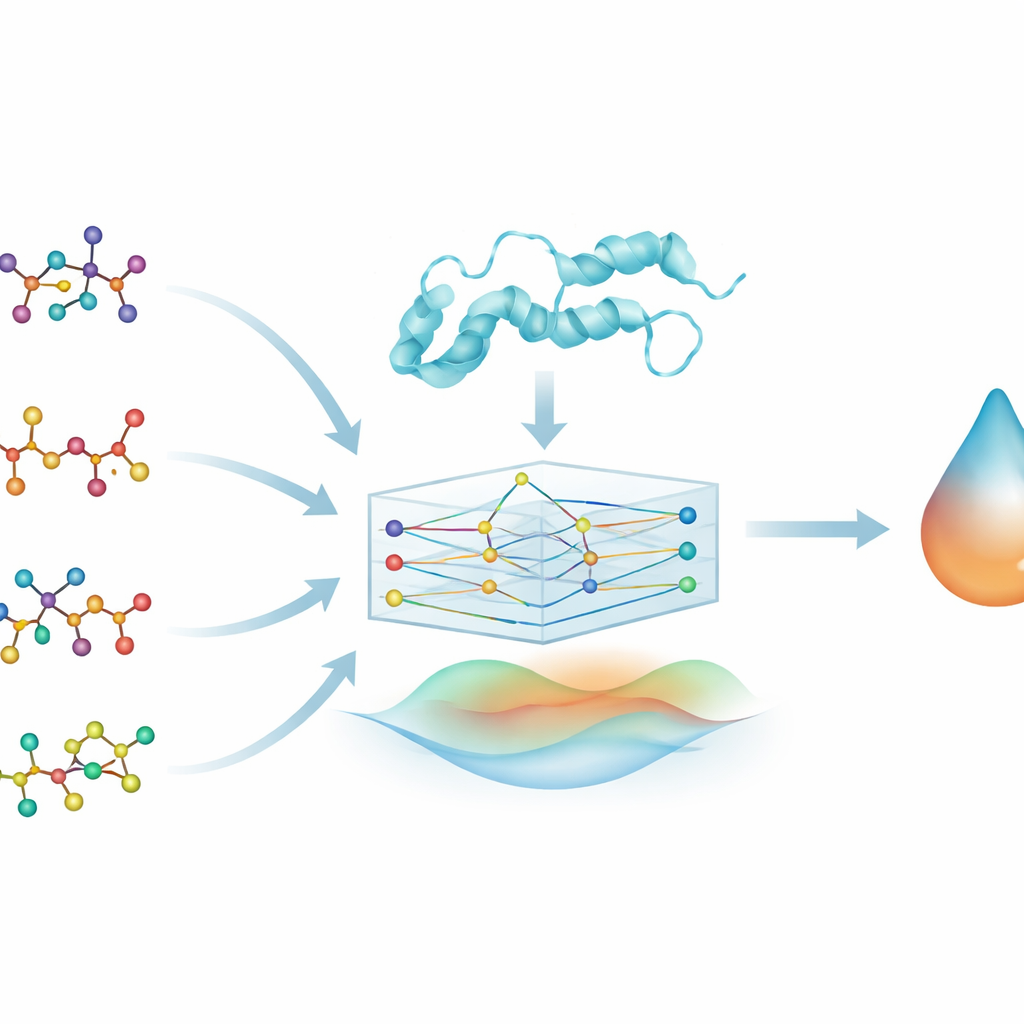
Ett nytt sätt att se på gamla läkemedel
I stället för att designa helt nya föreningar från grunden fokuserar forskarna på läkemedelsomplacering—att hitta nya användningsområden för mediciner som redan är godkända och anses relativt säkra. De undersöker fyra bekanta Alzheimer‑läkemedel (brexpiprazol, donepezil, galantamin och rivastigmin) och frågar hur tätt var och en kan binda till DYRK2, ett proteinkinas involverat i nervcellstillväxt och funktion. DYRK2 har knappt studerats i samband med Alzheimer, men tidiga fynd kopplar det till synapser, axoner och minne, vilket gör det till ett intressant mål som kan komplettera dagens terapier.
Att omvandla molekyler till nätverk
För att utforska dessa läkemedels–protein‑relationer förvandlar teamet varje läkemedelsmolekyl till en graf: atomer blir noder och kemiska bindningar blir kanter som förbinder dem. De gör något liknande för DYRK2‑proteinet och representerar dess aminosyrasekvens som en kedja av sammankopplade enheter. En typ av maskininlärningsmodell som kallas grafneuralt nätverk (GNN) kan naturligt arbeta med dessa grafformade indata, skicka information längs förbindelserna för att lära sig mönster i form och kemi. Detta gör att modellen, kallad PhysDual‑GCN, kan ”läsa” både läkemedlet och DYRK2 som interagerande nätverk snarare än som enkla strängar eller listor av egenskaper.
Att blanda fysik med artificiell intelligens
De flesta djupinlärningsverktyg inom läkemedelsupptäckt lär sig enbart från data, vilket kan göra deras inre mekanismer svåra att tolka. Här väver författarna medvetet in grundläggande fysiska idéer om hur atomer interagerar. Vid sidan av de inlärda grafegenskaperna beräknar PhysDual‑GCN två klassiska energibegrepp: en som fångar elektrisk attraktion och repulsion mellan partiella laddningar, och en annan som beskriver van der Waals‑krafternas tryck och drag. Dessa fysikbaserade energier kombineras med GNN:ens interna representation innan den ger ett förutsagt bindningsstyrkevärde. I praktiken tränas modellen att efterlikna beteendet hos standard‑dockningsprogram—i synnerhet AutoDock Vina och närliggande verktyg—men för att göra det snabbare, samtidigt som den förblir förankrad i välkända fysikaliska principer.
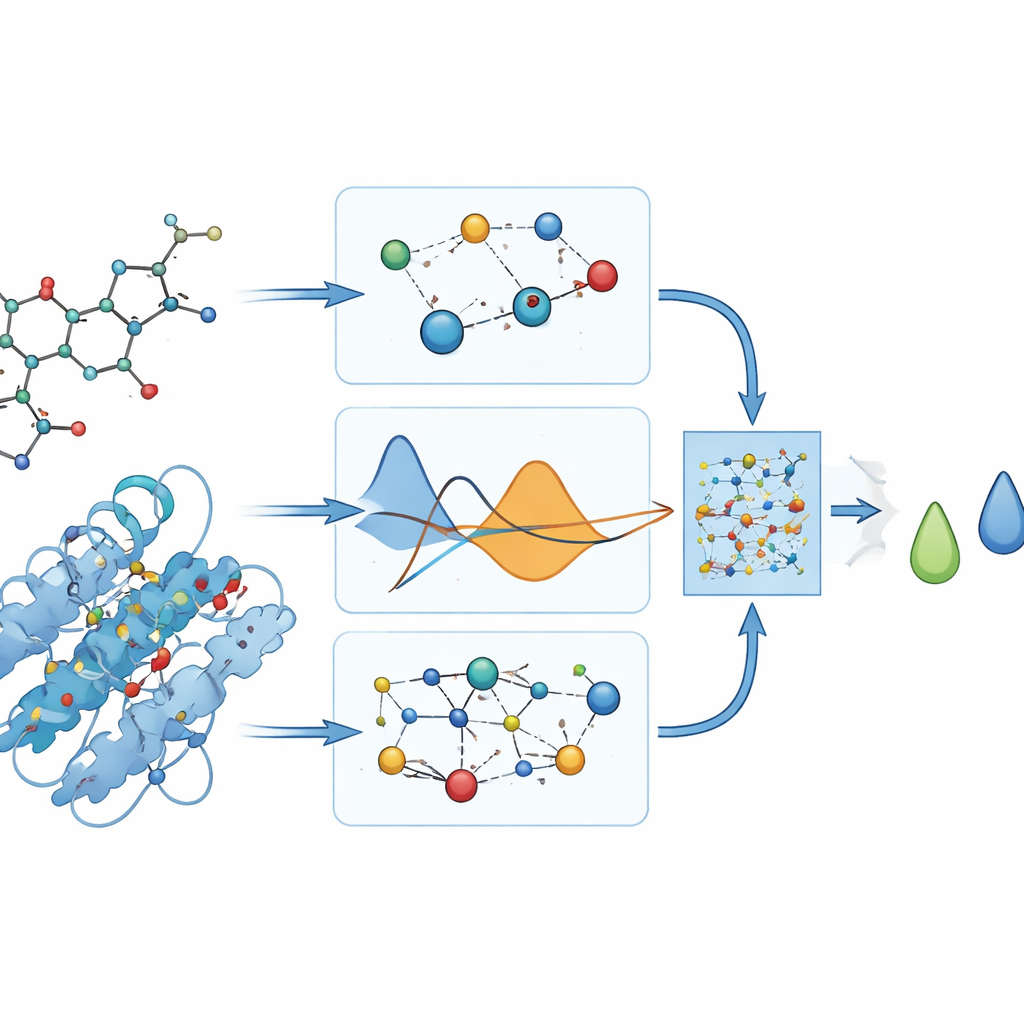
Vad modellen faktiskt förutsäger
Eftersom inga laboratoriemätningar finns för hur starkt dessa läkemedel binder till DYRK2 förlitar sig författarna på dockningsprogram för att tillhandahålla ”referens”‑bindningspoäng i energienheter. De undviker noggrant att mata in dessa poäng i träningsprocessen och använder dem i stället endast i efterhand för att bedöma hur väl PhysDual‑GCN har lärt sig. För de fyra Alzheimer‑läkemedlen reproducera modellen dockningsvärdena med små genomsnittliga fel (kring en tredjedel kilokalori per mol) och rangordnar föreningarna korrekt: donepezil och brexpiprazol framstår som de starkaste bindarna, medan galantamin och rivastigmin verkar svagare men fortfarande relativt stabila. Dessa resultat visar att den fysik‑informerade GNN:en kan fungera som ett beräkningsmässigt surrogat för långsammare dockningskörningar.
Löften och begränsningar i tillvägagångssättet
Trots dessa uppmuntrande siffror betonar författarna att deras studie har tydliga begränsningar. Endast fyra läkemedel undersöktes, och alla utvärderingar bygger på andra datorprogram snarare än verkliga biokemiska experiment. DYRK2‑proteinet modelleras huvudsakligen som en endimensionell sekvensgraf, inte som en full tredimensionell struktur, så modellen kan ännu inte ta hänsyn till bindningsfackens detaljerade form. De fysikaliska energierna själva är förenklade och använder standard parametrar och cutoff‑värden från kraftfält. Som en följd bör arbetet ses som en proof‑of‑concept: det visar att fysik‑vägledda grafneurala nätverk kan följa klassiska dockningspoäng nära i ett låg‑data‑scenario, men det bevisar ännu inte att förutsägelserna överensstämmer med verkligheten i provrör eller klinik.
Vad detta betyder för framtida Alzheimer‑forskning
För icke‑specialister är huvudbudskapet att intelligenta, fysik‑medvetna algoritmer kan hjälpa forskare att utforska nya Alzheimer‑mål som DYRK2 mycket snabbare än traditionella metoder ensamma. Genom att lyfta fram donepezil och brexpiprazol som lovande DYRK2‑bindare och erbjuda ett öppet sätt att approximera dockningsresultat ger PhysDual‑GCN en utgångspunkt för djupare laboratoriestudier. Med större läkemedelsbibliotek, rikare 3D‑proteininformation och experimentell validering skulle denna typ av modell kunna bli ett praktiskt verktyg för att skärma kandidatbehandlingar och styra insatser för läkemedelsomplacering som syftar till att bromsa eller förändra Alzheimers sjukdoms förlopp.
Citering: Gider, V., Budak, C. A physics-informed graph neural network to approximate docking-based binding affinity for DYRK2 in Alzheimer’s drug repurposing. Sci Rep 16, 8357 (2026). https://doi.org/10.1038/s41598-026-35102-7
Nyckelord: Alzheimers sjukdom, läkemedelsomplacering, grafneuronätverk, protein–ligand‑bindning, DYRK2‑kinas