Clear Sky Science · sv
Samevolution och värdbyte driver mångfalden av picornavirus och sapovirus hos malagassiska fruktfladdermöss
Varför fladdermusvirus är viktiga för oss
Fladdermöss har en anmärkningsvärd förmåga att leva sida vid sida med virus som kan vara farliga för andra djur, inklusive människor. Att förstå hur dessa virus utvecklas och sprids mellan värdar är avgörande för att kunna förutse framtida sjukdomshot. Denna studie utforskar en dold värld av tarmvirus som bärs av fruktfladdermöss på Madagaskar och visar hur uråldriga partnerskap mellan fladdermöss och virus, tillsammans med tillfälliga värdhopp, har skapat ett rikt och starkt strukturerat viralt ekosystem.
Öns fladdermöss och deras osynliga passagerare
Madagaskar är känt för sitt ovanliga djurliv, format av tiotals miljoner års isolering från det afrikanska fastlandet. Samma isolering har sannolikt också format de virus som lever i dess djur. Forskarna fokuserade på tre fruktfladdermusarter som endast finns på Madagaskar och ställde en enkel fråga: vilka tarmvirus bär de på, och hur är dessa virus släkt med sådana som redan är kända från afrikanska fladdermöss och andra djur? De koncentrerade sig på två virusfamiljer, picornavirus och sapovirus, som kan orsaka tarm- och leversjukdomar hos många däggdjur men som har studerats betydligt mindre hos fladdermöss än rubriksättande virus som coronavirus.
Läsa virala genom ur fladdermusspillning
Under flera år samlade teamet in mer än 800 avförings- och urinsamples från fladdermöss vid grottor och viloplatser runtom på Madagaskar. Istället för att söka efter ett virus i taget använde de en bred, DNA-liknande metagenomisk skanning som läser allt genetiskt material i ett prov och sedan använder kraftfulla datorverktyg för att identifiera vilka bitar som hör till vilka virus. Från detta rekonstruerade de 13 kompletta virala genom och 38 partiella. Dessa sekvenser tillhörde en överraskande bred uppsättning virustyper, inklusive flera sorters picornavirus—såsom hepatovirus och kobuvirus—såväl som sapovirus, som alla cirkulerade tyst i kolonier av malagassiska fruktfladdermöss.
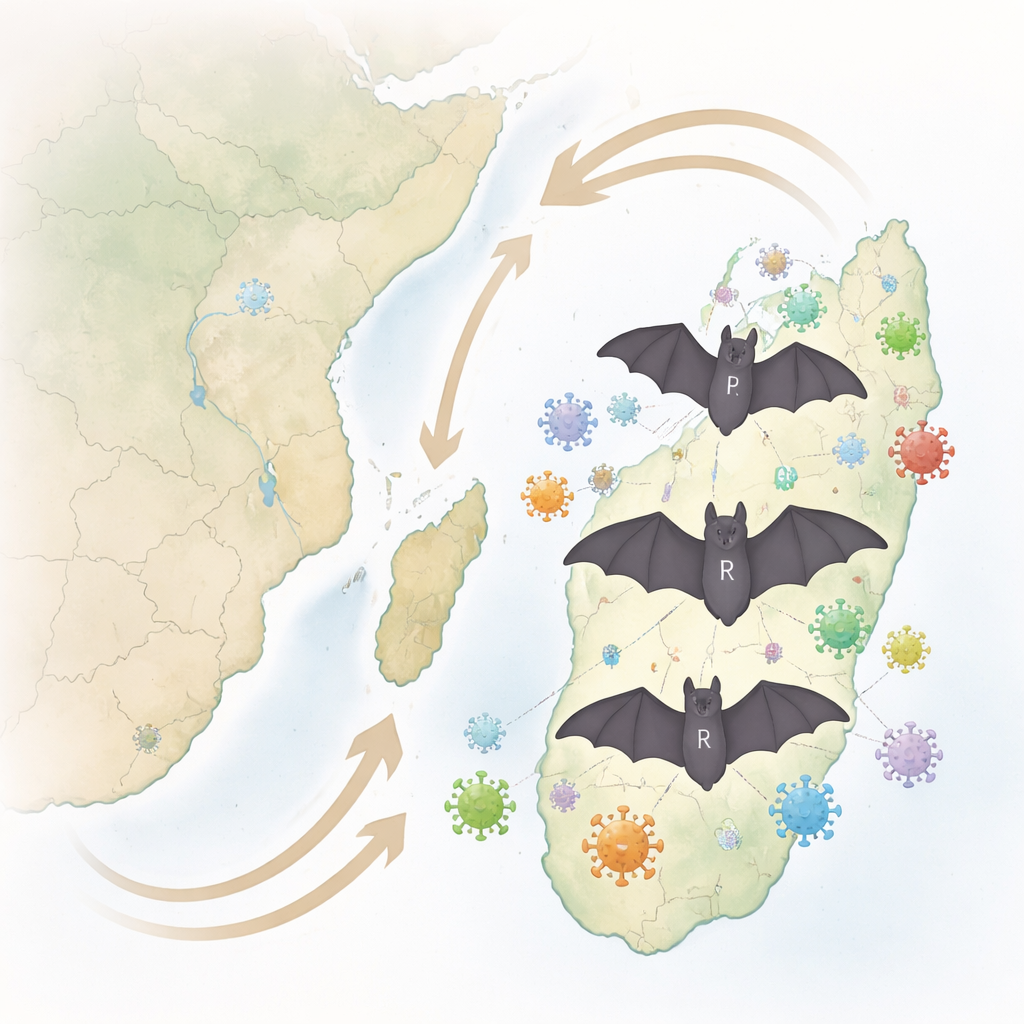
Släktträd över oceaner
För att förstå var dessa virus kom ifrån byggde forskarna evolutionära ”släktträd” som jämförde de nya genomen med hundratals referensvirus från hela världen. Om och om igen fann de att virus i malagassiska fladdermöss var närmast besläktade inte med dem hos människor eller boskap, utan med virus som hittats i närbesläktade fladdermusarter på det afrikanska fastlandet. Till exempel klustrade virus från malagassiska Eidolon- och Rousettus-fladdermöss bredvid virus från deras afrikanska systerarter, Eidolon helvum och Rousettus aegyptiacus. Detta tyder på att virala linjer har följt fladdermuslinjer över långa tidsperioder, ett mönster känt som co-speciation (samspeciering), snarare än att ständigt hoppa mellan många olika värdar.
När virus byter skepp
Berättelsen är dock inte en om strikt trohet. Genom att jämföra virus- och värdträd och skanna genomer efter tecken på blandning upptäckte teamet spår av värdbyte och rekombination—ögonblick när ett virus flyttade in i en ny värdart eller bytte genetiska segment med ett besläktat virus. Dessa händelser var särskilt tydliga i vissa genomregioner som är kända för att påverka hur virus interagerar med värdens immunsystem och vilka arter de kan infektera. Intressant nog, även om några av de malagassiska fladdermusarterna delar grottor och födovägar, såg forskarna få tecken på att samma virala stammar fritt cirkulerar mellan dem idag. Istället tenderar varje fladdermusart att hysa sina egna uppsättningar virus, vilket antyder att de flesta korsartshopp skedde långt tillbaka i tiden eller över Mozambiquekanalen mellan afrikanska och malagassiska fladdermöss.

Vad detta betyder för människors hälsa
För närvarande är de virala linjer som upptäckts i dessa fladdermöss avlägsna från dem som är kända för att infektera människor. De verkar specialisera sig på särskilda fladdermusvärdar, formade av långsiktig samevolution med endast tillfälliga hopp. Det betyder inte att de är utan risk—människor på Madagaskar och delar av Afrika jagar fladdermöss för föda, och rekombination kan ibland föregå uppkomsten av nya, mer anpassningsbara virus. Men huvudbudskapet i detta arbete är att majoriteten av diversifieringen i dessa fladdermusvirus kommer från långsam, delad evolutionär historia snarare än konstant, kaotiskt spillover. Att kartlägga den dolda historien är ett avgörande steg för att bedöma vilka virala grupper som är mer benägna att korsa över till människor och vilka som nöjer sig med att förbli en del av fladdermössens unika ö-mikrobiom.
Citering: Kettenburg, G., Ranaivoson, H.C., Andrianiaina, A. et al. Co-speciation and host-switching drives diversity of picornaviruses and sapoviruses in Malagasy fruit bats. Sci Rep 16, 6583 (2026). https://doi.org/10.1038/s41598-025-34969-2
Nyckelord: fladdermusvirus, Madagaskar, virusets evolution, värdbyte, zoonotisk risk