Clear Sky Science · sv
Genomsekvensering, de novo-assembly och annotering av den kommersiellt viktiga bambun Bambusa tulda Roxb
En snabbväxande gräsart med stor potential
Bambu kan se ut som en enkel trädgårdsväxt, men är i själva verket en kraftfull naturresurs för byggande, papper och till och med framtida biobränslen. En allmänt använd art, Bambusa tulda eller bengalisk bambu, växer snabbt, lagrar stora mängder vedartat material och blommar mycket sällan. Fram tills nu saknade forskare ett komplett "instruktionshäfte" för denna art. Den här artikeln beskriver hur forskare avkodade och organiserade hela DNA-sekvensen för B. tulda och skapade en grundläggande resurs som kan hjälpa till att förbättra bambu för industri, bevarande och klimatvänliga tekniker.
Varför avkoda bambuns DNA?
Bambusa tulda är vanlig på den indiska subkontinenten och i delar av Sydostasien, där dess starka stammar används i landsbygdens byggande, möbler och hantverk. Den väcker också intresse som källa till pappersmassa och förnybar energi. Ändå beter sig B. tulda på gåtfulla sätt: den kan växa mycket snabbt, lagra stora mängder segt vedartat material och sedan vänta omkring 50 år innan den blommar, ibland så att alla plantor i ett område blommar samtidigt. Utan en fullständig genomsekvens kunde forskare endast gissa vilka gener som styr dessa egenskaper. Genom att läsa och sätta ihop dess DNA ville författarna bygga en referenskarta som framtida forskare kan använda för att studera tillväxt, blomning, sjukdomsresistens och mer.
Mäta och läsa ett jättegenom
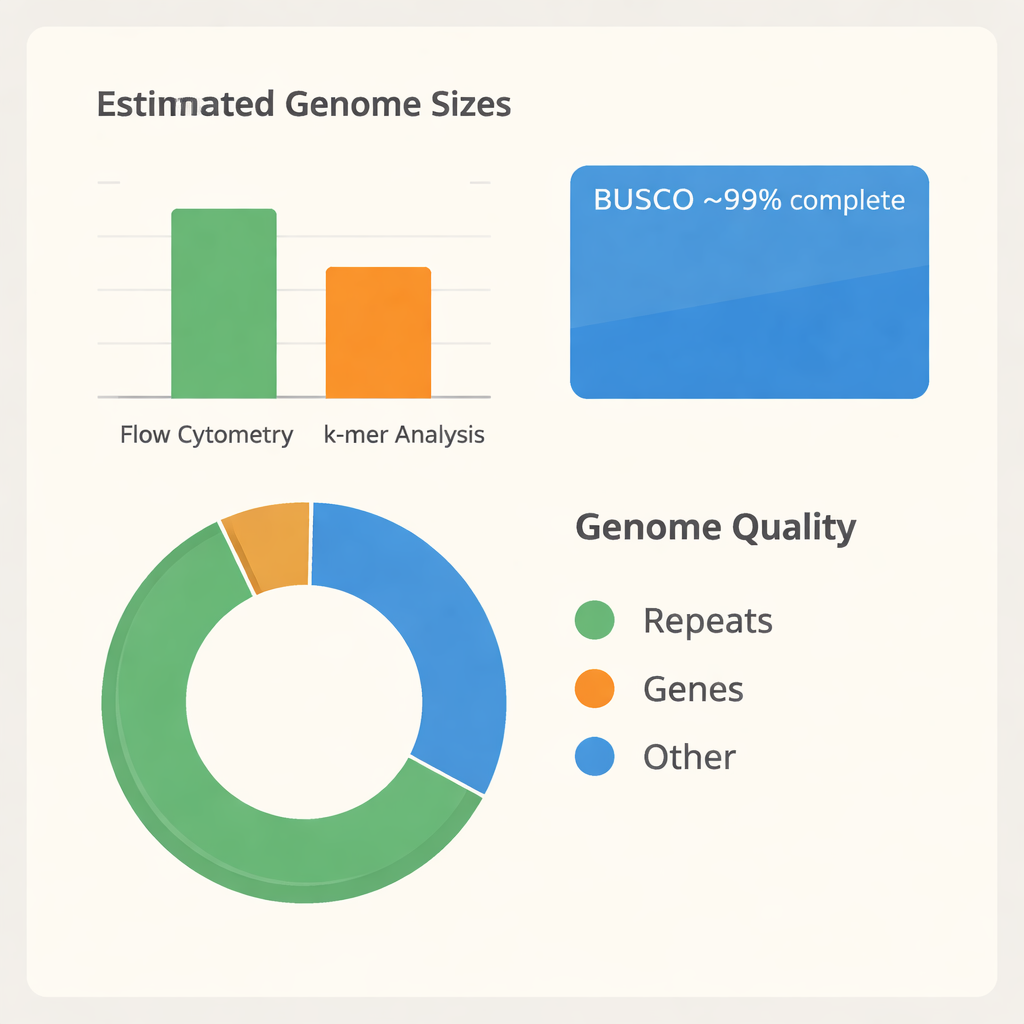
Teamet behövde först förstå hur stort B. tuldas genom är. Med en teknik kallad flödescytometri jämförde de DNA-innehållet i B. tuldas bladceller med tomat och majs, två växter vars genomstorlekar redan är kända. Detta antydde ett diploid genom på omkring 3 miljarder DNA-”bokstäver”. De använde sedan ett andra, oberoende angreppssätt baserat på hur korta DNA-fragment överlappar (k-mer-analys), vilket uppskattade en något mindre storlek på omkring 2,34 miljarder bokstäver och avslöjade att stora delar av genomet är repetitiva och sannolikt duplicerade. Med dessa mätningar i hand extraherade de mycket långt, högkvalitativt DNA från unga blad och sekvenserade det med avancerad PacBio HiFi-teknik, vilket genererade över 116 miljarder baser rådata — tillräckligt för att läsa genomet dussintals gånger om.
Sätta ihop bambuens ritning
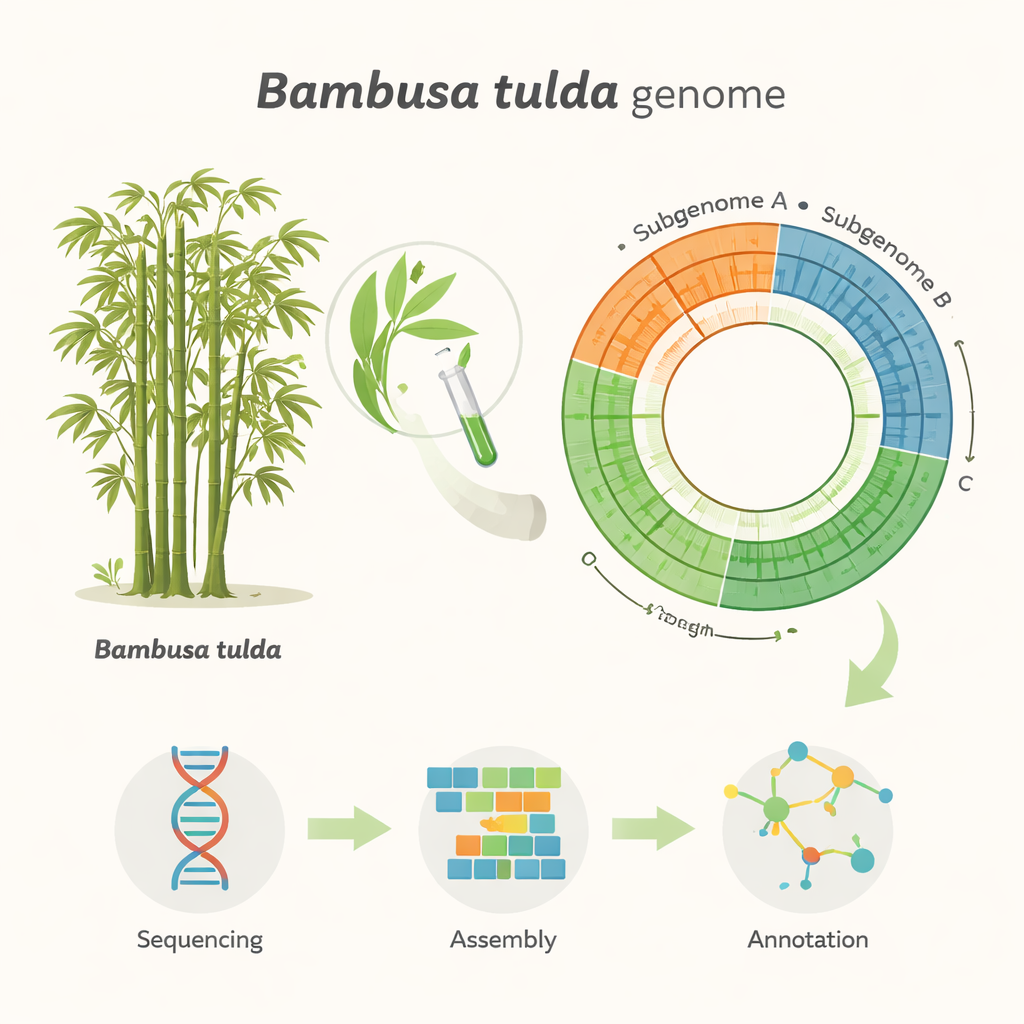
Att förvandla miljontals DNA-avläsningar till ett ordnat genom är som att lägga ett massivt pussel utan bild på paketet. Forskarna använde specialiserad mjukvara för att bygga både en sammanslagen primär assembly och två separata haplotyper, som speglar de två föräldrarnas kopior av genomet. Efter att ha tagit bort duplicerade och organell-ursprungna delar landade de i en strömlinjeformad "haploid" assembly av 43 stora segment, som täcker omkring 1,37 miljarder baser. Dessa segment faller in i tre subgenom, märkta A, B och C, vilket är förenligt med B. tuldas komplexa, polyploida ursprung. Ett allmänt använt kvalitetsprov kallat BUSCO visade att omkring 99 % av förväntade växtgener är närvarande och intakta, vilket indikerar att assemblyn både är fullständig och pålitlig för vidare studier.
Gener, repetitioner och evolutionära ledtrådar
När genomet väl var sammanfogat var nästa steg att identifiera dess fungerande delar. Genom att kombinera tre bevislinjer — förutsägelser från DNA-sekvensen själv, likhet med gener från andra bambuarter och RNA-data från aktivt uttryckta gener — annoterade teamet 56 890 proteinkodande gener, vilka upptar ungefär en femtedel av genomet. De katalogiserade också stora mängder icke-kodande RNA, inklusive över ett tusen transfer-RNA- och ribosom-RNA-gener som stödjer proteinproduktionen. Slående nog består omkring två tredjedelar av genomet av repetitiva element, särskilt mobila DNA-segment som kopierar sig och flyttar runt. Dessa repetitioner hjälper till att förklara varför tidigare storleksuppskattningar skilde sig åt och pekar på en dynamisk evolutionär historia. Genom att jämföra proteinfamiljer över tolv andra bambuarter, tillsammans med majs och banan som släktingar, placerades B. tulda tydligt bland paleotropiska vedartade bambuer med en hexaploid bakgrund, vilket bekräftar att dess genom är uppbyggt av flera ancestrala kopior.
En ny grund för framtida bambuforskning
För icke-specialister är huvudresultatet att B. tulda nu har ett högkvalitativt referensgenom — en indexerad, sökbar ritning av dess DNA. Denna resurs kommer att låta forskare zooma in på gener som styr snabb tillväxt, vedartning och fördröjd blomning, och jämföra dem med gener i andra gräsarter. Den kommer också att stödja ansträngningar att avla eller konstruera bambusorter bättre lämpade för byggnad, papper eller energi samtidigt som naturliga populationer bevaras. Kort sagt, genom att kartlägga det genetiska landskapet hos denna kommersiellt viktiga bambu, lägger studien grunden för smartare användning av en av världens mest mångsidiga växter.
Citering: Kundu, S., Rupp, O., Dey, S. et al. Genome sequencing, de novo assembly and annotation of the commercially important bamboo, Bambusa tulda Roxb. Sci Data 13, 175 (2026). https://doi.org/10.1038/s41597-026-06679-5
Nyckelord: bambugenom, Bambusa tulda, växtgenetik, vedartade gräs, förnybara biomaterial