Clear Sky Science · sv
En kromosomnivå-genomsekvens av Homatula variegata från Yangtze-flodens avrinningsområde
En liten bäckfisk med en stor genetisk historia
I de snabbströmmande, steniga bäckarna som matar Kinas övre Yangtze‑flod lever en liten, randig slöjstjärt kallad Homatula variegata. Den uppskattas både som matfisk och för akvarier hemma, men fram till nu var nästan ingenting känt om dess DNA‑ritning. Denna studie levererar den första nästan kompletta, kromosom‑för‑kromosom‑kartan av artens genom och öppnar dörren för smartare bevarande, mer effektiv avel och djupare insikt i hur livet anpassar sig till kalla, strömmande bergsvatten.
Varför kartlägga DNA hos en anspråkslös fisk?
Även om denna slöjstjärt bara blir ungefär 14 centimeter lång spelar den en oproportionerligt stor roll i lokala flodekosystem och regionalt vattenbruk. Den trivs i medelhöga bäckar med grusbottnar och jämn ström och lever av insekter, organiskt skräp och små fiskar. Eftersom den är både god och färgstark finns ett växande intresse för att odla den som en inhemsk prydnads‑ och matfisk. Men att föda upp och skydda en art är betydligt svårare utan en exakt genetisk referens. Ett komplett genom fungerar som en detaljerad reservdelslista och kopplingsschema, och visar vilka gener som formar tillväxt, färg, sjukdomsresistens och förmågan att klara av snabbt, kallt vatten. Hittills fanns ingen art i denna gren av fiskfamiljen med en så högkvalitativ referens, vilket lämnade ett stort kunskapsgap inom sötvattenfiskgenetik.
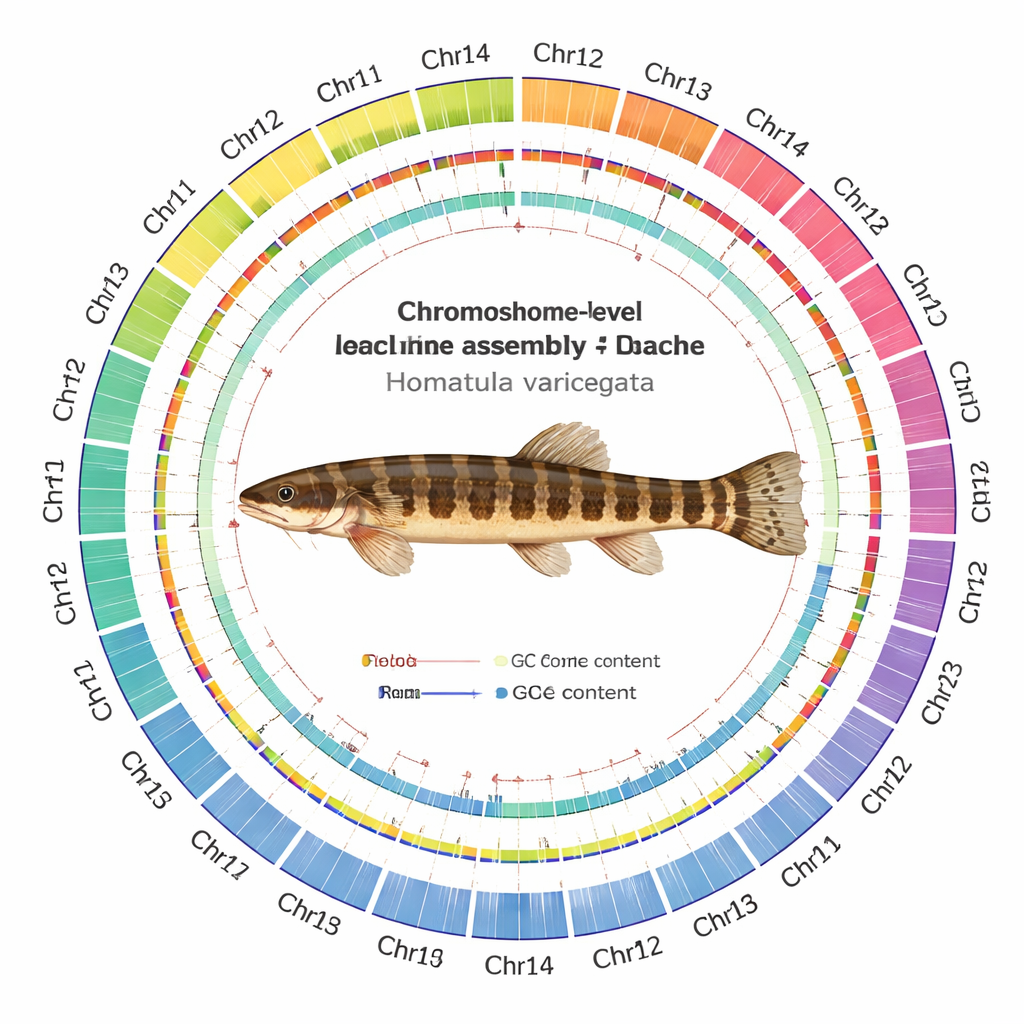
Att bygga en kromosom‑för‑kromosom‑DNA‑karta
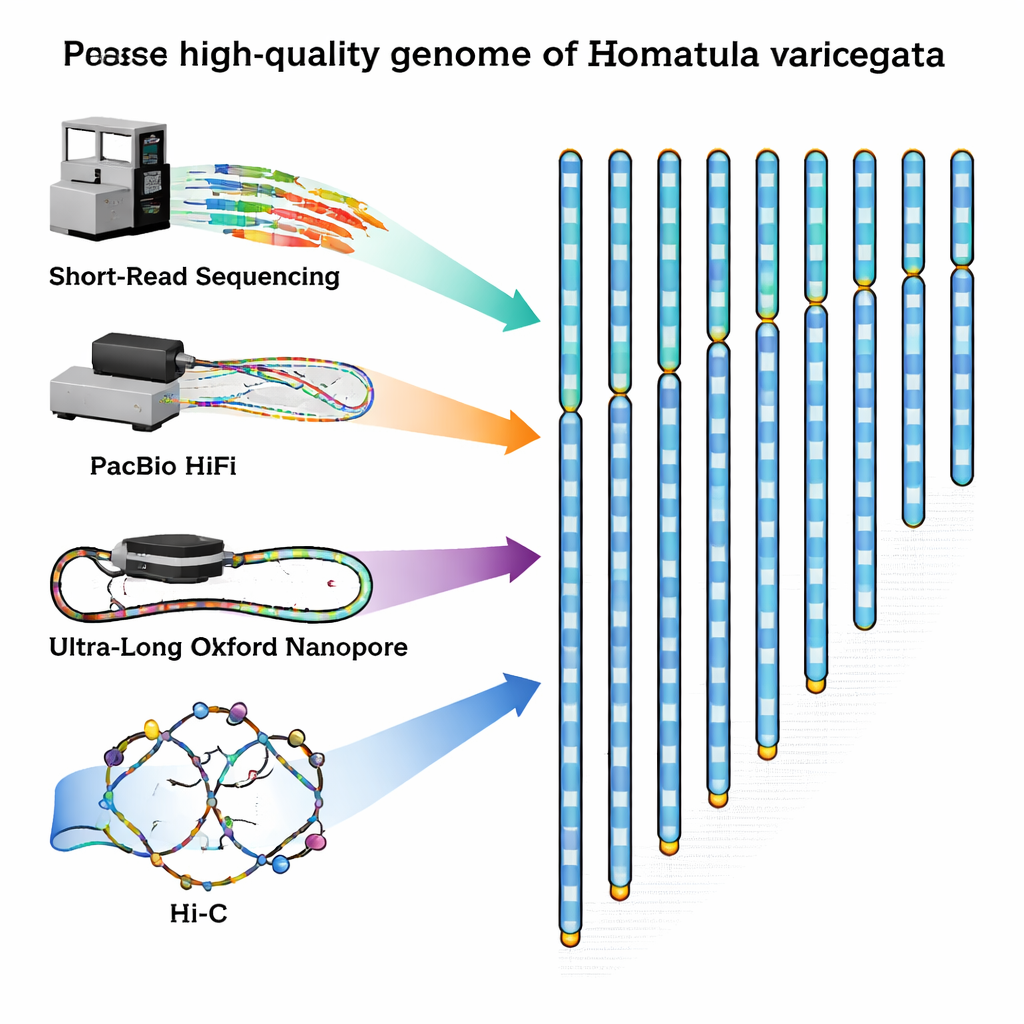
För att fylla detta gap fångade forskarna en frisk vuxen hanne från Qingyi‑floden, en biflod till Yangtze, och extraherade noggrant DNA och RNA från dess blod. De kombinerade sedan flera toppmoderna sekvenseringsmetoder, var och en med olika styrkor. Kortläsningsmaskiner från Illumina producerade mycket stora mängder högprecisionstexter av DNA. PacBio HiFi‑teknik levererade något längre fragment med utmärkt noggrannhet, medan Oxford Nanopore‑enheter genererade ultralånga strängar som kan sträcka sig över svåravkodade, repetitiva regioner. Slutligen fångade en metod kallad Hi‑C hur DNA‑strängar viks och interagerar inne i cellkärnan, vilket gav en 3D‑kontaktkarta som hjälper till att länka ihop fragment till kompletta kromosomer i korrekt ordning.
Vad det nya genomet visar
Genom att väva samman dessa data med modern monteringsprogramvara och noggranna kvalitetskontroller producerade teamet ett genom på 641 miljoner DNA‑bokstäver organiserat i 24 kromosomer. Anmärkningsvärt är att varje kromosom är monterad som ett enda kontinuerligt stycke, där 22 saknar luckor helt och endast två andra har mycket små luckor. De kunde lokalisera 24 sannolika centromerer—kromosomernas centrala ”bälte”—och upptäcka de flesta skyddande telomerhättorna i kromosomernas ändar. Forskarna katalogiserade 24 479 proteinkodande gener och kunde tilldela sannolika funktioner till cirka 93 % av dem genom jämförelse med stora internationella databaser. De kartlade också landskapet av upprepat DNA och fann att mer än en fjärdedel av genomet består av mobila genetiska element, särskilt DNA‑transposoner, som kan hoppa runt i genomet och ibland driva evolution.
Testning av kvaliteten under huven
Hög nivå‑siffror är bara meningsfulla om underliggande karta är pålitlig. Forskarna körde därför monteringen genom ett batteri av tester. Läsningar från alla sekvenseringsplattformar linjerade tillbaka mot det nya genomet i mycket höga andelar, med jämn täckning över större delen av kromosomerna. Oberoende verktyg som räknar korta DNA‑mönster antydde att nästan allt förväntat sekvensinnehåll finns med, och standardtester för genkompletthet visade att de allra flesta universella fiskgener är intakta. Hi‑C‑kontaktkartorna bildade rena, fyrkantiga mönster längs varje kromosom, med lite utspritt signal mellan dem, vilket indikerar att segmenten är korrekt hopfogade snarare än hopblandade.
Från DNA‑karta till verklig påverkan
För en icke‑specialist kan detta arbete låta som en teknisk triumf i sig, men dess konsekvenser är praktiska och långtgående. Att ha ett nästan änd‑till‑änd‑genom för Homatula variegata ger forskare en referens mot vilken de kan jämföra vilda populationer, följa genetisk mångfald och upptäcka tecken på inavel eller lokal anpassning. Uppfödare kan söka efter DNA‑markörer kopplade till önskvärda egenskaper som snabb tillväxt, tålighet eller slående färgteckning, och på så vis snabba upp selektiv avel samtidigt som artens naturliga karaktär bevaras. Ekologer kan undersöka hur denna slöjstjärt har utvecklats för att leva i kalla, snabbt rinnande bergsbäckar—insikter som också kan informera förvaltningen av närstående arter. Kort sagt förvandlar detta kromosomnivå‑genom en anspråkslös flodfisk till en kraftfull modell för att förstå—och skydda—det rika livet i asiatiska sötvattensmiljöer.
Citering: Tang, Y., Wu, Q., Wang, Y. et al. A chromosome level genome assembly of Homatula variegata from the Yangtze River basin. Sci Data 13, 303 (2026). https://doi.org/10.1038/s41597-026-06667-9
Nyckelord: fiskgenom, kromosommontering, sötvattensbiologisk mångfald, uppfödningsgenetik, Yangtze‑flodens slöjstjärt