Clear Sky Science · sv
En kuraterad resurs med kemolit-autotrofa genom och markörgener för förutsägelse av CO₂-fixeringsvägar
Mikrober som hjälper till att balansera jordens kolbudget
Gömda i jordar, hav och extrema miljöer kan vissa mikrober bygga sin egen biomassa med koldioxid (CO₂) som huvudsaklig kolkälla. Dessa mikroskopiska kemister är avgörande för att hålla jordens kolcykel i balans och kan inspirera nya sätt att fånga industriell CO₂. Ändå har forskare hittills saknat ett enkelt, tillförlitligt sätt att titta på en mikros genmaterial och avgöra vilken CO₂-fixeringsstrategi den använder. Denna studie presenterar ett kuraterat genkatalog och ett nytt datorverktyg, AutoFixMark, utformat för att fylla den luckan.
Flera vägar för att omvandla luft till biomassa
Alla organismer som fixerar CO₂ gör det inte på samma sätt. Mikrober har utvecklat minst sju naturliga vägar som omvandlar CO₂ till organiskt material. Vissa, som Calvin–Benson–Bassham-cykeln som är vanlig i växter och många bakterier, är välkända; andra, såsom den reduktiva glycinvägen som först upptäcktes 2020, är fortfarande dåligt kartlagda. Dessa vägar finns spridda över många grenar av livets träd och återanvänder ofta liknande enzymer, vilket gör det förvånansvärt svårt att skilja dem åt enbart utifrån genomsekvenser. Befintlig mjukvara kan förutsäga breda metaboliska förmågor, men den har inte optimerats eller noggrant testats för att exakt bestämma vilka CO₂-fixeringsvägar som används.
Bygga en ren referenskarta över CO₂-fixerande mikrober
Forskarna började med att samla två noggrant granskade genomekataloger. Först valde de 15 välstuderade mikrober vars CO₂-fixeringsvägar har kartlagts i detalj. Dessa referensorganismer, som spänner över flera bakteriella och arkala grupper, tjänade som ritningar för att definiera de nyckelenzymer som verkligen är distinktiva för varje väg. Därefter skapade de en referensuppsättning på 347 kemolit-autotrofa genom—mikrober som får energi från oorganiska kemikalier och bygger biomassa från CO₂. Varje genom i denna större samling kopplades manuellt till särskilda CO₂-fixeringsvägar utifrån litteraturen, vilket gav en robust sanningsuppsättning för att testa förutsägelser.
Markörgener och enkla regler istället för svarta lådor
Med hjälp av de 15 referensgenomen identifierade teamet ”markörgener” för var och en av de sju CO₂-fixeringsvägarna och kartlade dem till standardiserade KEGG Orthology (KO)-identifierare. Istället för att förlita sig på ogenomskinlig maskininlärning kodade de transparenta regler för hur dessa markörer kombineras. Vissa reaktioner kan utföras av någon av flera alternativa enzymer, vilket hanteras av en ”one_of”-regel. Andra förlitar sig på multisubenhetskomplex och måste ha ”all_of” ett definierat set av KO:er. För den reduktiva glycinvägen, där inte alla komponenter är fullständigt förstådda, använder verktyget ”at_least”-regler som kräver ett minimalt antal subenheter. Dessa logiska regler lagras i en maskinläsbar JSON-fil som utgör kärnkunskapsbasen för AutoFixMark.
Ett lättviktigt verktyg som överträffar etablerad programvara
AutoFixMark i sig är ett litet, regelbaserat program skrivet i Python. Det tar som indata en lista med KO-ID för generna i ett mikrobiskt genom, vanligtvis producerad av ett separat verktyg kallat KofamScan, och kontrollerar sedan vilka markörregler som uppfylls för var och en av de sju vägarna. Författarna jämförde AutoFixMark med två vida använda verktyg för metabolisk annotering, METABOLIC och gapseq, med hjälp av deras 347-genom referensuppsättning. Alla tre verktygen presterade väl på klassiska vägar som Calvin-cykeln, den reduktiva trikarboxylsyracykeln och Wood–Ljungdahl-vägen. Dock utmärkte sig AutoFixMark tydligt för nyare eller mindre vanliga vägar såsom 3-hydroxypropionat/4-hydroxybutyrat-cykeln, dicarboxylate/4-hydroxybutyrat-cykeln och den reduktiva glycinvägen, varav vissa inte ens täcks av konkurrenternas programvara.
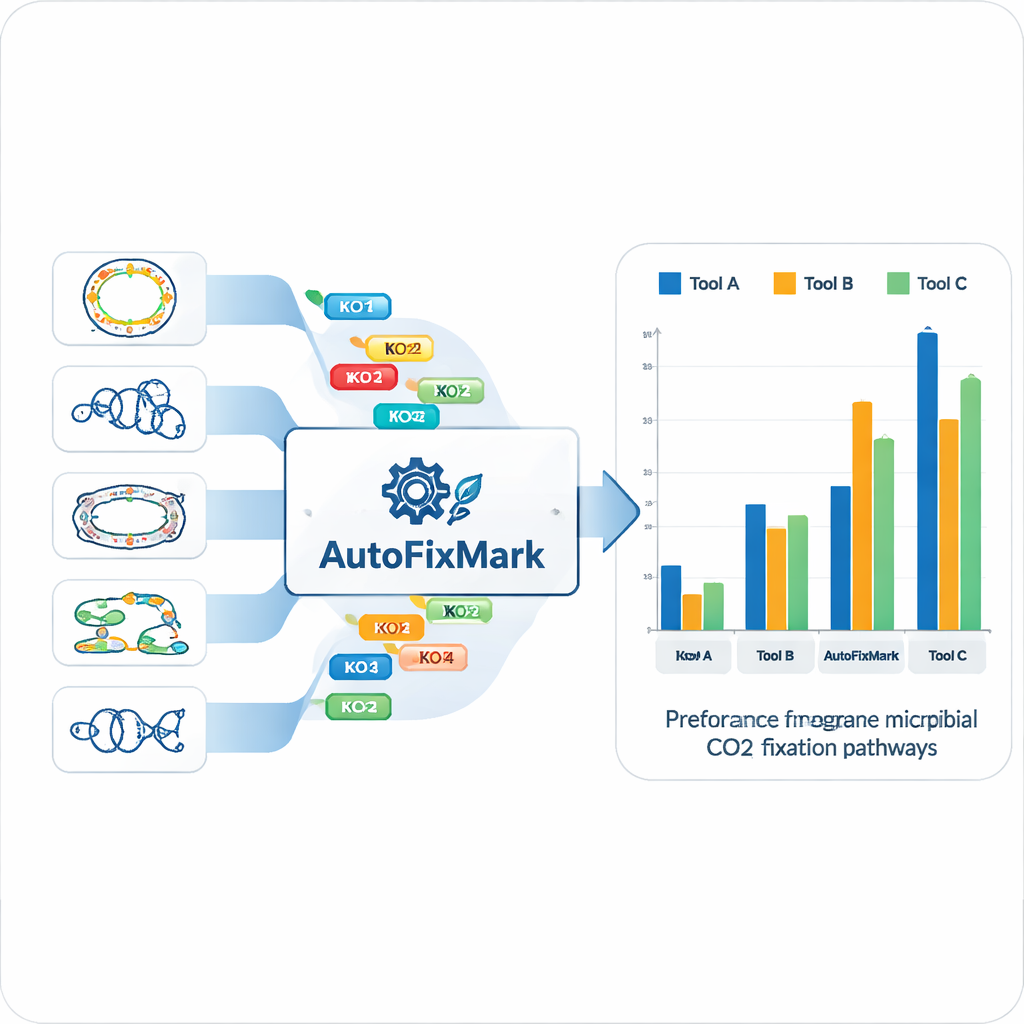
Vad dessa resultat betyder för klimat- och ekologistudier
De kuraterade genseten, AutoFixMark-programmet och hela referensuppsättningen av genom finns tillgängliga offentligt. Det innebär att forskare nu kan granska både isolerade mikrober och metagenom-assemblerade genom för att se vilka CO₂-fixeringsstrategier de genetiskt är utrustade att använda. Viktigt är att författarna betonar att AutoFixMark förutspår genetisk potential, inte huruvida en väg är aktiv under verkliga förhållanden. Många av dessa biokemiska vägar kan köras i omvänd riktning beroende på cellens energibalans. Ändå kommer det att bidra att ha ett robust, transparent sätt att flagga CO₂-fixerande mikrober — det hjälper forskare att kartlägga var och hur livet tar bort kol från atmosfären, styra experiment om framväxande vägar och stödja designen av framtida CO₂-baserade bioteknologier.
Citering: Kawashima, S., Okabeppu, Y., Miyazawa, S. et al. A curated resource of chemolithoautotrophic genomes and marker genes for CO₂ fixation pathway prediction. Sci Data 13, 121 (2026). https://doi.org/10.1038/s41597-026-06655-z
Nyckelord: mikrobiell kolinlagring, autotrof metabolism, genomannotering, CO2-fångst, metagenomik